Clear Sky Science · he
מסגרת למידת עומק מבוססת DNABERT לחיזוי אתרי קישור של גורמי שעתוק
מדוע חיזוי מתגי הבקרה של ה-DNA חשוב
לכל תא בגופך יש למעשה את אותה ה-DNA, ובכל זאת תאי מוח, כבד ומערכת חיסון מתנהגים באופן שונה מאוד. סיבה לכך היא חלבונים מיוחדים הנקראים גורמי שעתוק, שמתפקדים כמתגים מולקולריים — מפעילים או מכבים גנים על ידי עגינה לקטעים קצרים של DNA הידועים כאתרי קישור. איתור ניסויי של כל נקודות העגינה האלה לאורך הגנום הוא תהליך איטי ויקר. המחקר הזה מציג את TFBS-Finder, מודל בינה מלאכותית חדש היכול לקרוא את אותיות ה-DNA ולחזות במדויק יותר היכן גורמי שעתוק נקשרים, מה שעשוי לזרז מחקר בוויסות גנים ומחלות.
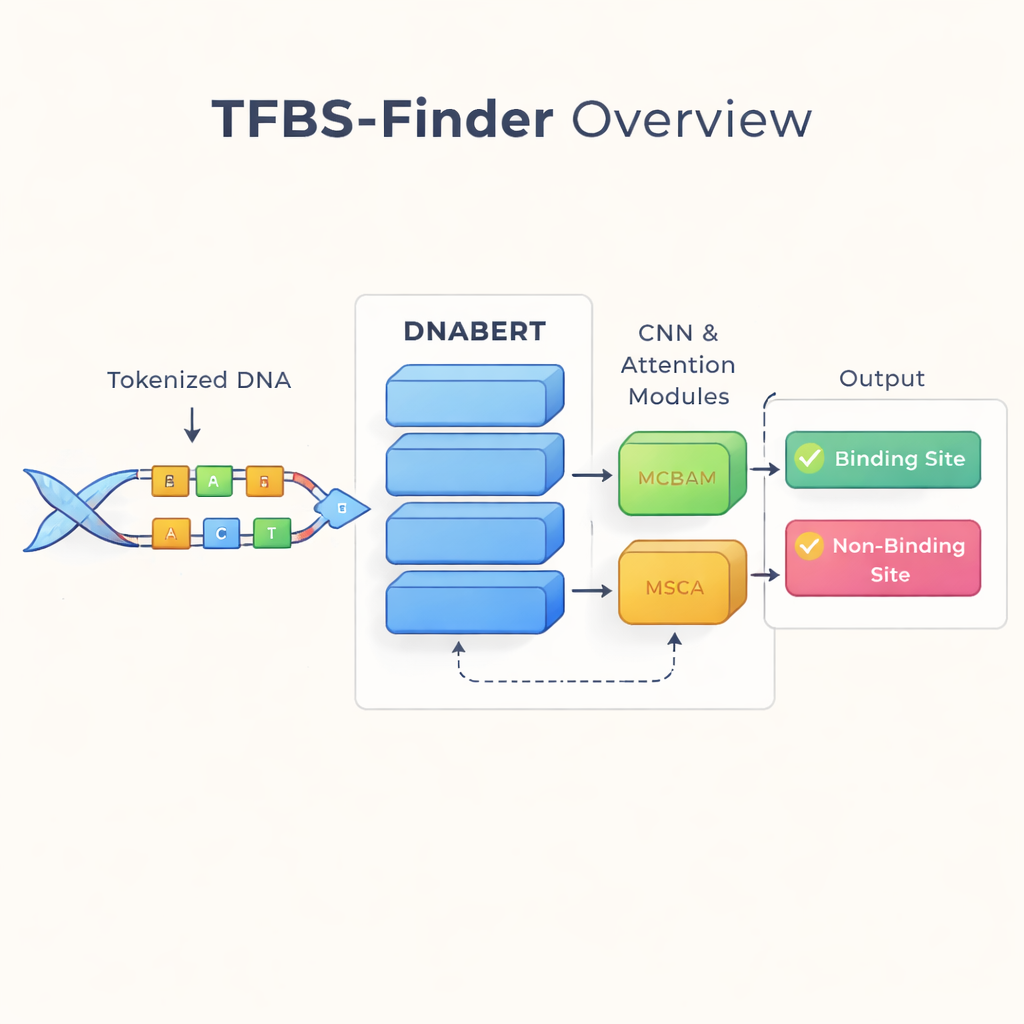
לקרוא את ה-DNA כמו שפה
המחברים בונים על רעיון ששינה את טכנולוגיית השפה: להתייחס ל-DNA כאילו היה טקסט. הם משתמשים ב-DNABERT, גרסה של מודל השפה BERT שאומנה מחדש על DNA אנושי במקום על מילים. DNABERT אינו מסתכל רק על אותיות בודדות; הוא מפרק את ה-DNA ל"מילים" חופפות קצרות באורך חמש אותיות ולומד כיצד חלקים אלה נוטים להופיע יחד. זה מאפשר למודל ללכוד הקשר בטווח ארוך, כמו כיצד דפוסים בקצה אחד של הרצף מתקשרים לדפוסים הרחק ממנו — בדומה להבנת משמעות של משפט במקום מילים מנותקות.
מציאת דפוסים מקומיים עם תשומת לב ממוקדת
בעוד DNABERT טוב בלכידת הקשר גלובלי, קשירת גורמי שעתוק לעתים קרובות תלויה במוטיבים קצרים ומדויקים — דפוסים מקומיים ב-DNA. לכן TFBS-Finder מוסיף מספר רכיבים על גבי DNABERT. רשת נוירונים קונבולוציונית (CNN) מסרקת את האמבדינגים של הרצף כדי להדגיש צורות מקומיות חוזרות, בדומה לאופן שבו תוכנות תמונה מזהות קצוות ופינות. שני מודולים של תשומת לב, שנקראים MCBAM ו-MSCA, פועלים כמו ספוֹטלייץ́ים מתכווננים — מחזקים את התכונות המידעיות ביותר וממעיטים ברעש. יחד, הבלוקים הללו מאזנים בין תמונה רחבה לפרטים עדינים כדי להכריע האם מקטע DNA מכיל אתר קישור אמיתי.
הוכחה שכל רכיב תורם
כדי לבדוק האם כל הרכיבים האלה נחוצים, הצוות ביצע ניסויי "אובלציה" נרחבים — הסירו או שינו מודולים באופן שיטתי ואימנו מחדש את המערכת על 165 מערכי מבחן תקניים המכסים 29 גורמי שעתוק ב-32 סוגי תאים. באמצעות מדדים סטנדרטיים של איכות חיזוי, מודל TFBS-Finder המלא הצטיין בעקביות. גרסאות פשוטות שהסתמכו רק על DNABERT או חסרו אחד ממודולי התשומת לב איבדו דיוק באופן בולט. בדיקות סטטיסטיות אישרו שירידות אלה בביצועים אינן מקריות, והראו כי השילוב של הבנה גלובלית של הרצף ותשומת לב מתוכננת לדפוסים מקומיים הוא קריטי.
עובד בין סוגי תאים ומתעלה על כלים ישנים
שאלה חשובה היא האם מודל שאומן בהקשר ביולוגי אחד יכול להכליל להקשר אחר. המחברים התמקדו בגורם שעתוק נחקר היטב בשם CTCF ואימנו את TFBS-Finder על נתונים משורת תאים אחת, ואז בדקו אותו על אחרות. בכל הצירופים המודל השיג ציונים גבוהים, מה שמרמז שהוא לוכד תכונות ליבה של קשירת CTCF המשותפות לרקמות שונות. בהשוואה לתשעה שיטות מובילות, כולל מודלים קודמים של למידת עומק ומודלים מבוססי BERT, TFBS-Finder הראה דיוק ממוצע גבוה יותר וייצר דירוגים מהימנים יותר של אתרי קישור. הוא גם רץ מעט מהר יותר ושיחרר פחות זיכרון בהשוואה למודל הדומה ביותר מהעבר, מה שמעיד על כך ששיפור בביצועים לא דרש חישוב כבד יותר.
להראות מה שלמד המודל
מערכות בינה מלאכותית מורכבות נתפסות לעתים קרובות כ"קופסאות שחורות." כאן ניסו החוקרים לפתוח את הקופסה על ידי ויזואליזציה של העמדות ב-DNA שהשפיעו הכי הרבה על החלטות TFBS-Finder. לשני גורמי שעתוק עם מוטיבים ידועים היטב, CEBPB ו-GATA3, הם ייצרו ציוני חשיבות לאורך הרצף וצברו את האותות החזקים ביותר לדפוסים קונסנסוס. מוטיבים אלה התאימו באופן צמוד למוטיבים ייחוס ממאגרי מידע מבוססים, והאזורים הנבנים לחיזוי חפפו עם מופעים של מוטיבים שהתגלו באופן עצמאי. ממצא זה מצביע על כך ש-TFBS-Finder אינו רק שינון דוגמאות, אלא שלמד חוקים ביולוגיים משמעותיים לגבי אופן ההכרה של גורמי שעתוק ב-DNA.
מה זה אומר לגנטיקה ולרפואה
TFBS-Finder מציע דרך מדויקת וברורה יותר למיפוי מתגי הבקרה הטמונים ב-DNA שלנו. על ידי איתור מדויק של המקומות שבהם סביר שגורמי שעתוק יקשרו, הוא יכול לסייע לחוקרים למפות רשתות ויסות גנים, לתעדף אילו וריאנטים גנטיים עלולים להפריע לאתרי בקרה קריטיים, ולעצב ניסויים ממוקדים יותר. אף על פי שהעבודה הנוכחית משתמשת ברצפים משולבים כשליליים מלאכותיים ומתמקדת רק באותיות ה-DNA, המחברים מתכננים להוסיף מידע מבני על צורת ה-DNA ולחקור רקעים מציאותיים יותר. ככל שהמודלים הללו ישתפרו, הם עשויים להפוך לכלים עוצמתיים להבנת האופן שבו שינויים ב-DNA שאינו מקודד תורמים להתפתחות, אבולוציה וסיכון למחלות.
ציטוט: Dutta, P., Ghosh, N. & Santoni, D. A DNABERT based deep learning framework for predicting transcription factor binding sites. Sci Rep 16, 7018 (2026). https://doi.org/10.1038/s41598-026-37483-1
מילות מפתח: אתרי קישור של גורמי שעתוק, למידת עומק, DNABERT, וויסות גנים, גנומיקה