Clear Sky Science · he
איסוף טרנסקריפטום מלא ופיתוח סמני SSR עבור Spinibarbus hollandi באמצעות רציפת PacBio SMRT
מדוע דג נהר צנוע חשוב
לרוחב הנהרות בדרום סין שוחה Spinibarbus hollandi, דג דמוי קרפיון שמוערך הן כאוכל והן כמין נוי. החקלאים היו רוצים לגדלו ביעילות רבה יותר, אך הדג גדל לאט, מבשיל מאוחר ומייצר יחסית מעט ביצים. המחקר המתואר כאן משתמש בכלי רציפה גנומית וטרנסקריפטומית מתקדמים כדי לבנות "רשימת חלקים" גנטית מפורטת למין זה. המידע הגנטי הזה יכול בסופו של דבר לסייע למגדלים לבחור דגים עמידים ומהירי גדילה ולתמוך בשימור אוכלוסיות בר.
הפיכת רקמות רבות למפה גנטית
כדי ללכוד כמה שיותר מידע גנטי, החוקרים אספו שש רקמות שונות — לב, זימים, מוח, סנפיר, כבד וגונדות — משישה זכרים ונקבות בוגרים. מהרקמות האלה הפיקו RNA, המולקולה שנושאת עותקים של גנים פעילים בתוך התאים. באמצעות טכנולוגיה בשם PacBio SMRT, שקוראת מקטעים ארוכים מאוד של עותקי RNA, הם הרכיבו את הטרנסקריפטום המלא הראשון עבור S. hollandi. במונחים פשוטים, הם בנו קטלוג ברזולוציה גבוהה של 15,197 גנים נבדלים ו‑23,403 רצפי טרנסקריפטים, רובם ארוכים ומלאים הרבה יותר ממה ששיטות קריאה קצרות ישנות יכלו להפיק.
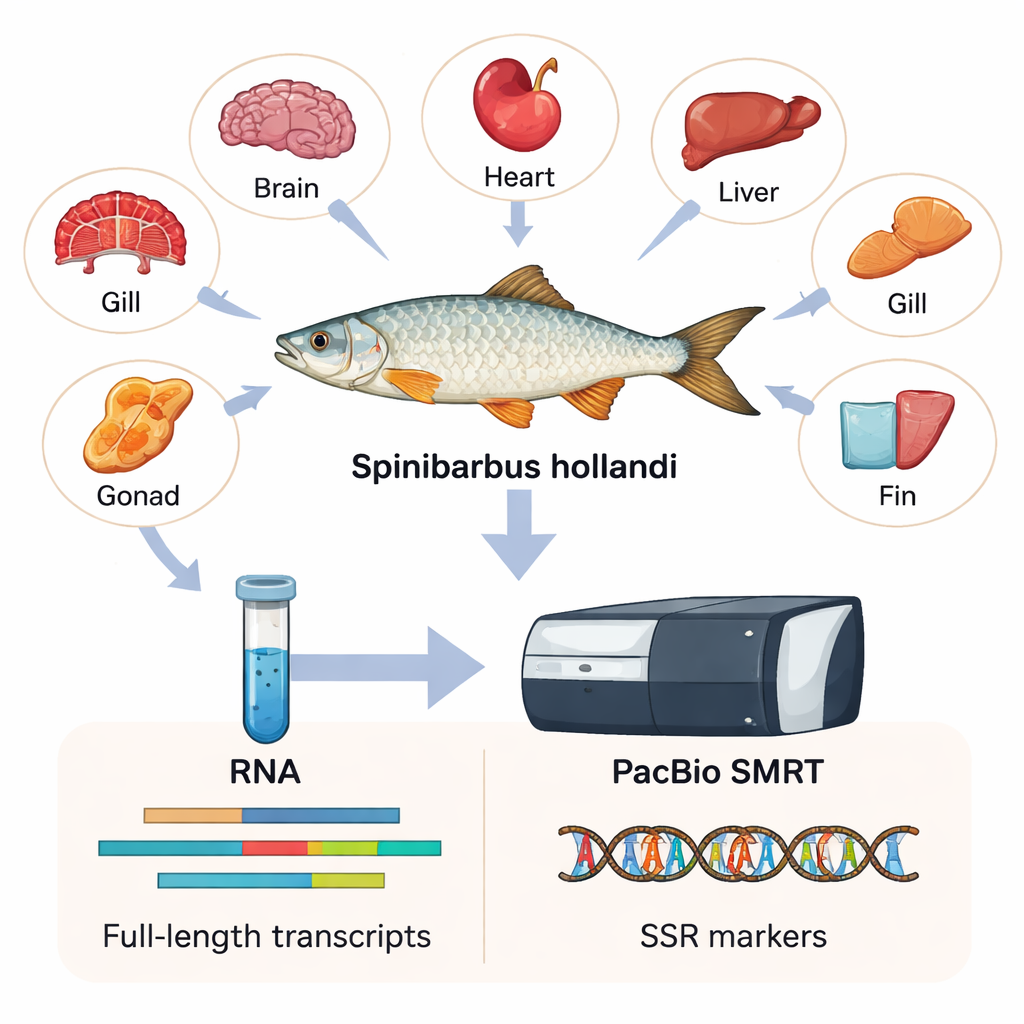
מה הגנים חושפים על הדג
בהמשך, הצוות בדק מה עושים הגנים האלה בפועל. הם השוו כל רצף מול מאגרי מידע ציבוריים גדולים הממיינים גנים לפי תפקוד. יותר מ‑95% מהגנים ניתנו להתאמה לערכים ידועים, שיעור הצלחה גבוה שמעיד על איכות נתונים טובה. גנים רבים נפלו לקטגוריות הקשורות לפעילויות תא בסיסיות כמו מטבוליזם, שידור אותות והתפתחות, ורובם זהים או דומים ביותר לגנים מדגים במשפחת הקרפיונים. הדבר מאשר שהטרנסקריפטום החדש יציב מבחינה ביולוגית ומהווה בסיס למציאת גנים הקשורים לתכונות כגון קצב גדילה, סיבולת למתח ורבייה ב‑S. hollandi.
שכבות שליטה חבויות ב‑RNA
מעבר לזיהוי גנים, המדענים בחנו גם כיצד גנים אלה נשלטים. הם מצאו 373 מקרים של ריבוי חיתוך (alternative splicing), שבהם אותו גן נחתך ומודבק בדרכים שונות כדי ליצור מסרי RNA שונים. התבנית הנפוצה ביותר שמרה חלקים של RNA שבמינים אחרים לעתים מוסרים, מה שמרמז על דרך מיוחדת שבה דג זה מכוונן את חלבוניו. הם גם גילו 2,397 RNA ארוכים שאינם מקודדים לחלבון (lncRNAs) — מולקולות RNA שאינן מייצרות חלבונים אך יכולות לווסת מתי והיכן גנים אחרים נדלקים. יחד, הממצאים האלה מראים של‑S. hollandi יש מערך עשיר של בקרות ברמת ה‑RNA שעשויות להשפיע על גדילה, הבשלה מינית והתאמה לסביבות מקומיות.
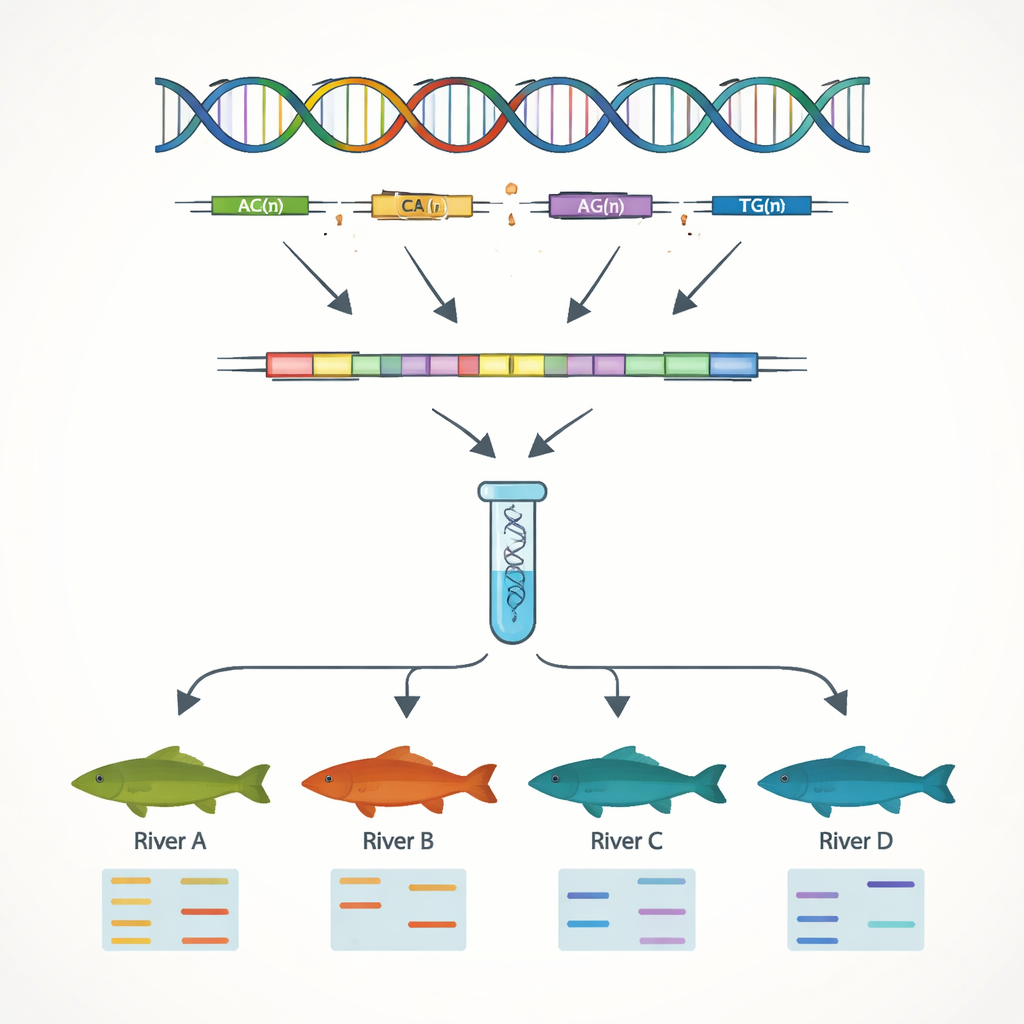
בניית סימני DNA לארגון הרבייה ושימור
מטרה מרכזית בעבודה הייתה לפתח סמני DNA פשוטים שיכולים להבדיל בין פרטים ואוכלוסיות. בהתמקדות ברצפי הגנים, המחברים חיפשו חזרות רצף פשוטות, או SSRs — מוטיבים קצרים של DNA כמו "AC" או "AAT" החוזרים פעמים רבות ברצף. מקטעים אלה נוטים להשתנות בין פרטים, מה שהופך אותם לשימושיים כ"ברקודים" גנטיים. הם גילו 7,449 אתרי SSR כאלה ועיצבו עשרות פריימרים קצרים להכפלה במעבדה. שלוש עשרה מהסמנים האלה התגלו כמשתנים ואמינים בעת מבחן ב‑51 דגים מארבע מערכות נהר. באמצעות 13 סמנים אלה בלבד, הצוות הצליח לזהות בבירור הבדלים גנטיים בין אוכלוסיות מנהר היאנגצה לאלו מנהר פנייתה, המשקפים את רכסי ההרים שמגבילים עירוב טבעי בין מאגרים.
מה המשמעות לחקלאי דגים ולנהרות
לקורא שאינו מומחה, המסקנה המרכזית היא שהמחברים יצרו ייחוס גנטי מפורט ואיכותי ל‑S. hollandi וערכת סמני DNA מעשית. כלי זה יעזור לחוקרים לאתר גנים מאחורי גדילה איטית או פוריות נמוכה, לסייע למגדלים בבחירת חומר רבייה עם תכונות רצויות, ולאפשר לשמרנים לעקוב אחר מגוון גנטי ברחבי מערכות נהר. על אף שיידרש עוד מחקר כדי לקשר גנים ספציפיים לביצועים בעשבים או בטבע, המחקר מניח את היסוד המולקולרי להפיכת דג נהר מסורתי למין אקווקולטורה מודרני ומנוהל בר־קיימא.
ציטוט: Li, S., Lai, J., Wu, M. et al. Full-Length transcriptome assembly and SSR marker development for Spinibarbus hollandi using PacBio SMRT sequencing. Sci Rep 16, 5629 (2026). https://doi.org/10.1038/s41598-026-36468-4
מילות מפתח: Spinibarbus hollandi, טרנסקריפטום של דג, רציפת PacBio, סמני מיקרוסטלייט, גנטיקה של אקווקולטורה