Clear Sky Science · he
IL2Pepscan: מסגרת למידת מכונה לחיזוי פפטידים שמשרים IL-2 וזיהוים בפרוטאומים ויראליים עולמיים
להדריך את המערכת החיסונית באמצעות חתיכות חלבון זעירות
חיסונים מודרניים וטיפולים בסרטן נשענים יותר ויותר על דחיפה מדויקת של המערכת החיסונית במקום טיפול פיזורני באמצעות תרופות. המחקר הזה בוחן כיצד חתיכות חלבון זעירות, הנקראות פפטידים, ניתנות לבחירה כדי להפעיל שליח חיסוני רב עוצמה, אינטרלוקין‑2 (IL‑2). בעזרת מודלים ממוחשבים מתקדמים מחפשים החוקרים הן במאגרי נתוני החיסון הקיימים והן במאגרי החלבונים של אלפי נגיפים אחר "מחט" מולקולרית של פפטידים שעשויים לסייע בעיצוב חיסונים ואימונותרפיות טובים יותר.
מדוע IL-2 חשוב לבריאות ומחלה
IL‑2 הוא מולקולת איתות קטנה הפועלת כגורם גדילה לתאי המערכת החיסונית המרכזיים הנקראים תאי T. כאשר תאים אלו נתקלים באיום—כמו וירוס או תא סרטני—הם יכולים לשחרר IL‑2, אשר מעודד את תאי ה‑T להתרבות, להתמחות ולזכור את הפולש. IL‑2 גם מסייע בשמירה על תאי T רגולטוריים שמונעים מהמערכת החיסונית לפנות נגד רקמות הגוף עצמו. בשל התפקיד הכפול הזה, נעשה שימוש ב‑IL‑2 כתרופה לטיפול בסרטנים כמו מלנומה, והוא נחקר גם במחלות אוטואימוניות. אולם מתן IL‑2 ישירות יכול להיות קשה לסיבולת החולים, ולכן יש עניין גובר בעיצוב פפטידים בטוחים שיגרמו לגוף לייצר IL‑2 באופן מבוקר וממוקד יותר.
ללמוד את "הטעם" של פפטידים שמעודדים IL-2
החוקרים התחילו באלפי רצפי פפטידים שנבדקו כבר בניסויים מעבדתיים וסומנו אם הם מעוררי IL‑2 או לא. הם ניקו את מערך הנתונים להסרת כפילויות, אבני בניין בלתי שגרתיות ופפטידים שקצרים מדי או ארוכים מדי, וסיימו עם למעלה מ‑6,000 דוגמאות מתועדות היטב. בבחינת אבני הבניין (חומצות אמינו) שמרכיבות את הפפטידים גילו החוקרים הבדלים ברורים בין שתי הקבוצות. פפטידים שמעודדים IL‑2 נטו להיות עשירים יותר בחומצות אמינו הידרופוביות, דוגמת ליאוצין ואלנין, בעוד שפפטידים שאינם מעוררים נטו להציג שיירים פולריים ומטענים. תבניות קצרות מסוימות, או מוטיפים, כמו "LEGS" ו"ALEG", הופיעו רק בפפטידים שמעוררים IL‑2, מה שמרמז על חתימות מבניות שעשויות לסייע בהפעלת תגובה חיסונית.
לאמן מכונות לזהות דפוסים שמגבירים חיסון
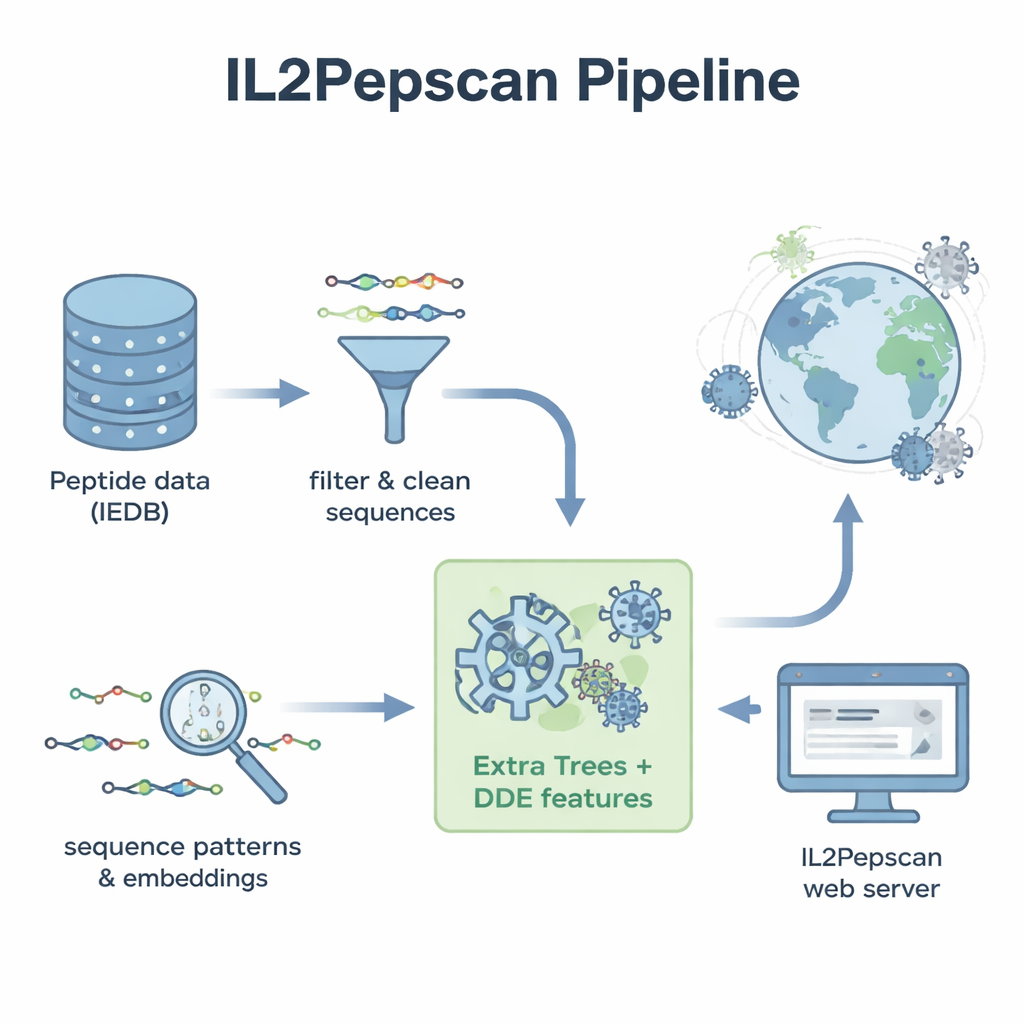
כדי להפוך דפוסים אלה לכלי חיזוי מעשי, הצוות המיר כל פפטיד לתיאורים מספריים המתארים את הרכבו ואת סדר חומצות האמינו. הם בחנו מגוון שיטות של למידת מכונה—כולל אלגוריתמים פופולריים כמו Random Forests, Support Vector Machines ועצים מועצמים—יחד עם ארכיטקטורות למידה עמוקה שבדרך כלל משמשות לעיבוד שפה ותמונה. בנוסף השתמשו במודל "שפת" חלבון גדול בשם ProtBERT, שאומן במקור על מאות מיליוני רצפי חלבון, וכיוונו אותו עדין לזיהוי אותות הקשורים ל‑IL‑2. לאחר בדיקות מקיפות עם CV (cross‑validation) וקבוצת מבחן עצמאית, המודל הבולט היה Extra Trees בשילוב עם ערכת תכונות הידועה כ‑dipeptide deviation from expected mean (DDE). מודל זה השיג דיוק קרוב ל‑80% וציון מתאם חזק, תוך שהוא עולה על כמה גישות של למידה עמוקה.
סריקת העולם הוויראלי אחר טריגרים חיסוניים חבויים
מצוידים במודל הטוב ביותר שלהם, המחברים פתחו רשת רחבה יותר. הם אספו רצפי חלבון רפרנסיים מיותר מ‑14,000 נגיפים, פרשו את החלבונים לכ‑156 מיליון פפטידים חופפים, וביקשו מהמודל לנבא אילו מהם עשויים לעודד IL‑2. בין המועמדים עם הציון הגבוה היו פפטידים ממשפחות ויראליות ידועות, כולל פליווווירוסים כגון West Nile, Zika, Yellow Fever ווירוס ההפטיטיס C, וכן מאינפלואנצה ו‑SARS‑CoV‑2. פפטידים מבטיחים רבים הגיעו מחלבוני מעטפת או נוקלאוקפסיד—אותם סוגי חלבונים שמחקרים קודמים הראו שיכולים לעורר תגובות IL‑2 בבעלי חיים. המודל גם זיהה פפטידים פוטנציאליים מעודדי IL‑2 המקודדים על ידי בקטריופאגים, נגיפים שמדביקים חיידקים, מה שמרמז על נוף רחב אף יותר של רצפים רלוונטיים לחיסון.
ממערכת אלגוריתמית לכלי נגיש
כדי להפוך את עבודתם לשימושית מעבר למעבדת המחשב, החוקרים בנו שרת אינטרנט ציבורי בשם IL2Pepscan. חוקרים יכולים להדביק רצפי פפטידים או חלבונים באתר כדי להעריך את הפוטנציאל שלהם לעידוד IL‑2, לעצב וריאנטים חדשים על‑ידי מוטציה של עמדות, לסרוק חלבונים שלמים אחרי נקודות חמות, או לחפש מוטיפים ידועים הקשורים ל‑IL‑2. בעוד שהמחקר עדיין לא מאשר ניסויית כל פפטיד שנחזה, ההסכמה עם ממצאים מעבדתיים קיימים מרמזת ש‑IL2Pepscan יכול לצמצם בצורה מהימנה את המועמדים למבחנים נוספים. עבור לא-מומחים, המסקנה היא שאלגוריתמים מאומנים בקפידה יכולים לסנן מאגרי ביולוגיה עצומים כדי לאתר חתיכות חלבון קטנות שעשויות יום אחד לעזור לחיסונים ולאימונותרפיות לגרות את המערכת החיסונית לתגובה חזקה—ומערכתי—יותר.
ציטוט: Arora, P., Abhigyan, R., Periwal, N. et al. IL2Pepscan: A machine learning framework for predicting IL-2 inducing peptides and their identification across global viral proteomes. Sci Rep 16, 6701 (2026). https://doi.org/10.1038/s41598-026-35977-6
מילות מפתח: אינטרלוקין-2, חיסוני פפטידים, למידת מכונה, פרוטאום ויראלי, אימונותרפיה