Clear Sky Science · he
תכנון בר‑מחשב של חיסון מולטי‑אפיטופי המכוון ל‑DENV‑1 ו‑DENV‑3
מדוע חיסונים לדנגה עדיין חשובים
קדחת הדנגה איננה עוד מחלה טרופית נדירה; היא מאיימת כיום על מיליארדי אנשים ביותר ממאה מדינות ושוטפת בתי חולים בחלקים של אסיה, אמריקה הלטינית ומקומות נוספים. למרות שני חיסונים מורשים שקיימים בשוק, ההגנה שלהם אינה אחידה, במיוחד בקרב אנשים שמעולם לא חלפו עליהם זיהום בדנגה ובאזורים שבהם כמה סוגי הנגיף מצטברים יחד. המחקר הזה שואל שאלה מעודכנת: האם תכנון מונחה מחשב יכול לסייע לנו לבנות חיסון בטוח ומדויק יותר, המיועד ספציפית לזיהומים משותפים מסוכנים משני סוגי דנגה שלעתים מכים בו‑זמנית?
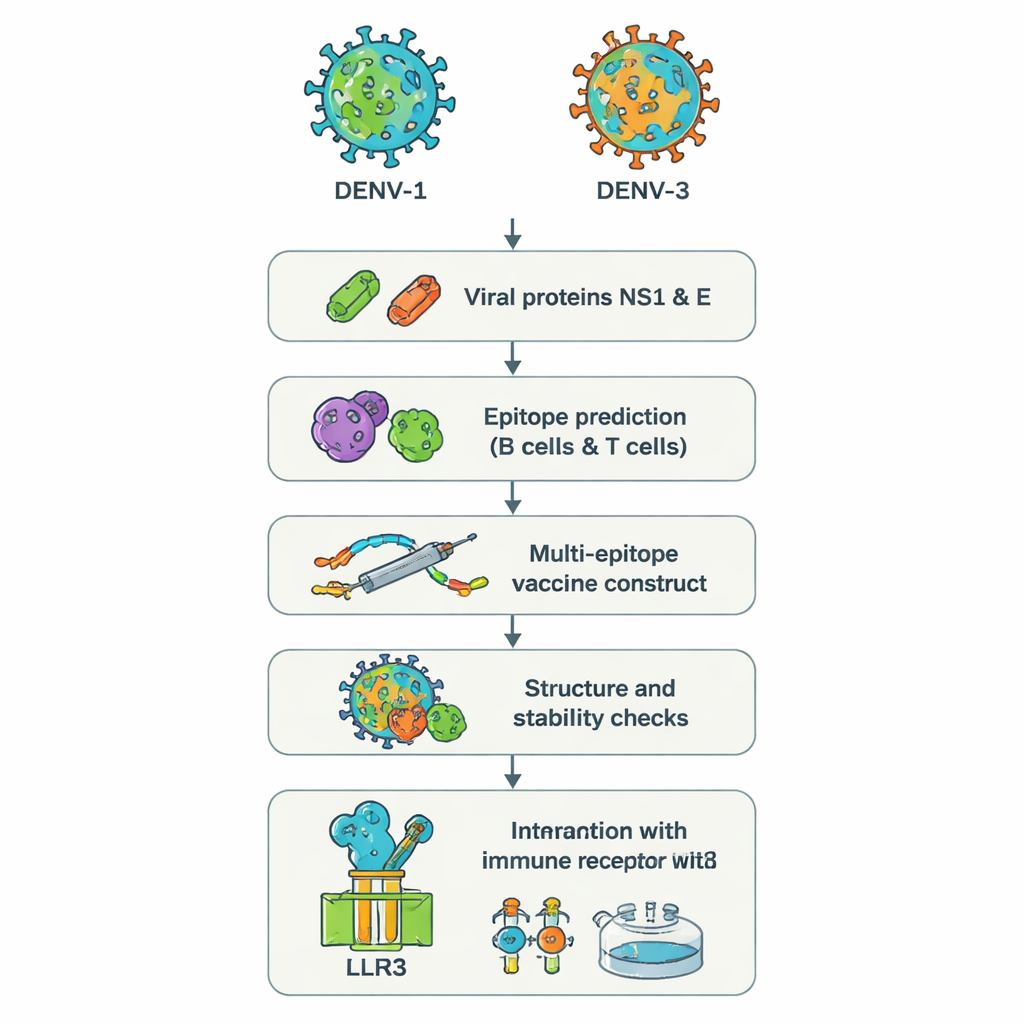
שני סוגי נגיף ערמומיים ולמה הם בעיה
נגיף הדנגה מופיע בארבע גרסאות, הנקראות סרוטיפים DENV‑1 עד DENV‑4. זיהום בכל אחד מהם יכול לגרום לחום גבוה, כאב חמור ובמקרים מסוימים לדימום או הלם מסכני חיים. לדאגה, הידבקות שנייה בסרוטיפ שונה יכולה לעתים להחמיר את המחלה במקום להגן, משום שנוגדנים קיימים עלולים לסייע לכניסת הנגיף לתאים ביתר קלות — תהליך הקרוי החמרה תלויה‑נוגדן (antibody‑dependent enhancement). בהתפרצויות האחרונות דווחו מקרים של מטופלים שנדבקו במקביל ב‑DENV‑1 ו‑DENV‑3, שילוב המקושר למחלה קשה יותר ולתוצאות בדיקה מבולבלות. החיסונים הקיימים אינם מגנים באופן מהימן על כל קבוצות הגיל ועל כל הסרוטיפים, במיוחד באנשים ללא חשיפה קודמת, ומשאירים פער מסוכן בהגנה.
תכנון חיסון מהמולקולה ומעלה
במקום לגדל נגיפים שלמים במעבדה, החוקרים השתמשו בגישה שלעיתים נקראת "חיסונולוגיה הפוכה". הם התחילו מהרצפים הגנטיים של שני חלבונים של הדנגה, NS1 ו‑E, מ‑DENV‑1 ו‑DENV‑3. חלבונים אלה חיוניים לאופן שבו הנגיף חודר לתאים וכיצד המערכת החיסונית מזהה אותו. כלים רבי‑עוצמה מבוססי רשת סרקו את רצפי החלבון כדי לאתר קטעים קצרים — אפיטופים — שעשויים להיתפס ביותר על ידי תאי B (המייצרים נוגדנים) ותאי T (הורגים תאים נגועים ומתאמים תגובות). מתוך מאות מועמדים בחר הצוות קבוצה קטנה שחזו שהיא תהיה גלויה בחוזקה למערכת החיסון, משותפת לשני הסרוטיפים ומסוגלת לעורר אותות אנטי‑ויראליים מועילים כגון אינטרפרון‑גמה.
בנייה של מולקולת חיסון אחת רב‑תכליתית
האפיקופים הנבחרים תפרו דיגיטלית יחד לחלבון מלאכותי ארוך אחד, חיסון "מולטי‑אפיטופי". מקשרי חומצות אמינו קצרים משמשים כרווחים גמישים כדי שכל אפיטופ ישמור על צורתו ויישאר נגיש לתאי החיסון. תוספת נוספת, מבוססת על פפטיד אנטימיקרוביאלי אנושי טבעי שנקרא בטא‑דפנסין, הוספה כאדג'ובנט להגברת התגובה הכוללת. ניתוחי מחשב חזו שהבניין הסופי, המורכב מ‑575 חומצות אמינו, יהיה יציב, הידרופילי (ולכן קל יותר להמיס) וככל הנראה לא יפעל כאלרגן. כלים נוספים לחיזוי מבנה ייצרו מודל תלת‑ממדי ובדקו שרוב הבלוקים הבונים יושבים במקומות ריאליסטיים, בדומה למבנים ידועים של חלבונים.
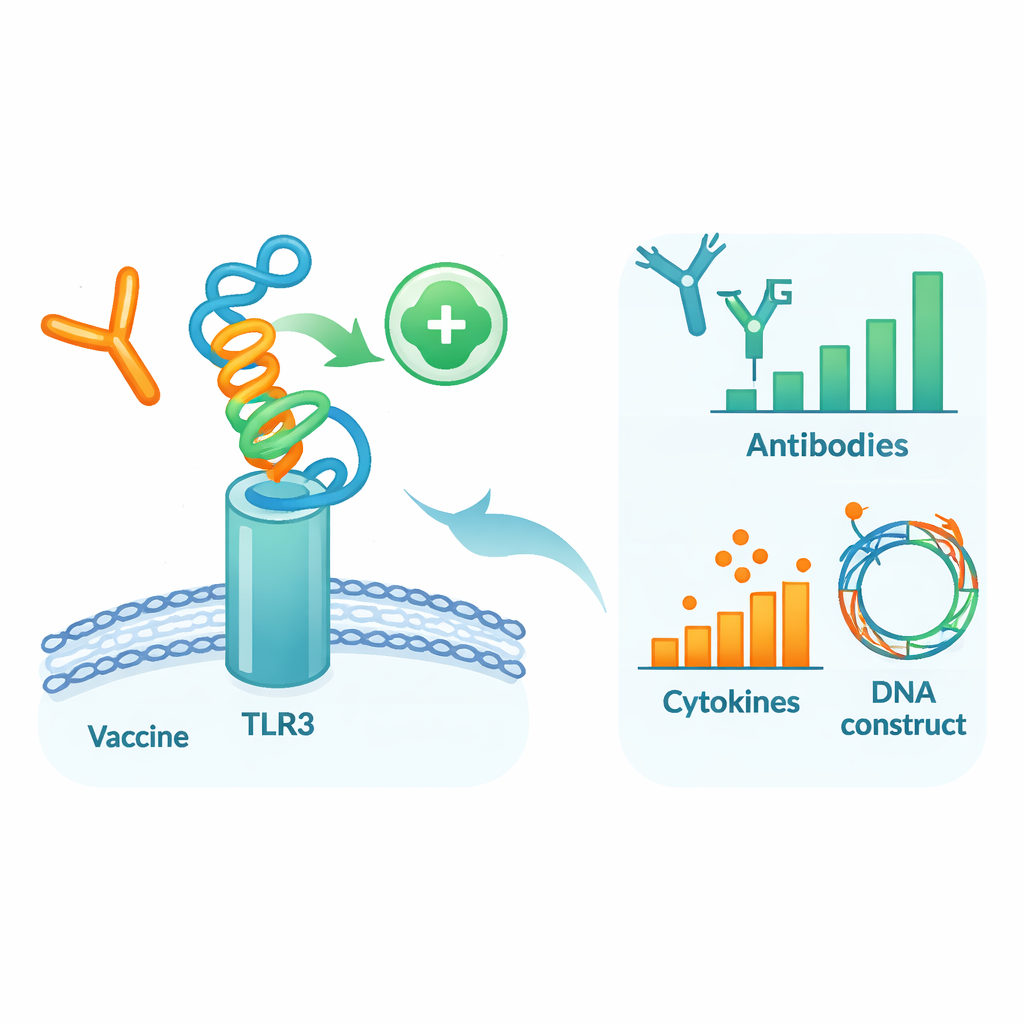
בדיקת המועמד בתוך גוף וירטואלי
כדי לראות כיצד החלבון המתוכנן יתנהג בהקשר דמוי‑אנושי, המחברים הריצו סדרת סימולציות מחשב מפורטות. תחילה דוק (הצמדה) של דגם החיסון אל TLR3, חלבון חישה על תאי חיסון שמגלה חומר ויראלי ועוזר להשיק הגנות מוקדמות. סימולציות של דינמיקת מולקולות — סרטים וירטואליים של אטומים בתנועה — הצביעו על כך שהחיסון ו‑TLR3 יוצרים קומפלקס יציב, בתמיכה של אנרגיות קשירה נוחות ורשתות רבות של קשרי מימן. ניתוחים נוספים של תנועה ואנרגיה הצביעו על אזורים ספציפיים בשני המולקולות שמתפקדים כ"נקודות חמות" למגע. לאחר מכן הושמע סימולטור מערכת חיסון שחיקה של שלוש מנות חיסון על פני כמה חודשים. מערכת החיסון הווירטואלית ייצרה גליי נוגדנים IgG חזקים, זיכרון ארוך‑טווח של תאי B ו‑T ומולקולות איתות התואמות לתגובה אנטי‑ויראלית איתנה.
ממודל מחשב לתוכנית מוכנה למעבדה
לבסוף, החוקרים התאימו את הקוד הגנטי של החיסון לייצור יעיל במיקרואורגניזמים מעבדתיים נפוצים והטמיעו בהצלחה את רצף ה‑DNA המותאם בפלסמיד ביטוי סטנדרטי, מוכן לניסויים עתידיים. במילים פשוטות, עבודתם מספקת תוכנית מפורטת לחיסון חדש לדנגה המכוון לקטעים שנבחרו בקפידה מ‑DENV‑1 ו‑DENV‑3, שחזויים להיות יציבים ובטוחים ולפעיל בעוצמה על שני הזרועות של המערכת החיסונית. בעוד שהתוצאות הן חישוביות בלבד ויש לאשרן בתאים, בחיות ובסופו של דבר בבני אדם, הן מדגימות כיצד ביואינפורמטיקה מודרנית יכולה לייצר במהירות מועמדי חיסון מותאמים לבעיות מורכבות כמו זיהומים משותפים של דנגה.
ציטוט: Ishwar, D., Padavu, S., Kumar, M. et al. In silico design of a multi-epitope vaccine targeting DENV-1 and DENV-3. Sci Rep 16, 5308 (2026). https://doi.org/10.1038/s41598-026-35678-0
מילות מפתח: חיסון לדנגה, מולטי‑אפיטופי, DENV‑1, DENV‑3, אימונואינפורמטיקה