Clear Sky Science · he
למידת דינמיקה מולקולרית מבוססת גרעין יעילה בנתונים מתוך כוחות ורעש
מדוע הקטנת מולקולות חשובה
סימולציה של התנועה הבלתי פוסקת של כל אטום בחלבון ובמי הסביבה שלו היא אחד הכלים הטובים ביותר להבנת האופן שבו החיים פועלים בקנה המידה המולקולרי. עם זאת, סימולציות מכל-אטום כאלה דורשות משאבי חישוב עצומים, כך שעקיבה אחרי חלבון בתהליכי קיפול, פירוק או אינטראקציה עם שותפים בזמנים בעלי משמעות ביולוגית עשויה לקחת חודשים על-גבי מחשב-על. מאמר זה מציג דרך חדשה לבנות מודלים מזורזים ומפושטים של חלבונים שעדיין מתנהגים בדומה למקבילותיהם האטומיות המלאות, אך זקוקים להרבה פחות נתונים לאימון וכוח חישוב מאשר בעבר.
מכל האטומים לתמונה פשוטה יותר
דינמיקה מולקולרית מסורתית עוקבת אחרי כל אטום ומחשבת את הכוחות ביניהם בכל צעד זמן זעיר. כדי להאיץ את החישוב, מדענים לעתים משתמשים במודלים מפושטים (coarse-grained), המקבצים הרבה אטומים ל"חרוזים" בודדים. מודלים מצומצמים אלה פועלים הרבה יותר מהר אך היסטורית התקשו להשיג את הדיוק של הסימולציות האטומיות המלאות, במיוחד עבור חלבונים עם התנהגות קיפול עשירה. עבודות לאחרונה פנו ללמידת מכונה כדי לגלות אוטומטית שדות כוח גרעיניים טובים יותר, אך אימון מודלים כאלה בדרך-כלל דרש מיליוני תמונות מדויקות, כל אחת מתוייגת עם הכוחות על כל אטום — נטל עצום של נתונים וחישוב.
שילוב כוחות פיזיקליים עם רעש מידעתי
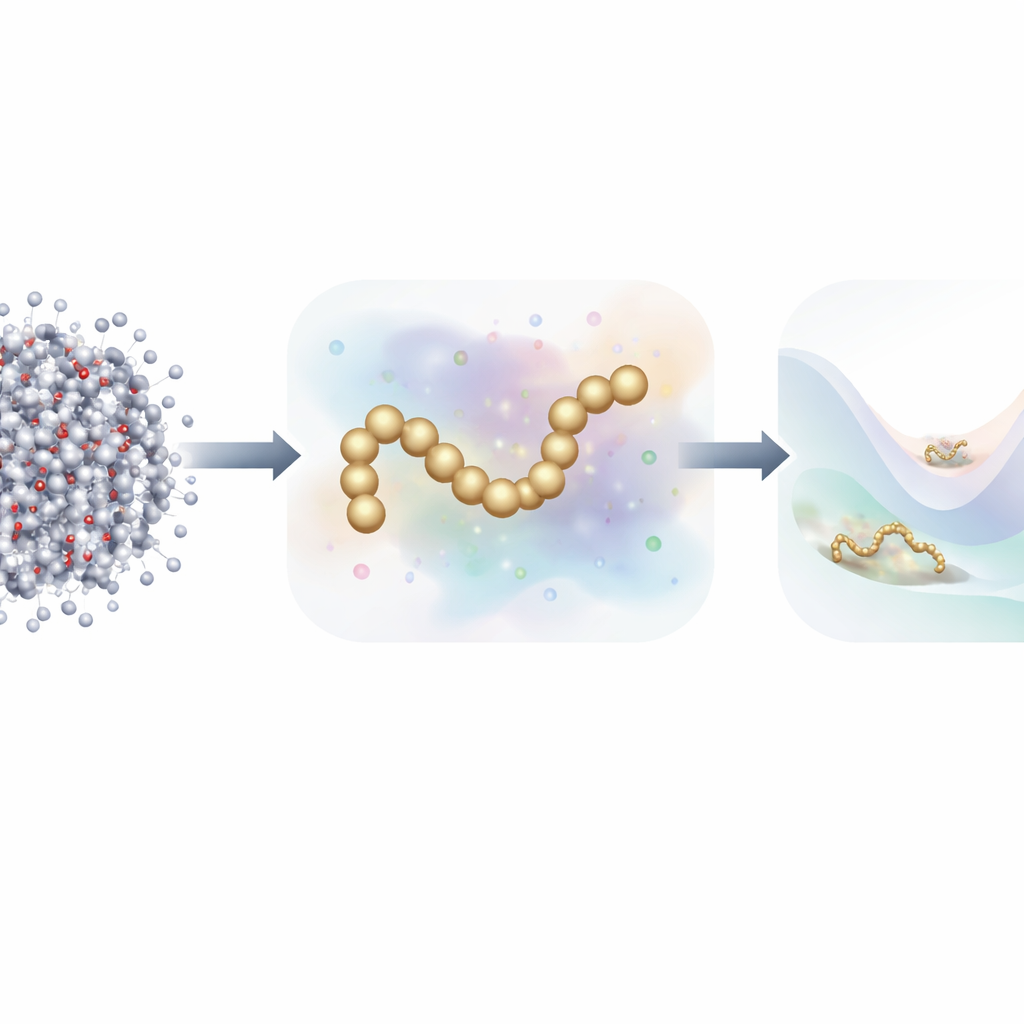
המחברים מציעים אסטרטגיית אימון חדשה השואבת השראה ממודלים גנרטיביים מבוססי דיפוזיה — אותה קטגוריית אלגוריתמים שעומדת מאחורי הרבה מייצרי תמונות מודרניים בבינה המלאכותית. במקום ללמוד רק מתוך הכוחות הפיזיקליים שמחשבים בסימולציות האטומיות, שיטתם לומדת גם מתוך האופן שבו מבנים מולקולריים מתפזרים במרחב על-ידי הוספת רעש מבוקר להגדרות הגרעיניות. במסגרת זו, הרעש אינו רק מטרד שיש להסיר; הוא הופך למקור מידע נוסף. באמצעות איחוד מתמטי של שיטת "התאמת כוחות" המסורתית עם טכניקות דנויזינג ממודלי הדיפוזיה, השיטה יכולה להסיק את נוף האנרגיה הבסיסי של חלבון תוך שימוש בהרבה פחות דוגמאות מתוייגות.
לימוד מודלים פשוטים לחקות חלבונים מורכבים
כדי לבדוק את הרעיון, החוקרים אימנו מודלי גרעין מבוססי רשתות עצביות עבור מספר חלבונים בעליית המורכבות: המיני-חלבונים הקטנים Chignolin ו-Trp-Cage, החלבון הבינוני NTL9, וחלבון 76-החומצות Ubiquitin. הם השוו בין שלוש מצבי אימון: שימוש רק בכוחות האטומיים, שימוש רק במידע מבוסס רעש, ושילוב של שניהם. עבור החלבונים הקטנים יותר הם הראו שהגישה המשולבת החדשה יכולה לשחזר את התכונות המרכזיות של נוף הקיפול — כמו היציבות היחסית של מצבי מקופל ופרוש וקיום מרכיבים ביניים — תוך שימוש עד מאה פעמים פחות נתוני אימון מאשר שיטות התאמת-כוחות סטנדרטיות. באופן מפתיע, במשטרים דלי-נתונים אפילו מודלים שאומנו רק עם מידע מבוסס רעש לעתים קרובות התאימו או עברו את דיוק האימון המבוסס-כוחות בלבד.
הגעה למערכות חלבון גדולות וקשות יותר
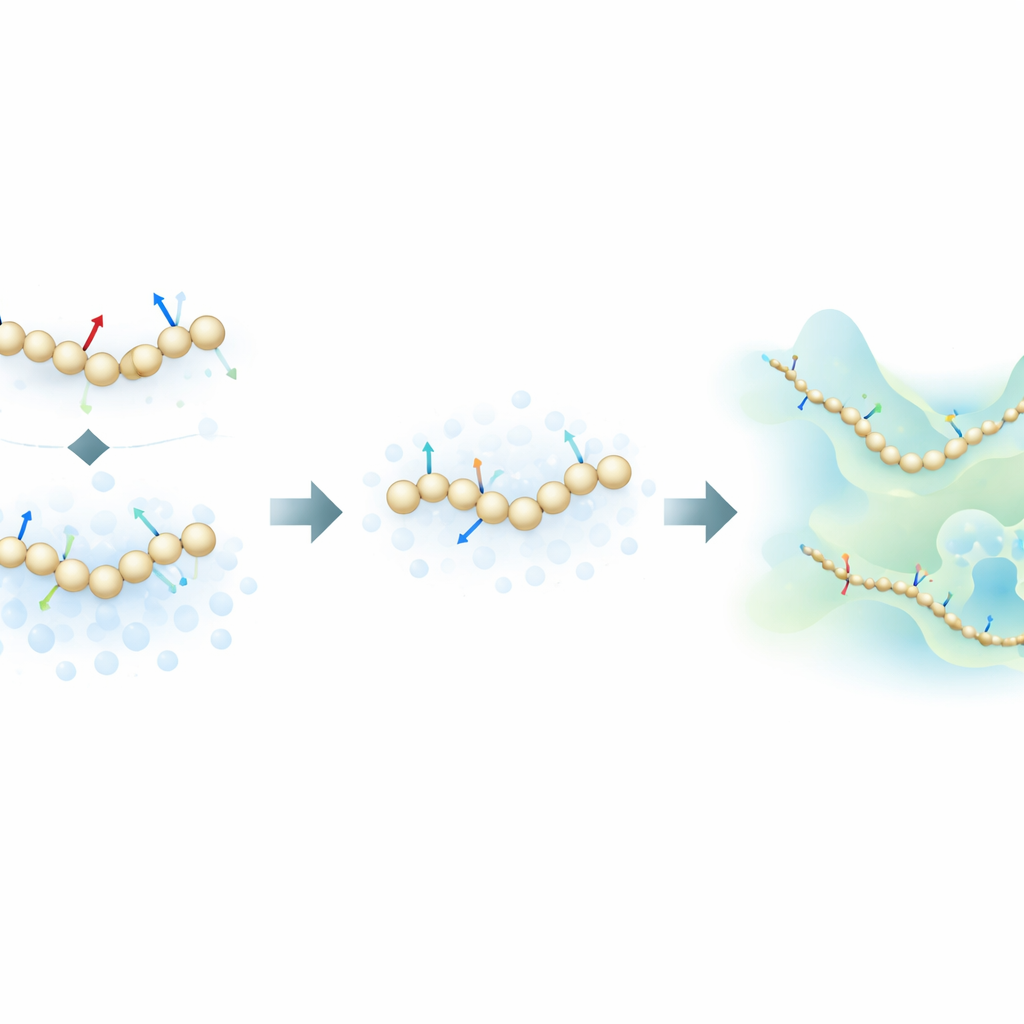
Ubiquitin הוא מבחן תובעני יותר: לכידת קיפולו ופתיחתו בטמפרטורות ריאליסטיות דרשה היסטורית חומרה מיוחדת וריצות אטומיות ארוכות במיוחד. כאן, המחברים מאמנים מודלים גרעיניים באמצעות קבוצת נתונים צנועה הכוללת סימולציות שיווי משקל קצרות סביב המצב המקופל ותספורות לא-שיווניות "נמשכות" שממתחות בכח את החלבון. למרות מערך האימון המוטה הזה והיעדר התייחסות אטומית מדויקת באותם תנאים, המודל שאומן עם שניהם — כוחות ורעש — משחזר תמונה ריאליסטית שבה מצבי מקופל ופרוש מתקיימים יחד, כאשר המצב המקופל מועדף מבחינת יציבות. לעומת זאת, מודל שאומן רק על כוחות נכשל ביצירת יציבות למצב המקופל כלל, ומודל מבוסס-רעש בלבד העדיף מבנים פרושים. באופן בולט, אף אחד מהמודלים הגרעיניים לא שינן פשוט את צורות המתיחה הקיצוניות מתוך נתוני האימון, מה שמעיד כי נוף האנרגיה הנלמד הוא בעל משמעות פיזיקלית ולא רק חותם של מסלולי הקלט.
מה המשמעות של זה עבור סימולציות בעתיד
על-ידי הפיכת הרעש לאות אימון ומיזוגו עם כוחות פיזיקליים, עבודה זו מראה כי ניתן לבנות מודלים גרעיניים מדויקים של חלבונים מתוך ערכות נתונים קטנות ופחות אידיאליות ממה שחשבו קודם. במעשה, זה אומר שחוקרים עשויים שלא להזדקק עוד לסימולציות אטומיות באורך מילישניות על מחשבי-על מיוחדים לפני שיוכלו לחקור את התנהגות המולקולה הביולוגית באמצעות דינמיקה גרעינית הנלמדת במכונה. במקום זאת, סימולציות צנועות יותר על חומרה נגישת תרשמנה מספקות די חומר לאימון מודלים מצומצמים רבי-עוצמה הלוכדים מסלולי קיפול מרכזיים ואיזונים תמאודינמיים. למרות שנותרו שאלות לגבי בחירה ופרשנות מיטביות של הרעש המתווסף וכיצד השיטה תתמודד עם צבירי ביומולקולות גדולים ומורכבים יותר, גישה זו מורידה משמעותית את הסף לשימוש בסימולציות גרעיניות מונעות נתונים ככלי שגרתי במדע המולקולרי.
ציטוט: Durumeric, A.E.P., Chen, Y., Pasos-Trejo, A.S. et al. Learning data-efficient coarse-grained molecular dynamics from forces and noise. Nat Commun 17, 2493 (2026). https://doi.org/10.1038/s41467-026-70818-0
מילות מפתח: דינמיקה מולקולרית גרעינית, שדות כוח בלמידת מכונה, סימולציות קיפול חלבונים, מודלים של דיפוזיה בכימיה, סימולציה חסכונית בנתונים