Clear Sky Science · he
תובנות מכנית לגבי פירוק מבוקר ע"י PCBP1 של DNA בצורת i-motif בבדיקת נקודת ה-G1/S
קפלים של DNA שפועלים כמו רמזורים
בתוך התאים שלנו, הקוד הגנטי הוא יותר מקפיצת סולם ישרה ופשוטה של ה-DNA. חלקים ממנו יכולים להתקפל לצורות לא שגרתיות הפועלות כמחוללים זעירים, ומסייעות לווסת מתי התאים מכפילים את ה-DNA שלהם ומתמיינים. מחקר זה מתמקד באחת הצורות הללו, המכונה i-motif, ובחלבון בשם PCBP1 שיכול לזהות ולפרום מבנים אלה בדיוק כשהתא מתכונן לשכפל את ה-DNA. הבנת האינטראקציה הזו מאירה כיצד תאים שומרים על יציבות הגנום ומה עלול להשתבש בסרטן.
קשרים מוזרים של DNA באזורים המשויכים לסרטן
רוב האנשים לומדים ש-DNA יוצר את סליל הכפול המפורסם, אבל מקטעים עשירים ב-'C' (ציטוזין) יכולים להתקפל לצומת בעלת ארבעה סיבובים המכונה i-motif. מבנים אלה נוטים להופיע באזורים בקרה של גנים המניעים גדילה תאית, כגון cMYC ו-BCL2. במשך שנים מדענים ודונו האם i-motif באמת נוצרים בתאים חיים, משום שהם נראים בקלות גדולה יותר בתנאי מבחנה חומציים מאשר בתנאים מניטרליים הקרובים לסביבה התאית. שימוש בנוגדנים מיוחדים שמזהים i-motif, עבודות עדכניות, כולל המחקר הנוכחי, אישרו כי הם אכן מופיעים בגרעיני התאים—ולעיתים קרובות מצטברים בקרבת גנים מרכזיים הקשורים לצמיחה וסרטן.
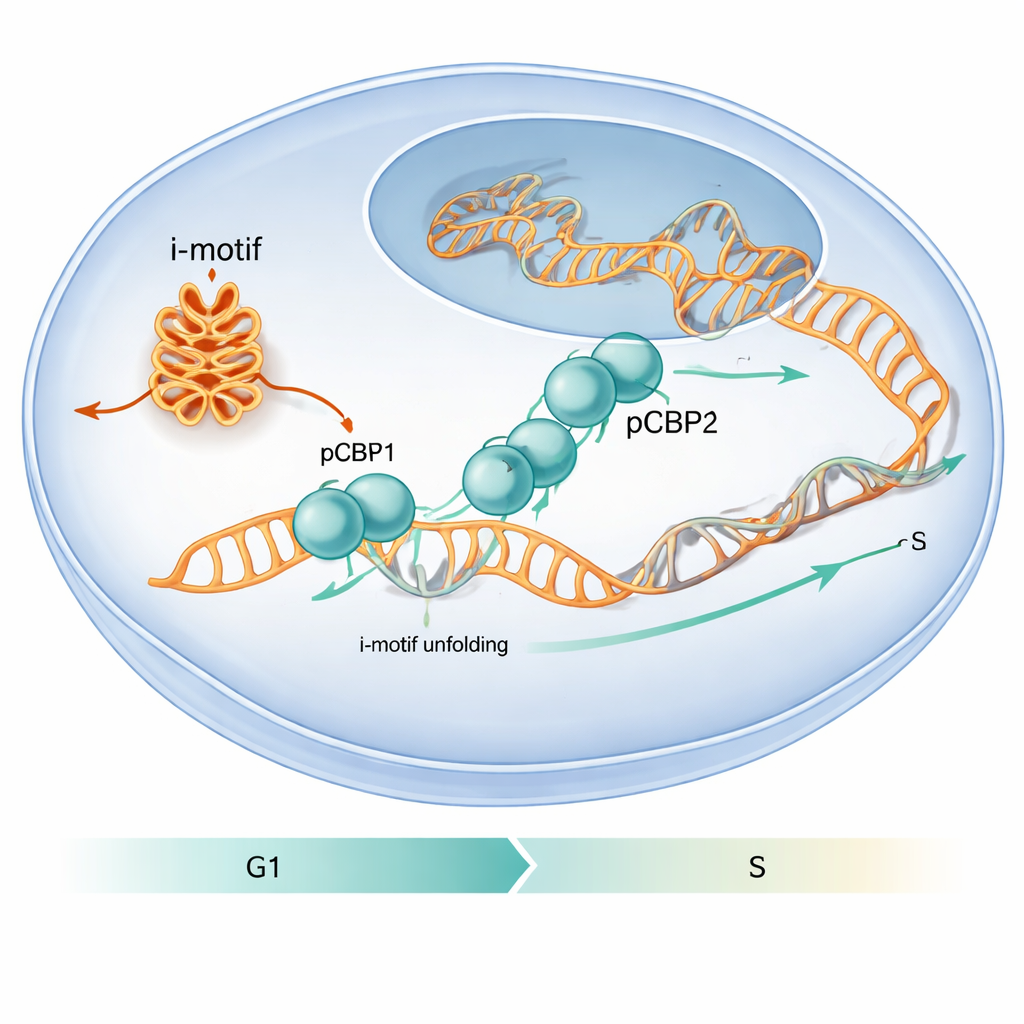
חלבון שבוחר קפלי DNA מסוימים
המחברים ניסו לגלות כיצד חלבונים בתא מתמודדים עם קפלי DNA לא שגרתיים אלה. הם התרכזו ב-PCBP1, חלבון הידוע כבר בקיבוע שלו למקטעים עשירים ב-C ב-DNA וב-RNA ובהשפעתו על מחזור התא. באמצעות ניתוח מפות קשירה על-גבי הגנום שנמצאות במאגר וקיום ניסויים ממוקדים, הם גילו כי PCBP1 נמצא לעתים תכופות על אזורים עשירים ב-C שיכולים ליצור i-motif, במיוחד סביב אתרי התחלת גנים. בניסויים בתאים על קווי תאים סרטניים אנושיים, מקטעים מתוך פרומוטרים של cMYC, BCL2 ושל רצף ILPR המקושר לאינסולין הראו גם אותות i-motif חזקים וגם כיסוי חזק של PCBP1, מה שמרמז ש-PCBP1 משמש שומר ייעודי של מבנים אלה.
איך PCBP1 תופס ומפרם את הצומת
בניסויי מבחנה, החוקרים השוו עד כמה PCBP1 נקשר ל-i-motifs מקופלים לעומת אותו רצף DNA במצב לא מקופל. הם כווננו את החומציות כך שה-DNA ישאר מקופל או יתיר את עצמו, תוך שמירה על יציבות החלבון. PCBP1 תמיד העדיף את ה-i-motif המקופל, וקשר אותו בכח בערך כפול לעומת אותו רצף כשהוא לא מקופל, ונקשר בחולשה לצורות DNA שאינן קשורות. לאחר הקשירה, PCBP1 יכל לקדם באופן פעיל פירום, מה שאיפשר לשרשרת ה-i-motif להיסתר עם המשלים שלה. עם זאת, לא כל ה-i-motifs פעלו באותו אופן: חלקם, כגון המבנה בפרומוטר של cMYC, נפרמו במהירות, בעוד אחרים, כמו אלה ב-BCL2, התנגדו ופרמו לאט יותר. תכונות נוספות כמו לולאות שיער בתוך ה-DNA ומידת הפרוטונציה של הציטוזינים (נשיאת מטען חיובי נוסף) יכלו לסייע או להפריע לפעילות הפירום של PCBP1.
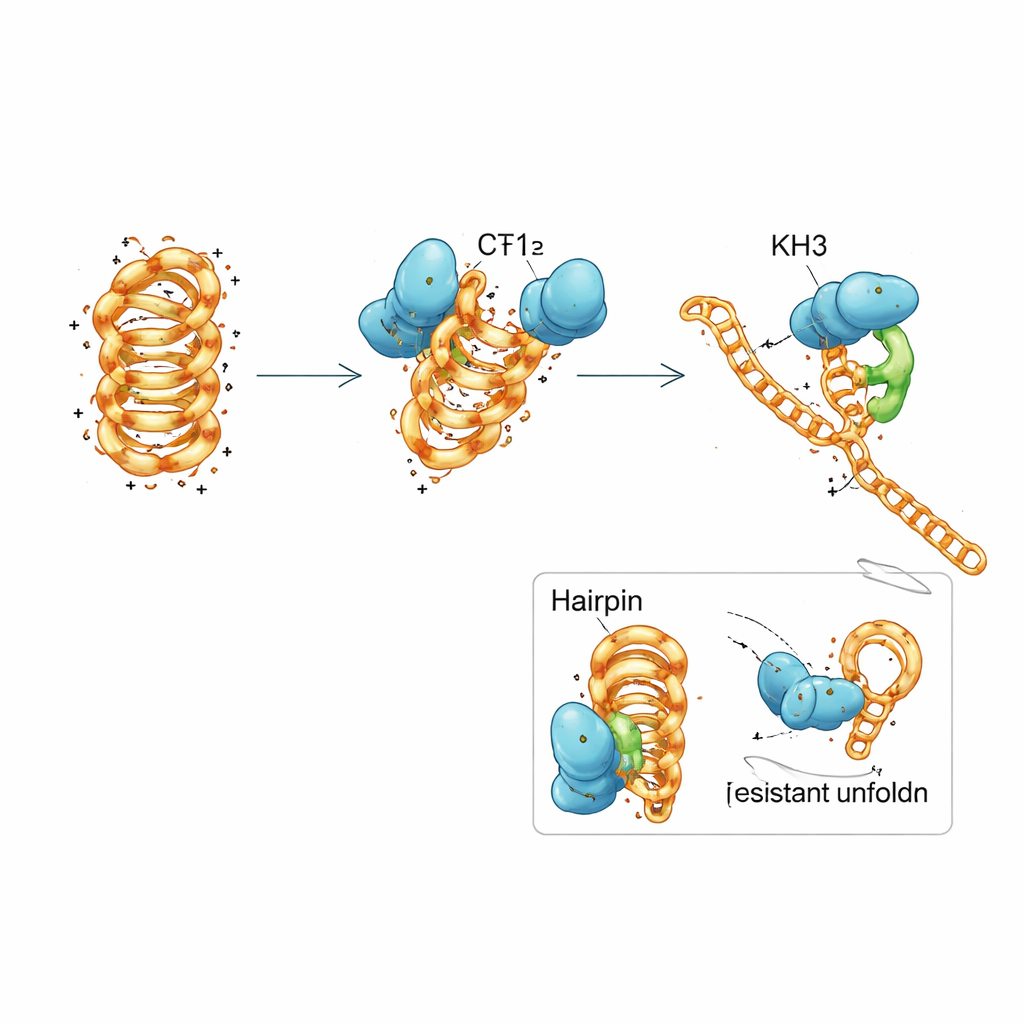
עבודת צוות בתוך חלבון בודד
PCBP1 מורכב משלושה מודולים חוזרים הנקראים דומייני KH, מוטיבים נפוצים שקושרים קטעים קצרים של חומצות גרעין. הצוות פירק את PCBP1 לחתיכות וגילה שאף דומיין KH יחיד אינו יכול לחקות במלואו את התנהגות החלבון השלם. שני הדומיינים הראשונים יחד יכלו להיצמד גם ל-DNA מקופל וגם ללא קיפול ולדחוף את ה-i-motif לכיוון צורה פחות יציבה, אך הם רק בקצב איטי קידמו פירום מלא. הדומיין השלישי בפני עצמו כמעט ולא התחבר כלל. כאשר כל שלושת הדומיינים היו נוכחים ויכלו לפעול יחד, החלבון שב וקיבל את העדפתו החזקה כלפי i-motifs מקופלים ואת יכולתו היעילה לפרום אותם. מדידות ביופיזיקליות מפורטות וסימולציות מחשב הציעו מנגנון בשלבים: KH1 ו-KH2 עוגנים תחילה לאזורי הלולאה הגמישים של ה-i-motif ופותרים בחלקם זוגות בסיס נבחרים, מה שמאפשר אז ל-KH3 להיכנס ולדחוף את המבנה למצב פתוח המוכן לשכפול.
שמירה על לוח הזמנים של מחזור התא
המחקר גם מראה שמחולל המולקולות הזה משנה את התנהגות התא. כאשר החוקרים הקטינו את רמות PCBP1 בתאים אנושיים, הופיעו יותר מבני i-motif בפרומוטרים מסוימים, סימני נזק ל-DNA עלו, והתאים נעצרו בנקודת הבדיקה הקריטית G1/S—השלב ממש לפני תחילת שכפול ה-DNA. בתנאים נורמליים, נוכחות PCBP1 באזורים היוצרים i-motif מגיעה לשיאה סביב נקודה זו, ואז יורדת כאשר מתחילה שלב S וה-i-motifs נפתרים. תזמון זה מרמז ש-PCBP1 פועל כאפוטרופוס: הוא נקשר ומפרום i-motifs מסוימים ברגע המתאים כך ששכפול ה-DNA יכול להמשיך באופן חלק והגנום ישמר שלם. לקורא שאינו מומחה, המסר הוא שקפלי DNA לא שגרתיים יכולים לפעול כחסימות זמניות, ו-PCBP1 הוא אחד הכלים המיוחדים שהתא משתמש בו כדי להסירם, מתוך מטרה למנוע שגיאות שעלולות לתרום להתפתחות סרטן.
ציטוט: Sengupta, P., Gillet, N., Obi, I. et al. Mechanistic insights into PCBP1-driven unfolding of selected i-motif DNA at G1/S checkpoint. Nat Commun 17, 1149 (2026). https://doi.org/10.1038/s41467-026-68822-5
מילות מפתח: DNA בצורת i-motif, חלבון PCBP1, נקודת ביקורת במחזור התא, יציבות הגנום, מבנה שניוני של DNA