Clear Sky Science · he
אטלס כמותי אבסולוטי של רנ״א קטנים שאינם מקודדים ברקמות ומוליכות תאים ממינים יונקים שונים
למה מולקולות רנ״א זעירות חשובות
בתוך כל תא, רוחות של מולקולות רנ״א זעירות מסייעות להחליט אילו גנים מופעלים או מושתקים. רנ״א קטנים אלה שאינם מקודדים מתפקדים כמו מתגי ווליום לתכניות הגנטיות שלנו, ועושים לדפוסי התפתחות, תפקוד אברים ומחלות. עם זאת, למרות טכנולוגיות ריצוף מתקדמות, מדענים התקשו למדוד במדויק כמה מהמולקולות הללו קיימות בתאים וברקמות שונות. המחקר הזה מציג שיטה מדויקת יותר לספירתן ובונה אטלס מפורט שמראה את השכיחות האמיתית שלהן ברקמות יונקים שונות ובשורות תאים נפוצות במעבדות.
דרך ברורה יותר לספור רנ״א קטנים
שיטות מסורתיות לריצוף רנ״א קטן מסתמכות על אנזימים שמצמידים אדפטורים לפני קריאת המולקולות. אנזימים אלה מעדיפים צורות וסיומות כימיות מסוימות, ולכן רנ״א מסוימים מתפסים ביעילות בעוד אחרים מפספסים או נספרים פחות. הטיה זו חמורה במיוחד עבור קטגוריות מסוימות כמו piRNA ורנ״א קטנים בצמחים, הנושאים קצוות כימיים מגנים. המחברים פיתחו פרוטוקול חדש, בשם 4NBoost, שמעצב מחדש את האדפטורים ותנאי התגובה כדי להחליש את ההעדפות הללו ומוסיף ברקוד מולקולרי משולב כדי להבחין בין מולקולות אמיתיות להעתקים שנוצרו בזמן ההגברה.
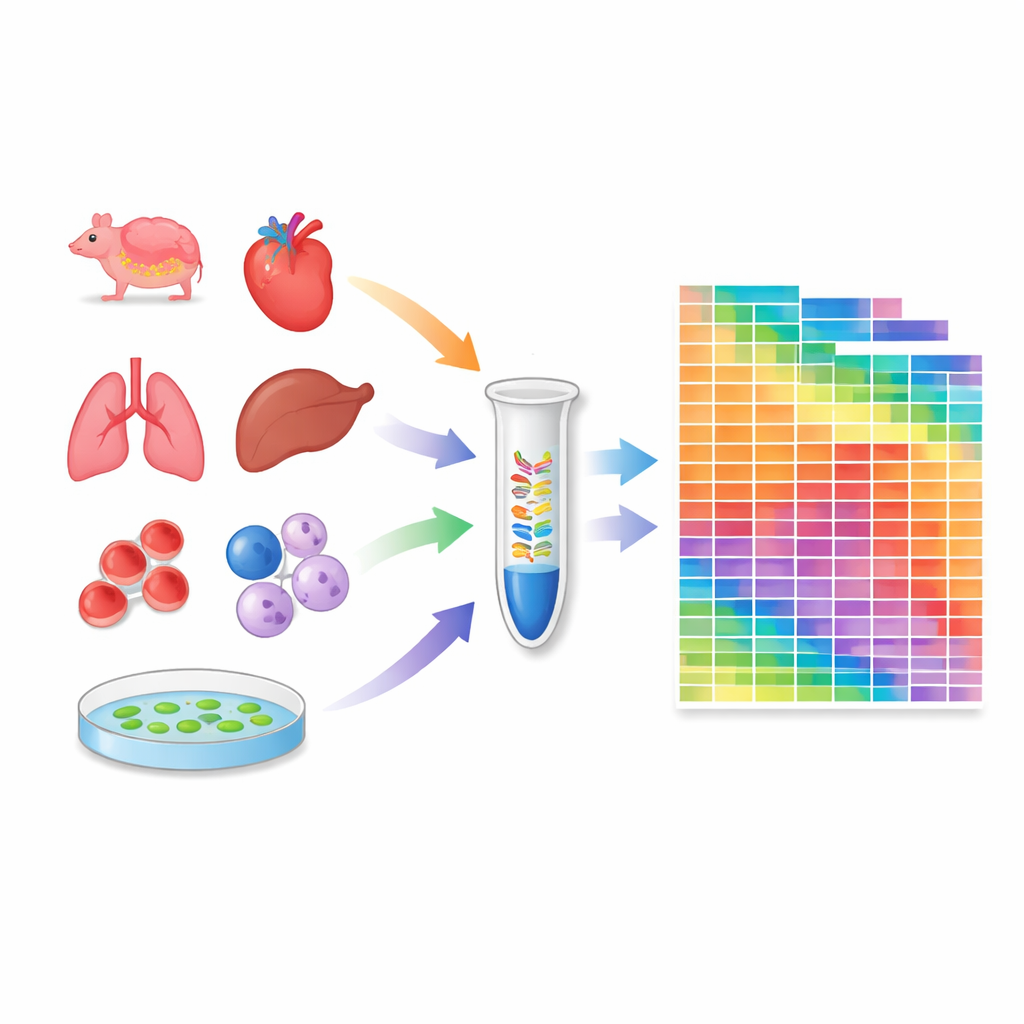
להפוך פרוטוקול לכלי מדידה
כדי להפוך את 4NBoost מקריאת יחסית לכלי מדידה ממשי, הצוות הוסיף רנ״א סינתטיים "ספייק‑אין" מתוכננים בקפידה בריכוזים ידועים וטווח רחב מאוד. על‑ידי השוואת כמה פעמים כל ספייק‑אין נקרא על ידי המכשיר לעומת כמה נוסף במקור, הם בנו עקומות תקן שממירות ספירות קריאה למספרי מולקולות אבסולוטיים. בדיקות עם תערובות ספייק‑אין שונות ורנ״א בקרה הראו ש‑4NBoost יכול לעקוב אחרי השכיחות בדיוק על פני סדרי גודל רבים, כולל רנ״א עם שינויים כימיים מטרידים. אפילו כאשר מתחילים מכמות כוללת של רנ״א של ננו־גרם אחד בלבד, השיטה עדיין תופסת ביושר את נוף הרנ״א הקטן.
בניית אטלס ברקמות ובשורות תאים
מצוידים בפרוטוקול המכויל הזה, החוקרים פרופילו 259 דגימות: 20 רקמות מחולדות, 18 ממקוקי קרב‑איט (crab‑eating macaques), 24 שורות תאים נפוצות של אדם וחולדה, וכמה רקמות מהצמח המודל Arabidopsis. עבור כל דגימה הם העריכו את המספר האבסולוטי של מולקולות לאלפי microRNA ו‑piRNA. זה חשף כמה מיני microRNA שונים נוכחים בכל הקשר ואיך כמויותיהם הכוללות משתנות בין רקמות ומינים. כמה שורות תאים ואיברים נושאים מאגר עשיר במיוחד של microRNA, בעוד אחרים, כמו תאי דם, נשלטים על‑ידי כמה מינים בעלי שוויון גבוה. האטלס גם חשף הבדלים משמעותיים בין רקמות חולדה לקוף, מה שמדגיש כי ויסות רנ״א קטן יכול להיות תלוי מין.
תיקון נתונים ישנים ותיקון הנחות מקובלות
כאשר השוו את האטלס החדש למאגרי רנ״א קטנים פופולריים שנבנו בשיטות מקובלות, הופיעו סטיות בולטות. כמה משפחות microRNA חשובות — כגון miR‑19 ו‑miR‑29 — נמצאו בשכיחויות גבוהות בהרבה ממה שחשבו קודם, בעוד אחרות — כגון משפחות let‑7 ו‑miR‑10 הנחקרות לעתים תכופות — הוערכו לעתים ביתר. המחקר גם בחן מחדש איזו "זרוע" של כל קיפולי‑המקור (hairpin) משמשת בפועל בתאים, וגילה מקרים שבהם האנוטציות הנוכחיות מציינות את הגדיל המרכזי הלא נכון. כדי להציל את המאגרים הממשיכים להכיל נתונים מוטים, המחברים אימנו מודל למידת מכונה שלומד כיצד מדידות מקובלות סטו מ‑4NBoost ואז מתקנים אותן מתמטית כדי לשקף טוב יותר שכיחויות אמיתיות.
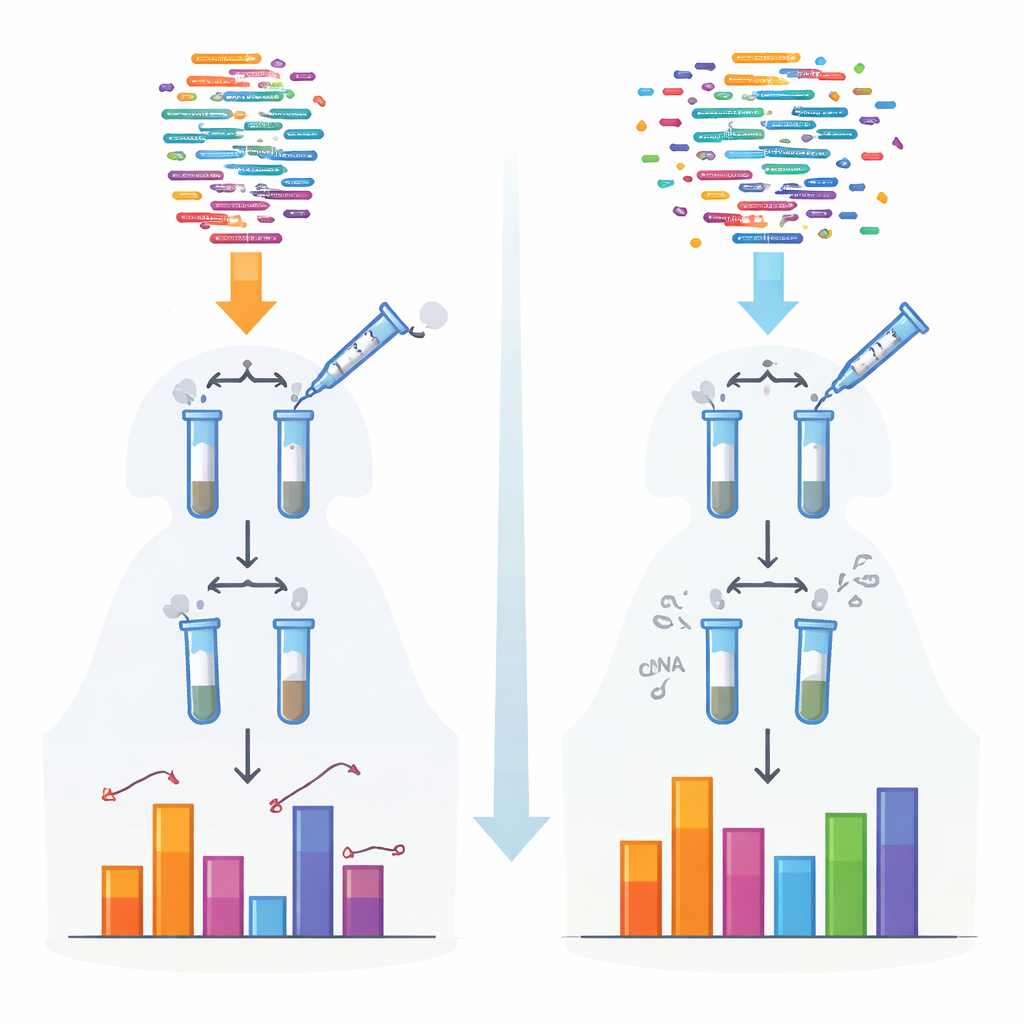
משאב ציבורי לחקירת רנ״א קטנים
כל המדידות של 4NBoost ומודל התיקון זמינים בחופשיות דרך פלטפורמה מקוונת בשם SmRNAQuant. חוקרים יכולים לגלוש או להוריד ערכי רנ״א קטנים אבסולוטיים לרקמות, שורות תאים או microRNA ספציפיים, והם יכולים להעלות את הנתונים שלהם שהוכנו בערכה מקובלת כדי לקבל ערכים מתוקנים מהטיה. עבור לא‑מומחים, המסר המרכזי הוא שספירה חשובה: הבדלים זעירים במספר העתקים של רנ״א קטן יכולים להכריע בין ויסות גני פעיל לבין חוסר השפעה. על ידי הצעת מספרים מהימנים יותר ודרך לתקן נתונים ישנים, עבודה זו מניחה יסוד כמותי איתן יותר להבנת האופן שבו רנ״א קטנים מעצבים ביולוגיה תקינה ומחלה.
ציטוט: Xiao, W., Zheng, Y., Zhang, H. et al. An absolute quantification atlas of small non-coding RNAs across diverse mammalian tissues and cell lines. Nat Commun 17, 2314 (2026). https://doi.org/10.1038/s41467-026-68812-7
מילות מפתח: כימות microRNA, רנ״א קטן שאינו מקודד, הטיה בריצוף רנ״א, אטלס הבעה ברקמות, תיקון למידת מכונה