Clear Sky Science · he
מיפוי אוטומטי של התקדמות מזלגות שכפול ה-DNA בתאי אדם באמצעות ForkML
מדוע חשוב לעקוב אחרי קצב העתקת ה-DNA
בכל חלוקה של תא אנושי יש להעתיק במהירות ובדיוק יותר משלושה מיליארדי אותיות DNA. אם תהליך ההעתקה מאט או נעצר, זה עלול לפגוע בגנום ולתרום לסרטן ולהפרעות בהתפתחות. עד היום לא היה שיטה פשוטה לראות בדיוק באיזו מהירות "מכונות ההעתקה" הבודדות נעות לאורך קטעים ספציפיים של ה-DNA האנושי. מאמר זה מציג את ForkML, טכניקה חדשה המשתמשת בריצוף נאנופור ולמידת מכונה כדי לאוטומט את המשימה בקנה מידה חסר-תקדים.
צפייה במכונות ההעתקה של התא באופן לא ישיר
ה-DNA מוכפל על ידי מכונות מולקולריות זעירות הנקראות מזלגות שכפול, שנעות לאורך הסליל הכפול ויוצרות שרשראות חדשות. ForkML מאפשרת לחוקרים לצפות במזלגות האלה באופן לא ישיר על ידי הוספת תג כימי חסר-נזק, BrdU, ל-DNA שנוצר בשתי התפרצויות קצרות מאוד המופרדות בזמן קבוע. כיוון שניתן לזהות BrdU במולקולות DNA יחידות ברצפי נאנופור, החוקרים יראו שתי "פסים" מתויגים בכל גדיל DNA היכן שמזלג עבר במהלך שתי הדקות. על ידי מדידת המרחק בין הפסים וחלוקה בהפרש הזמן הידוע, ניתן לחשב באיזו מהירות כל מזלג נע באזור זה של הגנום. 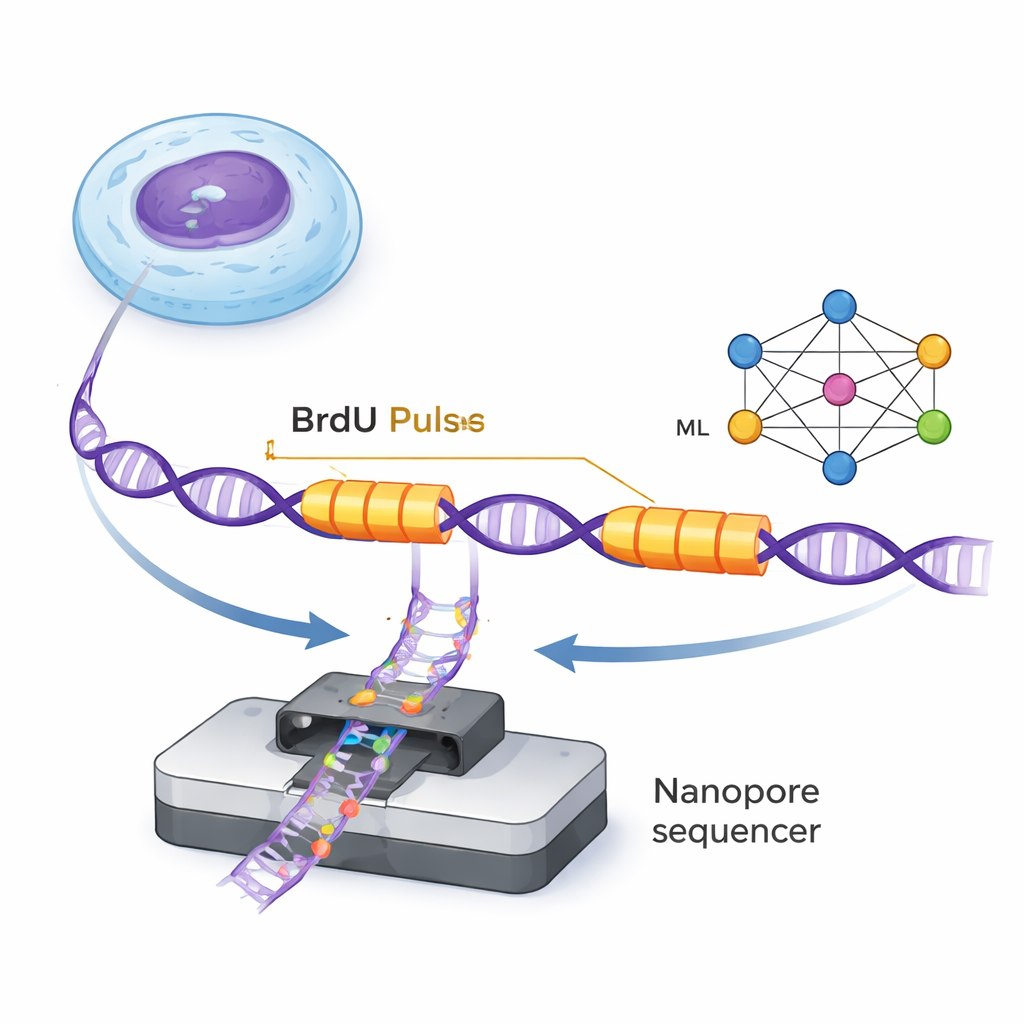
לימוד המחשב לקרוא את המסלולים הכימיים
בעבודות קודמות עם שמרים, המחברים יכלו לאתר את מסלולי ה-BrdU באמצעות חוקים פשוטים, אך בתאים אנושיים האותות חלשים ומורכבים יותר. מומחים אנושיים עדיין מצליחים לזהות את התבנית האופיינית — עלייה חדה ב-BrdU עם תחילת הפולס ואחריה ירידה מתונה כשמוסרים את התווית — אך לזהות זאת בעין עבור מיליוני מקטעי DNA אינו מעשי. ForkML פותרת זאת על ידי אימון רשת עצבית, צורת למידת מכונה, על אלפי דוגמאות שסומנו ידנית. המודל לומד לסווג כל מקטע DNA כרקע או כמזלג נע ימינה או שמאלה, ולמקד את תחילת כל פולס BrdU ברזולוציה גבוהה. זה מאפשר מיפוי אוטומטי מלא של אלפי מדידות מהירות מזלג בודדות מתוך ריצוף אחד.
מדידת סטרס ושונות ברחבי הגנום
בהפעלת ForkML על שורת תאי סרטן המעי הגס האנושית, הקבוצה השיגה מעל 2,000 מדידות מהירות מזלג לניסוי ומצאה שהמזלג הטיפוסי נע בכ-1.2 קילובס ללילה (ק להבדיל מילי בסיס בדקה), בהתאמה לשיטות קודמות בעלות תפוקה נמוכה יותר. כאשר טיפלו בתאים בתרופות הידועות כמאטות שכפול DNA, ForkML זיהתה בבירור את ההאטה, והראתה שהיא רגישה למדידת מתח שכפול. מכיוון שכל מזלג ממופה בחזרה למיקומו ברפרנס הגנומי, המחברים יכלו לקשר את המהירות לתכונות אחרות, כגון מתי אזור משתכפל במהלך מחזור התא, עד כמה ה-DNA דחוס, ועד כמה הוא מתורגם באופן פעיל ל-RNA. 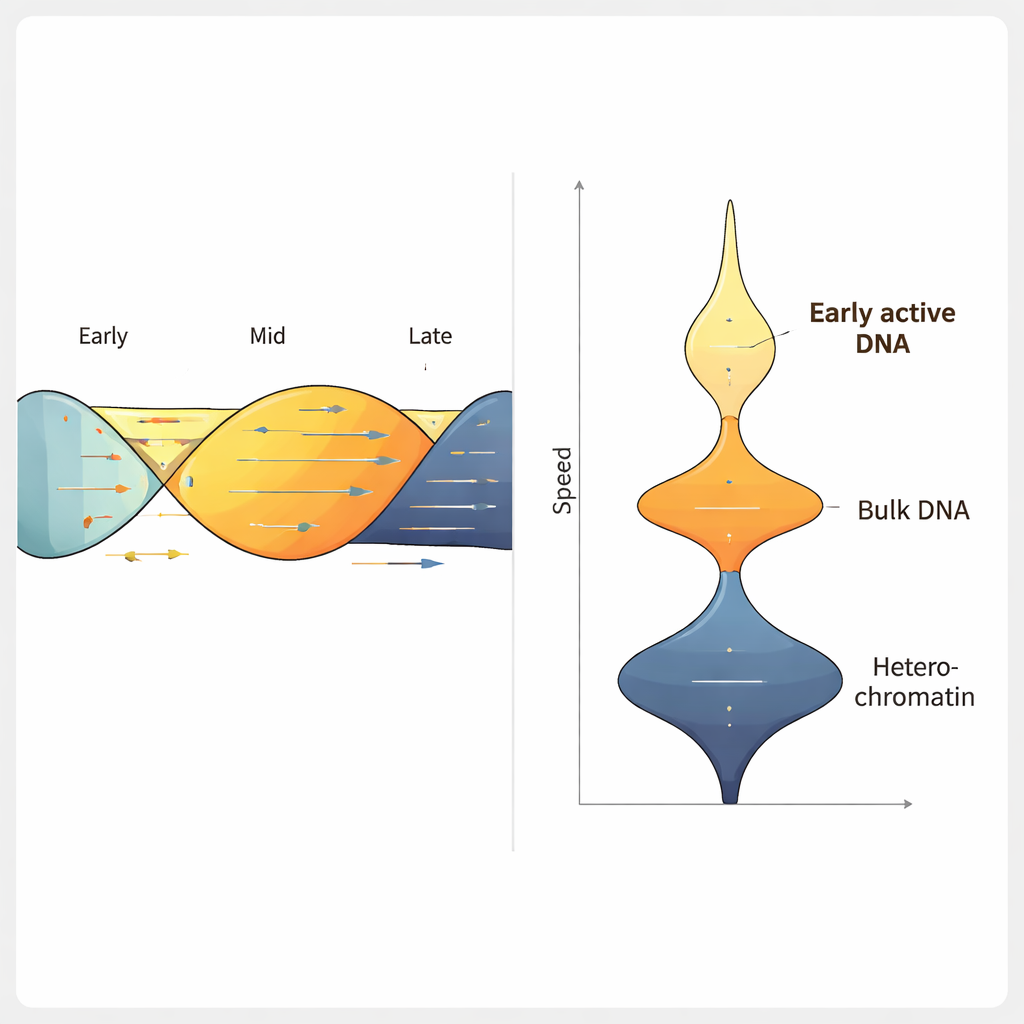
חשיפת מיקומי תחילת ההעתקה והבדלים בין הגדילים
מעבר למהירות, ForkML מזהה גם היכן מתחילה ומסתיימת שכפול ה-DNA, על ידי זיהוי נקודות שבהן מזלגות מתפצלות או מתכנסות על אותה מולקולה. על ידי מיפוי יותר מ-20,000 אתרי התחלה כאלה, המחברים מאשרים שתאי אדם משתמשים באסטרטגיה מעורבת: חלק מההתחלות מתרחשות באזורי ייזום מוגדרים היטב, אבל רוב ההתחלות מפוזרות ברחבי הגנום. על ידי שילוב כיוון המזלג עם באיזה גדיל DNA נקרא הרצף, ForkML גם יכולה להבחין בין קצבי הסינתזה של הגדיל המוביל והגדיל המטושטש — משהו ששיטות סיביות מסורתיות אינן מאפשרות. ניסויים בשש שורות תאים אנושיות שונות — נורמליות וממאירות כאחד — מראים שהתנאים הפשוטים של תיוג BrdU עובדים באופן רחב ומניבים הערכות מהירות יציבות בכל מקרה.
שדרוג דיגיטלי של טכניקה קלאסית
לא-מומחים יכולים לראות ב-ForkML גרסה מודרנית ודיגיטלית של assay סיבי ה-DNA הקלאסי: היא משתמשת בסכמת תיוג דומה, אך מחליפה מיקרוסקופיה ידנית בריצוף ארוך-קריאה ולמידת מכונה. זה מביא תפוקה גבוהה בהרבה, הצבה ישירה של כל מדידה על הגנום ומידע מפורט יותר על איפה ובאיזו מהירות ה-DNA מועתק. מאחר שהפרוטוקול פשוט, תואם לחומרת נאנופור קיימת וניתן להתאמה לאורגניזמים אחרים, ForkML צפוי להפוך לכלי סטנדרטי לחקר שכפול ה-DNA. למעשה, הוא מציע לחוקרים דרך חזקה לקשר בין מהירות העתקה מקומית — תקינה או תחת מתח — לבין פעילות גנים, מצב הכרומטין ושינויים בגנום הקשורים למחלות.
ציטוט: Rojat, V., Ciardo, D., Tourancheau, A. et al. Automated mapping of DNA replication fork progression in human cells with ForkML. Nat Commun 17, 1975 (2026). https://doi.org/10.1038/s41467-026-68750-4
מילות מפתח: שכפול DNA, מהירות מזלג השכפול, ריצוף נאנופור, תיוג BrdU, למידת מכונה בגנומיקה