Clear Sky Science · he
הערכת טכנולוגיות אטלסינג של single-cell ATAC‑seq באמצעות דוגמנות רצף-לפעולה
לקרוא את ספר ההוראות של התא
כל תא בגופך קורא את אותו DNA, אך תאי מוח, תאי שריר ותאי מערכת החיסון מתנהגים בצורה שונה מאוד. מאמר זה מתמודד עם חידה מרכזית שמאחורי המגוון הזה: כיצד מקטעים קצרים של DNA הנקראים מגבירים (enhancers) פועלים כמפתחות שמדליקים וכבים גנים בתאים מסוגים מסוימים. המחברים מראים שטכנולוגיה מעבדתית חדשה וזולה יותר יכולה לייצר את קבוצות הנתונים האדירות הדרושות לאימון מודלים מודרניים של למידה עמוקה שקוראים רצפי DNA ומנבאים אילו מגבירים פעילים באילו תאים, ובכך מקרבים אותנו לפיענוח אמיתי של "דקדוק" הוויסות הגנומי.
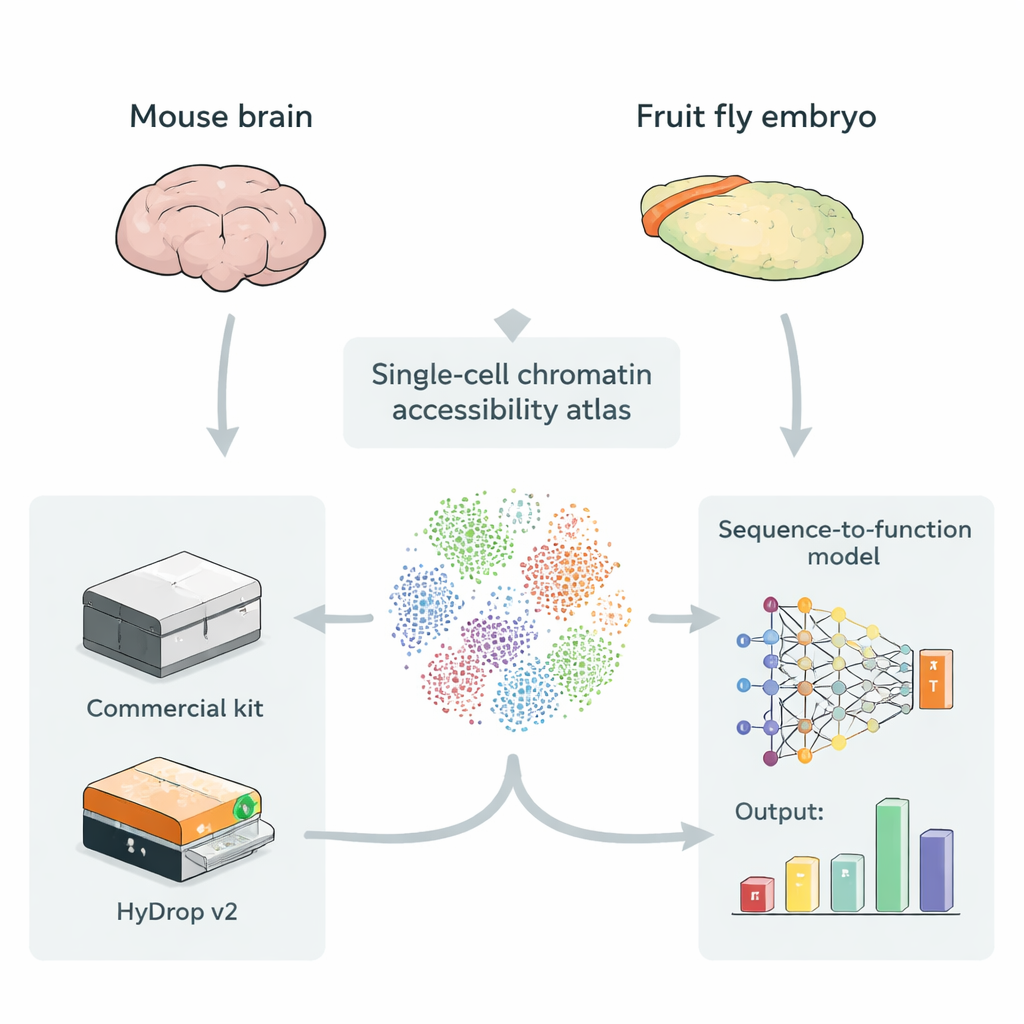
יצירת מפות של DNA פנוי בתאים יחידים
מגבירים בדרך כלל יושבים באזורי DNA שנגישים יותר ופתוחים יותר, מה שמקל על חלבוני ויסות להיקשר אליהם. טכניקה בשם single‑cell ATAC‑seq מודדת אילו חלקים של הגנום פתוחים באלפים עד מאות אלפי תאים בודדים בו‑זמנית, ויוצרת "אטלס" של DNA נגיש על פני סוגי תאים רבים. אטלסים אלה הם דלק אידיאלי למודלים של למידה עמוקה שלוקחים רצף גולמי של DNA כקלט ולומדים לחזות כמה חזק כל אזור קטן פועל כמגביר בכל סוג תא. עם זאת, עד כה רוב האטלסים הללו בוססו על מכשירים מסחריים יקרים, מה שהעלה את השאלה האם שיטות בעלות נמוכה ובקוד פתוח יכולות לספק נתוני אימון בעלי ערך שווה למודלים אלה.
חלופה בקוד פתוח לפלטפורמות מסחריות
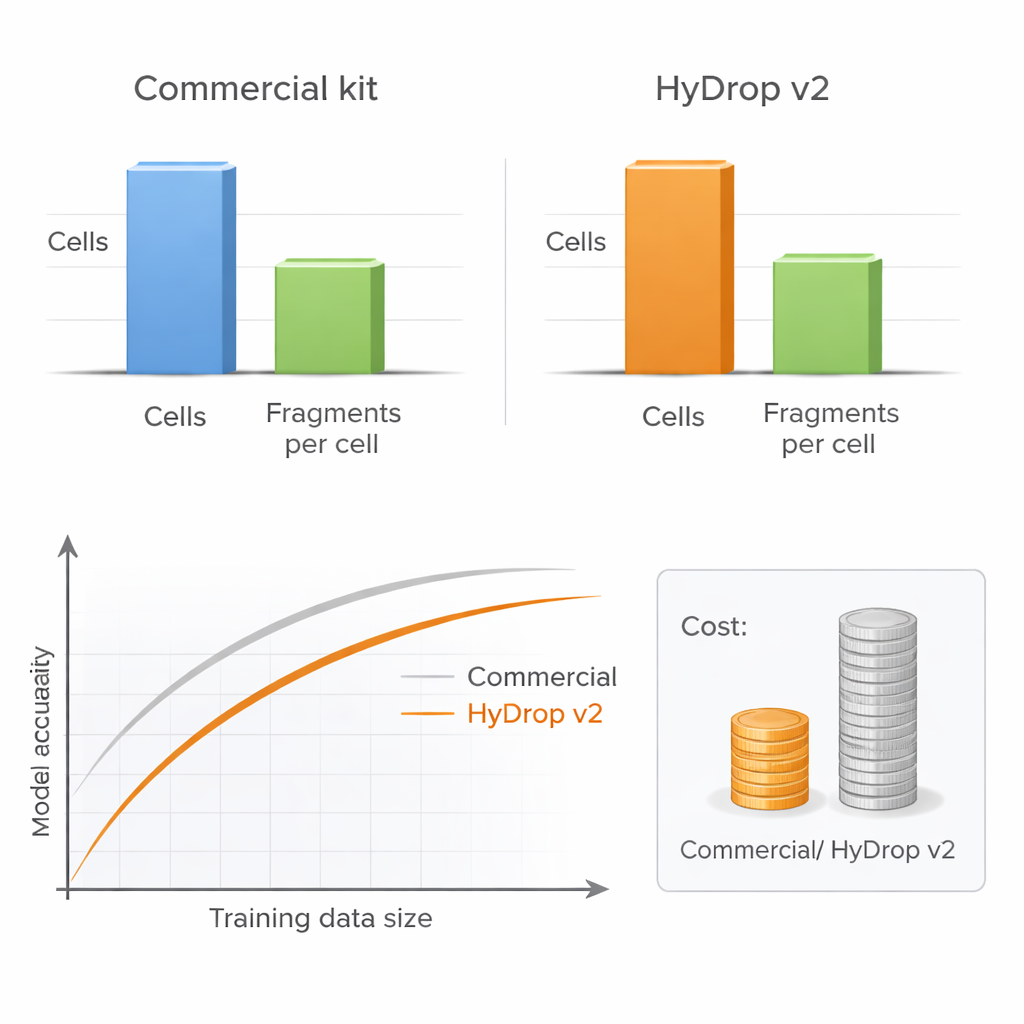
המחברים מציגים את HyDrop v2, שיטה משופרת מבוססת טיפות (droplet) ל‑single‑cell ATAC‑seq שמשתמשת בחרוזי הידרוגל מותאמים לתיוג ברקודים של תאים בודדים. הם משווים את HyDrop v2 לחבילת מסחרית נפוצה על ידי בניית אטלסים גדולים משני מערכות שונות מאוד: קליפת המוח המוטורית של עכבר בוגר ועוברים בשלבים מתקדמים של זבוב הפרי. HyDrop v2 מייצרת איכות נתונים דומה—משחזרת את אותם סוגי התאים העיקריים וקבוצות אזורים נגישים מאוד דומות—ובזול בערך פי ארבעה עשר לדגימת מוח עכבר. חשוב לציין שניתן לשלב בצורה חלקה נתונים מניסויים של HyDrop v2 עם נתונים מסחריים, כלומר חוקרים יכולים לערבב ולתאם פלטפורמות בעת בניית אטלסים מאוד גדולים.
אימון מודלים של למידה עמוקה לקריאת לוגיקת המגבירים
כדי לבחון האם נתונים זולים יותר מספיקים למודלים מתקדמים, הצוות מאמן מודלים של רצף‑ל‑פעולה מבוססי למידה עמוקה על אטלסים מסחריים או על אטלסים של HyDrop v2. מודלים אלה לומדים ישירות מרצף ה‑DNA לחזות כמה אזור נגיש בכל סוג תא, ויכולים להדגיש דפוסי רצף קצרים שלסביר שהם אתרי קשירה לחלבוני ויסות ספציפיים. בקורטקס העכבר, מודלים שאומנו על נתוני HyDrop v2 תואמים במדויק למודלים מבוססי נתונים מסחריים מבחינת הדיוק הכללי וביכולתם לשחזר "מתגי" מגביר ידועים שאומתו בעבר בחיות חיות. בעובר הזבוב, שתי הפלטפורמות תומכות במודלים שיכולים לזום לתוך אזורים של 2,000 בסיסים ולזהות את קטעי הליבה של כ‑500 בסיסים שמניעים בפועל פעילות מגביר ספציפית לרקמה, כגון אזורים השולטים בביטוי גנים בניורובלסט או שריר.
יותר תאים יכולים לגבור על עומק רב יותר
שאלה מעשית מרכזית לכל מעבדה היא האם לרצף כל תא לעומק רב או לפרופיל יותר תאים בעומק נמוך יותר. על‑ידי שינוי שיטתי של מספר התאים ומספר השברים (fragments) של DNA לכל תא, המחברים מראים שביצועי המודלים כמעט לא נפגעים כאשר עומק הרצף מוקטן לרמה מתונה, כל עוד נכללים מספיק תאים. לעומת זאת, קיצוץ במספר התאים פוגע בבירור בדיוק המודל, במיוחד כשבוחנים ביצועים על פני סוגי תאים רבים בו‑זמנית. מאחר ש‑HyDrop v2 זולה הרבה יותר לכל תא, חוקרים יכולים להוסיף בקלות עשרות אלפי תאים נוספים, ולהשיב או אפילו להתעלות על ביצועי המודלים מבוססי המסחרי בחלק קטן מהעלות.
לראות טביעות רגל של חלבונים על ה‑DNA
המחקר בודק גם האם פלטפורמות מעבדתיות שונות מטילות הטיות עדינות באופן שבו אנזים ה‑ATAC חותך את ה‑DNA, מה שעלול להטעות מודלים שמנסים להסיק היכן חלבונים יושבים על הגנום. באמצעות כלי רשת עצבית נפרד שמתקן העדפות אנזים, המחברים מראים ש‑HyDrop v2 והערכות מסחריות מייצרות דפוסי פעילות אנזימטית כמעט זהים הן בתאי עכבר והן בתאי זבוב. לאחר התיקון, שתי קבוצות הנתונים חושפות "טביעות רגל" בקנה מידה דק שבהן חלבוני ויסות ונוקלאוזומים נראים כמגנים על ה‑DNA מפני חיתוך, וטביעות אלו מסתדרות עם דפוסי הרצף שהודגשו על ידי מודלי הרצף‑ל‑פעולה. התאמה זו מציעה שפלטפורמות בקוד פתוח ומסחריות ראויות באותה מידה למחקר מפורט של אינטראקציות חלבון‑DNA.
מדוע זה חשוב לפיענוח הגנום
ללא‑מומחים, המסר המרכזי הוא שנוכל כעת לבנות מפות מאוד גדולות ונגישות של השימוש ב‑DNA בתאים בודדים, ולאמן מודלים עוצמתיים של למידה עמוקה על אטלסים אלה מבלי להסתמך רק על חומרה קניינית יקרה. HyDrop v2 מספקת נתונים התומכים בחיזוי גבירים, בפרשנות דפוסי רצף ובטביעות רגל של קשירת חלבונים ברמה שתואמת שיטות מסחריות מובילות, בתנאי שיטופלו מספיק תאים. הדבר פותח אפשרות לבניית אטלסים ארגאניזם‑רחבים של אלמנטים רגולטוריים בבריאות ובמחלה, ומאיץ מאמצים לקרוא את הוראות הוויסות של הגנום ולתכנן מתגים גנטיים חדשים ומדויקים למחקר ולתרפיה בעתיד.
ציטוט: Dickmänken, H., Wojno, M., Mahieu, L. et al. Evaluating single-cell ATAC-seq atlasing technologies using sequence-to-function modeling. Nat Commun 17, 1951 (2026). https://doi.org/10.1038/s41467-026-68742-4
מילות מפתח: single-cell ATAC-seq, מגבירים (enhancers), מודלים של למידה עמוקה, ויסות גנים, גנומיקה בקוד פתוח