Clear Sky Science · fr
Paysage génomique de la résistance aux antimicrobiens en Inde : résultats d'une étude de surveillance multi‑espèces
Pourquoi les super‑bactéries en Inde nous concernent tous
Les « super‑bactéries » résistantes aux antibiotiques sont une préoccupation mondiale croissante, mais nous en savons encore étonnamment peu sur la façon dont ces germes évoluent et se propagent dans de nombreuses régions du globe. Cette étude examine de près des bactéries dangereuses issues d’hôpitaux en Inde et lit leur ADN complet pour comprendre comment elles contournent nos antibiotiques les plus puissants. Les résultats révèlent non seulement ce qui rend ces microbes si difficiles à éliminer, mais évaluent aussi si des méthodes rapides basées sur l’ADN peuvent remplacer de façon fiable les tests de laboratoire plus lents — une question qui pourrait influencer la prise en charge des infections partout dans le monde.
Examiner de plus près les infections hospitalières
Les chercheurs ont collecté 266 échantillons bactériens auprès de patients gravement malades dans de grands hôpitaux du nord et de l’ouest de l’Inde entre 2022 et 2024. La plupart des prélèvements provenaient de sang, mais aussi d’urine et d’infections pulmonaires, et la majorité provenait d’unités de soins intensifs, où les patients sont les plus vulnérables. L’équipe s’est concentrée sur des germes problématiques bien connus — tels que Escherichia coli, Klebsiella pneumoniae, Acinetobacter baumannii, Pseudomonas aeruginosa, le Staphylococcus aureus résistant à la méticilline (SARM) et les entérocoques résistants à la vancomycine (ERV). Pour chaque échantillon, les médecins avaient déjà réalisé des tests standard de sensibilité aux antibiotiques, qui exposent les bactéries aux médicaments en laboratoire pour voir quels traitements restent efficaces. Les scientifiques ont ensuite séquencé les génomes des bactéries pour cartographier l’ensemble des gènes de résistance et ont comparé ce que l’ADN « prédisait » avec les résultats observés en éprouvette.
Quand gènes et éprouvettes divergent
En confrontant les prédictions génétiques aux résultats de laboratoire pour 56 antibiotiques différents, l’étude a réalisé plus de 5 000 comparaisons. Dans la plupart des cas, la méthode basée sur le génome et les tests traditionnels concordaient, mais près de 600 discordances ont été relevées. L’erreur la plus fréquente était que l’outil génomique prédisait qu’une bactérie serait résistante alors que le test de laboratoire indiquait qu’elle restait traitable. Cela s’est produit souvent pour des médicaments tels que la minocycline, la colistine et la gentamicine, en particulier chez E. coli. L’erreur opposée — lorsque le laboratoire détectait une résistance que les gènes n’expliquaient pas clairement — était moins fréquente mais plus préoccupante, car elle risque de passer à côté d’une résistance réelle. Ces discordances « très majeures » sont apparues de manière notable chez des bactéries intestinales appelées entérocoques, en particulier pour des antibiotiques de type pénicilline largement utilisés et pour la combinaison triméthoprime‑sulfaméthoxazole.
Arsenaux dissimulés dans l’ADN bactérien
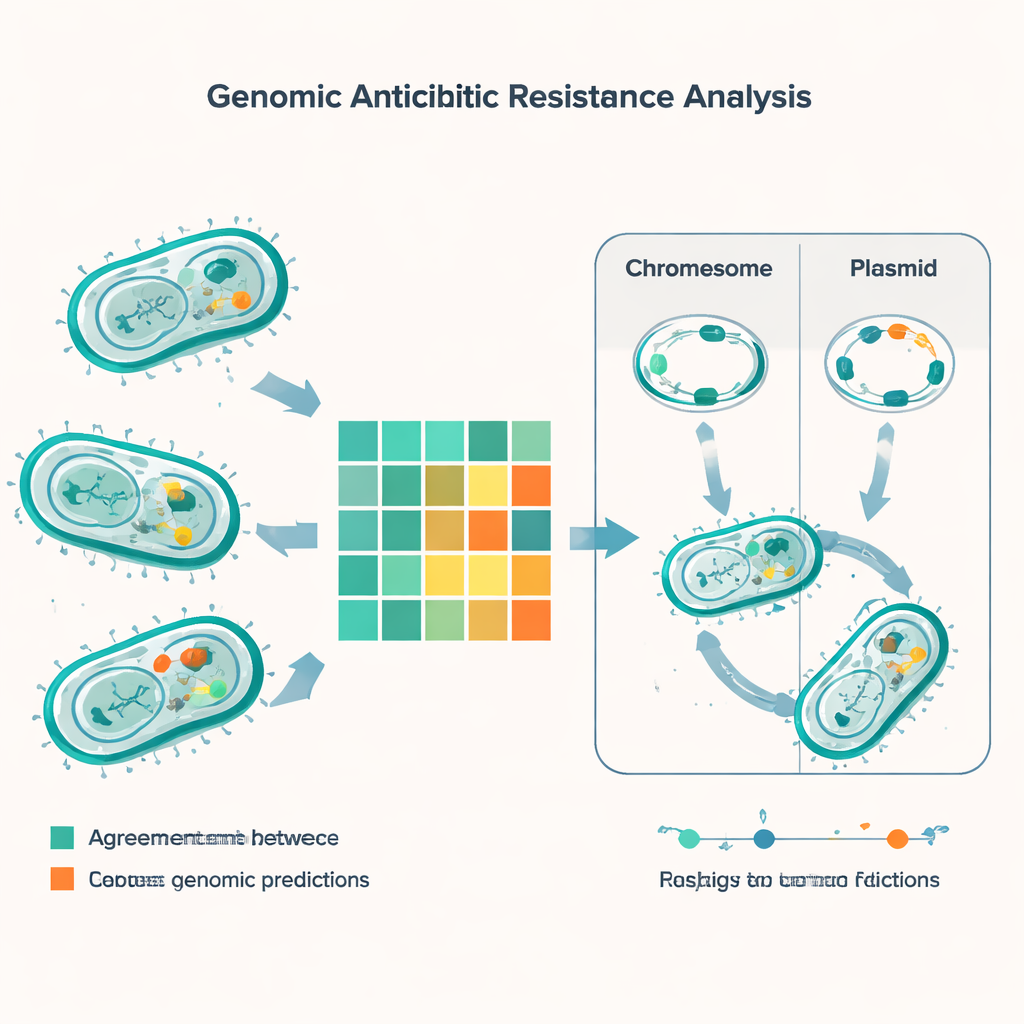
Le levé génomique a mis au jour un arsenal dense de gènes de résistance parmi les principales espèces. Chacun des pathogènes Gram‑négatifs courants portait au moins un gène codant une bêta‑lactamase, capable de dégrader la pénicilline et les médicaments apparentés, et de nombreuses souches possédaient plusieurs de ces gènes simultanément. Des coupables notoires comme les carbapénèmases de type NDM — qui neutralisent des antibiotiques de dernier recours — étaient répandus chez E. coli, Klebsiella, Acinetobacter et Pseudomonas. L’étude a aussi identifié des gènes aidant les bactéries à survivre à des antibiotiques puissants de type « peptide », comme la colistine, ainsi que le gène classique mecA conférant la résistance des SARM à la méticilline et des grappes de gènes de résistance à la vancomycine chez les entérocoques. En comparant des profils ADN appelés types de séquence, l’équipe a relié certains de ces gènes de résistance à des lignées bactériennes à haut risque déjà en expansion en Inde et dans le monde.
Échange de gènes via l’ADN mobile
Une partie cruciale de l’histoire ne réside pas seulement dans les gènes que portent les bactéries, mais dans l’endroit où ces gènes se trouvent. Beaucoup de gènes de résistance reposent sur de petits cercles d’ADN appelés plasmides, que les bactéries peuvent s’échanger comme des cartes à collectionner. À l’aide de logiciels spécialisés, les chercheurs ont prédit environ 1 400 plasmides parmi les échantillons, avec une diversité particulièrement élevée chez E. coli et Klebsiella. Dans ces espèces, une grande part des gènes de résistance — y compris plusieurs bêta‑lactamases critiques — étaient portés par des plasmides, ce qui facilite leur transfert entre souches et même entre espèces. D’autres traits de résistance étaient intégrés dans les chromosomes bactériens, ce qui signifie qu’ils peuvent persister même si les plasmides sont perdus. L’équipe a aussi catalogué des éléments génétiques mobiles — courts segments d’ADN capables de sauter et d’emporter des gènes de résistance avec eux — mettant en évidence une autre voie de dissémination rapide.
Ce que cela signifie pour les traitements futurs
Pour les non‑spécialistes, le message central est que la lecture de l’ADN bactérien peut grandement aider à lutter contre les super‑bactéries, mais la technologie n’est pas encore parfaite. Les outils génomiques avaient tendance à « sur‑annoncer » la résistance, ce qui est plus sûr que de manquer une souche dangereuse mais peut pousser les médecins à utiliser des antibiotiques plus puissants que nécessaire. En même temps, un plus petit nombre de cas montrait que les tests de laboratoire détectaient des résistances que les catalogues de gènes actuels n’expliquaient pas entièrement, soulignant des zones d’ombre importantes dans nos connaissances. En dressant une carte détaillée des gènes de résistance, des plasmides et des éléments mobiles dans les hôpitaux indiens, cette étude crée une base pour des diagnostics basés sur l’ADN meilleurs et plus rapides et pour une utilisation des antibiotiques plus informée — pas seulement en Inde, mais partout où les super‑bactéries menacent la médecine moderne.
Citation: Gheewalla, N., Karthikeyan, V., Jadhav, Y. et al. Genomic landscape of antimicrobial resistance in India: findings from a multi-species surveillance study. npj Antimicrob Resist 4, 13 (2026). https://doi.org/10.1038/s44259-026-00185-9
Mots-clés: résistance aux antimicrobiens, séquençage du génome, infections nosocomiales, bactéries résistantes aux médicaments, résistance médiée par plasmide