Clear Sky Science · fr
Analyse de l’expression génique de l’hôte pour détecter une étiologie bactérienne ou virale chez les enfants hospitalisés pour une suspicion d’infection sévère
Pourquoi cette recherche compte pour les enfants atteints d’infections graves
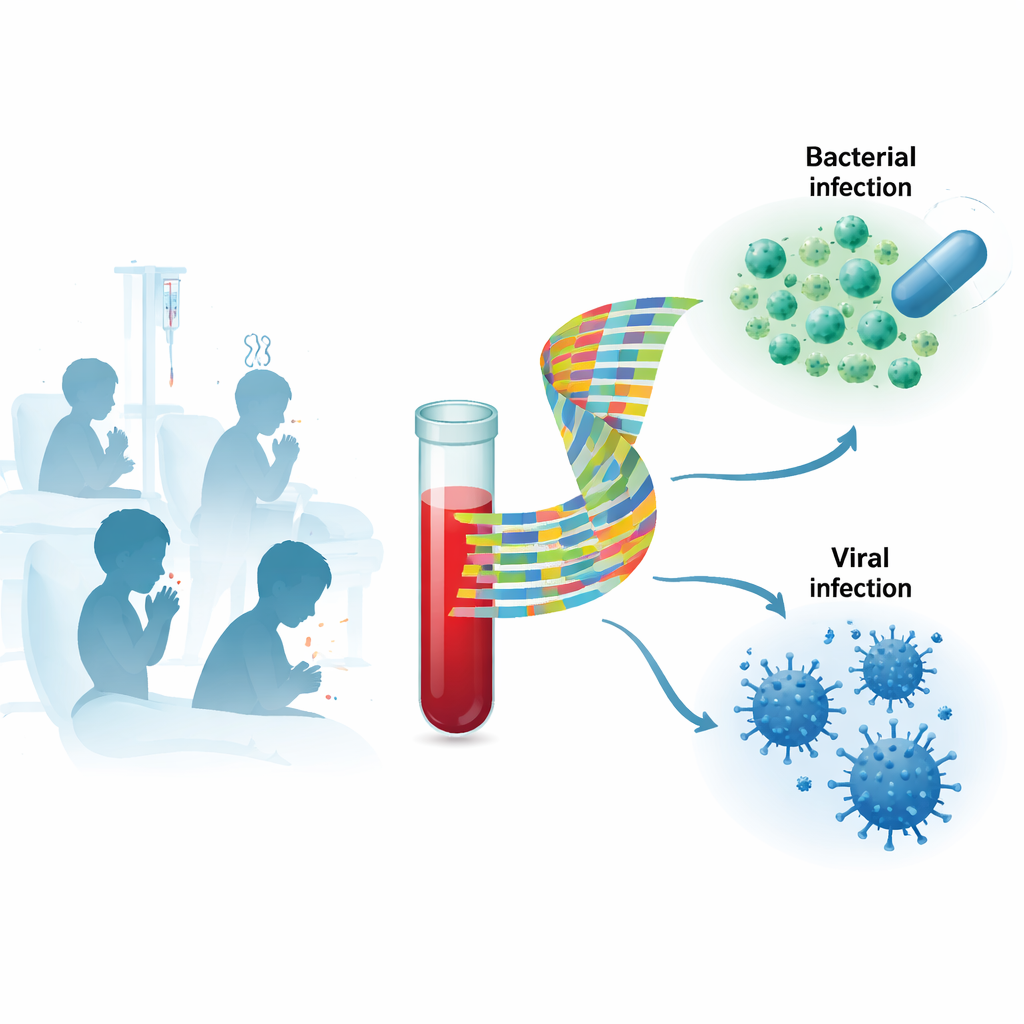
Quand un enfant arrive à l’hôpital avec une forte fièvre et un état général alarmant, les médecins doivent rapidement déterminer si la cause est une infection bactérienne, qui nécessite en général des antibiotiques, ou une infection virale, qui guérit souvent spontanément. Les tests actuels sont loin d’être parfaits, et beaucoup d’enfants reçoivent des antibiotiques « au cas où ». Cette étude a exploré si l’analyse des signaux internes du corps dans le sang — en particulier les profils d’activité génique — peut distinguer de façon plus précise infections bactériennes et virales chez des enfants suspectés d’avoir une maladie sévère.
Observer le système d’alarme de l’organisme plutôt que le microbe
Les tests traditionnels cherchent le microbe directement, par exemple en cultivant des bactéries à partir du sang ou en détectant du matériel génétique viral par PCR. Ces méthodes peuvent être lentes, manquer l’agent responsable et souvent détecter des virus « passagers » inoffensifs, surtout chez les jeunes enfants qui portent fréquemment des virus respiratoires. Les chercheurs se sont donc concentrés sur la réponse de l’hôte : quels gènes des cellules sanguines de l’enfant sont activés ou réprimés pendant l’infection. Comme le système immunitaire réagit différemment aux bactéries et aux virus, le motif d’expression génique peut servir de signature de type d’infection, même quand il est difficile de retrouver ou d’interpréter le microbe lui‑même.
Étudier un mélange d’enfants malades représentatif du terrain
L’équipe a recruté 268 enfants âgés de 4 semaines à 16 ans en Finlande. La plupart étaient hospitalisés pour suspicion d’infection sévère ; un plus petit groupe présentait des infections virales confirmées plus bénignes traitées en ambulatoire, et certains étaient des témoins sains. Les médecins ont collecté des données cliniques détaillées, des analyses standard comme la protéine C‑réactive et la procalcitonine, et des écouvillons nasaux pour les virus respiratoires. Des prélèvements sanguins ont servi à mesurer l’activité de milliers de gènes par séquençage de l’ARN. La maladie de chaque enfant a été soigneusement classée comme bactérienne, virale, mixte bactérienne–virale, incertaine ou non infectieuse, puis regroupée plus simplement en « bactérienne » ou « virale » pour les analyses principales.
Trouver un signal simple à deux gènes
Quand les scientifiques ont examiné globalement l’activité génique sanguine de tous les enfants, ils ont observé des regroupements d’échantillons, mais ces clusters ne correspondaient pas clairement aux étiquettes « bactérien » versus « viral ». Les enfants sains se distinguaient nettement de ceux ayant des infections bactériennes certaines, tandis que les profils géniques des infections virales certaines étaient plus hétérogènes. Pour dépasser cette complexité, les chercheurs ont divisé les patients en deux ensembles : un groupe de découverte composé d’enfants avec infections respiratoires et un groupe de validation avec d’autres types d’infections, comme rénales ou cutanées. Dans le groupe de découverte, ils ont recherché de très petites combinaisons de gènes capables de mieux distinguer infection bactérienne et virale, puis ont testé la performance des mêmes combinaisons dans le groupe de validation.
Ils ont identifié une paire de gènes particulièrement prometteuse, nommée TSPO et SECISBP2. Ensemble, les niveaux d’activité de ces deux gènes seuls permettaient de séparer les infections bactériennes (y compris les infections mixtes bactériennes–virales) des infections purement virales avec une grande précision. Mesuré par l’aire sous la courbe ROC, ce signal à deux gènes atteignait 0,93 dans l’ensemble de découverte et 0,81 dans l’ensemble de validation ; sur les deux groupes combinés, il était de 0,87, avec une sensibilité d’environ 77 % et une spécificité d’environ 87 %. Autrement dit, le signal identifiait correctement la majorité des cas bactériens tout en classant rarement à tort des infections virales comme bactériennes. Il a aussi surpassé des marqueurs sanguins largement utilisés comme la protéine C‑réactive et la procalcitonine dans cette population étudiée.

Ce que ces deux gènes pourraient faire
TSPO participe à la manière dont les mitochondries — les centrales énergétiques de la cellule — gèrent le stress et contribuent au contrôle de l’inflammation. Des travaux antérieurs ont associé une activité TSPO plus élevée à des infections bactériennes sévères et à la sepsie, et des expériences suggèrent que la stimulation des cellules immunitaires par des composants bactériens peut augmenter TSPO et favoriser la libération de molécules inflammatoires aidant à tuer les microbes. Dans cette étude, TSPO avait tendance à être plus actif lors d’infections bactériennes et moins actif lors d’infections virales. SECISBP2, en revanche, aide l’organisme à produire des protéines contenant du sélénium qui ont des rôles antioxydants, immunitaires et antiviraux. Le sélénium soutient la fonction des cellules immunitaires et réduit la sévérité de certaines infections virales. Ici, l’activité de SECISBP2 était généralement plus élevée dans les infections virales, ce qui concorde avec l’idée que l’organisme renforce les défenses liées au sélénium face aux virus.
Ce que cela pourrait signifier pour la prise en charge future
Les auteurs soulignent que leurs résultats sont précoces mais encourageants. Un test simple lisant seulement ces deux gènes à partir d’un petit échantillon sanguin pourrait un jour aider les équipes d’urgence à décider avec plus de confiance si un enfant très malade a besoin d’antibiotiques. Parce que le signal à deux gènes fonctionnait non seulement pour les infections pulmonaires mais aussi pour d’autres infections sévères, il pourrait être utile dans un large éventail de situations réelles, y compris quand des germes bactériens et viraux sont présents simultanément. Cependant, l’étude a été réalisée dans un seul pays et s’est appuyée sur des définitions bactérien/viral meilleures disponibles mais imparfaites. Des études plus larges dans différents hôpitaux et des versions rapides, adaptées au milieu clinique, du test seront nécessaires avant qu’il puisse guider les décisions quotidiennes. Néanmoins, ce travail montre que l’activité génique de l’hôte pourrait détenir la clé d’un usage plus rationnel des antibiotiques et d’une meilleure prise en charge des enfants atteints d’infections graves.
Citation: Piri, R., Valta, M., Lempainen, J. et al. Host gene expression analysis in the detection of bacterial and viral etiology in children hospitalized with a suspected severe infection. Commun Med 6, 204 (2026). https://doi.org/10.1038/s43856-025-01370-z
Mots-clés: infections pédiatriques, expression génique, bactérien versus viral, gestion des antibiotiques, diagnostics de la réponse de l’hôte