Clear Sky Science · fr
Rapport sur la réutilisabilité : Évaluation des performances d’un modèle fondamental de méta-apprentissage pour prédire l’activité antibactérienne des produits naturels
À la recherche de nouveaux antibiotiques, plus rapidement
La résistance aux antibiotiques augmente, tandis que la découverte de nouveaux médicaments reste douloureusement lente et dépend souvent d’essais et d’erreurs en laboratoire. Cette étude examine si un type puissant d’intelligence artificielle, initialement entraîné sur d’énormes collections de données pharmaceutiques, peut être adapté rapidement pour prédire quels composés naturels d’origine végétale pourraient combattre les bactéries — en n’utilisant que de petites quantités de nouvelles données expérimentales. Si cela fonctionne, de tels outils pourraient aider les scientifiques à concentrer le temps précieux de laboratoire sur les candidats les plus prometteurs et accélérer la recherche de la prochaine génération d’antibiotiques.
Pourquoi les produits chimiques végétaux comptent
Nombre de nos meilleurs antibiotiques sont apparus à l’origine comme des produits naturels issus de plantes et de micro-organismes. Ces molécules peuvent arrêter la croissance bactérienne, mais en trouver de nouvelles dans la nature revient un peu à chercher une aiguille dans une botte de foin. Les chercheurs doivent tester de nombreux composés contre de nombreuses souches bactériennes, et chaque test coûte cher. Pire encore, de grands jeux de données soigneusement annotés — dont les méthodes modernes d’apprentissage profond ont besoin pour bien fonctionner — sont rares dans ce domaine. Cela fait de la découverte d’antibiotiques un terrain d’essai idéal pour les « modèles fondamentaux » : de larges systèmes d’IA polyvalents qui peuvent être ajustés pour des tâches spécifiques avec seulement une poignée de nouveaux exemples.
Un modèle fondamental apprend à reconnaître les tueurs de germes
L’équipe s’est concentrée sur un modèle fondamental appelé ActFound, initialement entraîné pour prédire l’intensité avec laquelle différentes substances chimiques affectent des cibles biologiques, en utilisant d’immenses jeux de données tirés de ressources comme les bases ChEMBL et BindingDB. Au lieu de prédire un nombre unique pour chaque composé, ActFound apprend en comparant des paires de composés au sein d’une même expérience et en estimant lequel est le plus actif. Cet apprentissage « par paires », combiné à une stratégie d’entraînement connue sous le nom de méta-apprentissage, est conçu pour aider le modèle à s’adapter rapidement à de nouvelles tâches de prédiction lorsque seules peu d’exemples annotés sont disponibles — exactement la situation dans de nombreux criblages d’antibiotiques.
Tester le modèle sur des données végétales réelles
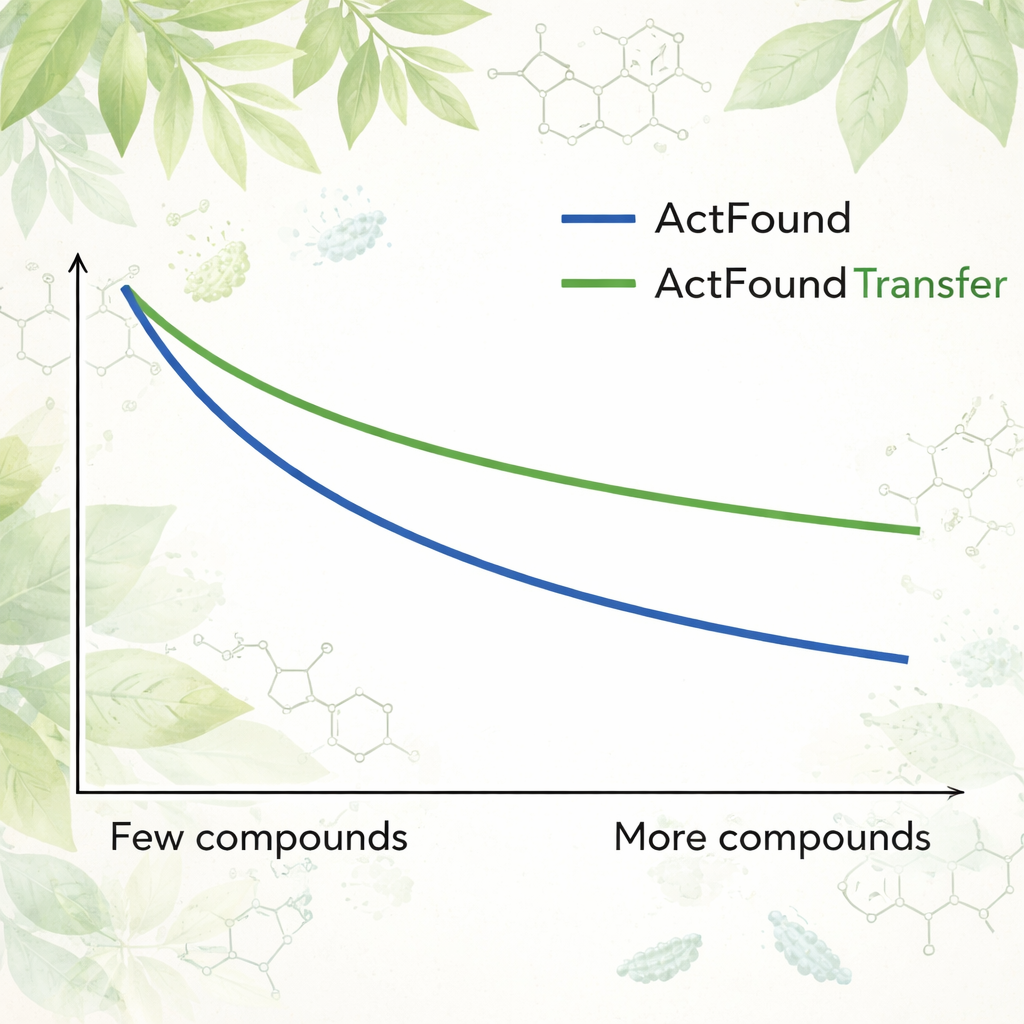
Pour évaluer la réutilisabilité d’ActFound, les auteurs l’ont ajusté (fine-tuning) sur un jeu de données soigné de produits naturels d’origine végétale testés pour leur capacité à inhiber la croissance de diverses bactéries. Chaque souche bactérienne a été traitée comme une tâche distincte, et le modèle a été adapté en n’utilisant que 8 à 128 composés par souche, ou des pourcentages fixes des données disponibles. Ils ont également comparé ActFound à des modèles plus simples de méta-apprentissage et de transfert d’apprentissage qui n’utilisent pas de comparaisons par paires. Dans ces tests, ActFound n’a pas atteint la précision observée dans des travaux antérieurs sur d’autres types de données pharmaceutiques. Cependant, lorsque très peu de données étaient disponibles — à peu près seulement quelques composés par souche — ActFound et sa variante par transfert d’apprentissage ont généralement égalé ou surpassé les méthodes alternatives.
Quand la similarité aide — et quand elle nuit
ActFound part du principe que des molécules similaires ont un comportement similaire, ce qui fonctionne bien lorsque les jeux de données sont organisés autour de groupes de composés apparentés. Le jeu de données de produits naturels, en revanche, était chimiquement divers et manquait souvent de « familles » de composés proches. Cette diversité, bien que scientifiquement précieuse, a compromis la stratégie d’apprentissage par paires : lorsque les composés au sein d’une expérience sont très différents les uns des autres, le modèle a du mal à apprendre des comparaisons stables. Les auteurs ont également constaté qu’un simple indicateur diagnostique, proposé dans l’article original sur ActFound pour prédire à l’avance la performance du modèle sur une nouvelle tâche, ne se vérifiait pas pour ces données de produits naturels, ce qui souligne une limitation importante lors du passage à de nouveaux espaces chimiques.
Ce que cela signifie pour la découverte de médicaments à venir
Pour les non-spécialistes, la conclusion est que des modèles fondamentaux comme ActFound sont des outils prometteurs pour la découverte de médicaments lorsque les données sont rares, mais ils ne constituent pas des solutions miracles. Dans cette étude, ActFound et sa version par transfert d’apprentissage ont souvent fait aussi bien ou mieux que des méthodes concurrentes quand seuls quelques composés végétaux étaient disponibles pour l’entraînement, mais ils ont peiné sur cet ensemble très divers de produits naturels. Le travail suggère que ces modèles d’IA sont les plus utiles lorsque les données incluent de nombreux composés chimiquement similaires — comme dans des études ciblées de relations structure–activité — mais qu’ils restent moins fiables pour prédire le comportement de types de molécules entièrement nouveaux. Autrement dit, l’IA peut aider à restreindre la recherche, mais la partie la plus difficile de l’exploration de véritables territoires chimiques nouveaux reste à venir.
Citation: Butt, C.M., Walker, A.S. Reusability Report: Evaluating the performance of a meta-learning foundation model on predicting the antibacterial activity of natural products. Nat Mach Intell 8, 270–275 (2026). https://doi.org/10.1038/s42256-026-01187-y
Mots-clés: découverte d’antibiotiques, produits naturels, apprentissage profond, méta-apprentissage, criblage de médicaments