Clear Sky Science · fr
Modèles génératifs de la dynamique cellulaire : des Neural ODEs au flow matching
Observer les cellules en train de changer
Chaque organe de notre corps est constitué de cellules qui, au départ, se ressemblaient presque toutes, puis ont progressivement adopté des rôles différents. Les biologistes aimeraient observer ces cellules évoluer en temps réel, mais les méthodes de mesure actuelles détruisent les cellules qu’elles analysent. Cet article de synthèse explore comment un nouvel outil d’intelligence artificielle, appelé Neural Ordinary Differential Equations, peut aider à reconstituer ces histoires cachées de changement à partir d’instantanés statiques — améliorant potentiellement notre compréhension du développement, des maladies et du fonctionnement des traitements.

Des instantanés vers des films vivants
Les technologies modernes de séquençage monocellulaire peuvent mesurer l’activité de milliers de gènes dans des cellules individuelles, produisant d’énormes tableaux de nombres. Chaque ligne correspond à une cellule, chaque colonne à un gène. Mais chaque cellule n’est mesurée qu’une seule fois, si bien que les scientifiques obtiennent une collection de photos fixes plutôt qu’un film montrant l’évolution d’une cellule au fil du temps. Les premières approches ont tenté d’ordonner ces instantanés de façon plausible à l’aide du « pseudotemps », en plaçant les cellules le long de trajectoires de développement selon la similarité de leurs profils d’expression génique. Cela a permis de révéler des grandes voies de différenciation cellulaire, mais a montré ses limites lorsque les cellules se scindent en plusieurs destins ou suivent des trajectoires complexes et bouclées.
Décrire le changement cellulaire comme un mouvement dans un paysage
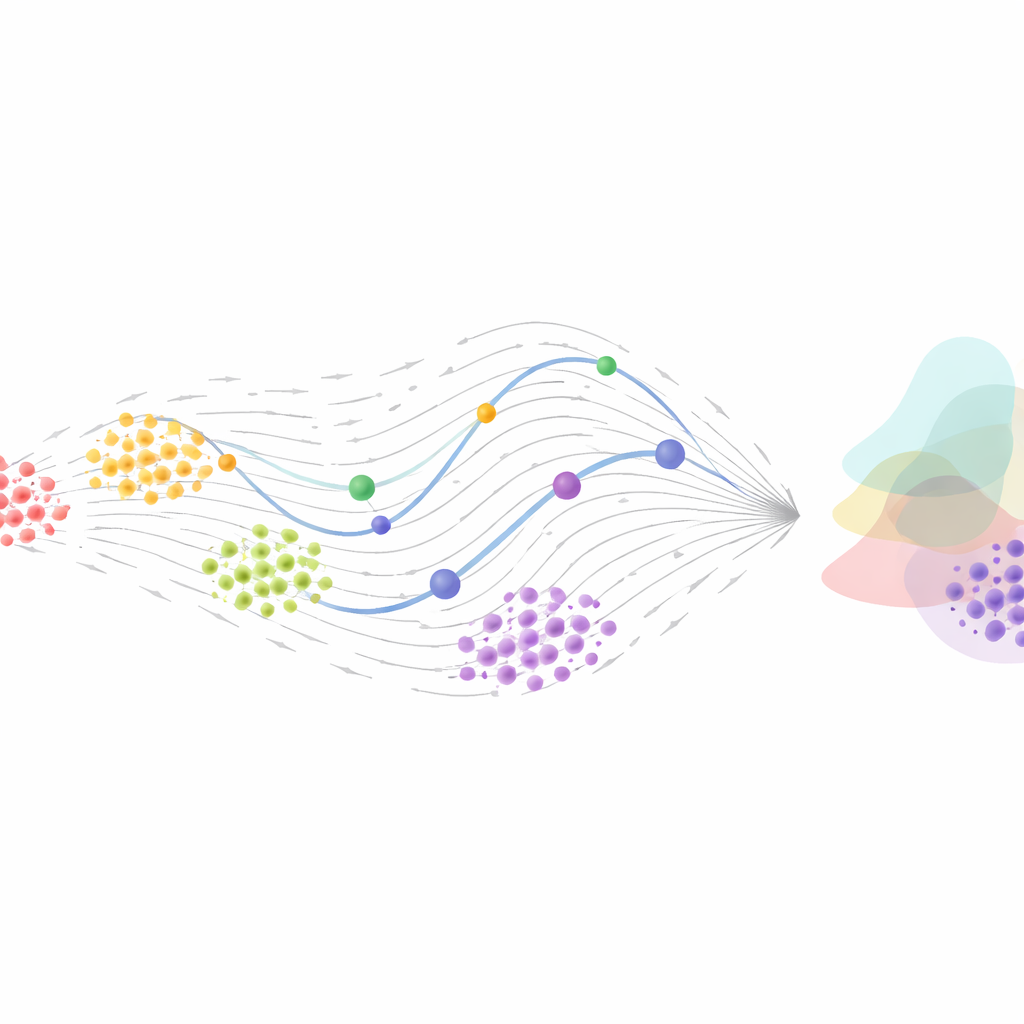
Pour dépasser de simples ordonnancements, les chercheurs décrivent les cellules comme des points se déplaçant dans un paysage : la position encode l’état d’activité génique actuel et le « moment » reflète la manière dont cet état évolue. Des outils classiques, comme la RNA velocity, estiment vers où se dirige une cellule en comparant différentes formes d’ARN à l’intérieur d’elle. D’autres reconstituent des champs de vecteurs — des cartes de flèches indiquant, en chaque point de cet espace, la direction probable du mouvement. Ces méthodes ont commencé à révéler comment les réseaux génétiques poussent les cellules vers des destins spécifiques et comment des régions instables du paysage peuvent annoncer des décisions imminentes. Toutefois, beaucoup de ces modèles reposent sur de fortes simplifications des interactions géniques et ne peuvent souvent pas générer des trajectoires pleinement continues qui correspondent aux données de population à plusieurs instants.
Neural ODEs : apprendre les règles du changement
Les Neural ODEs offrent une manière flexible d’apprendre les règles sous-jacentes qui gouvernent le mouvement cellulaire dans ce paysage. Plutôt que de prescrire des formules a priori, un réseau de neurones apprend une fonction qui indique, pour n’importe quel état cellulaire, comment cet état va évoluer ensuite. Un solveur d’EDO trace alors des trajectoires complètes dans le temps. Ce cadre a été adapté à plusieurs tâches monocellulaires : inférer des parcours de développement, mettre en évidence des événements de bifurcation, identifier des états instables ou « primés », et même reconstruire des réseaux de régulation génique — les relations de cause à effet entre gènes qui s’activent ou se répriment mutuellement. En favorisant la simplicité et la parcimonie des règles apprises, certaines méthodes peuvent proposer des schémas de régulation compacts, plus faciles à interpréter et à tester expérimentalement.
Flows génératifs : faire correspondre des populations au fil du temps
Une autre approche traite le problème au niveau des populations plutôt qu’en suivant des cellules individuelles. Ici, l’objectif est d’apprendre comment la distribution complète des états cellulaires à un instant se transforme en la distribution à un instant ultérieur. Des techniques issues du transport optimal, initialement développées pour trouver la façon la moins coûteuse de déplacer une masse d’une forme à une autre, ont été combinées aux Neural ODEs et aux modèles de « flow » associés. Les continuous normalizing flows et les méthodes récentes et plus efficaces de « flow matching » apprennent directement des champs de vecteurs qui déplacent une population de cellules vers une autre, sans relancer des simulations coûteuses pendant l’entraînement. Ces approches peuvent gérer un échantillonnage irrégulier, des mesures bruitées et même des dynamiques stochastiques (partiellement aléatoires), offrant des modèles génératifs capables de simuler des populations futures réalistes ou de reconstituer des états passés probables.
Opportunités et questions ouvertes
Malgré leur potentiel, ces modèles font face à des défis importants. Distinguer la véritable causalité des simples corrélations dans les réseaux géniques est difficile, surtout lorsque certains facteurs influents ne sont pas observés. Les chercheurs poussent également les Neural ODEs au-delà de l’ajustement des données observées pour qu’ils apprennent de véritables lois générales capables de prédire les réponses à de nouvelles conditions, comme des knock-outs géniques ou des traitements médicamenteux. La gestion du bruit, de l’aléa et de la multiplicité des types de données — par exemple en combinant l’activité génique avec la localisation spatiale ou d’autres couches moléculaires — reste un domaine de recherche actif. Néanmoins, ces mêmes idées sont déjà appliquées au-delà de la génomique, par exemple à la dynamique cardiaque, au comportement des médicaments dans l’organisme et aux séries temporelles médicales.
Pourquoi cela compte pour la santé et la maladie
Pour un non-spécialiste, le message clé est que les Neural ODEs et les modèles de flow matching permettent aux scientifiques de transformer des mesures cellulaires statiques en récits dynamiques. Au lieu de savoir seulement à quoi ressemblent les cellules à quelques stades isolés, ces outils aident à inférer comment les cellules sont susceptibles de se déplacer dans leur paysage développemental, quels commutateurs dans leurs circuits géniques pilotent ces mouvements et comment des interventions pourraient les rediriger. À long terme, de tels modèles pourraient permettre des expériences in silico qui prédisent comment une cellule souche peut être orientée vers un type souhaité, comment la population cellulaire d’une tumeur évoluera sous traitement, ou comment des thérapies complexes affectent des écosystèmes cellulaires entiers — nous rapprochant d’une compréhension mécaniste et prédictive de la vie au niveau unicellulaire.
Citation: Richter, T., Wang, W., Palma, A. et al. Generative models of cell dynamics: from Neural ODEs to flow matching. Commun Biol 9, 352 (2026). https://doi.org/10.1038/s42003-026-09758-w
Mots-clés: dynamique monocellulaire, neural ODEs, différenciation cellulaire, modèles génératifs, transport optimal