Clear Sky Science · fr
DANST permet la déconvolution des types cellulaires en transcriptomique spatiale grâce à des réseaux neuronaux adversariaux profonds
Voir les cellules dans leur voisinage
Les tissus humains sont des cités densément peuplées regroupant de nombreux types cellulaires, chacun remplissant un rôle propre. Les nouvelles technologies de « transcriptomique spatiale » peuvent mesurer quels gènes sont actifs à travers une coupe de tissu, mais chaque mesure mélange souvent les signaux de plusieurs cellules voisines. Cet article présente DANST, une méthode computationnelle intelligente qui démêle ces mélanges. En nous indiquant quels types cellulaires sont présents et où ils se situent dans les organes et les tumeurs, elle aide les chercheurs à mieux comprendre comment les tissus sont structurés, comment les maladies se propagent et où les traitements peuvent être les plus efficaces. 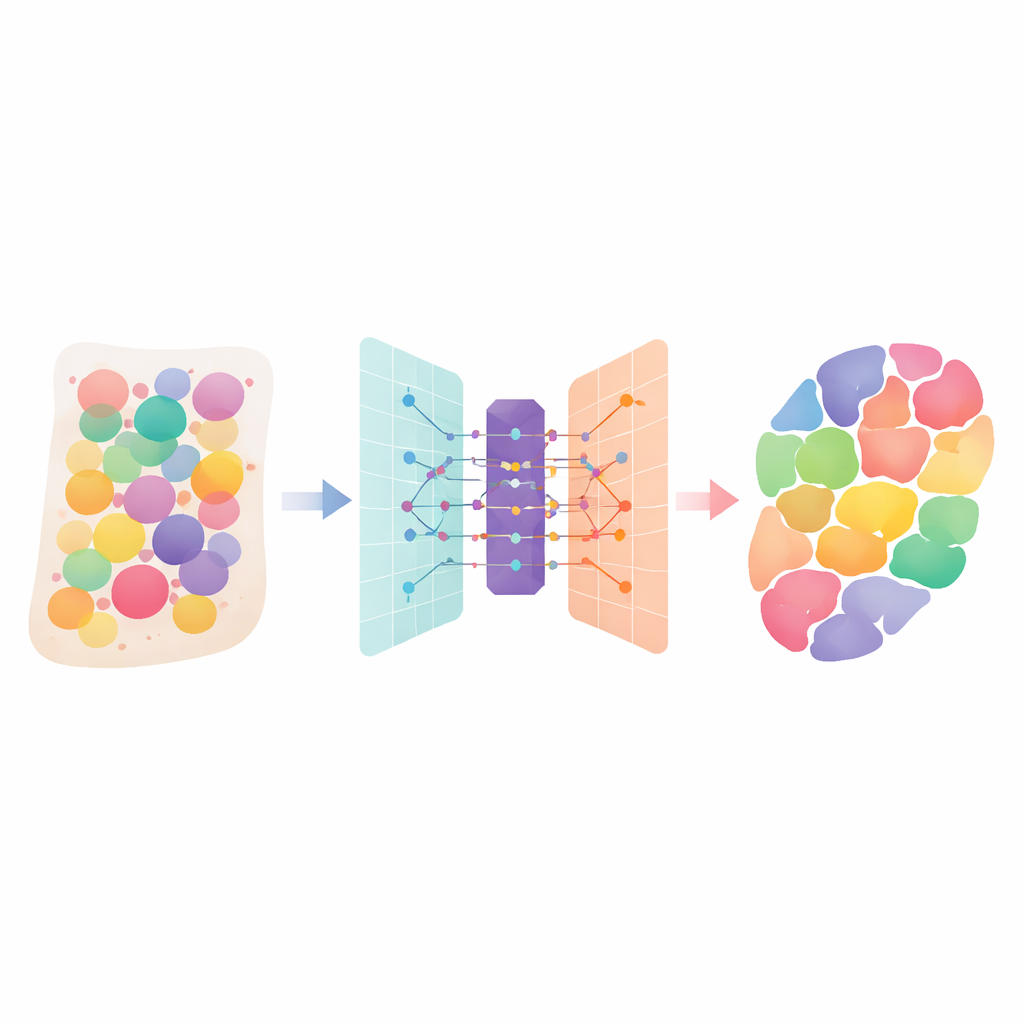
Le défi de démêler les foules cellulaires
Les outils modernes de lecture des gènes peuvent soit analyser très précisément des cellules individuelles, soit capturer l’agencement global d’un tissu, mais rarement les deux à la fois. Les technologies spatiales courantes enregistrent l’activité génique dans des « spots » relativement larges qui peuvent couvrir plusieurs cellules. Le résultat revient à entendre une chorale sans pouvoir dire qui chante quelles notes. Pour interpréter cela, les chercheurs ont besoin de méthodes de « déconvolution » qui estiment combien chaque type cellulaire contribue à chaque spot. Beaucoup d’approches existantes utilisent les données unicellulaires comme référence, mais elles peinent car les deux types de données proviennent d’expériences différentes et ne concordent pas parfaitement en qualité, bruit ou résolution.
Construire un pont entre deux mondes de données
DANST s’attaque à ce décalage en créant un pont entre les données unicellulaires et les données spatiales. D’abord, il utilise les profils détaillés des cellules uniques pour simuler de nombreux spots mixtes artificiels avec des proportions de types cellulaires connues. En parallèle, il regroupe les spots spatiaux réels selon leur emplacement dans le tissu et leurs motifs géniques, et utilise les distances à ces groupes pour assigner à chaque spot simulé une position « pseudo ». Cette étape crée une carte liée où spots artificiels et réels partagent un cadre spatial commun, permettant à la méthode d’apprendre à quoi ressemblent les signaux mélangés dans des voisinages spécifiques du tissu. 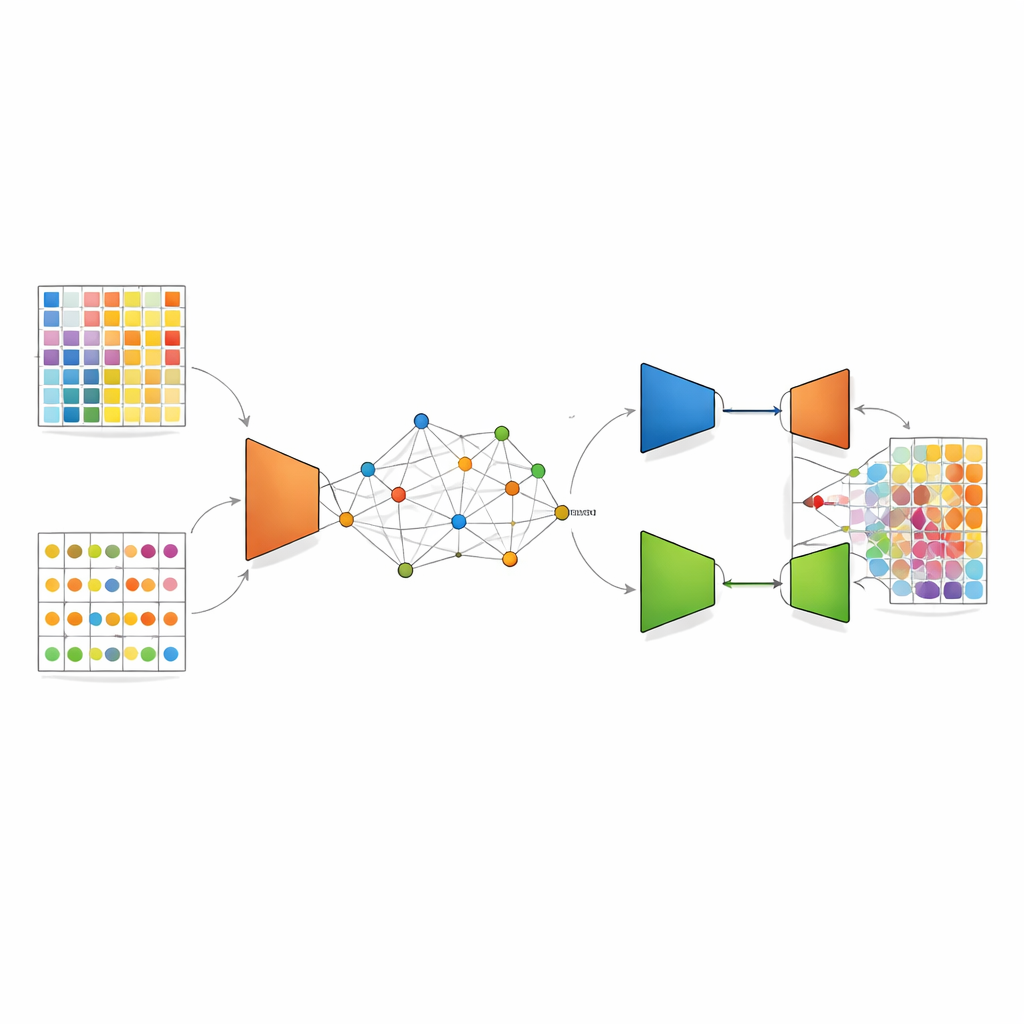
Nettoyer les signaux et aligner les domaines
Une fois cette carte conjointe en place, DANST applique un type d’apprentissage profond appelé autoencodeur variationnel. Ce réseau compresse les motifs géniques issus des spots réels et simulés en une représentation interne affinée puis tente de les reconstruire, ce qui permet en pratique de débruiter les données et de mettre en avant les caractéristiques importantes. Par-dessus cela, les auteurs ajoutent une composante adversariale : un second réseau essaie de déterminer si un motif affiné provient des données spatiales réelles ou des données simulées, tandis que l’extracteur de caractéristiques apprend à le tromper. Cette « lutte » pousse le modèle vers des caractéristiques performantes pour les deux sources de données, de sorte que les connaissances acquises à partir des spots simulés aux fractions cellulaires connues puissent être transmises de manière fiable aux spots tissulaires réels dont la composition est inconnue.
Tests sur cœurs, cerveaux et tumeurs
L’équipe a testé DANST sur des jeux de données artificiels et sur des échantillons biologiques réels de souris et d’humains. Comparé à plusieurs méthodes de pointe, DANST a récupéré plus précisément les proportions de types cellulaires dans des jeux de données synthétiques et a conservé son avantage à travers des tissus et des plateformes très différents. Dans un jeu de données de cerveau de souris, il a clairement reconstruit l’organisation en couches du cortex et s’est aligné sur des régions anatomiques définies par des experts. Dans une autre coupe de cerveau de souris, il a capturé des motifs fins dans des zones telles que l’hippocampe. Fait notable, dans un tissu de cancer du sein humain, DANST a tracé la disposition de diverses cellules immunitaires, de cellules de soutien et de cellules luminales sensibles aux hormones au sein et autour des régions tumorales. Ces cartes concordaient avec la biologie connue et ont suggéré des caractéristiques cliniquement pertinentes, comme la dépendance hormonale et un pronostic potentiellement plus médiocre là où certaines cellules immunitaires étaient peu présentes.
Ce que cela signifie pour la biologie et la médecine
Pour un non-spécialiste, DANST peut être vu comme un interprète puissant qui transforme des signaux flous et chevauchants en une image claire des types de cellules et de leur localisation dans un tissu. En séparant de façon fiable les types cellulaires dans l’espace, il offre aux chercheurs une vision plus nette de l’organisation des organes sains et de la manière dont la maladie la reconfigure. En cancérologie, cela peut révéler comment les cellules tumorales et immunitaires interagissent dans des régions spécifiques, ce qui peut orienter des thérapies ciblées et aider à prédire l’évolution des patients. À mesure que davantage de jeux de données spatiaux et unicellulaires seront disponibles, des outils comme DANST sont appelés à devenir essentiels pour décoder les voisinages cellulaires qui sous-tendent la santé et la maladie.
Citation: Zhang, X., Wu, Z., Wang, T. et al. DANST enables cell-type deconvolution in spatial transcriptomics using deep domain adversarial neural networks. Commun Biol 9, 388 (2026). https://doi.org/10.1038/s42003-026-09659-y
Mots-clés: transcriptomique spatiale, déconvolution des types cellulaires, apprentissage profond, microenvironnement tumoral, séquençage d’ARN unicellulaire