Clear Sky Science · fr
Les QTL moléculaires sont enrichis en variants structuraux dans une cohorte bovine séquencée en long reads
Pourquoi l’ADN bovin peut nous enseigner sur les caractères complexes
Agriculteurs, vétérinaires et généticiens veulent comprendre pourquoi certains animaux grandissent plus vite, résistent aux maladies ou produisent plus de lait que d’autres. Une grande partie de la réponse se trouve dans l’ADN, mais nos outils habituels se focalisent surtout sur de petits changements d’une seule « lettre » du génome. Cette étude montre que des modifications d’ADN beaucoup plus importantes — les variants structuraux — modèlent discrètement le fonctionnement des gènes chez les bovins, et que les nouvelles technologies de séquençage en longues lectures permettent enfin d’en mesurer l’impact complet.
Observer le génome avec une lentille plus précise
La plupart des études génétiques reposent sur de courtes séquences d’ADN, peu coûteuses et précises mais limitées dans les régions répétées ou complexes du génome. Les auteurs ont utilisé une technique plus récente, le séquençage long-read, sur 120 taureaux d’une race liée à la production laitière. Ces longues lectures couvrent des segments d’ADN beaucoup plus étendus, ce qui facilite la détection de grandes insertions, délétions et réarrangements appelés variants structuraux. L’équipe a comparé ces lectures longues aux données short-read existantes sur les mêmes animaux et a constaté que les longues lectures révélaient davantage de variants au global et amélioraient de façon spectaculaire la couverture des régions difficiles comme les chromosomes X et Y.
Mettre au jour des milliers de réarrangements d’ADN cachés
Avec les données long-read, les chercheurs ont catalogué environ 24 millions de petites variations d’ADN et plus de 79 000 variants structuraux parmi les taureaux. Beaucoup de ces modifications de grande taille étaient associées à des éléments d’ADN répétitifs qui se copient et se déplacent dans le génome. Environ un variant structural sur dix n’apparaissait que chez un ou deux animaux, révélant un riche réservoir de variations rares. Par rapport à un « pangenome » bovin antérieur construit à partir d’assemblages de haute qualité, le nouvel ensemble de données a ajouté des dizaines de milliers de variants structuraux supplémentaires, en particulier des insertions et des duplications complexes difficiles à détecter avec les anciennes méthodes. Cela suggère que les études long-read continuent de dévoiler des couches de diversité génétique auparavant invisibles chez le bétail.
Relier les modifications d’ADN à l’activité des gènes
Pour voir comment ces différences d’ADN affectent réellement la biologie, l’équipe s’est tournée vers un tissu important pour la fertilité mâle : le testicule. Pour 117 des taureaux, ils disposaient de données de deep RNA sequencing révélant quels gènes sont activés et comment leurs ARN sont épissés. En reliant statistiquement les variants génétiques proches de chaque gène à son activité, ils ont identifié plus de 27 000 « QTL moléculaires » — des sites génomiques qui modifient soit le niveau d’expression d’un gène, soit la façon dont son ARN est assemblé. Les variants structuraux sont apparus comme des acteurs clés : ils étaient plus de deux fois plus fréquents parmi les principaux signaux d’expression et plus de cinq fois plus fréquents parmi les principaux signaux d’épissage que prévu par hasard. Dans de nombreux cas, le variant le plus influent était une grande insertion, délétion ou duplication située dans un promoteur, un amplificateur, un exon ou un site d’épissage plutôt qu’un changement d’une seule lettre.
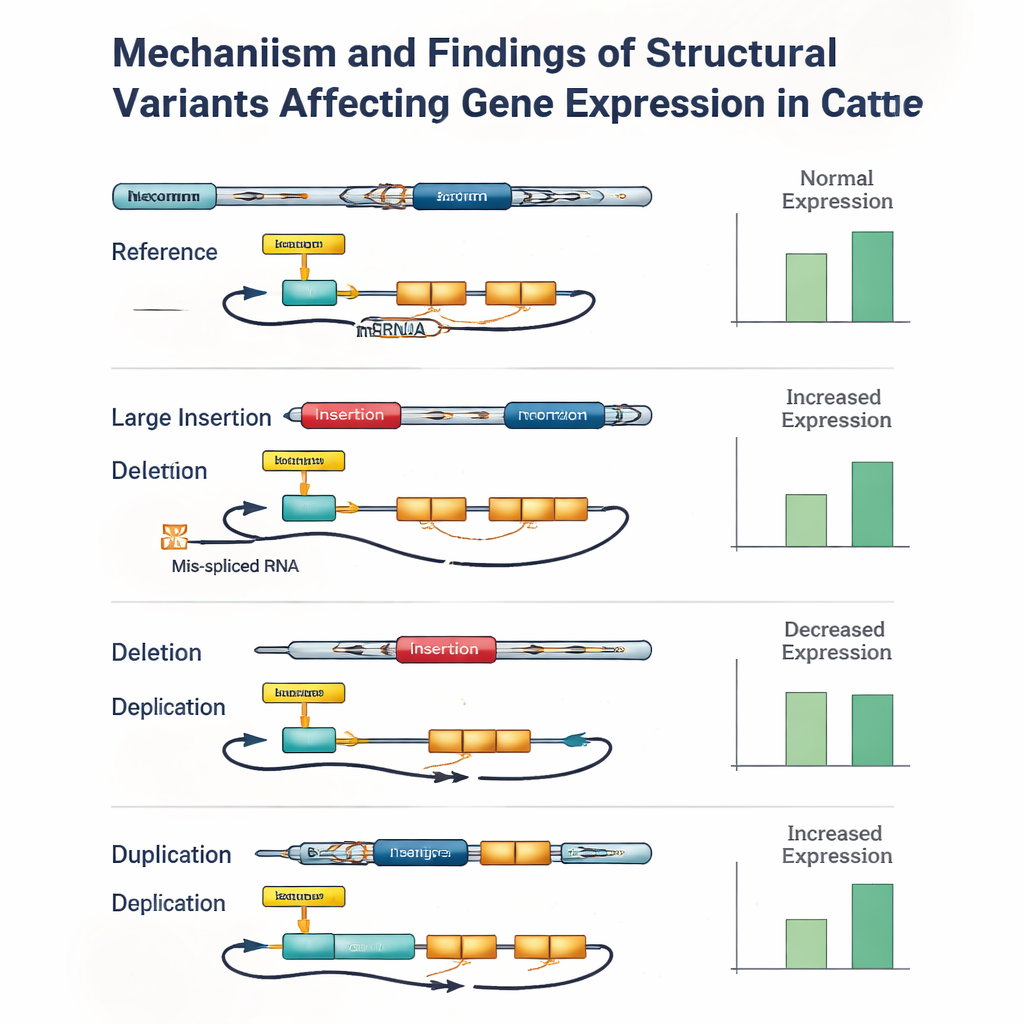
Quand des erreurs de génotypage masquent des signaux importants
Cependant, l’étude a également mis en évidence les limites des outils actuels. Même avec des lectures longues de haute qualité, attribuer avec précision les génotypes des variants structuraux à chaque animal restait difficile, en particulier pour les grandes insertions et les longues duplications. De petites erreurs — parfois impliquant un ou deux taureaux — pouvaient rendre un variant structural légèrement moins significatif statistiquement qu’un petit variant voisin parfaitement en déséquilibre de liaison avec lui. Lorsque les auteurs ont vérifié manuellement certains des signaux les plus forts, ils ont trouvé à plusieurs reprises des cas où un variant structural situé dans un gène ou une région régulatrice clé était l’hypothèse la plus plausible pour l’effet observé, mais où des erreurs de génotypage ou des données manquantes avaient permis à un petit variant lié d’arriver en tête du classement.
Ce que cela signifie pour l’élevage bovin et au-delà
Pour les non-spécialistes, la leçon est que les variations « importantes » d’ADN comptent beaucoup. Cette enquête long-read chez le bovin montre que les variants structuraux sont fortement enrichis parmi les sites génétiques qui contrôlent l’activation et l’épissage des gènes, en particulier dans les tissus reproducteurs. Pourtant, l’étude avertit aussi que les méthodes d’analyse actuelles omettent ou mal étiquettent encore beaucoup de ces variants, surtout lorsque la profondeur de séquençage est modeste. À mesure que le séquençage long-read devient moins coûteux et plus précis, et que des logiciels meilleurs émergent, éleveurs et chercheurs pourront relier des caractères économiquement importants — fertilité, résistance aux maladies et production laitière — à des variants structuraux spécifiques. Les mêmes principes s’appliquent à la santé humaine et à l’amélioration des plantes : pour comprendre pleinement les caractères complexes, il faut aller au-delà des changements d’une seule lettre et intégrer les plus grands réarrangements qui remodèlent les génomes.
Citation: Mapel, X.M., Leonard, A.S. & Pausch, H. Molecular QTL are enriched for structural variants in a cattle long-read cohort. Commun Biol 9, 290 (2026). https://doi.org/10.1038/s42003-026-09596-w
Mots-clés: variants structuraux, séquençage long-read, génomique bovine, expression génique, QTL moléculaires