Clear Sky Science · fr
Évaluation de la qualité des modèles 3D d’ARN à l’aide de l’apprentissage profond et de cartes 2D intermédiaires
Pourquoi il est important d’évaluer les formes de l’ARN
À l’intérieur de chaque cellule, les molécules d’ARN se tordent et se replient en formes tridimensionnelles complexes qui contribuent à contrôler l’expression des gènes, orienter des réactions chimiques et même combattre des virus. Aujourd’hui, des programmes informatiques puissants peuvent prédire beaucoup de ces formes, mais les scientifiques font encore face à un problème fondamental : quand l’ordinateur génère des dizaines ou des centaines de formes candidates pour le même ARN, laquelle se rapproche réellement de la réalité ? Cet article présente RNArank, un outil d’intelligence artificielle conçu pour traiter cette question en notant les modèles 3D d’ARN, à la manière d’un inspecteur de qualité structurelle, afin que les chercheurs puissent se concentrer sur les prédictions les plus fiables.
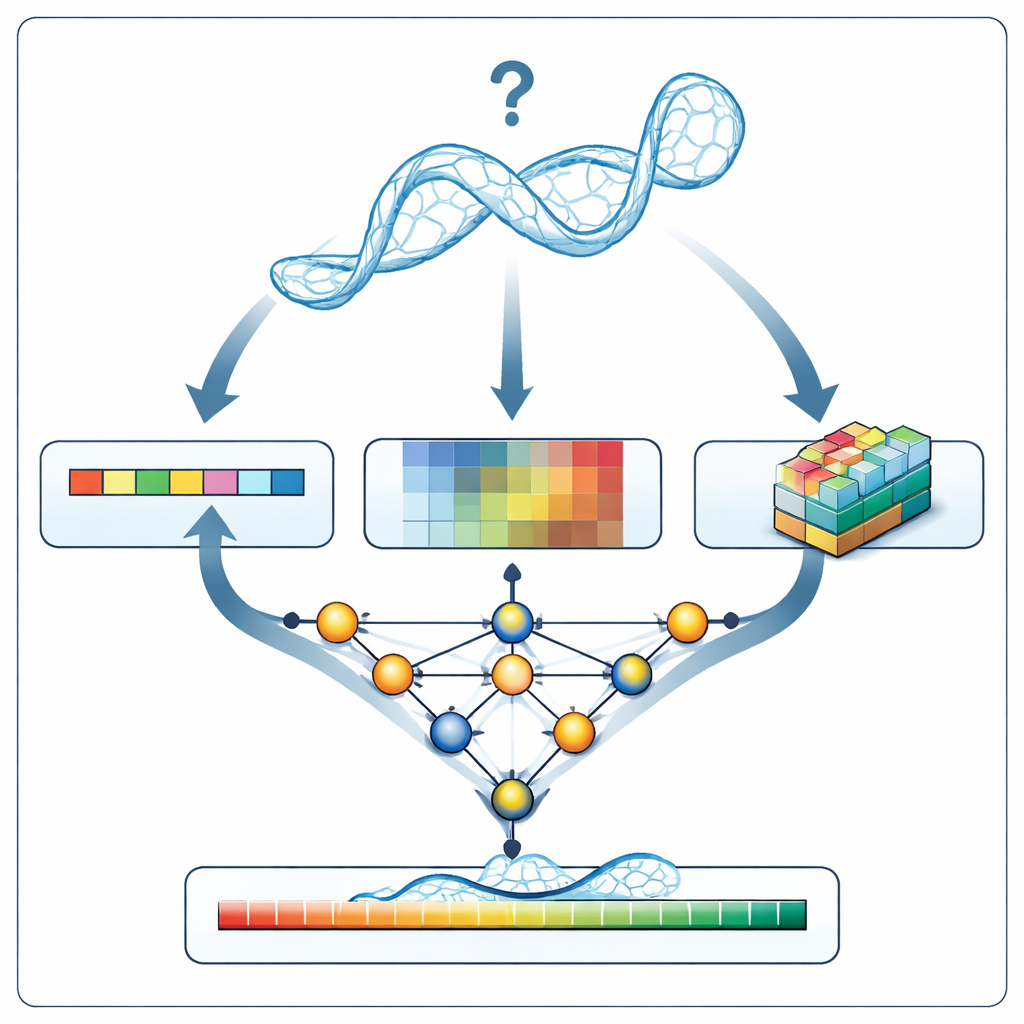
Un nouvel inspecteur pour les modèles d’ARN
RNArank a été conçu pour juger la qualité d’une forme d’ARN proposée sans avoir besoin de connaître la méthode qui l’a produite. Que le modèle provienne d’un système d’apprentissage profond, d’une simulation basée sur la physique ou d’un expert humain, RNArank n’examine que les coordonnées 3D finales. Il se demande en quelque sorte : « Cette structure ressemble-t-elle à un ARN réaliste ? » Ce type d’évaluation indépendante de la qualité est essentiel parce que, contrairement au domaine des protéines où des outils comme AlphaFold fournissent souvent des réponses très fiables dès le départ, la prédiction d’ARN bénéficie encore du croisement de méthodes multiples et de l’expertise humaine — et d’un moyen intelligent de classer les modèles obtenus.
Apprendre à l’IA à reconnaître un bon ARN
Pendant l’entraînement de RNArank, les auteurs ont rassemblé environ 200 000 structures d’ARN, couvrant un large spectre allant du clairement incorrect au presque parfait. Celles-ci ont été construites à partir de structures expérimentales connues en utilisant une grande variété d’approches, incluant des prédicteurs modernes par apprentissage profond, des simulations de dynamique moléculaire reproduisant le mouvement atomique, et des distorsions délibérées de structures exactes pour créer des « leurres ». Pour chaque modèle, l’équipe a calculé sa similarité avec l’ARN réel déterminé expérimentalement, en utilisant un score d’exactitude affiné adapté à l’ARN appelé lDDT_RNA. Ce score met l’accent sur la fidélité des distances entre paires de nucléotides, capturant à la fois le repliement global et les détails locaux sans être excessivement dépendant de la longueur de la molécule.
Comment RNArank lit et note un ARN
Quand RNArank examine un nouveau modèle d’ARN, il traduit d’abord la structure en trois types d’informations : une description 1D de la séquence et de la géométrie de l’épine dorsale le long de la chaîne, des descriptions 2D des relations entre chaque paire de nucléotides (leurs distances, des énergies d’interaction estimées et d’éventuels clashes atomiques), et des instantanés 3D en « voxels », de petites grilles capturant le nuage local d’atomes autour de chaque nucléotide. Un réseau neuronal à plusieurs volets tisse ces indices en une image unifiée puis prédit deux cartes 2D intermédiaires : quelles paires de nucléotides sont probablement en contact, et dans quelle mesure chaque distance modélisée est susceptible de dévier de la structure vraie inconnue. À partir de ces cartes, RNArank reconstruit à la fois un score de confiance par nucléotide et un score global pour l’ensemble du modèle d’ARN.
Mettre la méthode à l’épreuve
L’équipe a évalué RNArank sur trois jeux de données exigeants : un ensemble de 24 ARN nouvellement résolus extraits de la Protein Data Bank, et les cibles ARN de deux concours internationaux de prédiction à l’aveugle, CASP15 et CASP16, où de nombreux groupes soumettent des modèles sans connaître les réponses à l’avance. Sur des milliers de structures candidates, les scores de RNArank ont suivi la qualité réelle des modèles plus étroitement que plusieurs méthodes établies basées sur l’énergie et d’autres approches d’apprentissage profond. Il s’est montré particulièrement performant pour sélectionner les meilleurs ou quasi-meilleurs modèles dans un pool, et pour identifier quelles parties d’une structure étaient probablement peu fiables. Les auteurs ont également montré que RNArank conservait sa performance même sur des ARN clairement différents en séquence de ceux rencontrés durant l’entraînement, signe d’une généralisation réelle plutôt que d’une simple mémorisation.
Limites actuelles et perspectives
RNArank n’est pas parfait : il peine encore avec des ARN particulièrement flexibles qui adoptent de nombreuses conformations, et avec des ARN qui modifient leur forme lorsqu’ils sont liés à des protéines au sein de grands complexes moléculaires. Cependant, il est suffisamment rapide pour traiter de nombreux modèles d’ARN de quelques centaines de nucléotides en quelques secondes, et il aide déjà des serveurs automatisés à choisir des prédictions de meilleure qualité lors de tests communautaires. En fournissant un juge de modèles d’ARN indépendant de la méthode et reposant uniquement sur la structure, RNArank offre aux biologistes un filtre plus net pour transformer les sorties brutes des ordinateurs en hypothèses structurelles fiables, rapprochant le domaine d’une prédiction routinière et digne de confiance des formes d’ARN et, par conséquent, d’une compréhension plus approfondie du fonctionnement de ces molécules polyvalentes.
Citation: Liu, X., Wang, W., Du, Z. et al. Quality assessment of RNA 3D structure models using deep learning and intermediate 2D maps. Commun Biol 9, 293 (2026). https://doi.org/10.1038/s42003-026-09582-2
Mots-clés: Structure 3D d’ARN, apprentissage profond, évaluation de la qualité des modèles, bioinformatique structurale, RNArank