Clear Sky Science · fr
Plateforme de criblage virtuel pilotée par IA identifie de nouveaux candidats inhibiteurs de NSUN2 pour une thérapie anticancéreuse ciblée : une approche de découverte de médicaments par calcul
Nouvelles façons de déjouer les cancers récalcitrants
De nombreux cancers deviennent mortels non seulement parce qu’ils apparaissent, mais parce qu’ils apprennent à échapper à nos meilleurs médicaments. Cette étude explore une voie prometteuse pour neutraliser un aide essentiel à la croissance tumorale, en utilisant l’intelligence artificielle pour examiner plus de cent millions de molécules potentielles sur ordinateur avant d’en tester une seule en laboratoire.
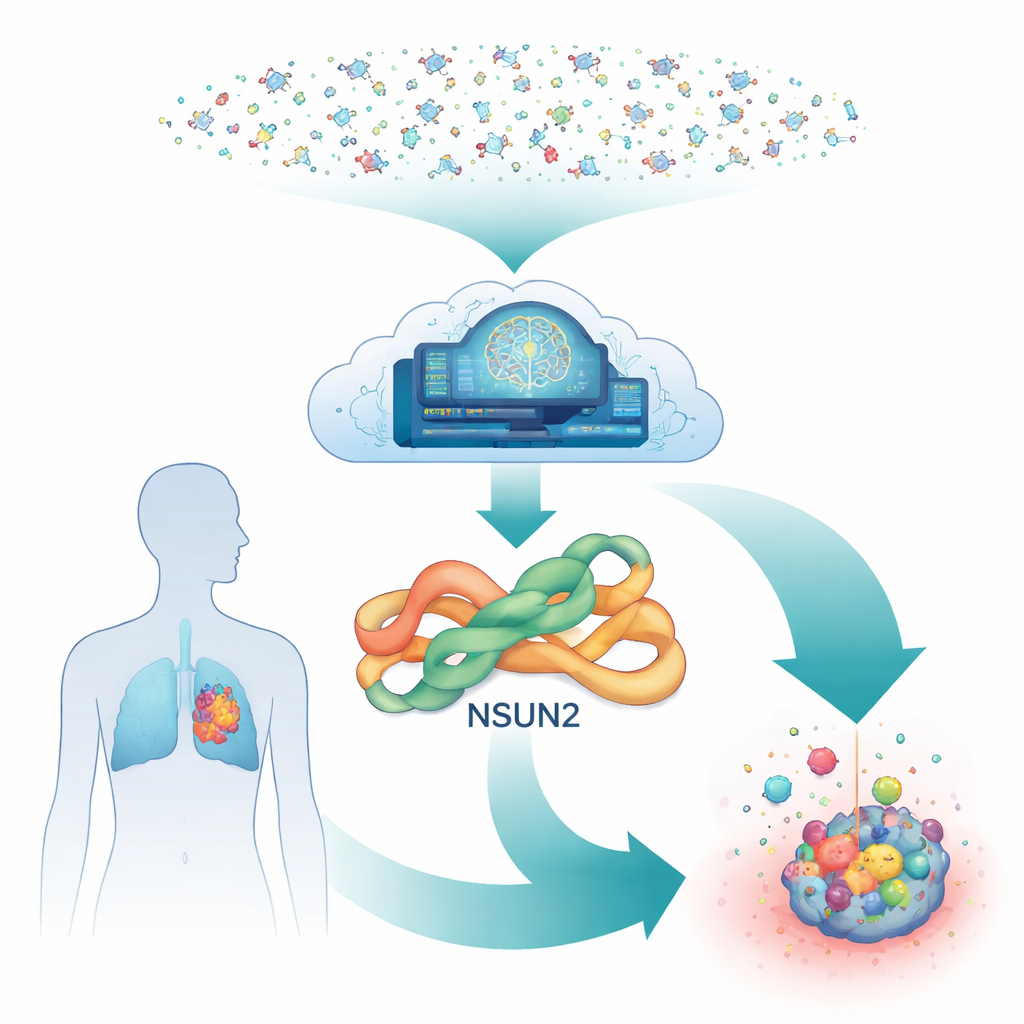
Un interrupteur caché à l’intérieur des cellules cancéreuses
Au cœur de nos cellules, une enzyme appelée NSUN2 agit comme un surligneur chimique pour l’ARN, la molécule qui aide à transformer les gènes en protéines. En ajoutant de petites marques chimiques à l’ARN, NSUN2 peut rendre les messages liés à la croissance plus stables et plus facilement lisibles. De nombreuses tumeurs, y compris celles du poumon, de l’estomac, du pancréas et du sein, augmentent les niveaux de NSUN2, ce qui renforce leur capacité à se diviser, à se disséminer et à résister aux traitements ciblés. Pourtant, malgré son importance, il existe très peu de candidats médicaments capables d’inhiber NSUN2 de manière sûre, en particulier des inhibiteurs réversibles qui n’endommagent pas radicalement l’enzyme.
Laisser l’IA fouiller un océan de molécules
La découverte de médicaments classique peinerait à tester des millions de molécules contre NSUN2 en laboratoire, car chaque expérience nécessite des mélanges complexes d’ARN et de cofacteurs. Les chercheurs ont donc construit une chaîne entièrement numérique. Ils sont partis d’une forme tridimensionnelle prédite de NSUN2 humain générée par AlphaFold, un système d’IA qui a révolutionné la prédiction de structures. Pour garantir la fiabilité de ce modèle, ils l’ont aligné sur une enzyme étroitement apparentée dont la structure est connue par diffraction des rayons X. La poche critique où NSUN2 se lie à son cofacteur naturel s’est avérée fortement conservée, donnant à l’équipe la confiance que le docking virtuel de médicaments potentiels dans ce site serait pertinent.
Des centaines de millions à une poignée
Avec la poche cible définie, l’équipe s’est tournée vers une vaste base de données publique de molécules commercialisables. Ils ont d’abord effectué le docking d’un jeu d’entraînement de composés dans la poche de NSUN2 et utilisé les scores obtenus pour apprendre à un modèle d’apprentissage automatique quelles formes étaient les plus prometteuses. Ce modèle a ensuite filtré rapidement environ 350 millions de molécules et a identifié à peu près 101 millions comme probables « hits ». Pour réduire encore le nombre, la meilleure fraction a été redockée avec des calculs plus précis, et seules les 12 000 meilleures, avec une affinité prédite forte, ont été conservées. Celles-ci ont ensuite été soumises à une batterie de contrôles de sécurité informatiques estimant comment l’organisme pourrait absorber, distribuer, métaboliser et tolérer chaque candidat. Après ces filtres, il ne restait que 34 molécules paraissant à la fois puissantes et présentant des propriétés pharmacologiques adéquates.
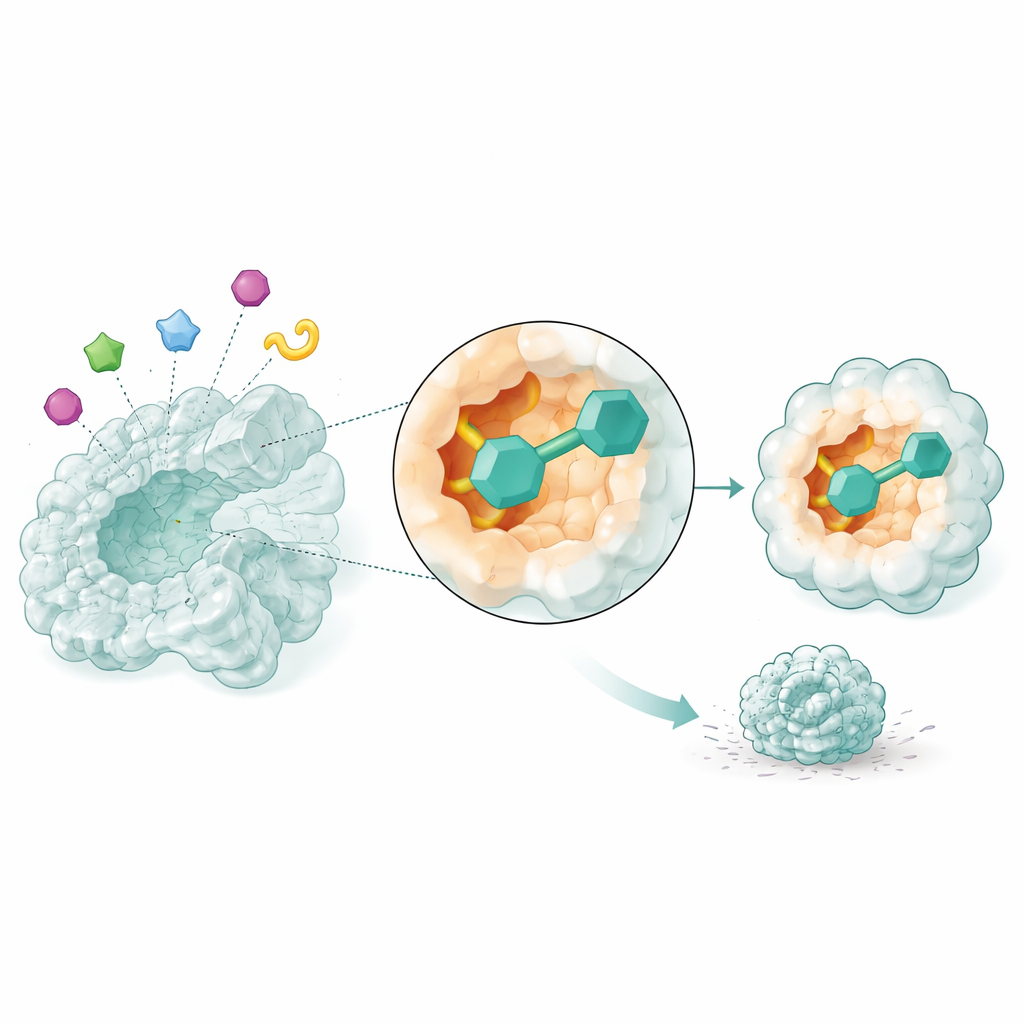
Observer les médicaments candidats en mouvement
Des instantanés statiques ne suffisent pas pour savoir si un médicament restera véritablement lié à sa cible. Les chercheurs ont donc utilisé des simulations de dynamique moléculaire, qui modélisent le mouvement des atomes au fil du temps, pour observer les trois candidats les plus prometteurs interagissant avec NSUN2 pendant 50 milliardièmes de seconde. Deux composés, identifiés uniquement par leurs codes de base de données, ont formé des complexes particulièrement stables : la structure de l’enzyme est restée compacte, ses régions clés sont demeurées fixes plutôt que flottantes, et les petites molécules ont gardé un ajustement serré dans la poche tout en établissant des contacts persistants. Ces simulations suggèrent que ces deux composés pourraient bloquer de façon fiable l’activité de NSUN2 dans des cellules réelles.
Ce que cela pourrait signifier pour les traitements futurs
Bien que tous les résultats de ce travail proviennent de calculs et doivent encore être validés en laboratoire, l’étude livre une liste restreinte de points de départ réalistes pour de nouveaux médicaments inhibant NSUN2. Parce que NSUN2 aide les cellules cancéreuses à stabiliser les signaux de croissance et de survie, de tels médicaments pourraient affaiblir les tumeurs et potentiellement les rendre à nouveau sensibles aux thérapies ciblées existantes, en particulier dans les cancers du poumon devenus résistants. Tout aussi important, l’étude met en valeur une méthode générale combinant IA et modélisation fondée sur la physique pour explorer rapidement et à moindre coût d’énormes espaces chimiques, offrant un raccourci puissant vers la prochaine génération de traitements anticancéreux de précision.
Citation: Yu, S., Peng, Q., Wei, W. et al. AI-driven virtual screening platform identifies novel NSUN2 inhibitor candidates for targeted cancer therapy: a computational drug discovery approach. npj Precis. Onc. 10, 98 (2026). https://doi.org/10.1038/s41698-026-01296-2
Mots-clés: NSUN2, épitranscriptomique, criblage virtuel par IA, découverte de médicaments contre le cancer, méthylation de l’ARN