Clear Sky Science · fr
PlantCLR : préentraînement auto-supervisé contrastif pour une détection généralisable des maladies des plantes
Pourquoi mieux repérer les maladies des plantes est important
Les maladies des plantes privent silencieusement le monde de denrées alimentaires, réduisant les rendements et affectant les revenus des agriculteurs. Dans de nombreuses régions, seuls quelques experts formés sont disponibles pour identifier les problèmes sur le terrain, et obtenir leur aide peut être lent voire impossible. Cette étude présente PlantCLR, un système informatique qui apprend à reconnaître les maladies à partir de photos de feuilles avec bien moins d’étiquettes fournies par des humains que d’habitude. En rendant le diagnostic automatisé plus précis, plus fiable et plus facile à déployer sur du matériel modeste, ce travail ouvre la voie à des outils sur smartphone ou caméra bon marché qui pourraient aider les agriculteurs à détecter rapidement les problèmes et à protéger leurs récoltes.
Des photos de feuilles aux alertes précoces
Aujourd’hui, de nombreuses maladies des plantes sont diagnostiquées à l’ancienne : une personne examine une feuille et décide si des taches, un jaunissement ou des enroulements sont des signes d’infection. Ce jugement varie d’un expert à l’autre et peut être facilement perturbé par des ombres, des arrière-plans encombrés ou différents stades de croissance. Les systèmes de vision par ordinateur basés sur l’apprentissage profond commencent à aider, mais ils exigent généralement des milliers d’images soigneusement étiquetées. En agriculture, ces images étiquetées sont rares et coûteuses à collecter, tandis que d’importantes quantités d’images non étiquetées provenant de téléphones mobiles et de caméras de terrain restent souvent inutilisées. PlantCLR est conçu pour exploiter ces données non étiquetées, apprenant à quoi ressemblent typiquement les feuilles malades et saines avant d’avoir vu une étiquette.
Apprendre par comparaison
PlantCLR repose sur une approche récente appelée apprentissage auto-supervisé contrastif, où le modèle s’enseigne lui-même en comparant des images plutôt qu’en lisant des étiquettes. D’abord, le système prend une image de feuille non étiquetée et crée deux versions légèrement différentes par des recadrages aléatoires, des retournements, des changements de couleur ou du flou. Ces deux versions doivent représenter clairement la même feuille, de sorte que le modèle est entraîné à les considérer comme une paire correspondante et à leur donner des représentations internes similaires, tout en écartant les représentations de feuilles différentes présentes dans le même lot d’entraînement. Cette phase de préentraînement utilise un noyau de traitement d’image compact mais moderne appelé ConvNeXt-Tiny, associé à un petit module supplémentaire utilisé uniquement durant cette étape d’apprentissage par comparaison. 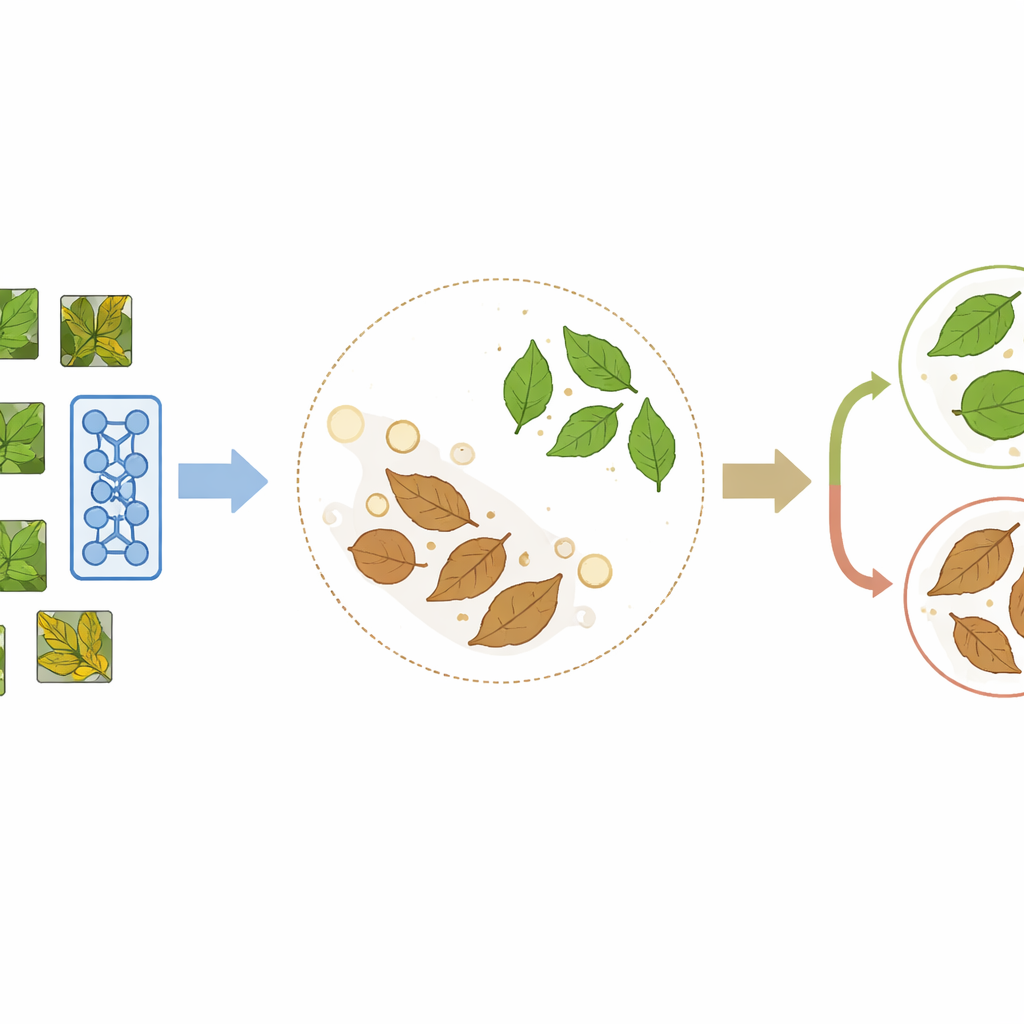
Mettre le système à l’épreuve
Pour évaluer l’efficacité de cette stratégie en pratique, les auteurs ont utilisé deux jeux de données de feuilles populaires qui reproduisent des contextes très différents du monde réel. Le jeu PlantVillage contient plus de 54 000 images de feuilles photographiées dans des conditions soignées et contrôlées, généralement avec des arrière-plans propres et des symptômes clairs répartis sur 38 catégories de maladies et de cultures. En revanche, le jeu de données Cassava Leaf Disease contient environ 21 000 images de feuilles de manioc prises directement sur le terrain, avec des arrière-plans désordonnés, un éclairage inégal et des feuilles qui se chevauchent ou se tordent dans de nombreuses directions, réparties en cinq classes, y compris plusieurs infections virales et bactériennes graves. L’étude utilise PlantVillage principalement comme source riche d’images non étiquetées pour le préentraînement, puis évalue les performances à la fois sur ce jeu de données et, de façon plus critique, sur les photos de manioc plus difficiles de type champ.
Performances robustes malgré des conditions changeantes
PlantCLR a atteint 99,10 % de précision sur l’ensemble de test PlantVillage et 96,83 % de précision sur l’ensemble de test Cassava, avec des scores F1 également élevés montrant que le modèle fonctionne bien même pour les maladies moins courantes. Ces chiffres surpassent une série de réseaux profonds bien connus, notamment DenseNet, ResNet, VGG et un modèle de vision transformer, tous entraînés de manière purement supervisée dans des conditions soigneusement assorties. 
Pourquoi cette approche représente une avancée
Pour les non-spécialistes, le message clé est que PlantCLR montre comment une machine peut devenir un « médecin » des plantes capable en apprenant d’abord à partir de grandes collections d’images non étiquetées, puis en raffinant ses compétences avec un jeu plus restreint et étiqueté. Cette stratégie non seulement atteint une très grande précision, mais tient aussi bien lorsque la caméra passe du laboratoire au champ, où les conditions sont bien moins propres. Parce que le modèle sous-jacent est relativement léger, il pourrait éventuellement être déployé sur du matériel abordable, rendant la détection avancée des maladies plus accessible aux agriculteurs et aux agents de vulgarisation du monde entier. En bref, l’étude démontre une voie pratique vers des outils de surveillance de la santé des plantes évolutifs, robustes et économes en annotations qui pourraient contribuer à protéger les approvisionnements alimentaires.
Citation: Shah, S.S.A., Saeed, F., Raza, M.U. et al. PlantCLR: contrastive self-supervised pretraining for generalizable plant disease detection. Sci Rep 16, 10550 (2026). https://doi.org/10.1038/s41598-026-45684-x
Mots-clés: détection des maladies des plantes, apprentissage auto-supervisé, apprentissage contrastif, IA agricole, surveillance de la santé des cultures