Clear Sky Science · fr
Étude des interactions entre la protéine d’immunité Colicine E9 d’Escherichia coli et l’ADN gyrase de Pseudomonas aeruginosa : approche computationnelle avancée pour développer de nouvelles stratégies antimicrobiennes
Transformer les armes bactériennes en nouveaux médicaments
À mesure que la résistance aux antibiotiques se répand, les médecins manquent d’options pour contrer des infections dangereuses. Certains des agents pathogènes les plus tenaces, comme Pseudomonas aeruginosa, peuvent résister à de nombreux traitements. Cette étude se tourne vers les bactéries elles‑mêmes pour trouver de nouvelles idées, en explorant comment la protéine protectrice d’un microbe pourrait être détournée pour désactiver une enzyme vitale d’un autre microbe. À l’aide de simulations informatiques avancées, les chercheurs montrent comment une petite protéine « d’immunité » peut se lier fortement à une enzyme bactérienne clé, suggérant une nouvelle voie pour de futurs antimicrobiens.
Un tout petit bouclier contre une toxine mortelle
Certaines souches d’Escherichia coli produisent de puissantes toxines protéiques appelées colicines, capables de tuer des bactéries voisines. Pour éviter de s’empoisonner elles‑mêmes, ces bactéries synthétisent aussi des protéines d’immunité correspondantes. L’une de ces protectrices, connue sous le nom de protéine d’immunité de la Colicine E9 (souvent appelée Im9), se fixe sur le domaine actif de la toxine et l’empêche d’endommager l’ADN de l’hôte. Parce que ce partenariat est si spécifique et solide, les scientifiques ont longtemps supposé que le comprendre en détail pourrait révéler de nouvelles façons de contrôler les bactéries nuisibles. Dans ce travail, les auteurs s’interrogent sur la possibilité qu’Im9 se lie également à l’ADN gyrase, une enzyme essentielle de Pseudomonas aeruginosa qui gère la torsion et la réplication de son ADN.
Cibler une enzyme vulnérable d’un germe difficile à traiter
Pseudomonas aeruginosa est un pathogène nosocomial majeur, capable de survivre dans des environnements hostiles et résistant à de nombreux médicaments. L’ADN gyrase est l’une de ses enzymes les plus importantes, responsable de maintenir les longues brins d’ADN correctement enroulés pour permettre leur réplication. Bloquer cette enzyme peut arrêter la croissance bactérienne, ce qui en fait une cible éprouvée pour certains antibiotiques. Les auteurs ont utilisé un outil d’apprentissage profond pour analyser la structure tridimensionnelle de l’ADN gyrase de Pseudomonas et repérer les « points chauds » probables — des amas d’acides aminés à la surface essentiels pour la liaison de partenaires. Ces régions forment la poche active de l’enzyme, où se déroulent les opérations normales sur l’ADN et où un inhibiteur potentiel s’attacherait idéalement.
Simuler une poignée de main moléculaire
Pour vérifier si Im9 pouvait s’emparer de ces points chauds, les chercheurs ont eu recours à des programmes de docking moléculaire qui « emboîtent » virtuellement les protéines comme des puzzles 3D. Ils ont d’abord nettoyé et complété les structures disponibles d’Im9 et de l’ADN gyrase, réparant une boucle manquante dans l’enzyme et réalisant de courtes simulations pour relâcher les régions sous tension. Ils ont ensuite utilisé deux outils de docking complémentaires, ClusPro et LightDock, pour générer de nombreux complexes candidats. Parmi ceux‑ci, ils ont sélectionné les arrangements les plus prometteurs et les ont soumis à de longues simulations de dynamique moléculaire couvrant des centaines de nanosecondes. Ces « films » temporels leur ont permis d’observer comment les deux protéines s’ajustaient, se fléchissaient et se stabilisaient en se liant l’une à l’autre.
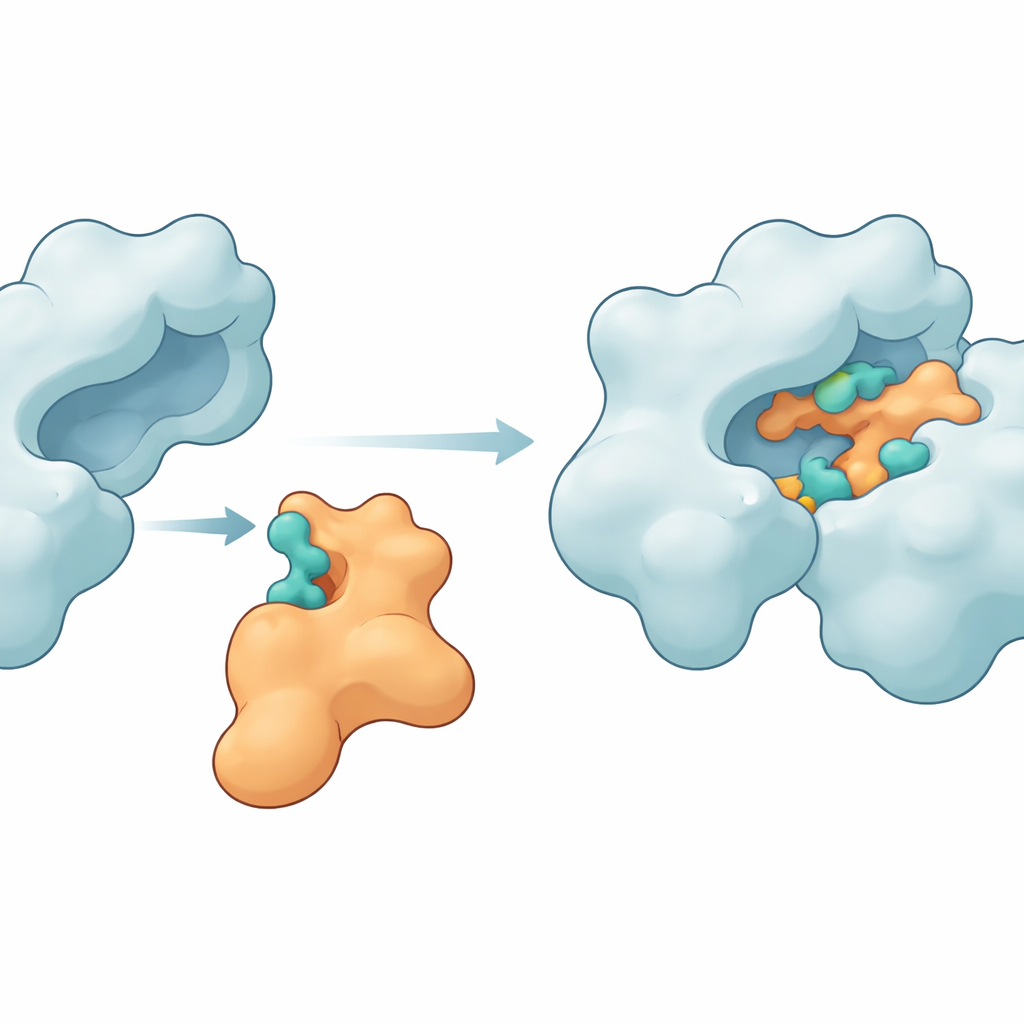
Points de contact clés qui maintiennent les protéines ensemble
Les simulations ont révélé qu’Im9 peut effectivement former un complexe compact et persistant avec l’ADN gyrase. Plusieurs acides aminés de l’enzyme — tels que MET27, ASP47, LYS105, LEU198, ASN199, ARG191 et GLU194 — ont formé à plusieurs reprises des liaisons hydrogène et d’autres forces d’attraction avec des sites correspondants sur Im9. Dans un modèle principal, les deux partenaires ont conservé entre six et dix liaisons hydrogène pendant la majeure partie de la simulation, signe d’une interface forte et bien organisée. D’autres mesures structurelles, y compris la compacité des protéines et l’amplitude de leurs fluctuations conformationnelles, montrent que l’enzyme restait intacte tandis que la protéine d’immunité se pliait juste assez pour s’adapter à la surface de la gyrase. Des calculs d’énergie par la méthode MM‑GBSA ont en outre soutenu l’idée que ces contacts créent une énergie libre de liaison favorable, quoique modeste, dominée par des contributions électrostatiques et de van der Waals.
Des modèles informatiques vers de futurs antimicrobiens
Dans l’ensemble, les résultats suggèrent que la protéine d’immunité de la Colicine E9 peut se lier de manière stable à la région active de l’ADN gyrase de Pseudomonas, formant un complexe durable qui pourrait, en principe, bloquer le rôle normal de l’enzyme dans la gestion de l’ADN. Bien que ces conclusions reposent uniquement sur des modèles informatiques et nécessitent encore des validations expérimentales, elles fournissent une feuille de route détaillée indiquant où et comment un inhibiteur d’origine protéique pourrait s’attacher. Pour le grand public, le message clé est que les armes et boucliers naturels des bactéries peuvent inspirer de nouvelles stratégies contre les infections difficiles à traiter. En comprenant cette poignée de main microscopique à l’échelle atomique, les chercheurs se rapprochent de la conception d’antimicrobiens innovants qui bloquent des enzymes bactériennes cruciales sans nuire aux cellules humaines.
Citation: Alfaraj, R., Alkathiri, F. & Chikhale, R. Investigating Escherichia coli Colicin E9 immunity protein interactions with DNA gyrase of Pseudomonas aeruginosa: advanced computational approach for developing novel antimicrobial strategies. Sci Rep 16, 10786 (2026). https://doi.org/10.1038/s41598-026-44427-2
Mots-clés: résistance aux antibiotiques, ADN gyrase, interactions protéine–protéine, conception de médicaments assistée par ordinateur, Pseudomonas aeruginosa