Clear Sky Science · fr
Identification morpho‑biochimique et moléculaire d’isolats de Bacillus licheniformis et Bacillus cereus issus de la rhizosphère du sorgho (Sorghum bicolor L.)
Des microbes bienveillants à la racine d’une culture résistante
Le sorgho est une céréale robuste qui nourrit des millions de personnes, notamment là où la chaleur et la sécheresse rendent l’agriculture difficile. Mais le sorgho ne survit pas seul dans les sols pauvres : ses racines sont entourées de partenaires microscopiques du sol qui peuvent l’aider à trouver des nutriments, lutter contre les maladies et supporter le stress. Cette étude explore quelles bactéries vivent autour des racines du sorgho dans l’est de l’Inde et examine de près deux aides clés du genre Bacillus, montrant comment un travail d’identification minutieux en laboratoire peut révéler qui elles sont et comment elles sont apparentées à leurs nombreux cousins.

Plonger dans la vie autour des racines
Les chercheurs ont collecté le sol adhérant aux racines de plusieurs variétés de sorgho cultivées dans trois sites autour de Bhubaneswar, en Inde, incluant un parc municipal, une station agricole et un campus universitaire. À partir de ces sols de la zone racinaire (rhizosphère), ils ont utilisé des techniques de culture classiques pour faire pousser des bactéries sur des milieux nutritifs, puis ont sélectionné des colonies différant par la couleur, la forme et la texture. Un premier examen au microscope et une coloration de Gram ont montré que la plupart des 13 isolats étaient des bactéries en bâtonnets avec des parois cellulaires épaisses, caractéristique de Bacillus et de ses proches apparentés, ainsi que quelques formes sphériques et une souche à paroi plus fine, Gram négative.
Tester les capacités des microbes
Pour aller au‑delà des apparences, l’équipe a réalisé des tests biochimiques simples qui révèlent comment chaque microbe gère l’oxygène, décompose certaines molécules et fermente les sucres. Par exemple, l’ajout de peroxyde d’hydrogène montre si les cellules produisent la catalase, une enzyme qui les protège des espèces réactives de l’oxygène, tandis que d’autres tests détectent la formation d’acide ou la capacité à décomposer l’acide aminé tryptophane. Les profils de ces réactions ont aidé à préciser l’identité probable de chaque isolat. Deux souches en bâtonnets, étiquetées AG3 et AG11, se sont distinguées : toutes deux toléraient bien l’oxygène, éliminaient efficacement des sous‑produits nocifs et présentaient un mode de fermentation similaire, typique des espèces de Bacillus connues pour prospérer autour des racines des plantes.
Lire le code-barres génétique des bactéries
Parce que de nombreuses espèces de Bacillus se ressemblent et se comportent de façon similaire, les scientifiques se sont tournés vers leur ADN pour obtenir une réponse plus précise. Ils ont ciblé le gène 16S rRNA, un « code‑barres » génétique largement utilisé pour les bactéries. Après extraction de l’ADN des isolats AG3 et AG11, ils ont copié ce gène par réaction en chaîne par polymérase et ont confirmé, sur gel, que les fragments avaient la longueur attendue. L’équipe a ensuite séquencé le gène par la méthode de Sanger et l’a comparé à des milliers de séquences connues dans la base de données publique du NCBI. Les correspondances furent frappantes : AG3 s’alignait presque parfaitement avec Bacillus licheniformis, tandis qu’AG11 correspondait exactement à Bacillus cereus. Les deux espèces sont courantes dans les sols agricoles et sont connues pour entretenir des interactions fortes avec les plantes, parfois stimulant la croissance et parfois, dans le cas de B. cereus, posant des problèmes de santé dans d’autres contextes.
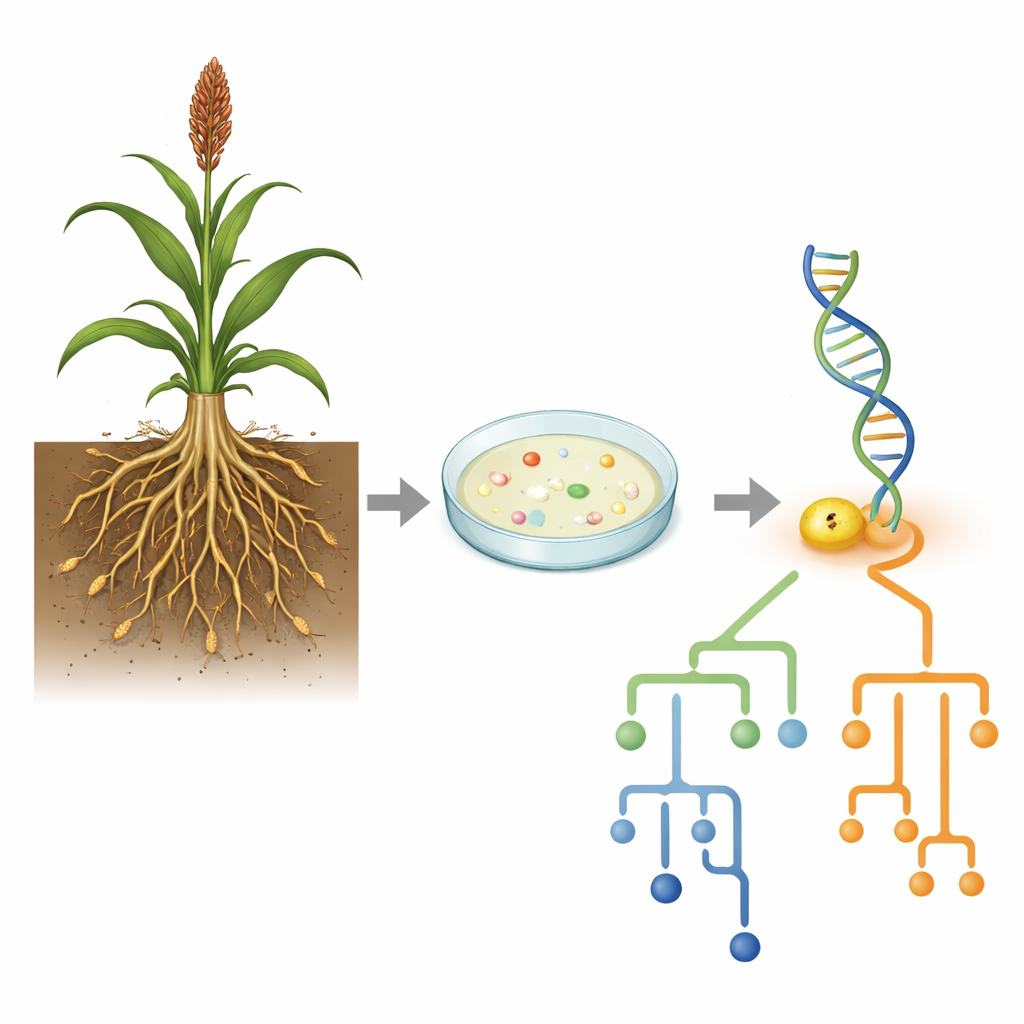
Placer ces découvertes sur l’arbre du vivant
Savoir quelle est la meilleure correspondance n’est qu’une partie de l’histoire ; les auteurs ont aussi voulu voir où ces isolats se situent dans l’arbre généalogique bactérien plus large. Ils ont construit des arbres évolutifs en alignant les séquences 16S d’AG3 et AG11 avec des dizaines de souches apparentées et en utilisant des modèles statistiques pour estimer la vitesse d’évolution des différentes positions du gène. Bacillus licheniformis AG3 s’est regroupé étroitement avec un grand ensemble de souches similaires, mais montrait une forte variation dans la vitesse d’évolution de différentes régions de son gène, suggérant des zones soumises à des pressions évolutives distinctes. En revanche, Bacillus cereus AG11 est tombé dans un sous‑groupe distinct au sein du complexe B. cereus, ses positions génétiques évoluant à des rythmes plus réguliers. Ces patrons indiquent que, même au sein d’un même genre, différentes lignées peuvent suivre des trajectoires évolutives différentes tout en occupant des niches pédologiques similaires.
Quelles implications pour l’agriculture future
L’étude montre que les racines du sorgho, dans une seule région, hébergent une diversité de bactéries et que la combinaison d’examens microscopiques et biochimiques simples avec le séquençage de l’ADN est un moyen puissant d’identifier des acteurs clés comme B. licheniformis et B. cereus. Pour le grand public, le message est que la santé et le rendement des cultures dépendent non seulement des semences et du sol, mais aussi de ces partenaires microbiens cachés. Bien que ce travail n’ait pas encore testé directement l’effet des souches identifiées sur la croissance du sorgho, il cartographie quelles microbes sont présents et comment ils sont apparentés — des étapes cruciales pour concevoir des inoculants microbiens ciblés et sûrs qui pourraient aider les agriculteurs à cultiver un sorgho plus résilient avec moins d’intrants chimiques.
Citation: Jurry, A.G., Sahoo, J.P., Sharma, S.S. et al. Morpho-biochemical and molecular identification of Bacillus licheniformis and Bacillus cereus isolates from sorghum (Sorghum bicolor L.) rhizosphere. Sci Rep 16, 8983 (2026). https://doi.org/10.1038/s41598-026-42932-y
Mots-clés: sorgho, bactéries de la rhizosphère, Bacillus licheniformis, Bacillus cereus, promotion de la croissance des plantes