Clear Sky Science · fr
Évaluation de la métagénomique en longues lectures pour le diagnostic des infections sanguines : étude pilote dans un hôpital tertiaire thaïlandais
Pourquoi des tests sanguins plus rapides sont importants
Lorsque des bactéries envahissent la circulation sanguine, chaque heure compte. Les médecins doivent rapidement choisir l’antibiotique adéquat, mais les analyses de laboratoire actuelles peuvent prendre plusieurs jours pour identifier l’agent en cause et déterminer quels médicaments risquent d’échouer. Cette étude menée dans un grand hôpital thaïlandais explore une nouvelle approche pour accélérer le processus en lisant le matériel génétique de tous les micro-organismes présents dans un échantillon de sang simultanément, à l’aide d’un séquenceur d’ADN portable. L’objectif est de passer de l’attente de plusieurs jours à l’obtention d’un portrait détaillé de l’infection au cours d’une seule journée de travail.
Une nouvelle façon de détecter les germes dans le sang
Les chercheurs se sont concentrés sur des patients présentant déjà des signes de croissance bactérienne dans des flacons de culture sanguine standards, utilisés couramment dans les hôpitaux du monde entier. Plutôt que de cultiver chaque bactérie sur des milieux séparés puis de réaliser une série de tests chimiques, ils ont prélevé le liquide directement dans 40 flacons de culture positifs et en ont extrait tout l’ADN microbien. Cet ADN a ensuite été séquencé sur un appareil Oxford Nanopore, un dispositif qui fait passer de longs brins de matériel génétique à travers de minuscules pores et lit leur séquence en temps réel. Parce que la méthode ne dépend pas de la culture de chaque organisme, elle peut, en principe, détecter de nombreuses espèces, leurs traits de résistance aux médicaments et leurs facteurs de virulence en un seul flux de travail simplifié.
Ce qui a été trouvé dans les infections sanguines en Thaïlande
Les analyses conventionnelles des mêmes 40 échantillons ont produit 45 isolats bactériens, reflétant le fait que quelques patients étaient infectés par plus d’une espèce. Le système de routine utilisé à l’hôpital, VITEK, a montré que deux bactéries intestinales familières, Escherichia coli et Klebsiella pneumoniae, étaient responsables d’environ 40 % de ces infections, et que beaucoup de ces souches étaient résistantes à plusieurs antibiotiques. L’approche nanopore concorde en grande partie avec ce tableau, identifiant 43 génomes bactériens distincts et confirmant la domination des Enterobacterales. Elle a aussi repéré quelques espèces inhabituelles ou mal classées, comme une bactérie d’environnement nommée Ralstonia mannitolilytica et le germe gastrique Campylobacter jejuni, que les méthodes habituelles avaient manqués ou seulement identifiés de manière générale. Dans certaines infections mixtes, toutefois, le séquençage a peiné à séparer complètement des micro-organismes étroitement apparentés lorsque l’un était présent à des niveaux beaucoup plus faibles que l’autre.
Regarder la résistance et les tactiques furtives
Parce que la nouvelle méthode lit de longues séquences d’ADN, elle peut faire plus que nommer les bactéries : elle peut révéler le matériel génétique qui leur permet de résister aux antibiotiques et de provoquer la maladie. L’équipe a analysé les génomes à la recherche de gènes de résistance connus et de gènes de « virulence » qui aident les germes à adhérer aux tissus, former des biofilms protecteurs, capter le fer ou produire des toxines. E. coli et K. pneumoniae portaient de nombreux de ces gènes, notamment ceux qui neutralisent des familles d’antibiotiques clés comme les bêta‑lactamines et les aminosides. Le séquençage a également mis en évidence de puissants ensembles de résistance chez des espèces nosocomiales résistantes telles qu’Acinetobacter baumannii et Pseudomonas aeruginosa, dont les génomes étaient riches en systèmes d’efflux et autres défenses. En parallèle, certaines bactéries sanguines plus rares présentaient des arsenaux relativement modestes, suggérant une menace moindre mais néanmoins significative.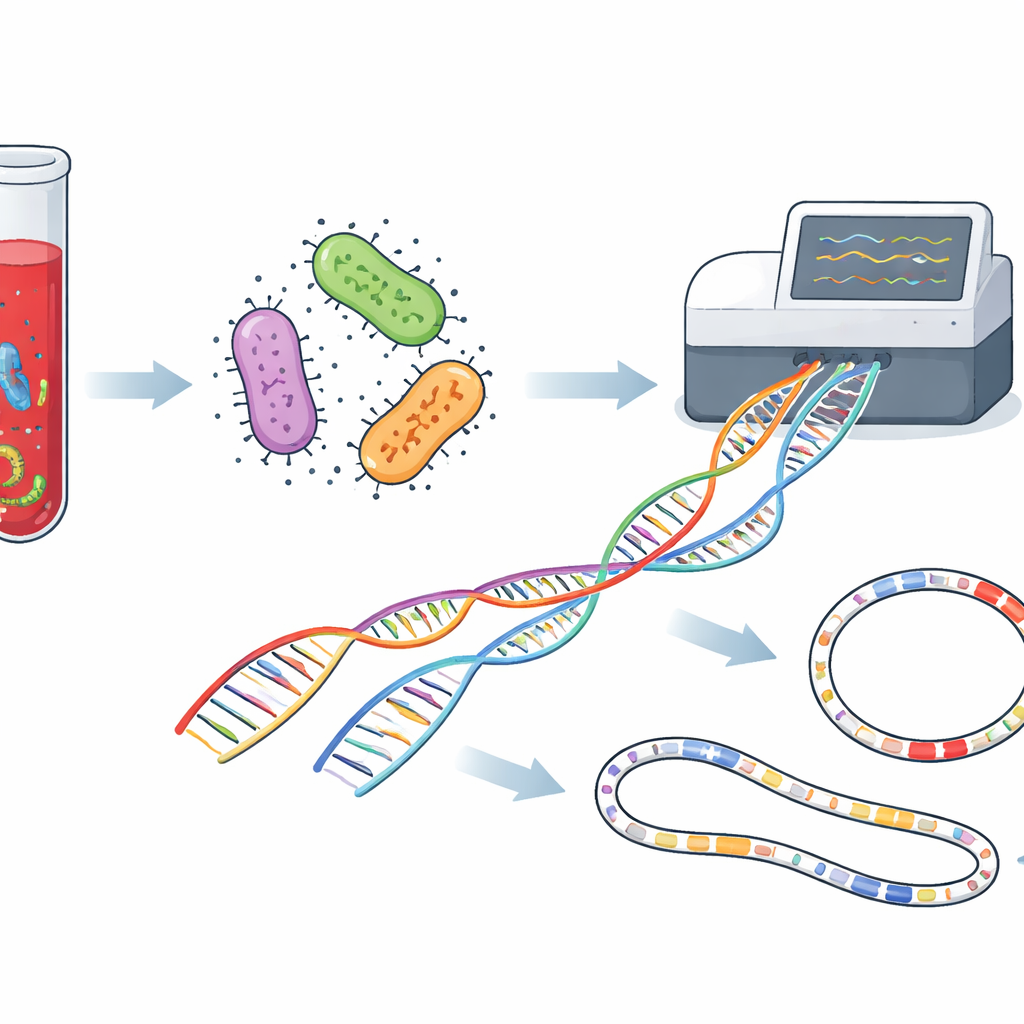
Suivre la résistance sur l’ADN mobile
Un autre avantage du séquençage en longues lectures est sa capacité à reconstituer des chromosomes bactériens complets ainsi que des molécules d’ADN circulaires appelées plasmides, qui peuvent passer d’une bactérie à l’autre et diffuser des gènes de résistance. Dans cette étude, les chercheurs ont répertorié des dizaines de types de plasmides. Certains étaient fortement associés à des espèces particulières, tandis que d’autres étaient partagés entre plusieurs types de bactéries, suggérant un échange de gènes en cours dans l’environnement hospitalier. Nombre d’entre eux portaient des facteurs connus d’échec thérapeutique, tels que des bêta‑lactamases à spectre étendu et des carbapénèmases — des enzymes qui rendent inefficaces certains des antibiotiques les plus importants. Cartographier ces éléments mobiles aide les équipes de contrôle des infections à comprendre comment des traits dangereux circulent dans un hôpital au fil du temps.
Accélérer les réponses pour les médecins et les hôpitaux
Le gain de temps est l’avantage le plus net de la nouvelle approche. Les méthodes standard demandent souvent cinq à sept jours depuis le moment où une culture sanguine devient positive jusqu’à l’obtention des résultats d’identification complète et de sensibilité aux antibiotiques. En revanche, le protocole nanopore de cette étude pilote a fourni des identifications d’espèces précoces en deux à quatre heures après le début de la course et a signalé des gènes de résistance clés en six à huit heures. Si des runs de séquençage plus longs amélioraient l’exhaustivité des génomes, ils ne modifiaient pas les principales conclusions cliniques. Bien qu’il s’agisse d’une petite étude de phase précoce qui n’a pas encore relié les résultats aux issues des patients ni évalué les coûts, elle suggère que l’intégration du séquençage métagénomique en longues lectures dans les laboratoires hospitaliers pourrait fournir des informations plus rapides et plus riches pour guider le traitement, soutenir la gestion raisonnée des antibiotiques et renforcer la surveillance régionale des infections résistantes aux médicaments.
Ce que cela signifie pour la prise en charge des patients
Pour un non‑spécialiste, la conclusion est que les médecins pourraient bientôt disposer d’un « instantané » génétique d’une infection sanguine le même jour où une culture devient positive, au lieu d’attendre presque une semaine. Cet instantané ne se contente pas de nommer le germe : il met aussi en lumière nombre de ses points faibles et son potentiel de transmission de la résistance à d’autres. Si des travaux supplémentaires sont nécessaires sur des cohortes plus larges, avec des contrôles de contamination renforcés et des analyses de coûts, cette étude pilote thaïlandaise montre que des séquenceurs d’ADN de la taille d’une poche peuvent nous rapprocher d’une prise en charge rapide et informée par le génome des infections sanguines potentiellement mortelles.
Citation: Yaikhan, T., Wongsurawat, T., Jenjaroenpan, P. et al. Evaluating long-read metagenomics for bloodstream infection diagnostics: a pilot study from a Thai Tertiary Hospital. Sci Rep 16, 9330 (2026). https://doi.org/10.1038/s41598-026-41247-2
Mots-clés: infection sanguine, résistance aux antimicrobiens, séquençage métagénomique, technologie nanopore, microbiologie clinique