Clear Sky Science · fr
Caractérisation génomique de souches d’Escherichia coli multirésistantes identifiées chez des patientes souffrant d’infections urinaires en Égypte
Pourquoi ces infections tenaces comptent
Les infections urinaires figurent parmi les motifs de consultation les plus courants en hôpital et en cabinet. Nombre d’entre elles sont causées par la bactérie Escherichia coli et sont généralement traitables par des antibiotiques standards. Mais dans le monde entier, y compris en Égypte, certaines souches d’E. coli sont devenues si résistantes aux médicaments que les options thérapeutiques se raréfient. Cette étude examine en détail le génome de deux de ces souches difficiles à traiter prélevées chez des patientes égyptiennes afin de comprendre comment elles échappent à de multiples antibiotiques et dans quelle mesure leur résistance peut se propager.
Deux patientes, deux germes dangereux
Les chercheurs se sont concentrés sur deux souches d’E. coli, nommées UPE7 et UPE139, isolées chez des femmes atteintes d’infections urinaires dans un hôpital de Mansoura, en Égypte. Testées contre un large éventail d’antibiotiques, les deux souches ont résisté à de nombreux médicaments que les médecins prescriraient normalement, y compris plusieurs traitements de dernier recours. Elles présentaient une résistance aux pénicillines et céphalosporines courantes, aux carbapénèmes puissants, aux fluoroquinolones largement utilisées et à d’autres classes médicamenteuses. Ce profil les classe sans équivoque parmi les bactéries multirésistantes, rendant les infections plus difficiles et coûteuses à traiter et augmentant le risque de complications.
Lire le mode d’emploi de l’ADN bactérien
Pour comprendre comment ces souches sont devenues si robustes, l’équipe a séquencé leurs génomes complets à l’aide de technologies de séquençage de nouvelle génération. Elle a ensuite employé des outils bioinformatiques spécialisés pour repérer les gènes associés à la résistance aux antibiotiques et les éléments favorisant la virulence. Les deux souches portaient de nombreux gènes de résistance cohérents avec leur comportement en laboratoire. Par exemple, elles hébergeaient plusieurs gènes « bêta‑lactamases » capables de dégrader des antibiotiques clés, ainsi que des gènes protégeant contre des médicaments tels que les aminosides, les tétracyclines, les macrolides, les sulfamides et le triméthoprime. Des modifications des enzymes centrales manipulant l’ADN, cibles des fluoroquinolones, expliquaient leur forte résistance au lévofloxacine. Les deux souches possédaient également un opéron connu pour modifier leur surface externe de manière à atténuer l’action des polymyxines.
Aides cachées qui propagent la résistance
Au‑delà des gènes de résistance isolés, l’étude met en lumière les vecteurs génétiques qui déplacent ces traits. De nombreux gènes de résistance étaient adjacents à des éléments génétiques mobiles tels que des séquences d’insertion et des transposons — de petites unités d’ADN capables de sauter d’un endroit à un autre — et se trouvaient sur des plasmides, des molécules d’ADN circulaires que les bactéries s’échangent. Par exemple, un gène de bêta‑lactamase à spectre étendu largement répandu, CTX‑M‑15, était associé à de tels éléments mobiles dans les deux souches, tandis que UPE139 portait aussi OXA‑244, une enzyme dégradant les carbapénèmes, intégrée entre des segments d’ADN mobiles sur le chromosome. Les mêmes types de plasmides identifiés ici ont été impliqués ailleurs dans des regroupements de gènes de résistance, ce qui suscite l’inquiétude que ces souches puissent transmettre leurs mécanismes de défense à d’autres bactéries en milieu hospitalier et dans la communauté.
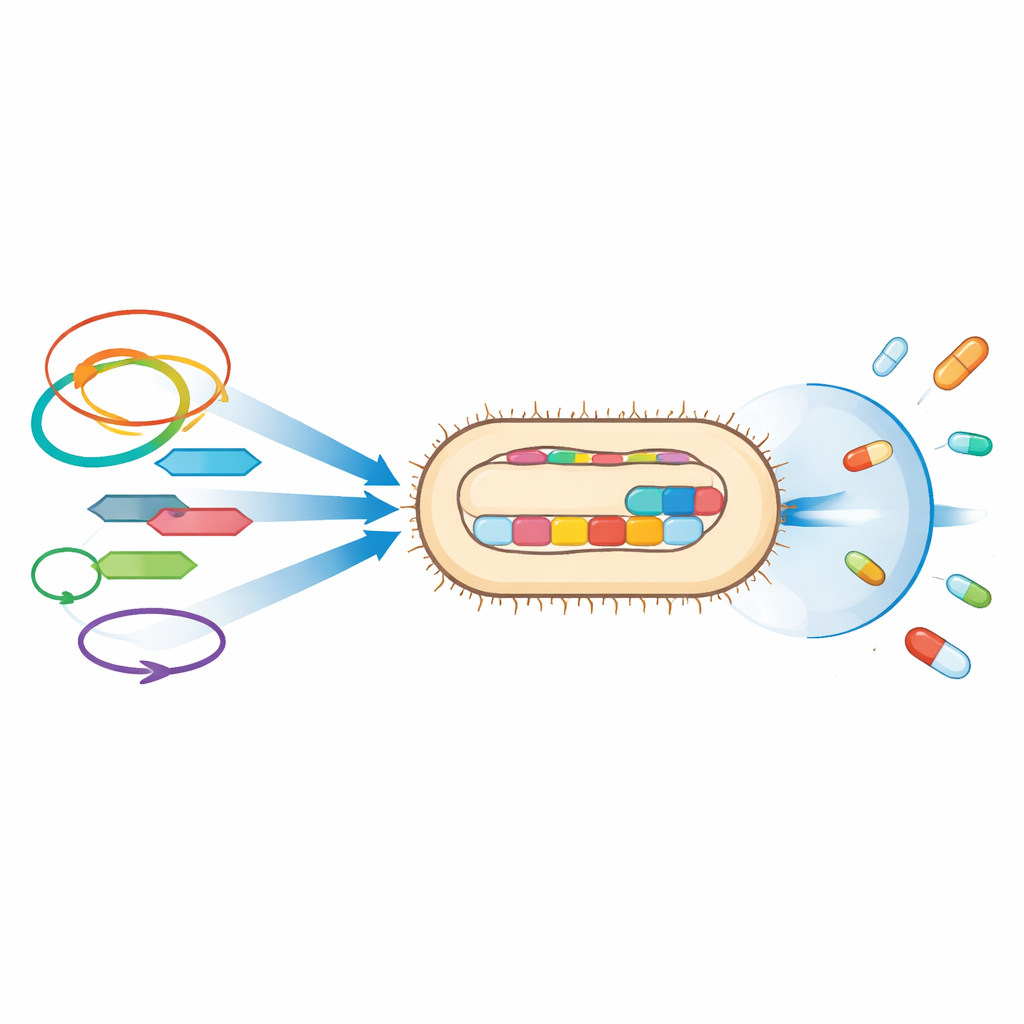
Outils d’infection et de survie
L’analyse génétique a également révélé de nombreux traits aidant ces souches d’E. coli à coloniser les voies urinaires et à endommager les tissus de l’hôte. UPE7 et UPE139 portaient plusieurs structures d’adhésion leur permettant de se fixer aux cellules et de former des biofilms, des communautés protectrices plus difficiles à éradiquer par les médicaments et le système immunitaire. Elles codaient des toxines telles que l’hémolysine, capable d’endommager les cellules de l’hôte, et des systèmes de captation du fer qui permettent aux bactéries de prospérer dans l’environnement pauvre en fer de l’organisme. UPE139, en particulier, possédait des gènes supplémentaires liés à la formation de capsule, à l’invasion et à l’évasion immunitaire, suggérant une capacité particulièrement marquée à persister et à se propager chez les patientes.
Ce que cela signifie pour les patientes et les médecins
En combinant les tests traditionnels de sensibilité aux médicaments avec le séquençage complet des génomes, cette étude montre comment un nombre limité de gènes et d’éléments mobiles peut transformer des bactéries urinaires ordinaires en agents pathogènes multirésistants redoutables. Elle révèle aussi que ces traits dangereux reposent sur des segments d’ADN bien adaptés au transfert vers d’autres souches, augmentant le risque d’une dissémination locale et régionale plus large. Pour les patientes, cela signifie que certaines infections courantes peuvent devenir plus difficiles à guérir. Pour les cliniciens et les responsables de santé, ces résultats soulignent la nécessité d’une surveillance génomique continue, d’un usage prudent des antibiotiques et d’études plus larges sur un nombre accru d’isolats afin de suivre les clones à haut risque, d’ajuster les recommandations thérapeutiques et de ralentir la progression de la résistance.
Citation: El Halfawy, N.M., Gouda, M.K., Elgayar, F.A. et al. Genomic characterization of multidrug-resistant Escherichia coli strains identified from patients with urinary tract infection in Egypt. Sci Rep 16, 8958 (2026). https://doi.org/10.1038/s41598-026-40536-0
Mots-clés: résistance aux antibiotiques, infection urinaire, Escherichia coli, séquençage du génome, éléments génétiques mobiles