Clear Sky Science · fr
Identification de sous-types liés aux lymphocytes T cytotoxiques centraux, établissement d’un modèle pronostique et analyse de l’infiltration du microenvironnement tumoral dans le HNSC
Pourquoi cela compte pour les personnes atteintes de cancer de la tête et du cou
Les cancers de la tête et du cou sont souvent découverts tardivement et peuvent être difficiles à traiter, même avec la chirurgie moderne, la radiothérapie et l’immunothérapie. Cette étude pose une question pratique aux conséquences vitales : des motifs dans les gènes liés à l’immunité d’une tumeur peuvent-ils indiquer quels patients sont susceptibles d’avoir un mauvais pronostic et qui pourrait bénéficier le plus de certains médicaments ou traitements immunitaires ? En décryptant la manière dont les tumeurs se cachent des lymphocytes T cytotoxiques, les auteurs visent à construire une « grille d’évaluation » simple et non invasive qui pourrait orienter une prise en charge plus personnalisée.
Classer les tumeurs selon leurs astuces d’échappement immunitaire
Les chercheurs se sont concentrés sur un groupe de 31 gènes qui aident les cellules cancéreuses à échapper aux attaques des lymphocytes T cytotoxiques, principaux « soldats » du système immunitaire contre les tumeurs. À partir de données de plus de 770 personnes atteintes de carcinome épidermoïde tête-et-cou dans de grandes bases publiques, ils ont examiné l’intensité d’expression de chacun de ces gènes dans les tumeurs individuelles. En regroupant les patients selon ces motifs d’échappement immunitaire, trois types de tumeurs distincts sont apparus. Ces types différaient non seulement par l’activité génique, mais aussi par la survie des patients et par le nombre de cellules immunitaires ayant réussi à pénétrer la zone tumorale.

Construction d’un score de risque à trois gènes
Pour convertir ces motifs complexes en un outil exploitable par les cliniciens, l’équipe a cherché un jeu réduit de gènes prédictifs de survie. Ils ont suivi les gènes différant entre les trois types tumoraux puis appliqué plusieurs niveaux de modélisation statistique pour éviter les pistes trompeuses. Ce processus a réduit la liste à trois gènes clés : SERPINE1, MMP1 et SPINK6. Une forte expression de SERPINE1 et de MMP1 signalait un risque accru, tandis qu’une expression plus élevée de SPINK6 s’associait à de meilleurs résultats. La combinaison de ces trois mesures en un score de risque unique a permis de classer les patients en groupes « à haut risque » et « à faible risque » dont les courbes de survie étaient nettement différentes.
Lier les motifs géniques au « voisinage » tumoral
Parce que le cancer ne se développe pas en isolation, les auteurs ont examiné la relation entre le score de risque et le « voisinage » tumoral composé de cellules immunitaires et de cellules de soutien. Ils ont constaté que différents types cellulaires immunitaires s’associaient aux scores élevés ou faibles, et que les tumeurs à score élevé présentaient des paysages immunitaires clairement modifiés. Ces tumeurs à haut risque présentaient des mutations génétiques très fréquentes mais, de façon intéressante, des signes légèrement moindres de caractéristiques de type souche. Elles avaient également tendance à afficher des signaux plus forts de molécules de points de contrôle immunitaires — des protéines de surface que l’on peut bloquer avec des médicaments d’immunothérapie approuvés pour réactiver les T cells. Cela suggère que, bien que les patients du groupe à haut risque aient un pronostic global plus mauvais, leurs tumeurs pourraient être particulièrement vulnérables aux immunothérapies modernes et à certains chimiothérapies.
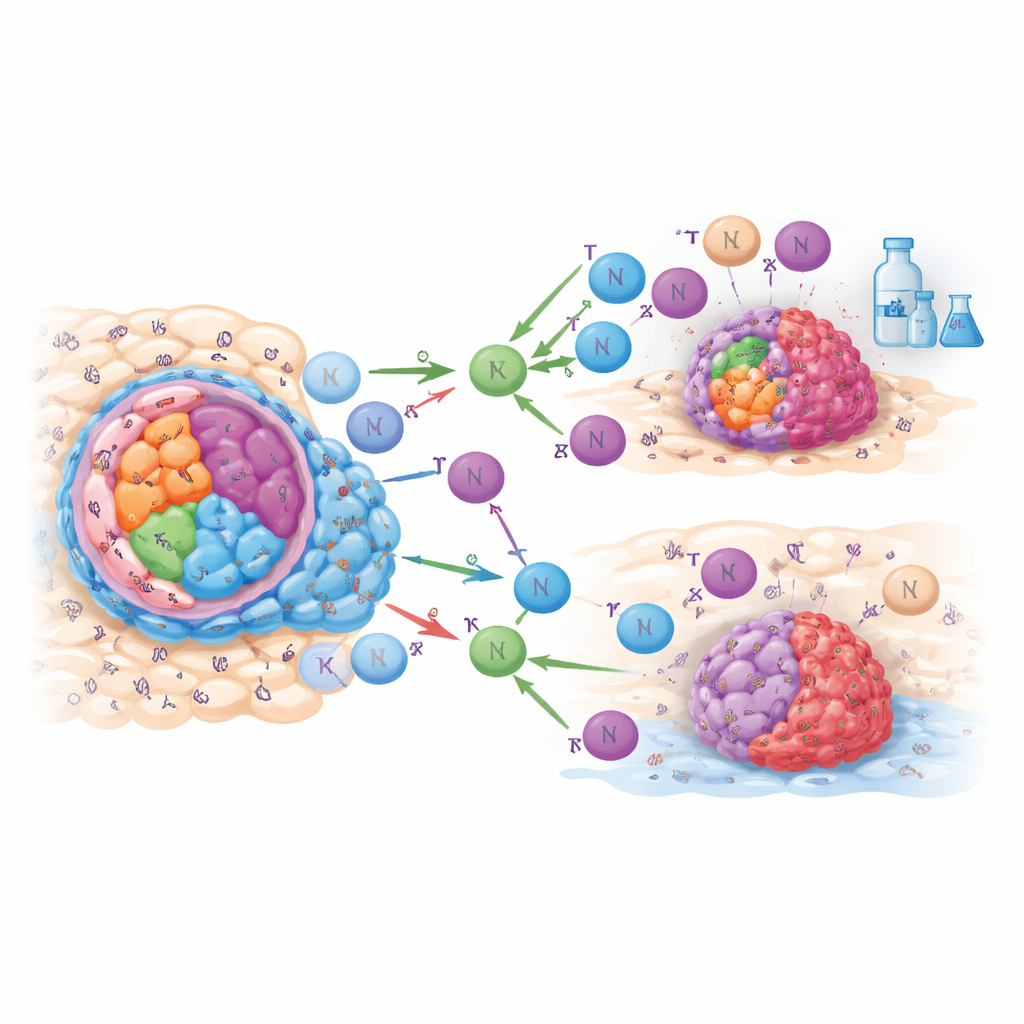
Mettre des chiffres dans un outil de chevet
Pour passer des statistiques à la clinique, l’équipe a combiné le score de risque à trois gènes avec des informations patient basiques telles que l’âge et le stade tumoral pour construire un « nomogramme » visuel — un graphique qui estime la probabilité d’être en vie à un, trois et cinq ans. Le test de cet outil sur des jeux de patients indépendants a montré qu’il reflétait bien les résultats réels. Les auteurs ont ensuite confirmé, dans un petit groupe de patients opérés, que les trois gènes étaient effectivement exprimés différemment dans le tissu tumoral comparé au tissu normal adjacent. Enfin, ils ont réduit directement les niveaux de SERPINE1 dans deux lignées cellulaires de cancer tête-et-cou en laboratoire. Lorsque ce gène a été silencé, les cellules proliféraient plus lentement et formaient moins de colonies, soutenant l’idée que SERPINE1 favorise activement la croissance de ces cancers.
Ce que cela implique pour les décisions thérapeutiques futures
En termes simples, cette étude montre qu’un panel court de trois gènes peut séparer les patients atteints de cancer de la tête et du cou en groupes présentant des risques et des perspectives de traitement très différents. Les tumeurs présentant un profil « à haut risque » sont plus agressives mais semblent aussi davantage exposées à l’attaque lorsque les médicaments appropriés sont utilisés, y compris les inhibiteurs des points de contrôle immunitaires et certaines chimiothérapies. Bien que des études prospectives plus larges soient encore nécessaires avant que ce score puisse guider la pratique courante, ce travail offre une feuille de route prometteuse pour adapter le traitement en fonction des mécanismes d’échappement immunitaire propres à chaque tumeur, plutôt que de traiter tous les patients de la même manière.
Citation: Jiang, W., Liu, Q., Chu, H. et al. Identification of core cytotoxic T lymphocyte-related subtypes, establishment of a prognostic model, and analysis tumor microenvironment infiltration in HNSC. Sci Rep 16, 9776 (2026). https://doi.org/10.1038/s41598-026-39801-z
Mots-clés: cancer de la tête et du cou, microenvironnement tumoral, immunothérapie, signature génique pronostique, SERPINE1