Clear Sky Science · fr
Modélisation prédictive des propriétés physico-chimiques des antibiotiques β-lactamines par des indices topologiques basés sur les valeurs propres et des techniques de régression non linéaire
Pourquoi cette étude est importante
Les antibiotiques sont des piliers de la médecine moderne, pourtant les bactéries développent des résistances plus rapidement que ne sont découverts de nouveaux médicaments. Concevoir de meilleurs antibiotiques dépend de plus en plus de modèles informatiques capables de prédire le comportement d’une molécule candidate — sa volatilité, son encombrement, ou ses interactions avec l’eau et les membranes cellulaires. Cet article explore une méthode mathématiquement élégante pour effectuer de telles prédictions sur une grande famille de médicaments, les antibiotiques β-lactamines, en utilisant des outils de la théorie des graphes et de la statistique plutôt que des essais de laboratoire coûteux seuls.
Transformer les molécules en réseaux
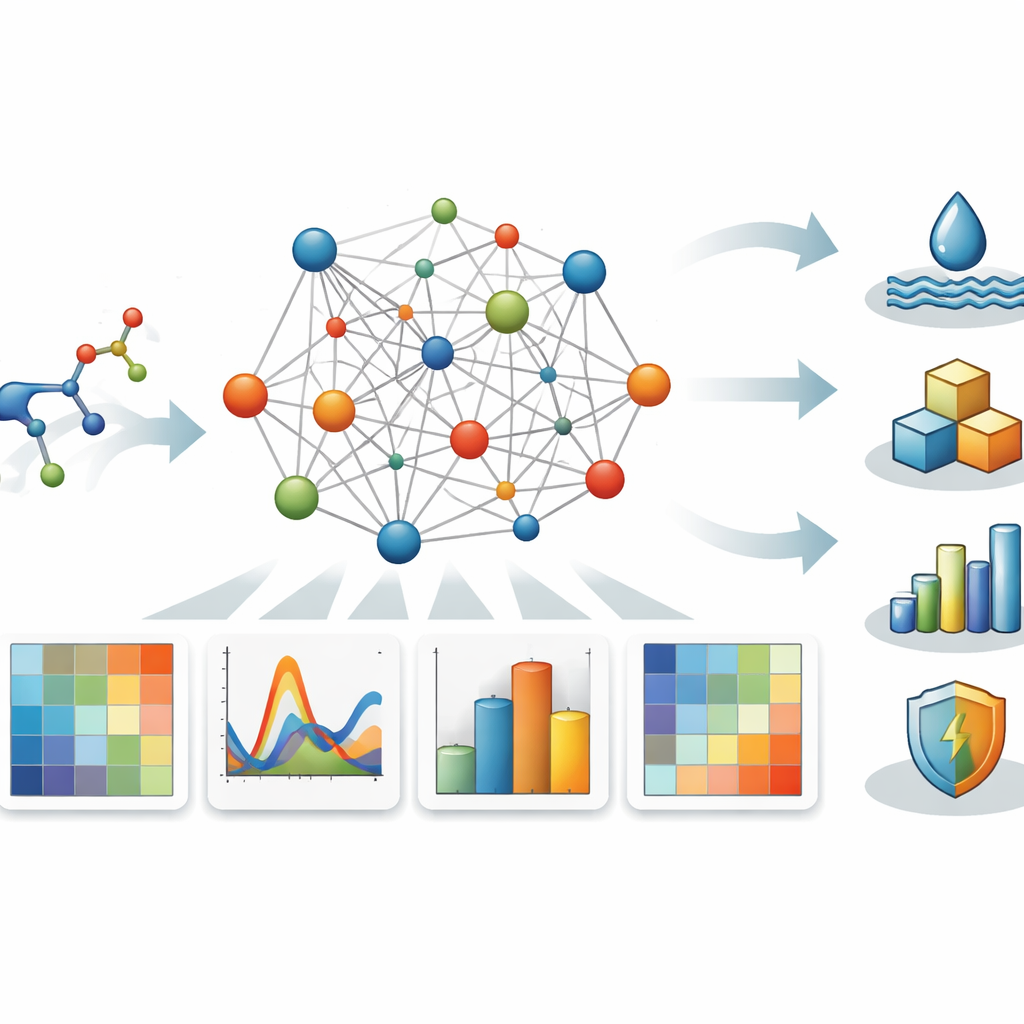
Plutôt que de considérer un médicament comme une simple structure boule-et-bâtonnets, les auteurs traitent chaque antibiotique β-lactame comme un réseau : les atomes deviennent des points (appelés sommets) et les liaisons chimiques des traits (appelés arêtes) reliant ces points. À partir de ce réseau, ils construisent plusieurs matrices mathématiques qui capturent comment les atomes sont connectés, combien de liaisons chaque atome possède, et la distance entre atomes le long des chemins de liaison. Ces matrices — connues sous les noms d’adjacence, Laplacien, Laplacien sans signe et distance — offrent différentes perspectives sur la « forme » et la connectivité globale de la molécule.
Mesurer les motifs cachés dans le réseau
Une fois ces tables de connexion établies, les chercheurs calculent leurs valeurs propres, des nombres qui résument des motifs structurels profonds du réseau. À partir de ces valeurs propres, ils construisent un ensemble de scores numériques appelés descripteurs spectraux, avec des appellations telles que énergie d’adjacence, connectivité algébrique et énergie de distance. Chaque descripteur mélange des informations issues de l’ensemble du graphe moléculaire, captant à la fois des détails locaux autour de chaque atome et l’architecture globale de la molécule. Comme les β-lactames peuvent différer subtilement au niveau des cycles et des chaînes latérales, de telles mesures sensibles et globales sont utiles pour relier structure et comportement.
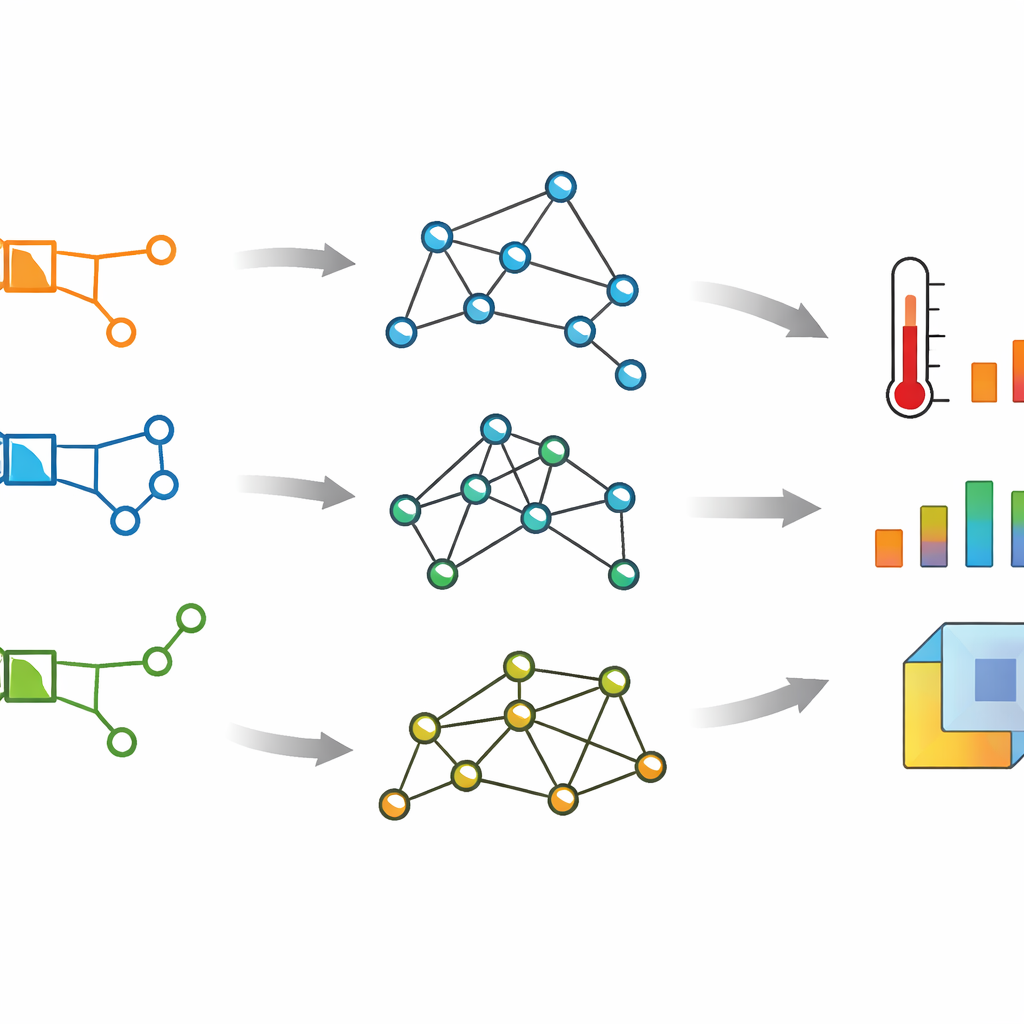
Relier les scores structurels aux propriétés quotidiennes
L’étude porte sur sept composés β-lactames d’importance clinique, incluant des médicaments bien connus comme l’amoxicilline et l’imipénem, choisis pour couvrir une gamme de tailles et de configurations de chaînes latérales. Pour chaque médicament, l’équipe rassemble des données expérimentales sur des propriétés physico-chimiques pratiques : point d’ébullition, volume molaire, réfraction molaire (mesure de la capacité à courber la lumière), fraction de surface polaire, facilité de polarisation des électrons (polarisabilité) et tension superficielle. Ils testent ensuite dans quelle mesure chaque descripteur spectral isolé peut prédire chaque propriété en ajustant trois types de relations courbes — quadratique, logarithmique et loi de puissance — à l’aide de logiciels statistiques standards.
Quelle est la qualité des prédictions ?
Les résultats montrent que plusieurs descripteurs corrèlent fortement avec des propriétés principalement gouvernées par la taille moléculaire et la densité de connexions entre atomes. Par exemple, la connectivité algébrique, l’énergie du Laplacien sans signe et l’énergie de distance se révèlent souvent particulièrement informatifs. Les équations quadratiques, qui permettent une relation courbe simple entre descripteur et propriété, s’avèrent généralement légèrement meilleures que les formules logarithmiques ou en loi de puissance, fournissant des coefficients de détermination plus élevés et des erreurs de prédiction plus faibles. Cela suggère que le lien entre la structure en réseau d’une molécule et son comportement macroscopique est souvent faiblement courbé plutôt que strictement linéaire.
Les limites de l’approche
La modélisation est moins performante pour des propriétés qui dépendent fortement de la répartition électronique sur la surface de la molécule et de la formation d’interactions spécifiques comme les liaisons hydrogène. La surface polaire et la tension superficielle, par exemple, montrent davantage de dispersion entre valeurs prédites et mesurées. Parce que les descripteurs basés sur les graphes utilisés ici se concentrent uniquement sur quelles liaisons existent et sur les distances topologiques, ils n’encodent pas explicitement les effets électroniques détaillés ni les interactions directionnelles avec le milieu. Cette limitation reflète la simplicité de la représentation sous-jacente, et non un échec des méthodes statistiques elles-mêmes.
Implications pour la conception future d’antibiotiques
Globalement, l’étude démontre que les descripteurs de graphe fondés sur les valeurs propres offrent une manière compacte et interprétable de prédire plusieurs propriétés clés des β-lactames sans réaliser une batterie complète d’expériences. En capturant l’agencement et la connectivité globale des atomes, ces scores mathématiques aident à prévoir la température d’ébullition d’un composé, l’espace qu’il occupe et son comportement en vrac dans son environnement. S’ils ne peuvent pas encore remplacer des modèles plus détaillés pour des propriétés dépendant finement de la structure électronique, ils constituent une base solide pouvant être combinée à d’autres familles de descripteurs et à des jeux de données plus vastes. Pour un public non spécialiste, la leçon est que des outils mathématiques intelligents appliqués aux plans moléculaires peuvent aider à filtrer et optimiser les futurs antibiotiques, accélérant potentiellement la recherche de médicaments capables de devancer la résistance bactérienne.
Citation: Yuvaraj, A., Kalaimurugan, G., Thamizhmaran, R. et al. Predictive modeling for physicochemical properties of \(\beta\)-lactam antibiotics through eigenvalue based topological indices and non linear regression techniques. Sci Rep 16, 9389 (2026). https://doi.org/10.1038/s41598-026-39436-0
Mots-clés: antibiotiques β-lactamines, modélisation QSPR, descripteurs de théorie des graphes, propriétés physico-chimiques, conception de médicaments