Clear Sky Science · fr
Intégration d’analyses multi-omiques identifie le gène lié aux lésions de l’ADN CLSPN comme biomarqueur dans le cancer gastrique
Pourquoi cette recherche est importante
Le cancer de l’estomac reste l’un des cancers les plus meurtriers au monde, en grande partie parce qu’il est souvent détecté tardivement et manque de signaux d’alerte précoces fiables. Cette étude explore en profondeur les « traces » génétiques laissées par les lésions de l’ADN et identifie un gène nommé CLSPN comme un marqueur prometteur susceptible d’aider les médecins à détecter plus tôt le cancer gastrique, à mieux estimer son agressivité et, potentiellement, à adapter les traitements avec plus de précision.
À la recherche de signaux de danger dans les tumeurs gastriques
Les chercheurs sont partis d’une idée simple : si les lésions de l’ADN contribuent au développement du cancer gastrique, alors les gènes impliqués dans la réponse à ces lésions pourraient contenir des indices importants sur qui développe la maladie et comment elle évolue. Pour tester cela, ils ont rassemblé plusieurs grands jeux de données. Ceux-ci comprenaient le séquençage ARN en masse, qui mesure l’activité génique moyenne dans des échantillons tumoraux complets ; le séquençage ARN en cellule unique, qui analyse des milliers de cellules individuellement ; et la transcriptomique spatiale, qui cartographie l’activité génique sur la coupe de tissu. Ils ont aussi compilé une longue liste de gènes déjà associés aux lésions de l’ADN. À partir de ces ressources, ils ont cherché quels gènes liés aux lésions de l’ADN étaient le plus fortement associés au cancer gastrique et à la survie des patients.
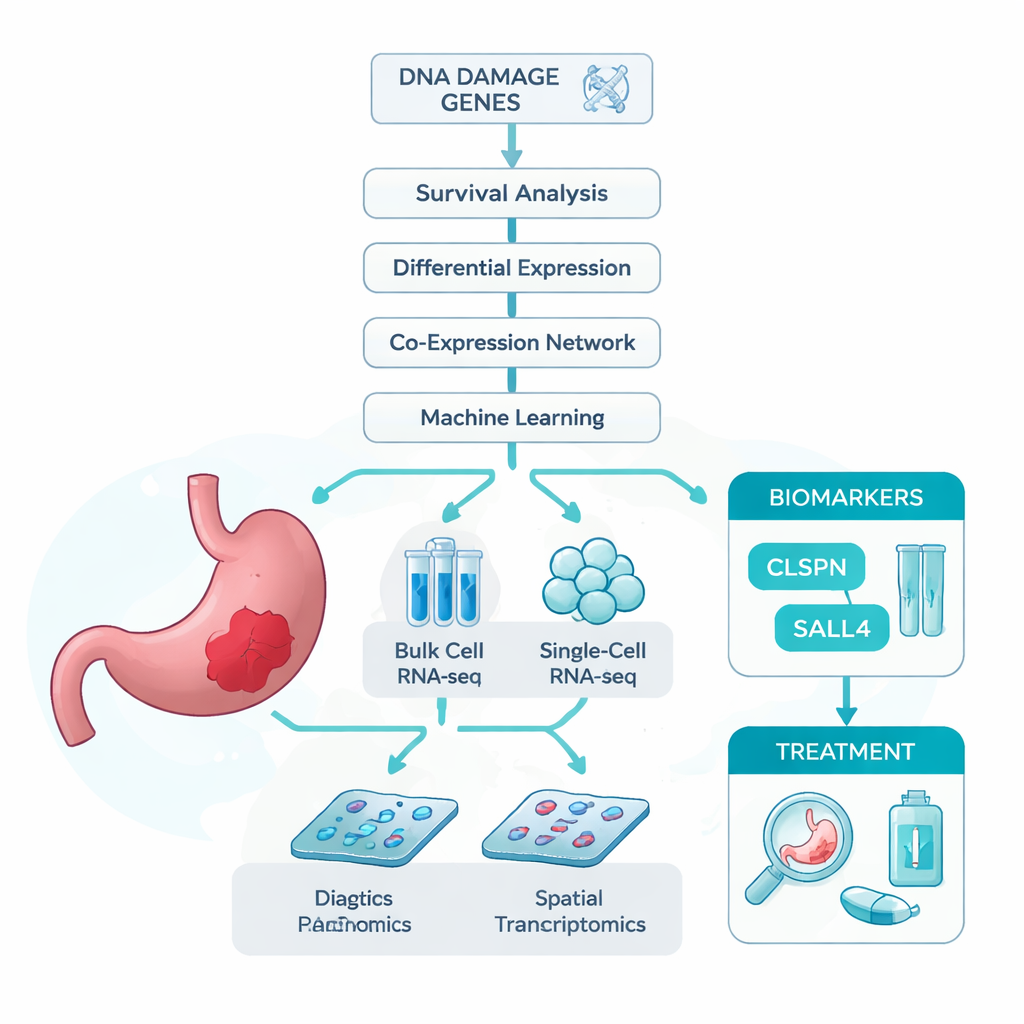
Utiliser des algorithmes intelligents pour trouver les gènes clés
Parce que des milliers de gènes sont altérés dans le cancer, l’équipe a eu recours à une panoplie d’outils statistiques et d’apprentissage automatique pour réduire le nombre de candidats. Ils ont d’abord filtré les gènes qui étaient à la fois dérégulés dans les tumeurs et clairement liés à la durée de survie des patients. Ils ont ensuite regroupé les gènes selon leurs profils d’expression corrélés, et recoupé ces groupes avec la liste des gènes liés aux lésions de l’ADN. Ce criblage en plusieurs étapes a produit 13 gènes candidats solides. Pour déterminer lesquels étaient les plus utiles pour distinguer tissu tumoral et tissu normal, ils ont entraîné sept modèles d’apprentissage automatique différents, chacun classant les gènes selon leur utilité pour la classification. Dans tous les modèles, deux gènes — CLSPN et SALL4 — sont systématiquement ressortis en tête, avec des taux de précision proches ou supérieurs à 97 % et des aires sous la courbe ROC supérieures à 0,96, ce qui suggère un excellent potentiel diagnostique.
Zoom sur CLSPN au sein de la tumeur
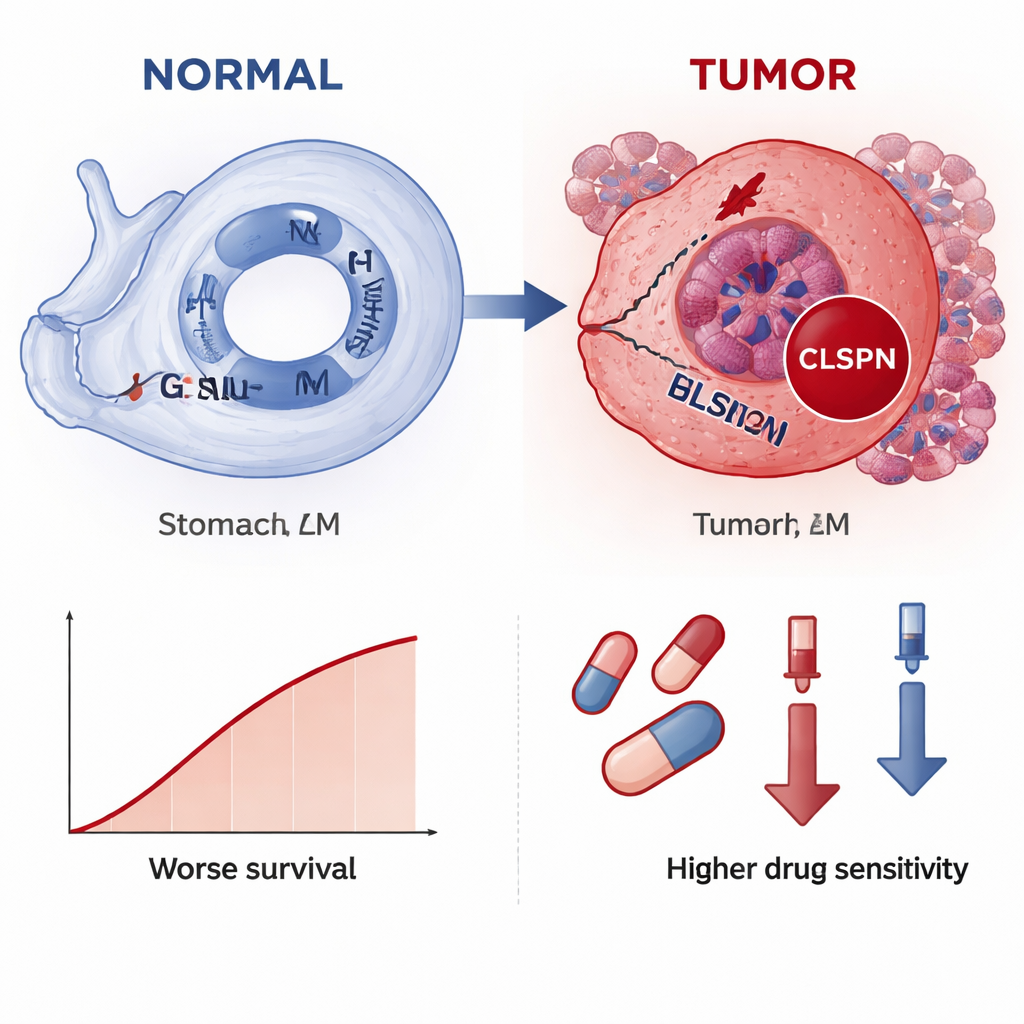
Parmi ces deux gènes principaux, CLSPN s’est distingué comme le plus informatif au global ; les auteurs l’ont donc examiné plus en détail. Dans des données en cellule unique portant sur plus de 30 000 cellules, CLSPN était beaucoup plus actif dans les cellules tumorales que dans les cellules normales voisines ou les cellules de soutien, ce qui indique un rôle spécifique à la tumeur. La cartographie spatiale des sections de tissu patient a montré un schéma similaire : l’expression de CLSPN s’est regroupée dans des régions que les pathologistes reconnaissaient comme cancéreuses. Lorsque l’équipe a divisé les cellules tumorales en groupes « CLSPN élevé » et « CLSPN faible », le groupe à haute expression montrait une activité plus importante dans des voies liées à la réplication de l’ADN, à la division cellulaire et à la réparation — des processus qui, lorsqu’ils sont hyperactifs ou mal régulés, peuvent alimenter une croissance incontrôlée. L’analyse en pseudotemps, qui reconstitue comment les cellules évoluent sur une chronologie notionnelle, a suggéré qu’au fur et à mesure de la progression des cellules tumorales, les niveaux de CLSPN tendent à augmenter, laissant penser que la surexpression de CLSPN pourrait participer à la transition vers un état plus malin.
Liens avec le système immunitaire et la réponse au traitement
L’étude a également exploré comment CLSPN se rapporte à l’environnement tumoral et aux traitements potentiels. Les tumeurs à expression élevée de CLSPN présentaient des compositions différentes de cellules immunitaires, en particulier des macrophages et certains lymphocytes T et NK, ce qui suggère que CLSPN pourrait contribuer à façonner un microenvironnement immunosuppresseur. La modélisation de la sensibilité aux médicaments a indiqué que les cancers exprimant davantage CLSPN pourraient être plus vulnérables à plusieurs agents chimiothérapeutiques et thérapies ciblées, puisque des niveaux plus élevés de CLSPN étaient associés à des doses prédites plus faibles nécessaires pour inhiber la croissance. De façon importante, lorsque les auteurs ont coloré de vrais échantillons de tissu provenant de 70 patients, les niveaux protéiques de CLSPN étaient clairement plus élevés dans le cancer que dans l’estomac normal et étaient associés à des tumeurs plus volumineuses, une invasion plus profonde, une atteinte ganglionnaire et une survie globale réduite.
Ce que cela pourrait signifier pour les patients
Concrètement, l’étude suggère que CLSPN se comporte comme un témoin d’alerte pour le cancer gastrique : il s’exprime principalement dans les cellules tumorales, s’intensifie dans les maladies plus avancées et signale un risque accru de mauvais pronostic. Comme il peut être détecté à la fois au niveau de l’ARN et par des méthodes d’immunohistochimie standard en milieu hospitalier, CLSPN pourrait devenir un biomarqueur pratique pour aider les pathologistes à confirmer le cancer gastrique, à stratifier les patients selon le risque et peut‑être à orienter le choix des médicaments. Bien que des validations cliniques supplémentaires soient nécessaires avant une utilisation de routine, ce travail illustre comment l’analyse combinée des empreintes des lésions de l’ADN sur de multiples couches de données peut révéler de nouveaux outils pour un diagnostic plus précoce et des traitements plus personnalisés du cancer gastrique.
Citation: Ma, Q., Yang, X., Sun, N. et al. Integrating multi-omics analysis identifies DNA damage-related gene CLSPN as a biomarker in gastric cancer. Sci Rep 16, 7789 (2026). https://doi.org/10.1038/s41598-026-39387-6
Mots-clés: cancer gastrique, lésions de l’ADN, CLSPN, biomarqueur, analyse en cellule unique