Clear Sky Science · fr
Nouveaux gènes marqueurs pour la détection simultanée de Salmonella, EHEC O157:H7 et Cronobacter
Pourquoi cela compte pour la sécurité alimentaire au quotidien
Des salades aux hamburgers en passant par les préparations pour nourrissons, les aliments auxquels nous faisons confiance peuvent parfois abriter des germes dangereux. Trois des coupables les plus préoccupants — certains types d’E. coli, Salmonella et une bactérie moins connue appelée Cronobacter — peuvent provoquer des maladies graves, en particulier chez les jeunes enfants et les adultes vulnérables. Cette étude montre comment des scientifiques exploitent d’énormes bases de données d’ADN et des tests de laboratoire ingénieux pour repérer ces trois menaces à la fois, rapidement et avec précision, avant que des aliments contaminés n’atteignent votre table.
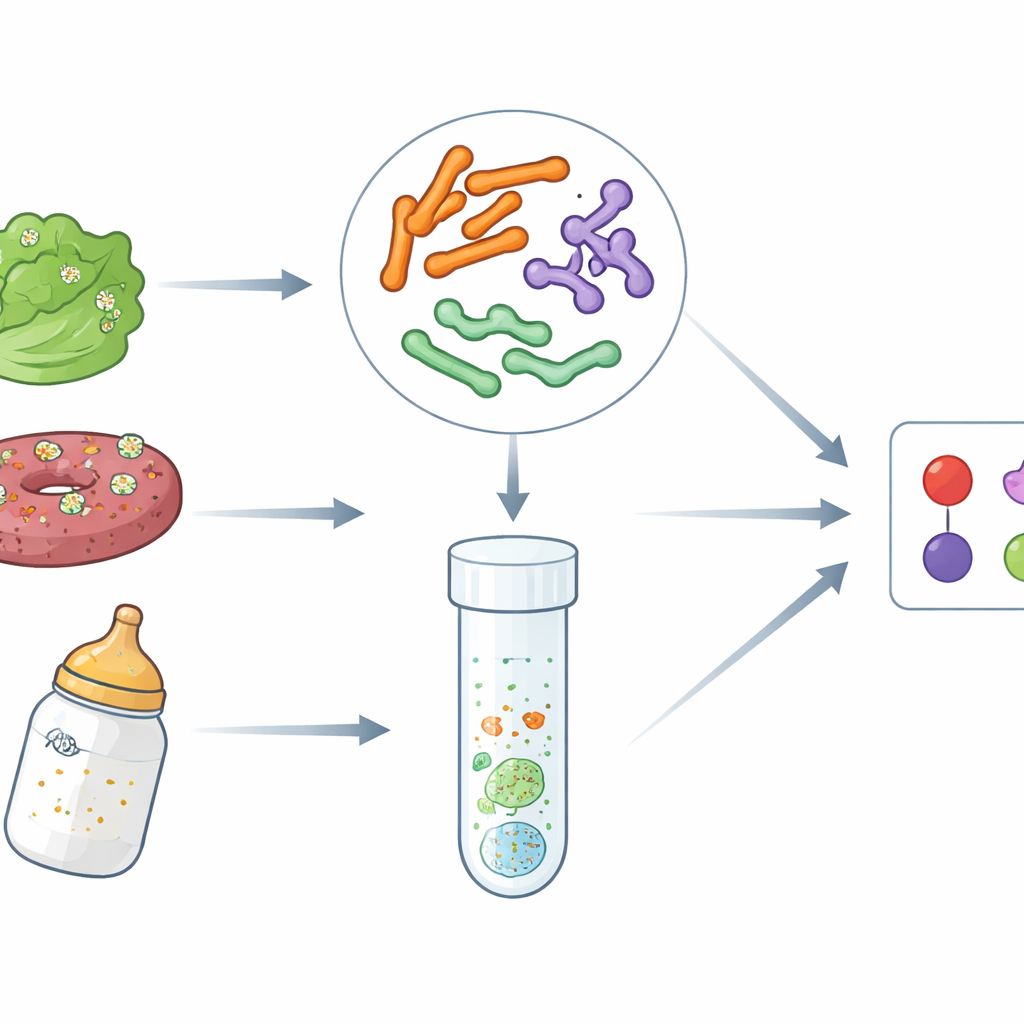
Dangers cachés dans des aliments courants
Les maladies d’origine alimentaire ont augmenté au cours de la dernière décennie, en partie à cause des chaînes d’approvisionnement mondiales et du volume croissant d’aliments transformés et prêts à consommer. L’EHEC O157:H7, une forme hautement toxique d’E. coli, peut provoquer des diarrhées sanglantes et une insuffisance rénale. Salmonella cause chaque année des millions de cas d’intoxication alimentaire, et Cronobacter, bien que moins connu, peut être mortel chez les nouveau-nés, notamment en lien avec les préparations infantiles en poudre. Les méthodes de laboratoire traditionnelles se concentrent souvent sur un germe à la fois et nécessitent des jours de culture, ce qui ralentit les enquêtes sur les éclosions et le contrôle de routine. Les auteurs ont voulu mettre au point des tests ADN plus rapides capables de signaler ces trois agents pathogènes ensemble dans une procédure unique et simplifiée.
Trouver des « codes-barres » dans un océan d’ADN
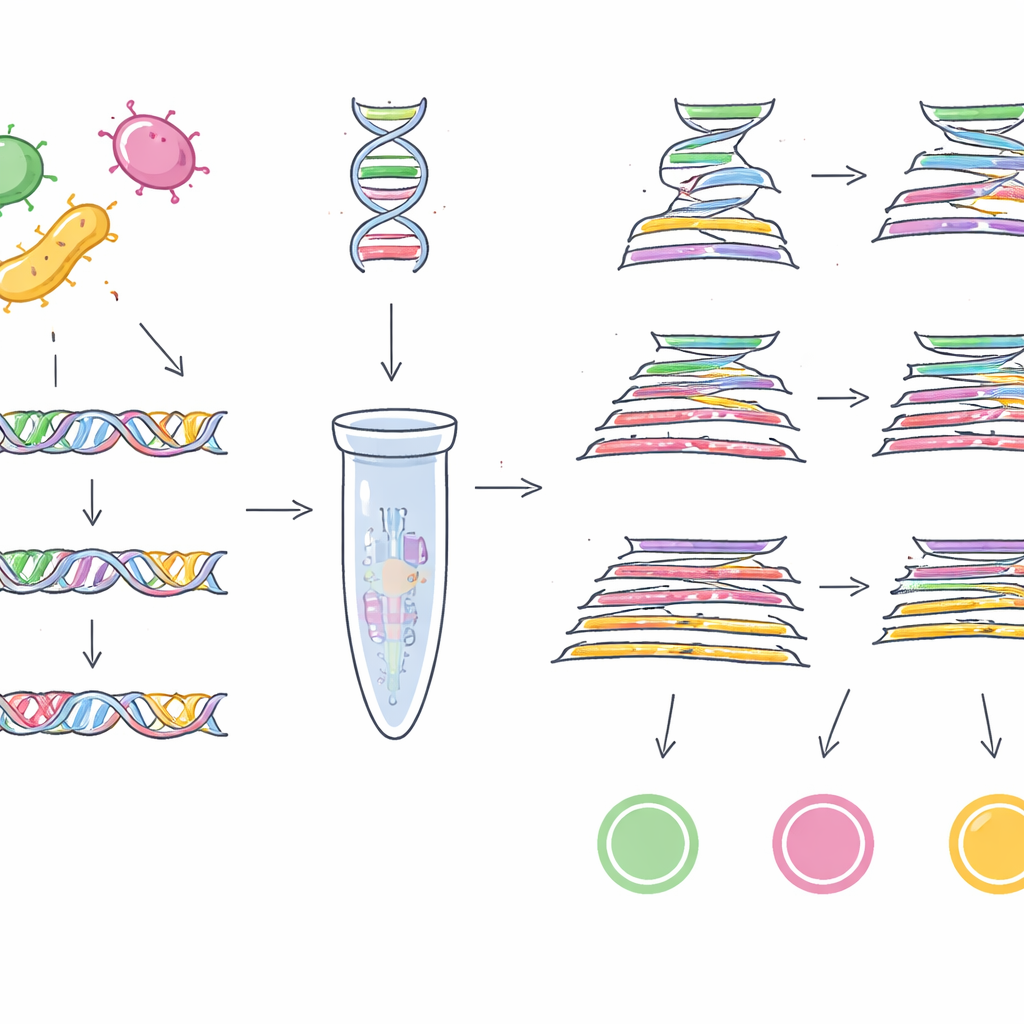
Pour cela, l’équipe avait d’abord besoin de « codes-barres » génétiques fiables — de courts segments d’ADN présents dans presque toutes les souches d’un germe cible mais absents des autres. Plutôt que d’examiner une poignée de génomes, ils ont puisé dans une vaste collection publique de 1,46 million de génomes bactériens issus de 50 genres différents. Pour l’EHEC O157:H7, ils ont comparé des milliers de génomes d’E. coli et parcouru plus de 100 000 familles de gènes accessoires pour trouver des séquences d’ADN uniques à ce sous-type dangereux. Après plusieurs étapes de filtrage et de vérifications croisées contre plus d’un million de génomes non-E. coli, ils ont retenu un gène nommé z0340 comme marqueur hautement spécifique de l’EHEC O157:H7. En appliquant une stratégie similaire à plus d’un demi-million de génomes de Salmonella et à près d’un million d’autres génomes bactériens, ils ont identifié un autre gène, sbcC, comme marqueur fiable pour le groupe Salmonella dans son ensemble.
Transformer les marqueurs en tests opérationnels
Avec ces deux nouveaux codes-barres — ainsi qu’un gène spécifique de Cronobacter, ygcB, que le groupe avait découvert précédemment — les chercheurs ont conçu des tests de laboratoire capables de détecter les trois pathogènes en une seule fois. Ils ont mis au point des essais PCR multiplex, qui fonctionnent comme des photocopieuses moléculaires ciblant des segments d’ADN précis, et une version TaqMan qPCR plus sensible qui mesure en temps réel la quantité d’ADN cible présente. Lorsque ces tests ont été soumis à l’épreuve de 23 souches des trois agents pathogènes et de 100 souches d’autres bactéries courantes, ils n’ont détecté que les cibles attendues à chaque fois, montrant une spécificité de 100 %. La PCR multiplex de base pouvait détecter jusqu’à 1 picogramme d’ADN par microlitre, tandis que la version TaqMan descendait jusqu’à 0,5 picogramme, indiquant une grande sensibilité.
Mettre les méthodes à l’épreuve des aliments
La précision en laboratoire n’est utile que si les tests fonctionnent sur des échantillons réels et complexes. Pour vérifier cela, les scientifiques ont contaminé délibérément de la salade, du bœuf haché et des préparations infantiles en poudre avec des quantités connues d’EHEC O157:H7, de Salmonella ou de Cronobacter. Après des étapes d’enrichissement standard pour permettre la multiplication des bactéries présentes, ils ont appliqué leurs essais PCR multiplex et TaqMan qPCR. Dans tous les cas, les méthodes ont correctement détecté l’agent pathogène introduit et n’ont pas produit de faux positifs dans les témoins négatifs. Les performances étaient cohérentes sur les trois types d’aliments, ce qui suggère que les graisses, les composants végétaux ou les ingrédients complexes n’ont pas significativement entravé la détection.
Limites et améliorations futures
Malgré les résultats solides, les auteurs soulignent que leur panel de validation représente encore une infime partie de la diversité microbienne présente dans la nature. Par exemple, ils n’ont testé en laboratoire qu’une seule souche d’EHEC O157:H7, alors que leur criblage basé sur les génomes couvrait des dizaines de milliers de telles souches. Ils ont également travaillé avec des niveaux de contamination relativement élevés comparés aux très faibles nombres de bactéries qui peuvent néanmoins provoquer des maladies. Les travaux futurs devront tester beaucoup plus d’isolats issus du monde réel, examiner des aliments naturellement contaminés et ajouter des contrôles internes pour se prémunir contre des substances alimentaires susceptibles d’inhiber l’amplification de l’ADN.
Ce que cela signifie pour les consommateurs
Concrètement, cette étude montre que des codes-barres ADN soigneusement choisis permettent aux laboratoires de sécurité alimentaire de dépister simultanément plusieurs germes à haut risque, avec une grande précision et en moins de temps que les méthodes classiques fondées sur la culture. En exploitant des millions de génomes, les chercheurs ont identifié trois signatures génétiques — une pour l’EHEC O157:H7, une pour Salmonella et une pour Cronobacter — qui semblent à la fois très spécifiques et stables. Les tests qui en résultent pourraient renforcer la surveillance de routine d’aliments comme les salades, les viandes et les préparations pour nourrissons, détectant la contamination plus tôt et de façon plus fiable. Au-delà de ces trois agents pathogènes, la même approche axée sur les génomes pourrait servir à concevoir des tests rapides pour de nombreux autres microbes dangereux, offrant un nouvel outil puissant pour renforcer la sécurité de l’approvisionnement alimentaire mondial.
Citation: Zhang, H., Xiong, P., Lu, Z. et al. Novel marker genes for simultaneous detection of Salmonella, EHEC O157:H7, and Cronobacter. Sci Rep 16, 9362 (2026). https://doi.org/10.1038/s41598-026-38990-x
Mots-clés: agents pathogènes d’origine alimentaire, PCR multiplex, marqueurs génomiques, Salmonella et EHEC, détection de Cronobacter