Clear Sky Science · fr
Une étude pilote sur la cohérence des protocoles et la reproductibilité des métriques de graphe dans les connectomes pondérés par la microstructure
Pourquoi la cartographie des connexions cérébrales a besoin d’un contrôle de fiabilité
Médecins et chercheurs considèrent de plus en plus le cerveau comme une vaste carte de câblage, où des régions communiquent entre elles via des faisceaux de fibres nerveuses. De nouvelles méthodes fondées sur l’IRM transforment ce câblage en réseaux mathématiques susceptibles de révéler des signes précoces de maladies comme la sclérose en plaques ou la maladie d’Alzheimer. Mais avant que ces mesures puissent guider le diagnostic ou le traitement, il faut vérifier un point élémentaire : si l’on scanne à plusieurs reprises le même cerveau sain, ou sur différents appareils avec des réglages légèrement différents, obtient-on essentiellement le même réseau ?
Du mouvement de l’eau aux cartes des autoroutes cérébrales
Pour construire ces cartes de connexions, les auteurs utilisent une forme d’IRM qui suit le déplacement des molécules d’eau dans les tissus cérébraux. Dans la substance blanche, où de longues fibres nerveuses isolées courent ensemble, l’eau préfère se déplacer le long des fibres plutôt qu’à travers elles. En mesurant ce mouvement directionnel selon de nombreuses orientations, des algorithmes peuvent inférer des faisceaux de fibres et assembler un « connectome » – une matrice qui enregistre quelles régions de matière grise sont reliées par quels trajets de matière blanche. Plutôt que de se limiter à compter le nombre de fibres virtuelles reconstruites entre les régions, cette étude s’intéresse aux connectomes « pondérés par la microstructure », où chaque connexion est marquée par des propriétés tissulaires elles‑mêmes, comme l’ordre des fibres ou leur densité apparente.
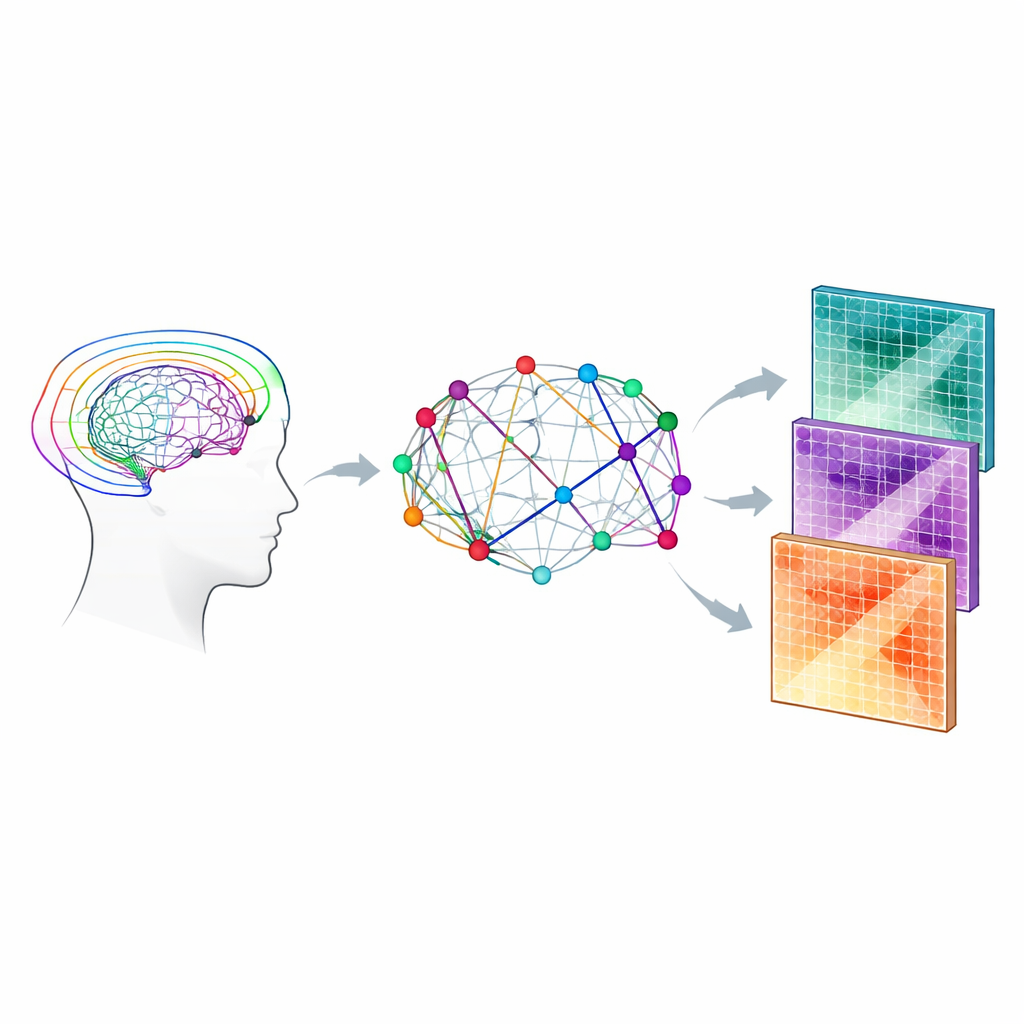
Ajouter du détail biologique au réseau
L’équipe a combiné deux familles de modèles qui interprètent le signal d’IRM de diffusion. Le premier, l’imagerie par tenseur de diffusion, résume à quel point le mouvement de l’eau est directionnel et la vitesse moyenne de diffusion. Le second, appelé Bingham‑NODDI, va plus loin en estimant quelle part de chaque petit volume de tissu est occupée par de l’eau à l’intérieur des fibres nerveuses, à l’extérieur, ou dans des espaces remplis de liquide. En utilisant un protocole d’acquisition relativement riche à « quatre shells » conçu pour mieux capturer la géométrie complexe des fibres, ils ont calculé plusieurs paramètres microstructuraux, notamment l’anisotropie fractionnelle et la diffusivité moyenne (à partir du modèle tenseur) ainsi que les fractions de volume intra‑neurite et extra‑cellulaire (à partir de Bingham‑NODDI). Ces paramètres ont ensuite été propagés le long de chaque faisceau de fibres reconstruit et combinés pour attribuer un poids biologiquement informé à chaque connexion du réseau.
Tester la chaîne d’analyse
La fiabilité a été évaluée de trois manières complémentaires. D’abord, les chercheurs ont scanné à plusieurs reprises un fantôme physique soigneusement conçu – un enchevêtrement de fibres synthétiques dans de l’eau salée qui imite des caractéristiques clés du tissu cérébral – afin de tester la stabilité des paramètres sur de courtes périodes. Ensuite, ils ont scanné quatre volontaires sains dans deux hôpitaux, en utilisant la même marque et le même modèle d’appareil ainsi que les mêmes réglages, pour sonder les différences inter‑sites. Enfin, ils ont comparé le protocole à quatre shells à un protocole plus court et plus conventionnel à deux shells, pour vérifier si les deux fournissaient des valeurs de paramètres similaires. Pour les données cérébrales, ils ont reconstruit plusieurs versions du connectome pondérées par différents paramètres et extrait des mesures de graphe telles que l’efficacité globale du réseau, le degré de regroupement des connexions et la force de connexion moyenne de chaque région avec le reste du cerveau. Ils ont ensuite mesuré dans quelle mesure ces mesures variaient d’un site à l’autre et dans quelle proportion la variation reflétait de réelles différences entre individus plutôt que du bruit de mesure.
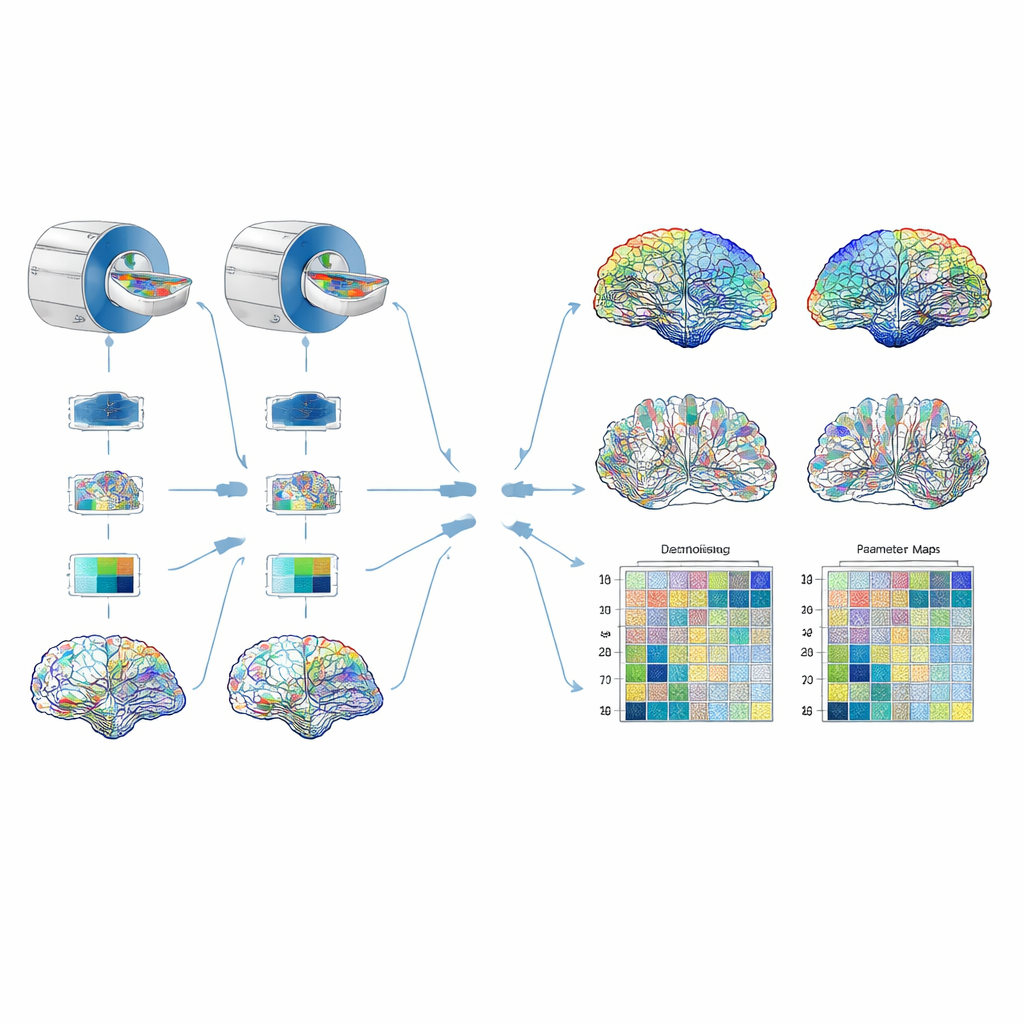
Ce qui s’est avéré digne de confiance
Plusieurs mesures tissulaires clés se sont révélées remarquablement cohérentes. L’anisotropie fractionnelle, la diffusivité moyenne et les fractions de volume intra‑neurite et intra‑cellulaire variaient de moins de cinq pour cent entre scans répétés, entre sites et (pour la plupart des régions) entre les protocoles à deux et quatre shells. En revanche, les grandeurs décrivant la dispersion des orientations de fibres – et un paramètre connexe de « concentration » – se sont montrées plus erratiques et ont donc été exclues de la construction des réseaux. Lorsque les chercheurs ont construit des connectomes pondérés par les mesures les plus stables, de nombreuses propriétés du réseau, y compris la densité, l’efficacité globale, le coefficient moyen de clustering et la force moyenne des connexions, étaient reproductibles entre sites. Une exception notable fut la modularité, une mesure de la façon dont le réseau se compartimente en communautés distinctes ; elle s’est montrée plus sensible aux petites variations des poids sous‑jacents. Les connectomes pondérés par la fraction de volume extra‑cellulaire ont globalement donné les pires résultats, plusieurs mesures de graphe affichant un faible accord entre sites.
Pourquoi cela importe pour la santé cérébrale
Cette étude montre qu’il ne suffit pas de compter les fibres reconstruites pour chercher des marqueurs de maladie dans le câblage cérébral. En sélectionnant soigneusement des paramètres microstructuraux stables pour pondérer chaque connexion, les chercheurs peuvent construire des réseaux plus riches et biologiquement fondés dont les propriétés clés sont répétables entre appareils et protocoles. Dans les conditions testées, les connectomes pondérés par l’anisotropie fractionnelle, la diffusivité moyenne et la fraction de volume intra‑neurite semblaient suffisamment robustes pour que leurs statistiques de réseau de base puissent servir de biomarqueurs candidats dans des troubles qui altèrent la connectivité cérébrale. Parallèlement, le travail met en garde contre des mesures plus fragiles, telles que la modularité et certains indices microstructuraux avancés, qui devront être traitées avec prudence tant que des études multicentriques plus larges n’auront pas confirmé leur fiabilité.
Citation: Cavallo, M., Ricchi, M., Axford, A. et al. A pilot study on protocol consistency and graph metric reproducibility in microstructure-weighted connectomes. Sci Rep 16, 8288 (2026). https://doi.org/10.1038/s41598-026-38964-z
Mots-clés: connectivité cérébrale, IRM de diffusion, connectome, reproductibilité des réseaux, imagerie de la microstructure