Clear Sky Science · fr
Un nouveau réseau de neurones convolutionnel pour l’identification bactérienne sur des jeux de données de microscopie confocale
Pourquoi repérer les germes plus rapidement compte
Lorsque les médecins cherchent à déterminer quelles bactéries causent une infection, le temps est critique. Les tests de laboratoire traditionnels peuvent prendre de nombreuses heures, voire des jours, et exigent des experts hautement qualifiés pour examiner les images au microscope visuellement. Cette étude présente un nouveau système de vision par ordinateur, appelé CM-Net, capable de lire automatiquement des images microscopiques spécialisées et de distinguer rapidement deux bactéries courantes d’importance médicale, tout en reconnaissant si les cellules sont vivantes ou mortes. Le travail suggère une piste vers des diagnostics plus rapides et plus fiables qui pourraient un jour être utilisés dans les hôpitaux et les laboratoires de recherche du monde entier.
Transformer des germes fluorescents en images exploitables
Les chercheurs ont commencé par un outil d’imagerie puissant, la microscopie confocale à balayage laser. En termes simples, ce microscope utilise un laser focalisé et des colorants fluorescents pour faire apparaître les bactéries en différentes couleurs selon qu’elles sont vivantes ou mortes. Les cellules vivantes se manifestent en vert, tandis que les cellules mortes apparaissent en rouge. En balayant l’échantillon en couches très fines, le microscope reconstruit des images nettes et détaillées des bactéries sur des lames de verre. L’équipe a travaillé avec deux espèces bien connues, souvent responsables d’infections nosocomiales : la forme allongée Escherichia coli et la forme ronde Staphylococcus aureus. Ces images de haute qualité constituent la matière première que CM-Net doit apprendre à interpréter.
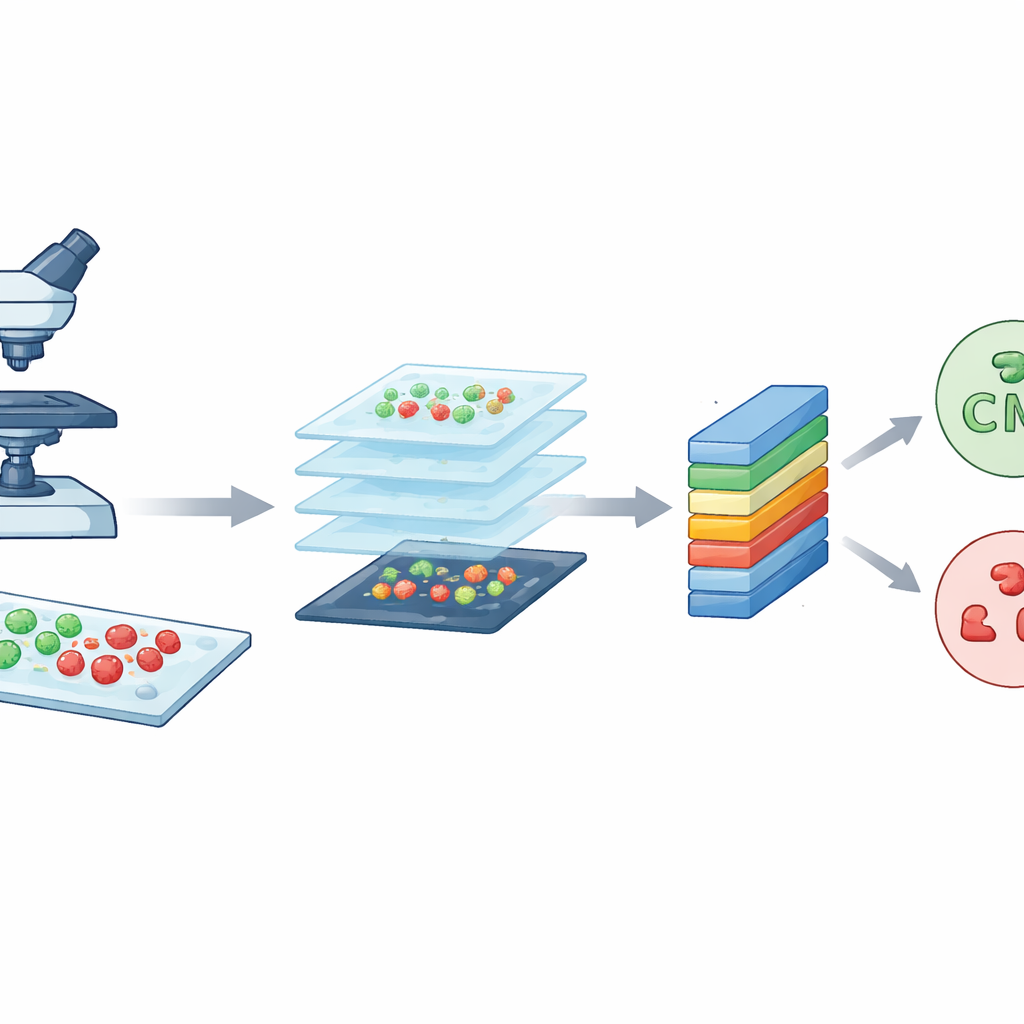
Découper les grandes images en nombreux petits carreaux
Bien que chaque image confocale soit riche en détails, elle est aussi très volumineuse, environ 3000 sur 3000 pixels. Entraîner un modèle informatique directement sur de telles images massives serait lent et demanderait une puissance de calcul excessive. Pour remédier à cela, l’équipe a découpé chaque grande image en de nombreux petits carreaux carrés, chacun de 224 sur 224 pixels, une taille standard en analyse d’images. Ce processus, assimilé à de l’augmentation de données, réduit à la fois la charge technique et multiplie le nombre d’exemples d’entraînement. À partir d’un jeu initial de 300 images par type bactérien, ils ont généré au total 7 066 carreaux. Ces extraits capturent des motifs locaux de formes, de couleurs et de textures issus de différentes régions des lames, offrant au modèle un ensemble d’exemples diversifié et équilibré pour l’apprentissage.
Comment l’observateur numérique apprend à voir
CM-Net est un modèle d’apprentissage profond soigneusement conçu spécifiquement pour la microscopie bactérienne, plutôt qu’une adaptation de collections photographiques générales. Il s’agit d’un type de réseau de neurones convolutionnel, une classe d’algorithmes particulièrement efficace pour détecter des motifs dans les images. CM-Net traite chaque carreau à travers une série d’étapes. Les premières couches recherchent des indices visuels simples comme des contours et des taches ; les couches profondes combinent ces éléments en motifs plus complexes qui permettent de distinguer les bâtonnets des sphères et les cellules vivantes des cellules mortes. Le réseau utilise des techniques telles que la normalisation par lots, qui maintient ses signaux internes stables, et une forme tronquée de sa fonction d’activation, qui prévient des réponses extrêmes pouvant déstabiliser l’apprentissage. Les couches finales condensent l’information extraite et prennent la décision finale sur le type bactérien et l’état cellulaire.
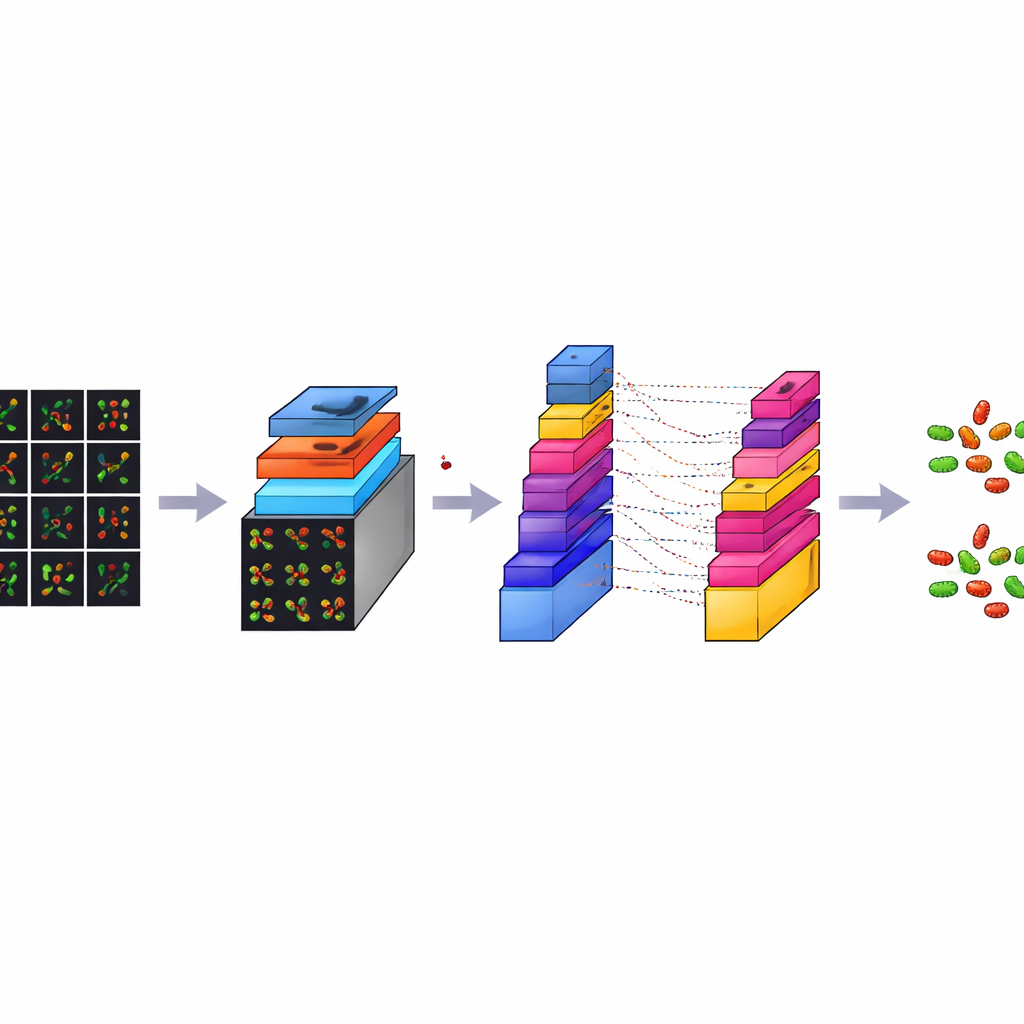
De meilleures performances que des modèles prêts à l’emploi populaires
Pour évaluer les performances de CM-Net, les auteurs l’ont entraîné et testé 30 fois, en procédant à chaque itération à une nouvelle division des données en ensembles d’entraînement et de test. Ils ont mesuré l’exactitude (à quelle fréquence le modèle a raison en moyenne), la sensibilité (sa capacité à détecter chaque cible), la spécificité (sa capacité à éviter les faux positifs) et plusieurs autres scores standards. CM-Net a atteint environ 96 % d’exactitude en moyenne, avec une sensibilité et une spécificité également proches de 96 %, et un fort équilibre entre les deux classes. Il nécessitait aussi moins de paramètres internes et moins de mémoire que plusieurs modèles pré-entraînés largement utilisés, notamment GoogLeNet, MobileNetV2, ResNet18 et ShuffleNet, tout en étant plus rapide à l’exécution. Des outils de visualisation ont montré que CM-Net concentre son attention sur les corps bactériens eux‑mêmes dans les images, plutôt que sur des éléments de fond aléatoires, ce qui soutient l’idée qu’il apprend des indices biologiquement pertinents.
Ce que cela signifie pour le travail en laboratoire à l’avenir
Concrètement, l’étude montre qu’un système d’apprentissage profond conçu pour cet usage peut apprendre à « lire » des images microscopiques complexes de bactéries de façon précise, efficace et en accord avec les préoccupations des experts humains. Pour l’instant, CM-Net a été entraîné sur seulement deux espèces bactériennes et sur des données issues d’un seul type de microscope ; des travaux supplémentaires sont donc nécessaires avant qu’il puisse servir d’outil diagnostique général. Les auteurs prévoient de l’étendre à davantage d’espèces, à différents états cellulaires et à des jeux de données plus larges et plus variés. Néanmoins, les résultats suggèrent que des systèmes comme CM-Net pourraient à terme aider les laboratoires à identifier les infections plus rapidement, orienter les décisions thérapeutiques et rendre l’analyse automatisée d’expériences de microbiologie accessible à des utilisateurs sans expertise spécifique en imagerie.
Citation: Al-Jumaili, A., Al-Jumaili, S., Alyassri, S. et al. Novel convolutional neural network for bacterial identification of confocal microscopic datasets. Sci Rep 16, 8123 (2026). https://doi.org/10.1038/s41598-026-38861-5
Mots-clés: classification d’images bactériennes, microscopie confocale, apprentissage profond, réseaux de neurones convolutionnels, diagnostic médical