Clear Sky Science · fr
Séquençage du génome de Bacillus daqingensis et d’Alkalicoccus luteus : éclairages taxonomiques et mécanismes d’adaptation
La vie dans les milieux salés
Des lacs salés aux sols alcalins, certains micro‑organismes prospèrent dans des conditions qui dessécheraient et tueraient la plupart des autres formes de vie. Cette étude explore l’ADN de deux de ces bactéries halophiles pour comprendre comment elles survivent en milieux extrêmes et pour préciser leur place réelle dans l’arbre du vivant. En comparant leurs génomes en détail, les chercheurs montrent que ce qui était considéré comme des espèces bactériennes distinctes correspond en réalité au même type d’organisme, et ils mettent au jour les astuces moléculaires que ces microbes utilisent pour faire face à un stress salin intense.
Pourquoi ces amateurs de sel comptent
Les bactéries au centre de cette recherche ont été initialement nommées Bacillus daqingensis et Alkalicoccus luteus. Les deux ont été isolées d’environnements salins et alcalins, comme des lacs sodiques et des sols salins, où la plupart des organismes peinent à vivre. Les scientifiques supposaient que Bacillus daqingensis pouvait en fait appartenir au genre Alkalicoccus, mais l’absence de son génome complet maintenait son statut officiel en suspens. En séquençant et en analysant les génomes complets de ces microbes et en les comparant à des espèces apparentées, les auteurs visaient à résoudre ce casse‑tête taxonomique tout en comprenant comment les membres du genre Alkalicoccus survivent dans des conditions si rudes.
Lire et comparer des génomes microbiaux
L’équipe a cultivé les bactéries en laboratoire, extrait leur ADN et l’a séquencé avec des méthodes à haut débit. Ils ont ensuite assemblé les millions de petits fragments d’ADN en cartes génomiques quasi‑complètes et vérifié leur qualité. Bacillus daqingensis et Alkalicoccus luteus se sont révélés avoir des génomes de taille similaire, d’environ 3,4 à 3,5 millions de paires de bases, avec un contenu génétique quasiment identique et une très grande complétude. Un marqueur génétique clé, le gène 16S rRNA, était essentiellement identique dans les deux organismes : une comparaison a montré 99,8 % d’identité par rapport à des mesures antérieures, et surtout les séquences 16S des deux souches étaient parfaitement identiques à 100 % entre elles.
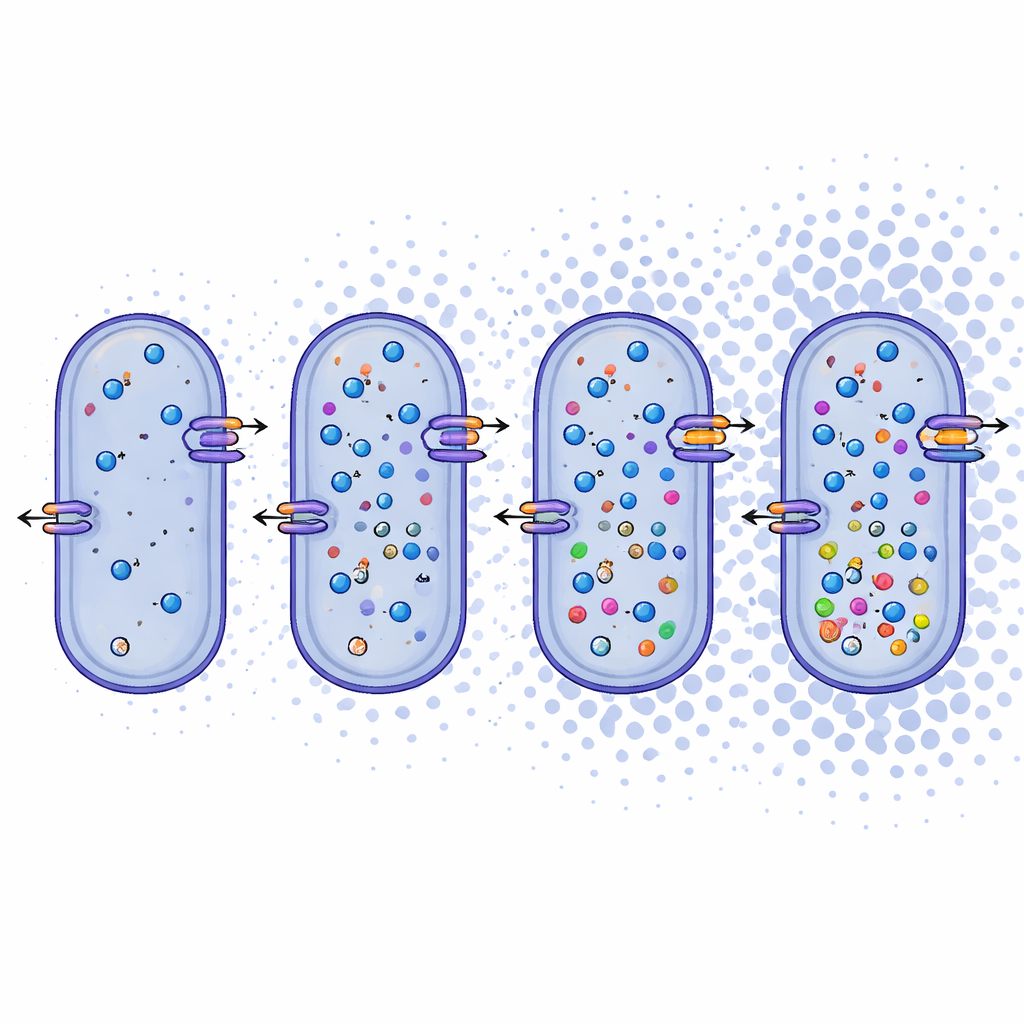
Décoder la survie face au sel et au stress
Au‑delà des noms, les chercheurs ont examiné ce que révèlent les génomes sur le mode de vie de ces microbes. Ils ont constaté que Bacillus daqingensis et toutes les espèces d’Alkalicoccus étudiées partagent des voies métaboliques centrales, y compris des routes classiques de dégradation des sucres et un cycle modifié appelé shunt glyoxylate qui aide à conserver le carbone en situation de stress. Plus frappant encore, les génomes portent un arsenel riche pour faire face à une forte salinité. Les bactéries semblent utiliser deux stratégies complémentaires : des systèmes « salt‑in » qui déplacent des ions inorganiques comme le sodium et le potassium à travers la membrane cellulaire, et des systèmes « salt‑out » qui synthétisent ou importent de petites molécules organiques — telles que la bétaïne, l’ectoine et certains acides aminés — qui jouent le rôle d’amortisseurs internes contre la déshydratation. Des gènes codant pour des transporteurs d’ions, des antiporteurs et la biosynthèse de ces solutés compatibles se retrouvent dans l’ensemble du genre, indiquant une réponse osmotique robuste et flexible.
Prouver qui est qui
Pour trancher la question taxonomique, les auteurs ont comparé les génomes entiers en utilisant plusieurs indicateurs numériques désormais standard en systématique microbienne. L’identité moyenne des nucléotides (ANI) mesure la similarité des séquences d’ADN sur l’ensemble du génome, tandis que l’identité moyenne des acides aminés (AAI) fait de même au niveau des protéines. Entre Bacillus daqingensis et Alkalicoccus luteus, l’ANI a atteint 98,2 % et l’AAI 98,5 % — bien au‑dessus des seuils habituels définissant une même espèce voire un même genre. Des arbres phylogénétiques construits à partir de nombreux gènes, ainsi que des comparaisons de clusters protéiques partagés, montrent que ces deux souches forment un groupe serré et partagent plus de clusters géniques entre elles qu’avec toute autre espèce d’Alkalicoccus. Des caractères traditionnels tels que la morphologie cellulaire, les profils d’acides gras et les réactions biochimiques clés étaient également essentiellement identiques entre elles.
Ce que cela change pour les noms microbiens
En regroupant toutes les lignes de preuve, l’étude conclut que Bacillus daqingensis ne représente pas un type distinct de bactérie. Il appartient plutôt au genre Alkalicoccus et est la même espèce qu’Alkalicoccus luteus, précédemment connu sous le nom de Bacillus luteus. Les auteurs proposent formellement la nouvelle combinaison Alkalicoccus daqingensis et traitent ce nom, ainsi que l’ancien nom Bacillus, comme des synonymes postérieurs de Bacillus luteus/Alkalicoccus luteus. Pour les non spécialistes, l’essentiel est que le séquençage génomique soigné peut révéler quand des étiquettes différentes sont appliquées au même microbe, ce qui aide à clarifier le système de nomenclature. Parallèlement, le travail met en évidence comment ces bactéries halophiles s’appuient sur un mélange de pompes à ions et de molécules protectrices pour survivre dans des environnements autrement trop salés pour la vie.
Citation: Narsing Rao, M.P., Wang, Kk., Zhu, Ky. et al. Genome sequencing of Bacillus daqingensis and Alkalicoccus luteus reveals taxonomic insights and adaptive mechanisms. Sci Rep 16, 9720 (2026). https://doi.org/10.1038/s41598-026-38640-2
Mots-clés: bactéries halophiles, séquençage du génome, taxonomie microbienne, adaptation au stress salin, Alkalicoccus luteus