Clear Sky Science · fr
Enregistrement non rigide automatisé et robuste d'images microscopiques en coupes sériées avec PiCNoR
Voir les tissus en 3D sans perdre les détails
La biologie moderne s'appuie souvent sur la reconstitution de coupes fines de tissu en vues 3D complètes d'organes et de cerveaux. Mais lorsque chaque coupe microscopique est découpée, colorée et imagée, elle peut s'étirer, se déchirer ou se déplacer. Si ces coupes ne sont pas correctement alignées, l'image 3D résultante peut être trompeuse. Cet article présente une nouvelle méthode informatique appelée PiCNoR qui aide les scientifiques à aligner ces images de manière plus précise et automatique, de sorte que les structures fines des embryons et des cerveaux soient préservées dans les reconstructions 3D.
Pourquoi l'alignement des coupes est si difficile
Pour construire une vue 3D, les chercheurs imagent de longues séries de sections ultra-fines prélevées dans le même morceau de tissu. En théorie, chaque coupe devrait s'empiler parfaitement sur la précédente, comme des cartes dans un paquet bien rangé. En réalité, chaque coupe peut se déformer différemment lors de la découpe et de la coloration. Les couleurs peuvent varier, des zones peuvent s'étirer et des motifs peuvent se déplacer. Les méthodes « rigides » traditionnelles supposent que chaque coupe ne subit que des translations ou des rotations, ce qui est souvent insuffisant. Des méthodes plus flexibles, « élastiques », existent, mais elles peuvent être lentes, nécessiter un réglage fin par des experts, ou dépendre fortement de la luminosité des images, qui peut varier d'une coupe à l'autre.
Une nouvelle approche : des pièces locales qui agissent ensemble
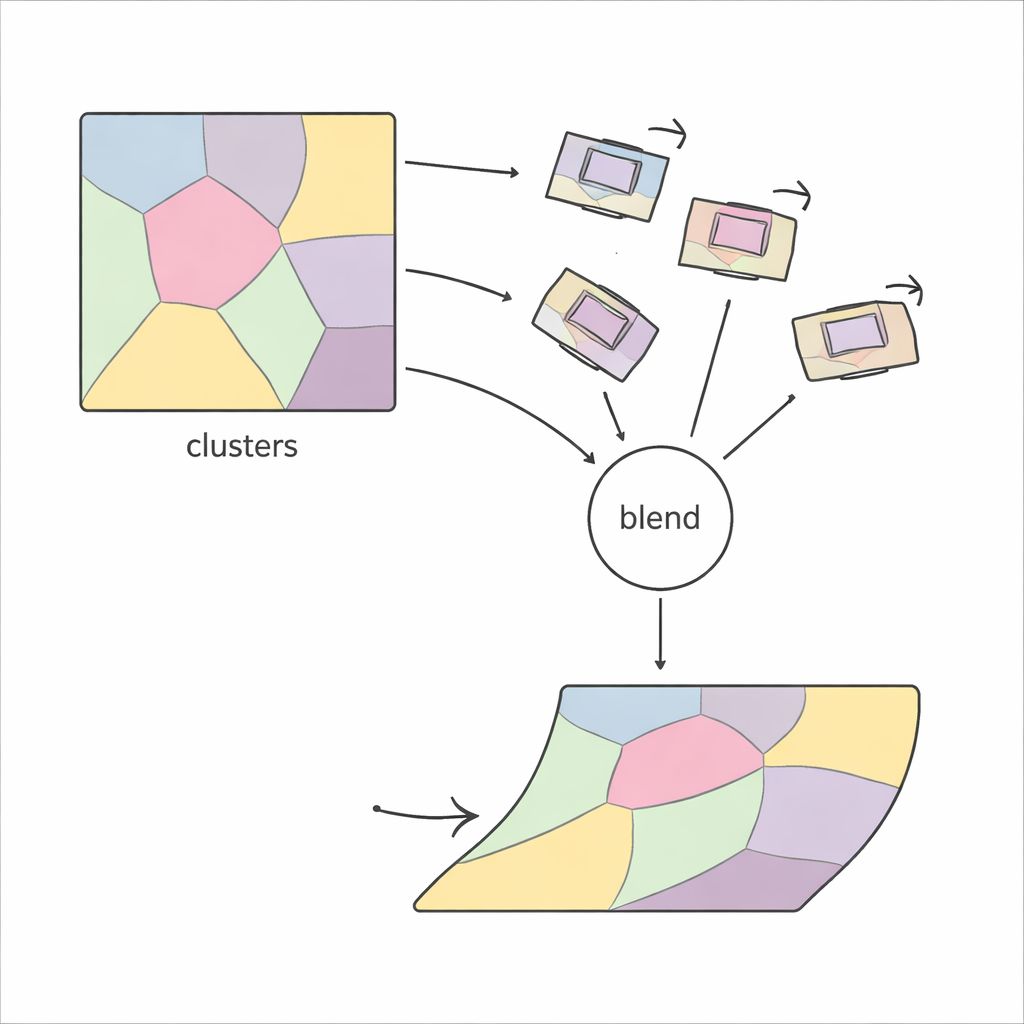
PiCNoR adopte une vision différente, plus locale, du problème. Plutôt que d'essayer de déformer une image entière d'un coup, il divise d'abord chaque coupe en de nombreuses régions en se basant sur le motif des caractéristiques de l'image. Dans chaque région, la méthode repère des points correspondants entre deux coupes voisines à l'aide de détecteurs de caractéristiques robustes, puis estime comment cette région doit se déplacer et tourner pour s'aligner. Ces mouvements locaux sont ensuite vérifiés pour leur plausibilité et combinés en douceur, de sorte que chaque pixel de la coupe reçoit un mouvement qui fusionne harmonieusement les informations des régions alentours. Le résultat est un alignement flexible, « non rigide », qui reste contrôlé et réaliste.
Laisser les données choisir la bonne complexité
Un défi clé des méthodes basées sur les régions est de décider combien de régions utiliser : trop peu et la méthode ne corrigera pas les déformations fines ; trop nombreuses et elle devient instable et lente. Les approches précédentes reposaient souvent sur des essais-erreurs, en vérifiant visuellement la qualité du résultat. PiCNoR évite ce réglage manuel en utilisant un outil statistique appelé critère d'information bayésien, qui équilibre automatiquement le niveau de détail et le risque de surapprentissage. Concrètement, cela signifie que l'algorithme peut décider par lui-même du nombre de régions nécessaires pour un jeu de données donné, sans supervision humaine, ce qui fait gagner du temps et réduit les biais.
Maintenir la fiabilité et l'efficacité des résultats
Tous les mouvements locaux estimés ne sont pas fiables : certains peuvent être déformés par le bruit ou de mauvaises correspondances. PiCNoR traite cela en représentant chaque région comme un nœud d'un graphe, où les régions voisines s'influencent mutuellement. Les mouvements qui paraissent irréalistes en termes de rotation ou de translation sont remplacés par une moyenne pondérée des mouvements plus fiables des régions voisines. Une représentation mathématique compacte permet de combiner ces mouvements efficacement. Enfin, le déplacement de chaque pixel est calculé comme une combinaison pondérée probabiliste des mouvements régionaux, garantissant que les transitions entre régions restent lisses, sans cassures ni plis abrupts dans le tissu.
Démonstration sur des données biologiques réelles
Les chercheurs ont testé PiCNoR sur trois jeux de données très différents : des sections d'embryons humains de la collection de Kyoto, une pile en microscopie électronique d'un cordon nerveux de drosophile, et une nouvelle pile en microscopie optique de l'hippocampe de rat. Sur ces exemples, PiCNoR a systématiquement produit un meilleur recouvrement entre les coupes que les méthodes rigides standard et de nombreuses méthodes non rigides courantes. Il a maintenu la continuité des structures délicates dans les vues 3D et évité les distorsions exagérées parfois observées avec d'autres outils. Fait important, il a réalisé cela en utilisant moins de régions locales que certains concurrents, et avec des coûts de calcul qui restent pratiques pour de grandes piles d'images.
Ce que cela signifie pour la microscopie 3D à venir
Pour les non-spécialistes, la conclusion est que PiCNoR offre une manière plus fiable de transformer des piles d'images microscopiques 2D en reconstructions 3D fidèles. En choisissant automatiquement le niveau de détail de l'alignement et en se protégeant contre les mauvaises corrections locales, il préserve les formes réelles des tissus tout en maintenant des temps de traitement raisonnables. Cela facilite la confiance des biologistes et des pathologistes dans ce qu'ils observent en 3D, qu'ils étudient le développement d'un embryon ou l'organisation des cellules cérébrales, et cela jette les bases d'analyses automatisées plus précises de jeux de données microscopiques complexes.
Citation: Adi, P.M., Shabani, H. & Mansouri, M. Automated and robust nonrigid registration of serial section microscopic images using PiCNoR. Sci Rep 16, 7559 (2026). https://doi.org/10.1038/s41598-026-38548-x
Mots-clés: microscopie 3D, enregistrement d'images, imagerie cérébrale, histologie, alignement non rigide