Clear Sky Science · fr
Profils du microbiote intestinal et du réservoir de résistance des expatriés suisses en Afrique révélés par la métagénomique Nanopore
Pourquoi vos microbes intestinaux changent quand vous vivez à l'étranger
De nombreuses personnes passent des mois ou des années à l'étranger, souvent dans des régions où les bactéries résistantes aux antibiotiques sont courantes. Cette étude pose une question simple mais importante : lorsque des expatriés suisses vivent dans des pays africains où le fardeau des infections multirésistantes est élevé, la communauté microbienne et les gènes de résistance présents dans leur intestin changent‑ils d'une manière qui pourrait affecter leur santé et la propagation de la résistance aux antimicrobiens ?
La communauté invisible en nous
Nos intestins hébergent des billions de microbes, principalement des bactéries, qui aident à digérer les aliments, entraînent le système immunitaire et empêchent les germes nuisibles de s'installer. À côté de ces microbes utiles se trouve le « résistome » : l'ensemble des gènes rendant les bactéries résistantes aux antibiotiques. Même des personnes en bonne santé portent de nombreux de ces gènes. Quand des individus déménagent ou voyagent dans des régions où les bactéries multirésistantes sont fréquentes, ils peuvent silencieusement acquérir de nouveaux gènes de résistance et les éléments d'ADN mobiles, appelés plasmides, qui les propagent. Comprendre comment cela se produit est essentiel pour maîtriser la résistance aux antibiotiques au niveau mondial.
Comparer les expatriés en Europe et en Afrique
Les chercheurs ont analysé des échantillons de selles provenant de 72 expatriés suisses en bonne santé de retour en Suisse : 39 avaient vécu dans des pays africains et 33 dans d'autres pays européens. Plutôt que de cultiver des bactéries en laboratoire, ils ont utilisé une technologie de séquençage à lectures longues appelée métagénomique shotgun Nanopore, qui lit tout le matériel génétique d'un échantillon en une seule fois. Cela leur a permis de cartographier quelles bactéries étaient présentes (le microbiote) et quels gènes de résistance et plasmides elles portaient (le résistome et le plasmidome). Chaque échantillon a été séquencé deux fois pour la fiabilité, et des logiciels sophistiqués ont servi à identifier les groupes bactériens et les gènes de résistance et à assembler de plus longs fragments de génome à partir de l'ADN mixte.
Surprenante stabilité du microbiote intestinal
Bien qu'un plus grand nombre de personnes du groupe Afrique aient été colonisées par des bactéries intestinales multirésistantes lors de tests antérieurs basés sur la culture, la composition globale de leur microbiote intestinal paraissait remarquablement similaire à celle des expatriés ayant vécu en Europe. Les mesures de diversité — combien de types différents de bactéries étaient présents et leur répartition — ne différaient pas selon le continent, et les analyses statistiques n'ont montré aucun regroupement net des échantillons Afrique versus Europe. Dans les deux groupes, des habitants intestinaux familiers tels que Blautia, Faecalibacterium et Bacteroides dominaient, ce qui suggère qu'une résidence prolongée à l'étranger ne bouleverse pas nécessairement la communauté bactérienne de base chez les adultes en bonne santé.
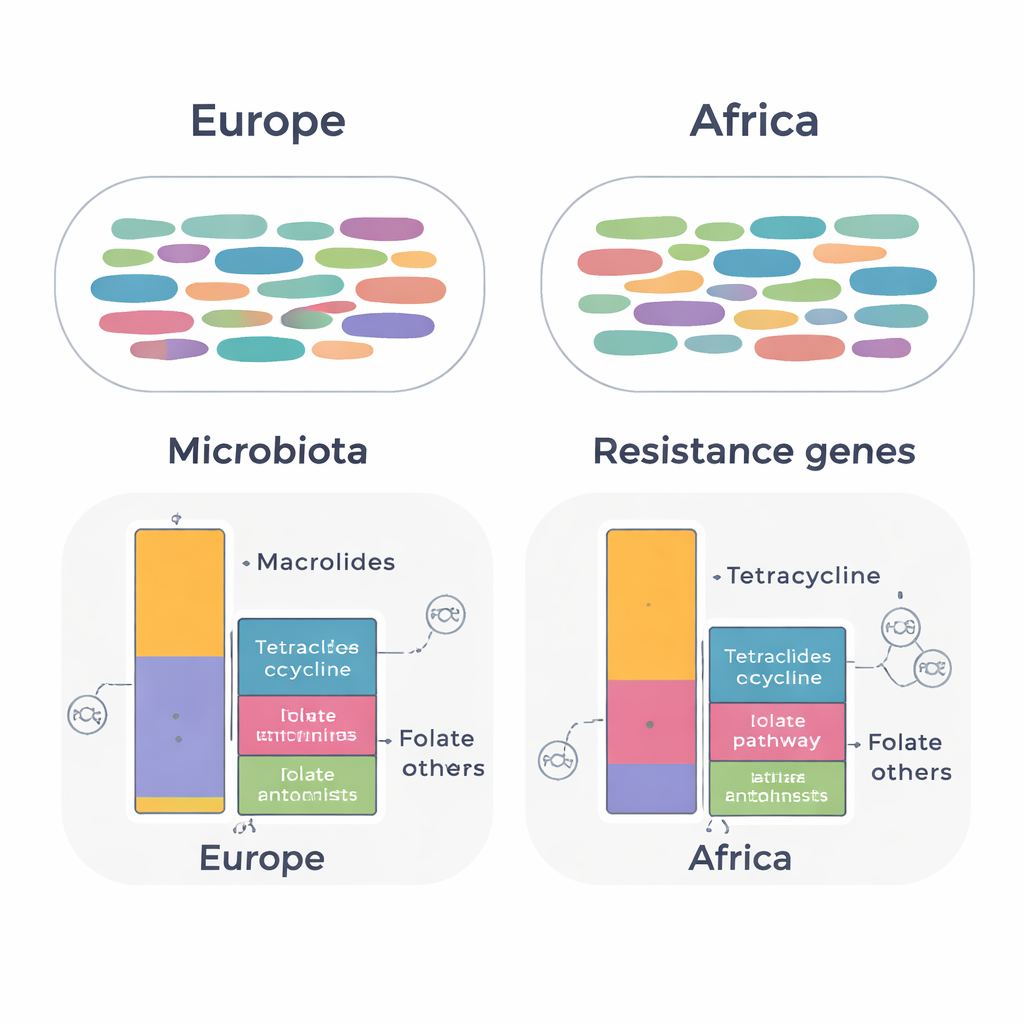
Les gènes de résistance et l'ADN mobile racontent une autre histoire
Quand l'équipe s'est concentrée sur les gènes de résistance, des différences plus subtiles mais importantes sont apparues. Sur l'ensemble des échantillons, ils ont trouvé 134 gènes de résistance distincts appartenant à 14 classes d'antibiotiques. Le profil global des gènes était largement similaire entre les continents, mais les expatriés ayant vécu en Afrique portaient des niveaux plus élevés de gènes protégeant les bactéries contre les tétracyclines et les médicaments ciblant la voie de l'acide folique (comme le triméthoprime‑sulfaméthoxazole). En revanche, les expatriés des pays européens présentaient des niveaux plus élevés de gènes conférant une résistance aux macrolides. Beaucoup de ces gènes étaient liés à des bactéries intestinales communes, notamment Ruminococcoides, Bifidobacterium et Bacteroides. Des gènes d'importance clinique, tels que blaCTX‑M‑15, capable d'inactiver des céphalosporines de dernier recours, ont été détectés chez Escherichia coli dans les deux groupes.
Les plasmides, navettes mondiales de la résistance
L'étude a aussi suivi les plasmides — de petits cercles d'ADN souvent transférables qui transportent des gènes de résistance entre bactéries et à travers les environnements. Grâce aux lectures longues, les chercheurs ont parfois pu observer des gènes de résistance et des marqueurs de « réplicon » plasmidique sur le même fragment d'ADN assemblé, confirmant qu'ils circulaient ensemble. Ils ont identifié 46 types de plasmides différents, certains propres à chaque continent et d'autres partagés. Notamment, certains plasmides portaient plusieurs gènes de résistance et ressemblaient à des plasmides connus provenant d'humains, d'animaux, d'aliments et d'eaux usées dans différentes régions du monde. Un type de plasmide, souvent associé à Enterococcus et retrouvé dans le poulet et les eaux usées, était plus fréquent dans les selles des expatriés en Afrique, ce qui souligne comment l'alimentation, les animaux et l'environnement peuvent tous contribuer à ce qui se retrouve dans notre intestin.
Ce que cela signifie pour le quotidien et la santé publique
Pour le lecteur non spécialiste, le message clé est que vivre dans une région à risque élevé ne paraît pas remodeler radicalement les bactéries intestinales que vous hébergez, mais peut modifier la composition des gènes de résistance et des éléments d'ADN mobile qui les propagent. Ces changements cachés, en partie façonnés par les usages locaux d'antibiotiques, peuvent avoir des conséquences pour de futures infections et pour la façon dont les caractères de résistance circulent entre personnes, animaux et environnement. Ce travail montre aussi que le séquençage portable à lectures longues peut servir d'outil d'alerte précoce, révélant comment gènes de résistance et plasmides circulent chez les voyageurs et expatriés sains avant qu'ils ne causent des maladies.
Citation: Campos-Madueno, E.I., Aldeia, C. & Endimiani, A. Gut microbiota and resistome profiles of Swiss expatriates in Africa revealed by Nanopore metagenomics. Sci Rep 16, 7016 (2026). https://doi.org/10.1038/s41598-026-38302-3
Mots-clés: microbiote intestinal, résistance aux antibiotiques, expatriés, plasmides, métagénomique