Clear Sky Science · fr
Classification du cancer par radiomique dans des modèles précliniques contrôlés
Lire le cancer à partir d’examens et du sang
Les soins modernes contre le cancer reposent de plus en plus sur des ordinateurs capables de fouiller les images médicales et les analyses de laboratoire à la recherche de motifs difficiles à percevoir pour l’œil humain. Cette étude pose une question simple mais importante : pour déterminer quel type de cancer un patient a, est‑il préférable d’extraire l’information cachée de ses images ou de son sang ? En utilisant des expériences soigneusement contrôlées chez la souris, les chercheurs ont comparé directement ces deux approches pour voir laquelle fournit des réponses plus fiables.
Ce que signifie une « biopsie virtuelle »
La radiomique est une méthode en plein essor qui considère chaque image médicale comme une source riche de données plutôt que comme une simple photo. Des logiciels spécialisés parcourent des images CT tridimensionnelles d’une tumeur et les convertissent en centaines de caractéristiques numériques décrivant sa forme, son intensité et sa texture fine. En principe, ces motifs pourraient refléter la biologie de la tumeur de manière analogue à une biopsie, mais sans aiguilles ni chirurgie — une « biopsie virtuelle ». Ses promoteurs espèrent que la radiomique aidera à classer les cancers, évaluer leur agressivité et orienter les choix thérapeutiques. Mais des préoccupations subsistent : les résultats peuvent être difficiles à reproduire, facilement confondus par des artefacts techniques et difficiles à interpréter pour les médecins.
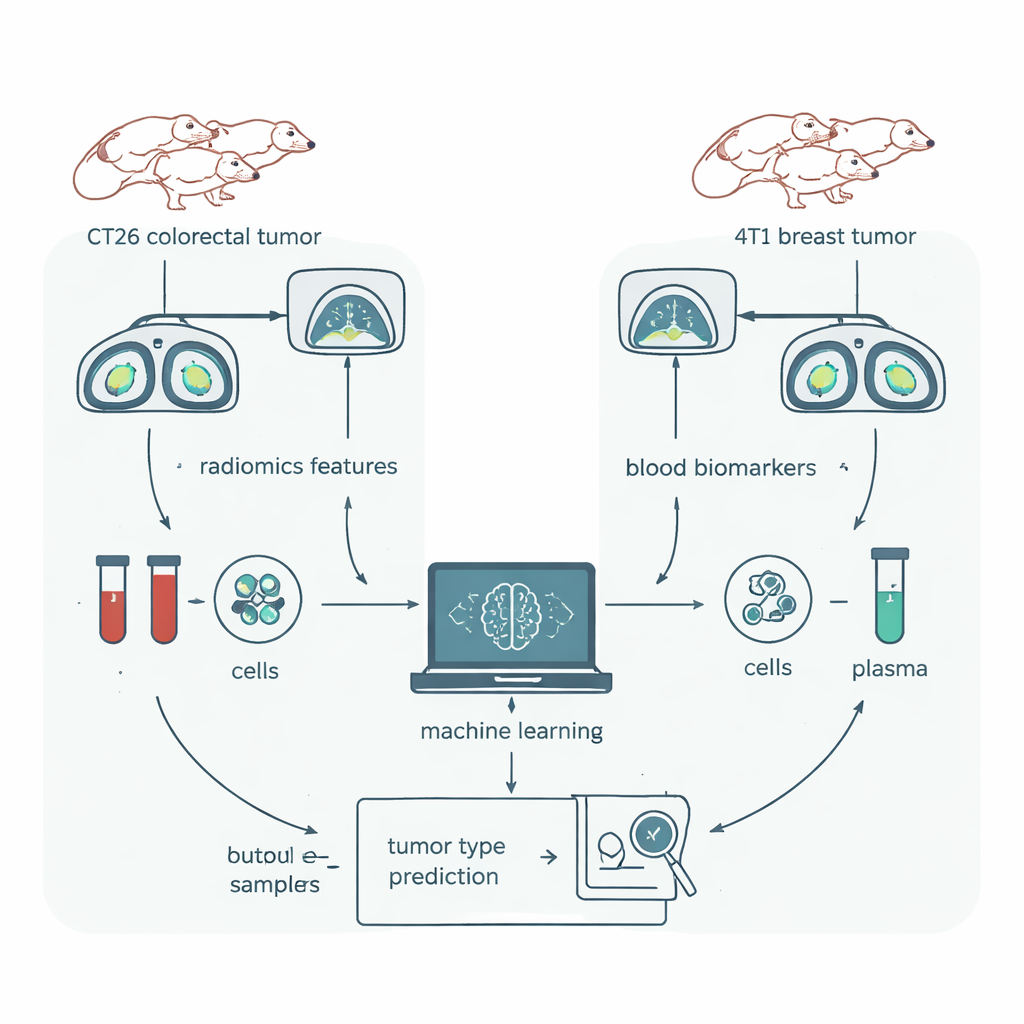
Un test direct et équitable chez la souris
Pour tester rigoureusement la radiomique, l’équipe a utilisé un modèle murin où presque tout pouvait être contrôlé. Des groupes de souris génétiquement identiques ont été implantés avec l’un des deux types de tumeurs : CT26, modèle de cancer colorectal, et 4T1, modèle de cancer du sein. Tous les animaux étaient de la même souche, du même sexe et d’un âge similaire, maintenus dans le même environnement et scannés sur le même appareil CT. Les tumeurs ont été soigneusement délimitées en 3D dans un logiciel, et un paquet de radiomique courant a extrait 1 409 caractéristiques numériques de chaque image. En parallèle, les chercheurs ont prélevé du sang chez les mêmes animaux et mesuré les types de cellules immunitaires et des dizaines de protéines — des biomarqueurs que leurs travaux antérieurs avaient déjà montré capables de distinguer presque parfaitement ces modèles tumoraux.
Compresser des milliers de détails d’image en un signal utile
La plupart des caractéristiques d’image brutes se sont révélées peu utiles : certaines variaient à peine d’une souris à l’autre, et beaucoup étaient presque redondantes. Après plusieurs étapes de filtrage statistique, il ne restait que 18 caractéristiques radiomiques non redondantes, décrivant principalement des motifs de texture subtils plutôt que la taille ou la forme simples. L’équipe a ensuite utilisé une méthode d’apprentissage automatique standard, Random Forest, pour mesurer dans quelle mesure ces caractéristiques d’image affinées pouvaient séparer les deux types tumoraux. Ils ont également utilisé des outils de visualisation pour vérifier si les données formaient naturellement des groupes séparés pour chaque type de cancer sans connaître les étiquettes à l’avance.
Les signaux sanguins surpassent les signaux d’imagerie
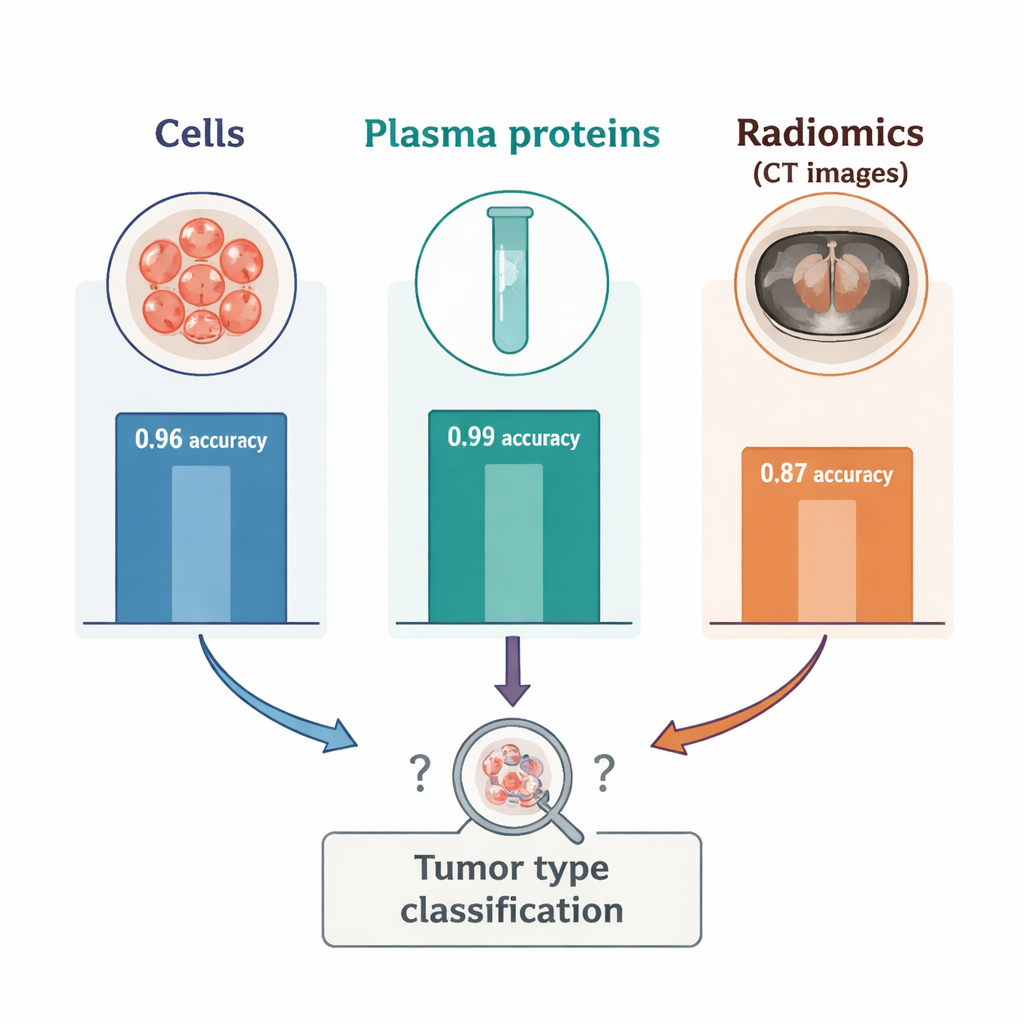
Le contraste entre le sang et l’imagerie fut saisissant. Lorsqu’ils ont réduit les données de cellules sanguines et de protéines plasmatiques en deux dimensions, les deux types tumoraux ont formé des groupes nettement séparés, confirmant que le sang capturait des signaux puissants et spécifiques à la tumeur. Dans les données radiomiques, en revanche, trois groupes mixtes sont apparus, chacun contenant un mélange des deux cancers, suggérant que d’autres facteurs inconnus influençaient les images. Dans les tests supervisés, la radiomique seule a classé le type tumoral avec une précision d’environ 87 % — bonne, mais sensiblement inférieure aux 96 % obtenus avec les décomptes de cellules immunitaires et aux 99 % obtenus avec les protéines plasmatiques. L’ajout de la radiomique aux marqueurs sanguins n’a pas amélioré la performance ; dans certaines combinaisons, cela a légèrement réduit la précision. Une expérience supplémentaire a montré que n’utiliser qu’une petite région sphérique à l’intérieur de la tumeur, au lieu de délimiter toute la masse, dégradait encore la performance de la radiomique, soulignant la sensibilité de ces caractéristiques à la façon dont la tumeur est tracée sur l’image.
Ce que cela signifie pour les tests du cancer à venir
Pour le lecteur non spécialiste, la conclusion est claire : si l’analyse d’images avancée peut fournir quelques indices utiles, dans cette étude elle a été surpassée par des tests sanguins relativement simples pour distinguer deux types de cancer. Même dans un contexte de laboratoire strictement contrôlé, avec des souris identiques et une imagerie standardisée, de petites différences techniques et la complexité du traitement d’image semblaient brouiller le signal radiomique. Les auteurs concluent que la radiomique n’est pas encore prête à servir de classifieur de cancer autonome et hautement fiable. Ils soutiennent plutôt qu’une meilleure standardisation de l’imagerie, des outils de contouring améliorés et des liens plus explicites entre les motifs d’image et la biologie sous‑jacente seront nécessaires avant que les biopsies virtuelles puissent guider de manière fiable les décisions cliniques aux côtés, ou à la place, des biomarqueurs sanguins bien établis.
Citation: Drover, K., Davis, D.A.S., Gosling, K. et al. Cancer classification with radiomics in controlled preclinical models. Sci Rep 16, 6647 (2026). https://doi.org/10.1038/s41598-026-37757-8
Mots-clés: radiomique, biomarqueurs du cancer, imagerie médicale, apprentissage automatique en oncologie, tests sanguins pour le cancer