Clear Sky Science · fr
Un cadre adaptatif à la structure du génome pour l’estimation de la consanguinité basée sur les ROH chez Penaeus vannamei
Pourquoi l’arbre généalogique des crevettes compte pour votre assiette
Les fermes de crevettes modernes fournissent une grande partie des produits de la mer consommés dans le monde, mais le fait d’élever répétitivement les mêmes lignées familiales peut affaiblir insidieusement leur santé. Lorsque des proches se reproduisent, des gènes délétères cachés peuvent se retrouver appariés, réduisant la croissance, la survie et la résistance aux maladies. Cette étude pose une question apparemment simple mais aux grandes implications pour l’aquaculture mondiale : comment mesurer la consanguinité des crevettes d’élevage avec une précision suffisante pour préserver des stocks sains et productifs ?
Empreintes génétiques cachées de la consanguinité
La consanguinité laisse des traces reconnaissables dans l’ADN. Plutôt que de porter deux versions légèrement différentes de nombreux gènes, les animaux consanguins présentent souvent de longs segments où les deux copies sont identiques. Les généticiens appellent ces segments « runs of homozygosity » (ROH). En additionnant la proportion du génome se trouvant dans ces runs, les chercheurs peuvent estimer le niveau de consanguinité d’un individu plus précisément que par les seuls fichiers de pedigree, souvent incomplets ou entachés d’erreurs. Cette mesure basée sur les ROH, dite FROH, est devenue une référence chez les bovins, les porcs et d’autres animaux d’élevage, mais les génomes de crevettes posent des défis particuliers rendant les méthodes standard peu fiables.
Pourquoi les génomes de crevettes sont particulièrement délicats
La crevette blanche (Penaeus vannamei), la crevette la plus élevée au monde, possède un génome très fragmenté et complexe. Plutôt que de longues séquences chromosomiques continues, de nombreuses cartes génomiques disponibles sont morcelées en milliers de petits fragments, séparés par des lacunes et des régions répétées. Les marqueurs génétiques y sont répartis de façon inégale et l’espèce présente une très forte diversité génétique. Les méthodes et paramètres logiciels conçus pour des génomes de mammifères bien cartographiés peuvent donc confondre des lacunes techniques avec de véritables ruptures des ROH, ou prendre de courtes similarités de fond pour de vrais signes de consanguinité. Le résultat est un risque élevé de mauvaise estimation du degré de consanguinité d’une crevette.
Construire une règle de mesure sensible à la structure du génome
Pour y remédier, les auteurs ont conçu un cadre « adaptatif à la structure du génome » qui ajuste l’analyse des ROH aux particularités de l’ADN de crevette. Ils ont créé treize familles de crevettes fortement consanguines par accouplements contrôlés, puis séquencé en profondeur le génome de cinq de ces familles ainsi que de leurs parents. De façon cruciale, ils ont aligné ces mêmes données de séquençage sur deux génomes de référence très différents : une ancienne assembly fragmentée et une version plus récente et hautement continue. En utilisant l’outil d’analyse courant PLINK, ils ont testé systématiquement comment huit paramètres clés influençaient les appels de ROH, en se concentrant sur trois paramètres particulièrement sensibles à la structure du génome : la densité minimale de marqueurs requise, la taille maximale d’un intervalle autorisé entre marqueurs à l’intérieur d’un run, et la longueur minimale d’un run pour qu’il soit pris en compte. Ils ont construit des fenêtres génomiques empiriques non chevauchantes pour suivre l’espacement local des marqueurs et les données manquantes, et ont utilisé la « couverture génomique » de ces fenêtres, ainsi que la stabilité de FROH et des longueurs de ROH, comme guides objectifs pour choisir des seuils pertinents.
Des réglages différents, la même image de consanguinité
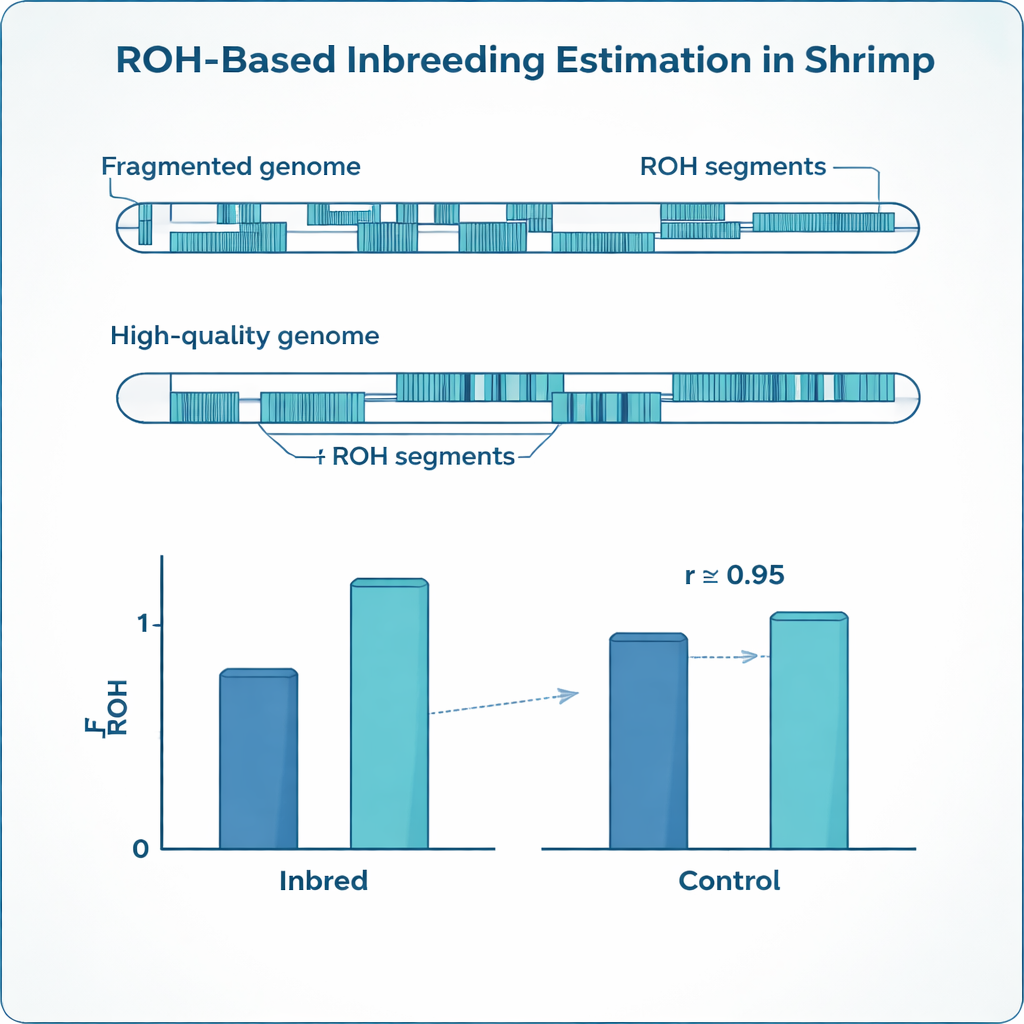
Les paramètres optimisés se sont révélés très différents selon les deux génomes de référence. Le génome fragmenté requérait des marqueurs beaucoup plus denses, des intervalles autorisés plus courts et des longueurs minimales de run plus faibles que le génome de haute qualité pour éviter de fractionner de vrais ROH en de nombreux petits segments. Pourtant, après avoir ajusté ces paramètres séparément, les estimations de consanguinité obtenues à partir des deux références ont convergé : la FROH moyenne chez les crevettes inbred était d’environ 0,24 dans les deux cas, correspondant étroitement à la valeur attendue d’après les accouplements planifiés et en fort accord mutuel. Parallèlement, le génome plus continu révélait moins de segments ROH mais beaucoup plus longs, tandis que la carte fragmentée morcelait nombre d’entre eux en courts tronçons. L’étude a également mis en évidence des différences marquées entre frères et sœurs : au sein d’une même portée, les niveaux de consanguinité variaient fortement, une variabilité que les simples registres de pedigree ne peuvent capturer.
Des outils plus précis pour des stocks de crevettes en meilleure santé
Pour les non‑spécialistes, le message est simple : mesurer la consanguinité à partir de l’ADN peut être très précis chez les crevettes d’élevage, mais uniquement si la méthode tient compte de la structure sous‑jacente du génome. En fournissant une recette pratique pour ajuster l’analyse des ROH aux génomes fragmentés des crustacés, ce travail permet aux sélectionneurs de surveiller la consanguinité individu par individu, plutôt que de s’en remettre à des arbres généalogiques imparfaits. Cela peut aider à concevoir des plans d’accouplement qui préservent la diversité génétique tout en améliorant la croissance et la résilience, soutenant une aquaculture de crevettes plus durable et offrant un modèle pour d’autres espèces aquacoles confrontées à des difficultés génomiques similaires.
Citation: Zou, X., Zhou, H., Liu, M. et al. A genome-structure adaptive framework for ROH-based inbreeding estimation in Penaeus vannamei. Sci Rep 16, 6769 (2026). https://doi.org/10.1038/s41598-026-37622-8
Mots-clés: élevage de crevettes, consanguinité, sélection génomique, runs of homozygosity, génétique de l'aquaculture