Clear Sky Science · fr
Conjugaison d’ADN sur surfaces plastiques fonctionnalisées pour séquençage itératif et séquentiel d’une seule molécule
Stocker les données de demain dans des brins minuscule
Imaginez sauvegarder vos photos, livres ou archives scientifiques sous une forme pouvant durer des siècles et tenir dans une particule plus petite qu’un grain de sable. L’ADN — la même molécule qui porte nos gènes — émerge comme un candidat puissant pour un stockage ultra-dense et durable. Cet article explore une nouvelle façon de « garer » des données encodées en ADN en toute sécurité à l’intérieur de tubes en plastique ordinaires, puis de les relire encore et encore sans détruire les molécules originales.
Un nouveau type de « clé USB »
Les disques durs et mémoires flash d’aujourd’hui s’usent, et ils contiennent bien moins d’information par gramme que ce que l’ADN pourrait offrir. Des chercheurs ont déjà démontré comment traduire des fichiers numériques en séquences de « lettres » d’ADN. Mais à chaque copie ou séquençage de ces brins d’ADN, une partie du matériel original est consommée, un peu comme une encre qui pâlit si l’on photocopie trop de fois. Dans cette étude, les auteurs ont transformé le modeste tube PCR en plastique — déjà standard dans les laboratoires de biologie — en un dispositif de stockage physique réutilisable. Ils ont fixé chimiquement des brins d’ADN portant des données encodées sur la surface intérieure du tube, de sorte que l’ADN reste en place pendant que des copies sont répétitivement produites et lues. 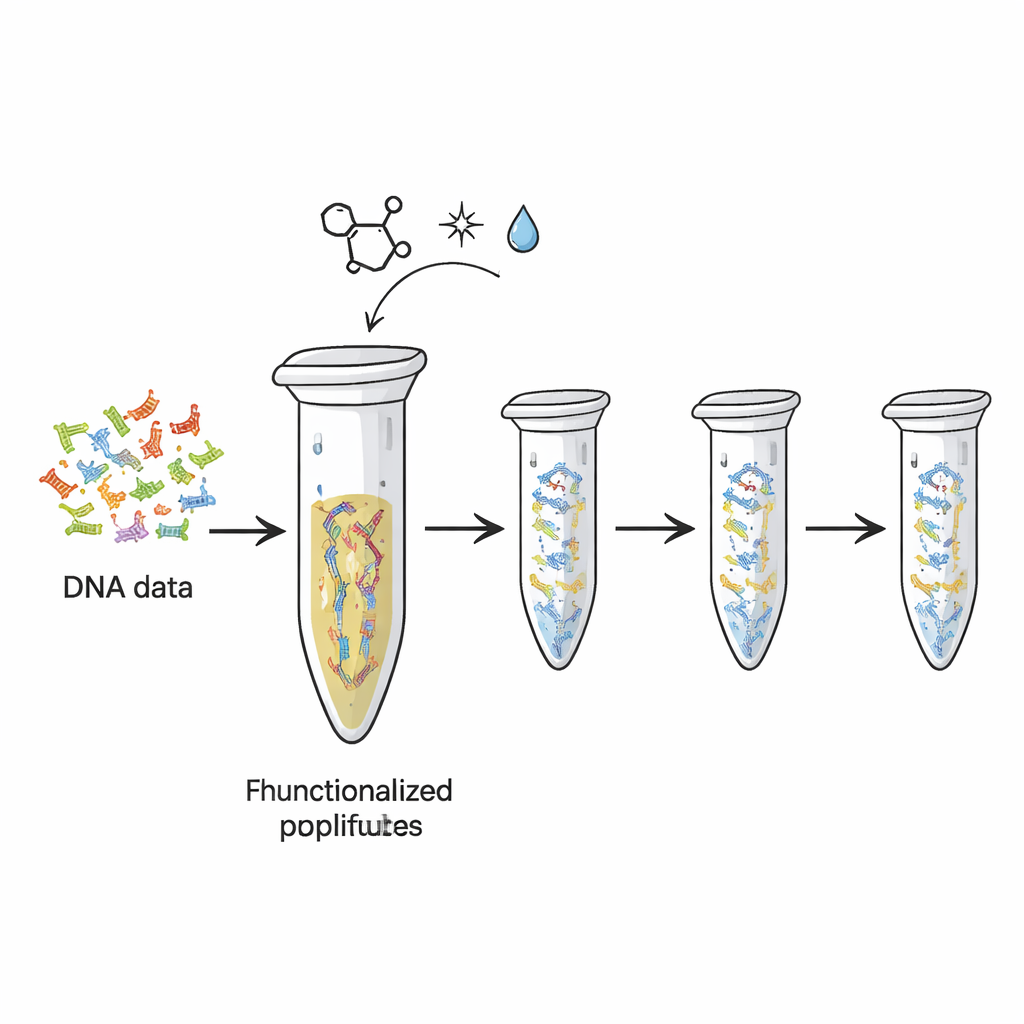
Cliquer l’ADN sur le plastique
L’équipe s’est appuyée sur un type de « chimie click » hautement spécifique — une famille de réactions prisée pour leur rapidité, fiabilité et douceur. D’abord, ils ont ajouté des queues chimiques spéciales aux extrémités des brins d’ADN représentant différents « fichiers » de données. Ces queues, basées sur une molécule appelée TCO, sont conçues pour se verrouiller sur des groupes complémentaires (MTz) greffés sur la surface plastique du tube. Quand les deux se rencontrent, elles forment une liaison covalente stable, collant effectivement l’ADN au plastique. Des tests avec un fragment d’ADN témoin ont montré qu’après incubation, presque tout l’ADN avait disparu de la solution, indiquant qu’il était désormais immobilisé sur la paroi du tube. La plateforme pouvait retenir de l’ordre de centaines de femtomoles d’ADN, ce qui suggère une capacité suffisante pour des jeux de données pratiques.
Récupérer des « fichiers » numériques à la demande
Pour vérifier si cet ADN fixé se comportait toujours comme une archive exploitable, les chercheurs ont encodé du texte et d’autres données dans un pool d’environ 15 000 courts brins d’ADN, regroupés en 18 « groupes de fichiers ». Chaque groupe pouvait être copié sélectivement à l’aide de sa propre paire d’amorces — de courtes séquences de départ qui dirigent la machinerie de copie vers les bonnes cibles. L’équipe a réalisé à plusieurs reprises des réactions PCR standard dans le même tube, choisissant à chaque fois un groupe de fichiers différent à amplifier. Après chaque cycle, ils ont retiré l’ADN copié, nettoyé le tube avec des enzymes qui digèrent les produits résiduels en solution, puis sont passés au fichier suivant. Le séquençage par nanopore du matériel copié a montré que la plupart des groupes de fichiers étaient récupérés avec une grande précision, et que la contamination croisée provenant de runs antérieurs restait extrêmement faible, typiquement autour de 1 % ou moins.
Trouver une méthode de lecture plus douce
Cependant, il y avait un hic : en répétant la PCR dans le même tube jusqu’à 18 fois, la quantité d’ADN récupérée diminuait régulièrement. La PCR repose sur des cycles rapides de chauffage et de refroidissement, et les auteurs ont déduit que les fortes températures répétées endommageaient l’ADN immobilisé ou sa liaison au plastique, même si des tests témoins suggéraient que l’ADN ne se rinçait pas simplement dans la solution. Pour remédier à cela, ils se sont tournés vers l’amplification par recombinase-polymérase (RPA), une méthode plus récente qui fonctionne à une unique température relativement basse, proche de la température corporelle. En utilisant la RPA sur des tubes fraîchement enrobés d’ADN, ils ont de nouveau interrogé séquentiellement les 18 groupes de fichiers. Cette fois, les rendements étaient élevés — autour de 60 ng/µL — et n’ont pas montré la même tendance à la baisse. Le profil des brins favorisés ou défavorisés lors de la copie correspondait également de près à celui observé quand l’ADN était libre en solution. 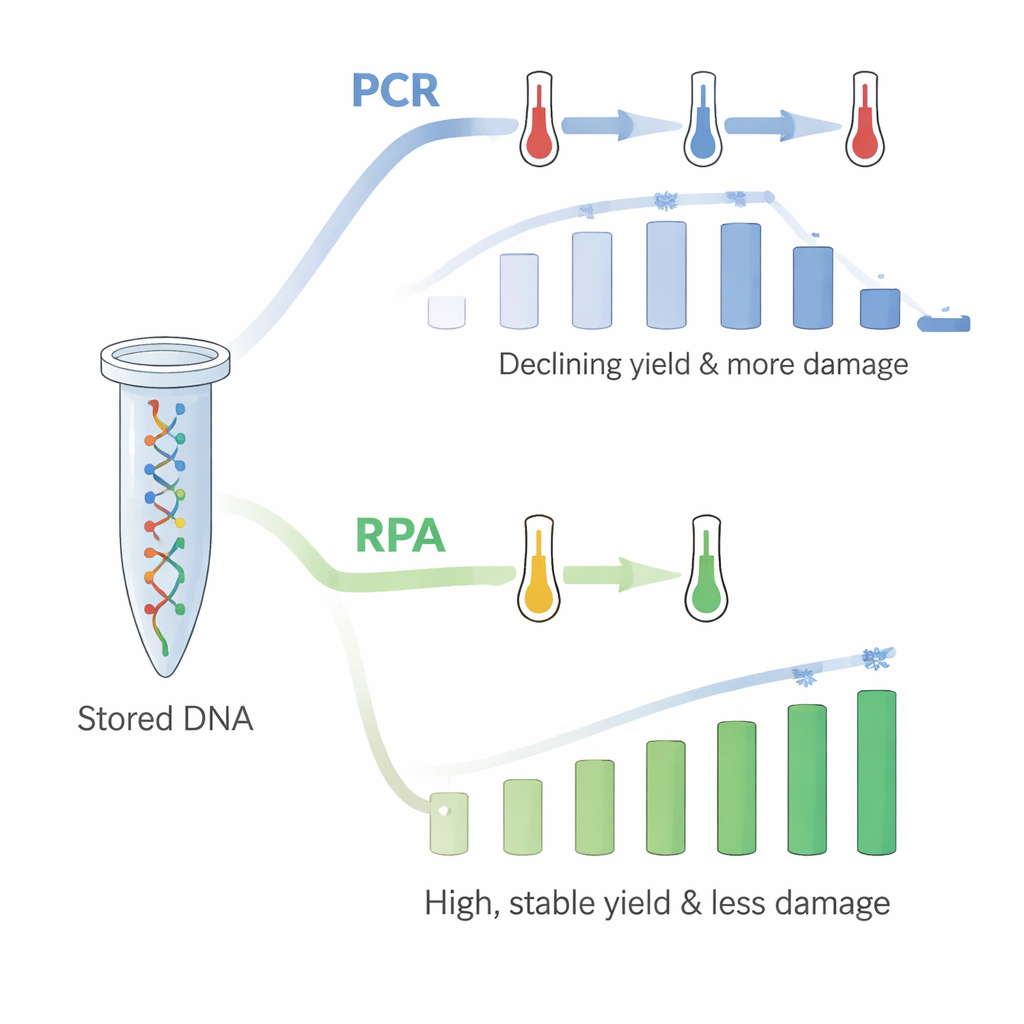
Vers une mémoire ADN portable et durable
En combinant une chimie click robuste avec une copie d’ADN à basse température, ce travail ouvre la voie à une manière pratique de transformer de simples tubes en plastique en cartouches de données ADN réutilisables. L’ADN reste physiquement verrouillé sur le tube, où il peut être interrogé de manière répétée pour des « fichiers » spécifiques sans consommer les molécules originales, en particulier lorsque l’on utilise la méthode plus douce RPA. Pour les non-spécialistes, le message clé est que l’ADN n’est pas seulement le code de la vie — il peut aussi servir de support de stockage numérique compact et durable. Des méthodes comme celle-ci nous rapprochent d’un avenir où vos sauvegardes à long terme pourraient ne plus résider sur des disques tournants, mais dans des molécules soigneusement conçues posées tranquilement sur une étagère de laboratoire.
Citation: Roy, S., Ji, H.P. & Lau, B.T. DNA conjugation on functionalized plastic surfaces for sequential, iterative single molecule sequencing. Sci Rep 16, 6467 (2026). https://doi.org/10.1038/s41598-026-37575-y
Mots-clés: stockage de données sur ADN, chimie click, conjugaison sur surface plastique, amplification par recombinase-polymérase, séquençage nanopore