Clear Sky Science · fr
Quantification et suivi rapides d’organoïdes sans apprentissage avec OrganoSeg2
Pourquoi de minuscules tissus cultivés en laboratoire comptent
Dans des laboratoires du monde entier, des scientifiques cultivent désormais des versions miniatures de tissus humains appelées organoïdes. Ces petits amas cellulaires tridimensionnels peuvent reproduire le comportement d’organes réels ou de tumeurs, ce qui en fait des outils puissants pour étudier les maladies et tester des traitements. Mais il existe un goulot d’étranglement : les chercheurs peuvent collecter des milliers d’images microscopiques à faible grandissement d’organoïdes, sans parvenir à mesurer comment chacun croît, change de forme ou meurt au fil du temps. Cet article présente OrganoSeg2, un logiciel repensé qui transforme ces images grises et simples en mesures riches et fiables sur chaque organoïde individuel — sans nécessiter d’entraînement par intelligence artificielle ni d’équipements d’imagerie coûteux.
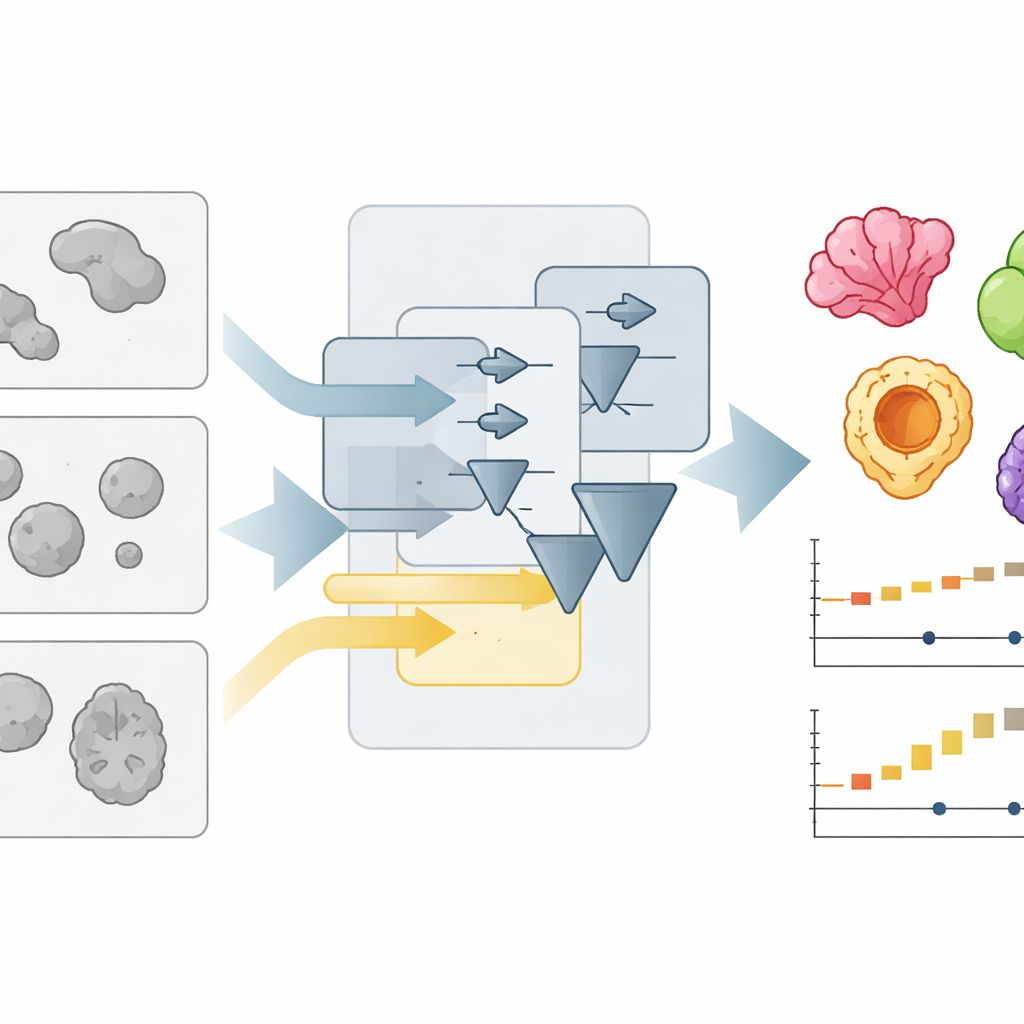
Une nouvelle façon d’interpréter des images microscopiques surpeuplées
Les organoïdes sont généralement imagés avec des microscopes en champ clair simples, qui les montrent comme des taches pâles et chevauchantes. Dresser automatiquement le contour de chaque tache — la « segmentation » de l’image — est beaucoup plus difficile qu’il n’y paraît, surtout lorsque les laboratoires utilisent des formats de culture, des éclairages ou des optiques différents. Les auteurs avaient précédemment créé OrganoSeg, un programme capable de gérer la segmentation de base mais qui ralentissait et devenait peu pratique quand les collections d’images atteignaient des centaines d’exemplaires. Avec OrganoSeg2, ils ont reconstruit le logiciel de zéro dans une interface moderne, simplifié le code interne et exposé plusieurs paramètres cachés pour que les utilisateurs puissent affiner la séparation des organoïdes et du fond, séparer les voisins qui se touchent et ignorer les artefacts en bordure d’image. L’application conserve désormais ces choix en métadonnées afin que les analyses soient reproductibles et partageables.
Accélérer le travail sans sacrifier le détail
Au-delà de la flexibilité, l’équipe s’est beaucoup concentrée sur la vitesse et l’expérience utilisateur. Dans les versions antérieures, le logiciel calculait automatiquement toutes les mesures possibles pour chaque organoïde, même lorsque seules quelques-unes étaient nécessaires. OrganoSeg2 calcule maintenant uniquement ce que l’utilisateur sélectionne et réorganise les calculs liés pour réutiliser efficacement les étapes longues. Il réduit aussi la quantité d’informations affichées à l’écran, n’affiche les étiquettes que lorsque c’est utile et ajoute des raccourcis clavier et des outils interactifs pour supprimer rapidement débris ou objets non‑organoïdes. Ces choix de conception réduisent d’environ dix fois le temps des opérations courantes — segmentation des images, affichage des contours et export de données — rendant possible le traitement d’images larges et mosaïquées et d’expériences en time‑lapse longues sur un ordinateur ordinaire.
Des performances supérieures aux concurrents high‑tech sur des données réelles
Pour évaluer OrganoSeg2, les auteurs l’ont comparé à plusieurs autres outils de segmentation, y compris des systèmes d’apprentissage profond nécessitant un entraînement sur exemples annotés manuellement. Ils ont rassemblé des jeux d’images issus de six sources différentes — par exemple des organoïdes du côlon, du poumon, du pancréas, du cerveau et du sein, ainsi que des corps embryonnaires — pour lesquels des experts humains avaient déjà tracé les frontières des organoïdes. En utilisant un score d’exactitude standard mesurant le recouvrement entre contours automatisés et manuels, OrganoSeg2 a égalé ou dépassé les outils spécialisés sur la plupart des jeux de données et s’est démarqué sur les images difficiles de cancer du sein, riches en matériel étranger et en organoïdes aux formes atypiques. Fait notable, OrganoSeg2 a atteint ces performances sans nécessiter des dizaines de milliers d’exemples d’entraînement et a tourné au moins aussi vite que ses concurrents, y compris ceux basés sur l’intelligence artificielle.
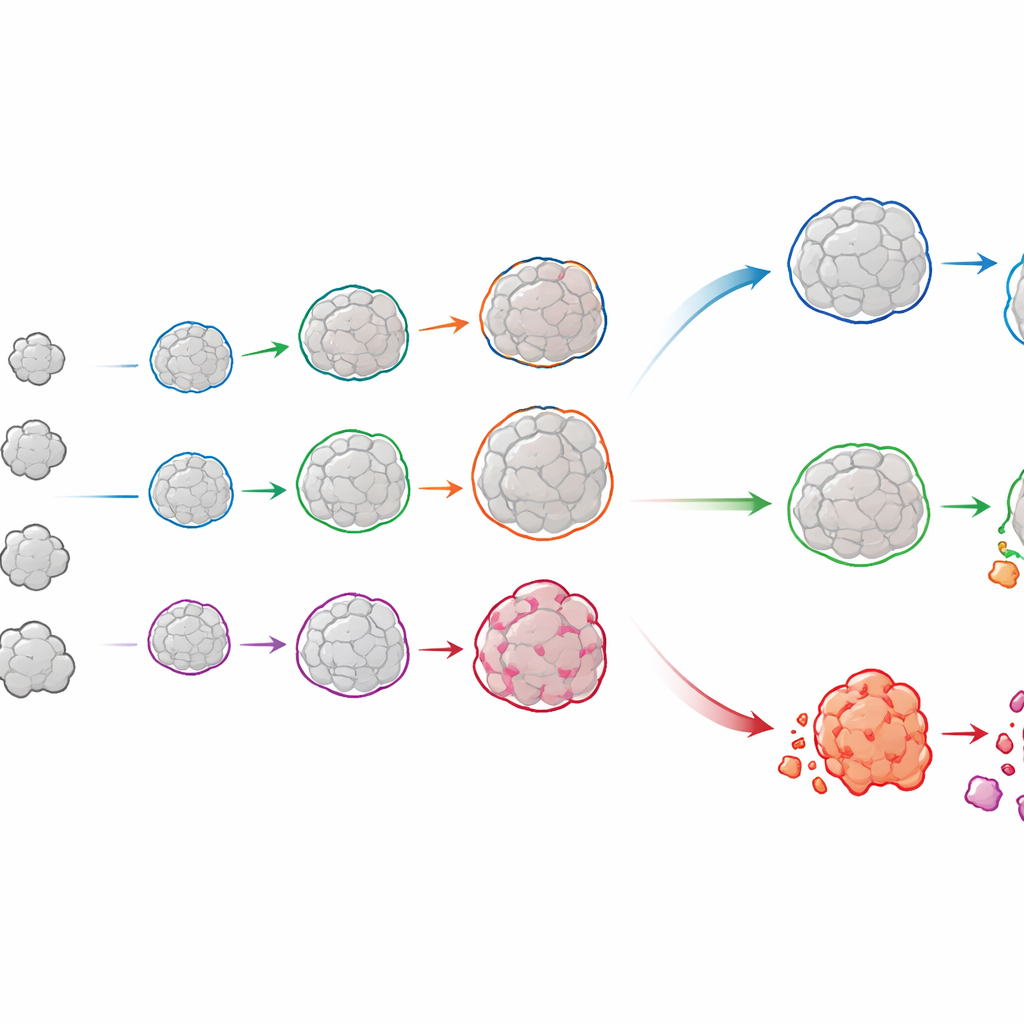
Suivre l’histoire de vie de chaque organoïde
OrganoSeg2 fait plus que tracer des contours sur des images isolées. Il peut aligner des images prises à différents jours et relier un même organoïde à travers le temps, construisant ainsi un historique de croissance pour chacun. Lorsque les auteurs ont appliqué cette méthode à des organoïdes cultivés directement à partir de tumeurs luminales du sein de patients, ils ont observé que les organoïdes individuels croissaient rarement de façon régulière ; beaucoup ralentissaient ou atteignaient un plateau, reflétant la présence, au sein des tumeurs réelles, d’un mélange de régions à croissance rapide et lente. En ajustant ces trajectoires à un modèle de croissance simple, l’équipe a pu quantifier à la fois la vitesse d’expansion de chaque organoïde et la taille qu’il était susceptible d’atteindre. La comparaison de ces profils entre patients a révélé que des tumeurs ayant une croissance globale similaire peuvent masquer des mélanges très différents de comportements sous-jacents — des différences susceptibles d’être importantes pour prédire la réponse au traitement.
Observer les cellules cancéreuses vivre et mourir sous radiation
Le logiciel relie également les images en champ clair à des colorants fluorescents qui rendent compte de l’état des cellules. Dans de nouvelles expériences, les auteurs ont exposé des organoïdes de cancer du sein à des doses de radiation comparables à celles utilisées en clinique et les ont marqués avec un marqueur de cellules vivantes s’éclairant pendant la mort cellulaire programmée, ainsi qu’un second colorant révélant les cellules mortes au dernier point temporel. OrganoSeg2 a utilisé l’image en champ clair pour définir la forme de l’organoïde puis a mesuré les signaux fluorescents à l’intérieur de chacun sur plusieurs jours. Cela a permis à l’équipe de suivre, organoïde par organoïde, le moment et l’intensité de la mort induite par la radiation. Les organoïdes de certains patients ont à peine répondu, tandis que d’autres montraient une forte sensibilité même à faibles doses, soulignant la grande variabilité des réponses tumorales.
Ce que cela signifie pour la recherche et les soins futurs
Pris dans leur ensemble, ces travaux montrent qu’un traitement d’image soigné et ajustable peut rivaliser avec, voire dépasser, des méthodes complexes d’apprentissage profond pour une large gamme d’images d’organoïdes, tout en restant transparent et facile à paramétrer. OrganoSeg2 transforme de simples films d’organoïdes à faible grandissement en enregistrements détaillés de la croissance et de la survie de chaque petit tissu dans différentes conditions. Pour les chercheurs fondamentaux, il offre une méthode robuste pour disséquer la diversité cachée au sein des cultures d’organoïdes. Pour les études sur le cancer en particulier, il ouvre la voie à l’utilisation d’organoïdes dérivés de patients non seulement pour des criblages oui/non de médicaments, mais pour des mesures riches et résolues dans le temps de la croissance et de la mort cellulaire qui pourraient, un jour, aider à adapter les traitements de façon plus précise.
Citation: Wells, C.J., Labban, N., Showalter, S.L. et al. Fast learning-free organoid quantification and tracking with OrganoSeg2. Sci Rep 16, 7928 (2026). https://doi.org/10.1038/s41598-026-37526-7
Mots-clés: organoïdes, analyse d’images, recherche sur le cancer, microscopie, réponse aux radiations