Clear Sky Science · fr
Analyse comparée des caryotypes de onze espèces de Lilium de Chine par FISH avec des sondes oligo d’ADNr
Pourquoi les chromosomes de lys ont de l’importance au-delà du laboratoire
Les lys de jardin ne sont pas seulement de belles fleurs ou des remèdes traditionnels : ce sont aussi des modèles génétiques qui aident les scientifiques à comprendre comment de nouvelles espèces végétales émergent et comment les classer correctement. Cette étude examine l’intérieur des cellules de onze espèces de lys chinoises, dont beaucoup sont utilisées comme aliments ou en médecine, pour observer l’organisation et les marques de leurs chromosomes. En comparant ces structures cachées, les auteurs éclaircissent quelles espèces de lys sont réellement apparentées et fournissent des éléments pour trancher des débats de longue date sur l’arbre généalogique des lys.
Démêler un arbre phylogénétique compliqué chez les lys
Le genre Lilium comprend environ 125 espèces réparties dans l’hémisphère Nord, la Chine étant l’un de ses principaux centres de diversité. Depuis plus d’un siècle, les botanistes tentent de regrouper ces espèces en sections naturelles principalement sur la base de caractères visibles comme la forme des fleurs. Mais des fleurs ressemblantes ne signifient pas toujours une parenté proche, et les études génétiques du chloroplaste et du noyau ont parfois donné des réponses contradictoires sur les relations entre les lys. En particulier, un groupe appelé Leucolirion et ses deux sous-sections (6a et 6b), ainsi que plusieurs espèces du sud-ouest et du centre de la Chine, ont été difficiles à placer avec certitude.
Lire des codes-barres sur les chromosomes
Pour aborder ce problème, les auteurs se sont tournés vers la cytogénétique, l’étude des chromosomes. Les onze espèces examinées partagent toutes le même jeu de base de douze chromosomes, généralement présents sous forme de 24 chez les diploïdes ; deux populations de Lilium lancifolium étaient triploïdes avec 36 chromosomes. Au microscope, chaque espèce montre deux chromosomes plus grands et dix plus petits, mais des différences subtiles de forme et de longueur sont parfois difficiles à percevoir à l’œil nu. L’équipe a donc mesuré précisément les tailles chromosomiques et utilisé une technique appelée hybridation in situ fluorescente (FISH) pour fixer des étiquettes d’ADN fluorescentes sur des régions spécifiques d’ADN ribosomique (ADNr), qui agissent comme des codes-barres lumineux le long de chaque chromosome.
Trouver des tendances dans les génomes des lys
Les chercheurs ont cartographié deux types d’ADNr — 5S et 35S — sur les chromosomes de chaque espèce. La plupart des lys présentaient un site 5S et entre deux et six sites 35S, souvent à des positions caractéristiques. Par exemple, quatre espèces traditionnellement placées dans la sous-section Leucolirion 6a (L. leucanthum, L. sargentiae, L. sulphureum et L. regale) partageaient des motifs d’ADNr très similaires sur les mêmes paires chromosomiques, ce qui indique une parenté étroite, même si L. regale présentait quelques changements supplémentaires. En revanche, les espèces de la sous-section sœur 6b et certains Lys du groupe Sinomartagon affichaient des arrangements d’ADNr nettement différents, soulignant une véritable séparation entre ces deux groupes. En dehors de Leucolirion, des motifs fortement partagés rapprochaient le très cultivé L. lancifolium de L. pumilum et L. davidii, ce qui concorde avec des études antérieures basées sur des séquences d’ADN qui les avaient regroupés ensemble.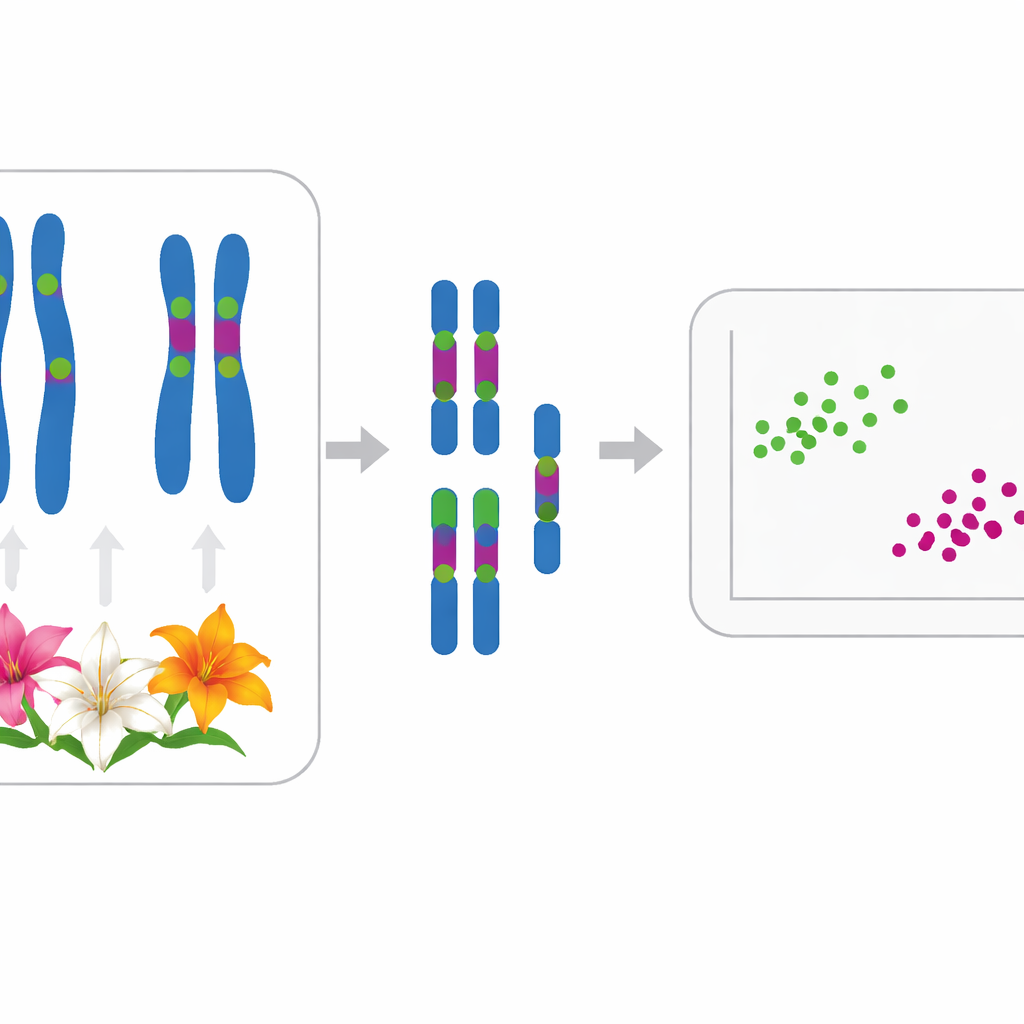
Transformer des mesures en carte des relations
Au-delà des positions des codes-barres, l’équipe a quantifié à quel point chaque caryotype était inégal — à la fois dans la position des centromères (la « taille » du chromosome) et dans les longueurs chromosomiques. Ils ont utilisé deux indices statistiques, MCA et CVCL, pour saisir ces caractéristiques et ont tracé les onze espèces dans un graphe bidimensionnel. Chaque espèce occupait sa propre position distincte, montrant que des caryotypes apparemment similaires peuvent être distingués lorsqu’on les mesure avec précision. Une analyse statistique plus large (analyse en coordonnées principales) a ensuite regroupé les lys en deux grappes principales qui correspondent bien à leur histoire évolutive déduite. Une grappe contenait L. pumilum, L. jinfushanense, L. brownii var. viridulum, L. regale, et les formes de L. lancifolium et L. davidii ; l’autre regroupait L. leucanthum, L. sargentiae, L. sulphureum, L. henryi et L. rosthornii.
Ce que cela implique pour la nomenclature et l’usage des lys
En combinant des mesures chromosomiques détaillées avec des cartes de codes-barres ADNr, cette étude montre que les espèces de lys diffèrent davantage dans leurs caryotypes qu’on ne le pensait et que ces différences portent un signal évolutif clair. Sur le plan pratique, le travail soutient le traitement de la sous-section Leucolirion 6a comme un groupe naturel bien défini au sein du genre Lilium, en accord avec des propositions de classification récentes. Pour les obtenteurs, les praticiens de la phytothérapie et les gestionnaires de la conservation, disposer d’un portrait plus précis des parentés entre lys peut guider le croisement, préserver la diversité génétique et garantir que les variétés médicinales et alimentaires sont correctement identifiées et utilisées.
Citation: Yang, YD., Jiang, XH., Zhang, BY. et al. Comparative karyotype analysis of eleven species of Lilium from China using FISH with rDNA oligo-probes. Sci Rep 16, 9446 (2026). https://doi.org/10.1038/s41598-026-37297-1
Mots-clés: Lilium, chromosomes, hybridation in situ fluorescente, évolution des plantes, cytotaxonomie