Clear Sky Science · fr
Développement et évaluation préliminaire d'essais PCR en temps réel pour six bactéries lactiques
Des micro‑organismes bienveillants derrière nos aliments quotidiens
Beaucoup des aliments qui remplissent les rayons des supermarchés — du yaourt et du fromage aux cornichons et légumes fermentés — doivent leur saveur et leurs éventuels bénéfices pour la santé à des bactéries « amies » connues sous le nom de probiotiques. Mais pour exploiter ces « bons » micro‑organismes de façon sûre et fiable, les entreprises doivent être absolument certaines des espèces bactériennes réellement présentes dans leurs produits. Cette étude décrit de nouveaux tests de laboratoire capables d’identifier rapidement et avec précision six bactéries probiotiques prometteuses utilisées en alimentation, contribuant ainsi à rapprocher la microbiologie de pointe des aliments que nous consommons au quotidien.
Pourquoi ces bactéries probiotiques comptent
Les six bactéries au cœur de ce travail appartiennent toutes à un groupe plus large appelé bactéries lactiques, employées depuis longtemps dans la fermentation. Des recherches récentes suggèrent qu’elles font bien plus que faire tourner le lait ou le chou. Certaines souches de Ligilactobacillus agilis et Ligilactobacillus salivarius pourraient aider à contrer des germes intestinaux nuisibles, calmer l’inflammation et soutenir une barrière intestinale saine. Limosilactobacillus fermentum a été associée, dans des études animales, à une meilleure régulation de la pression artérielle et à des effets antioxydants. Lactobacillus johnsonii semble contribuer à équilibrer le microbiote intestinal de façons susceptibles de protéger plusieurs organes. Pediococcus pentosaceus et Weissella cibaria montrent un potentiel pour abaisser le cholestérol, lutter contre le gâchage et même soutenir la santé buccale. Face à une telle gamme de bénéfices potentiels, l’industrie alimentaire est impatiente d’utiliser plus largement ces espèces — mais seulement si elles peuvent être identifiées en toute confiance.
Le défi de distinguer des microbes qui se ressemblent
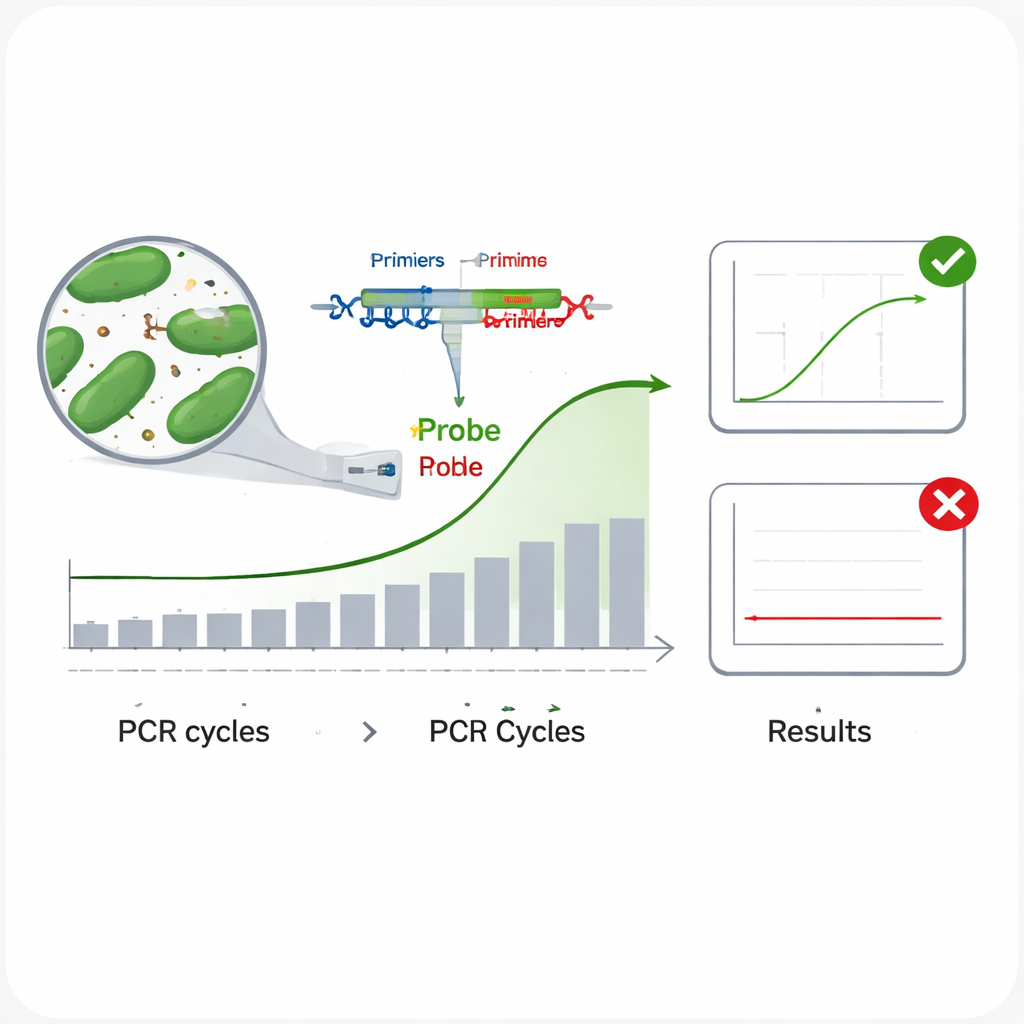
Les méthodes traditionnelles d’identification bactérienne — les cultiver en laboratoire et réaliser des tests biochimiques — sont lentes et exigeantes en main‑d’œuvre. Les méthodes modernes basées sur l’ADN, en particulier la PCR en temps réel, sont beaucoup plus rapides. En PCR en temps réel, de courtes séquences d’ADN appelées amorces et une sonde fluorescente ciblent un fragment unique du code génétique d’un micro‑organisme ; lorsque le microbe ciblé est présent, l’appareil détecte un signal lumineux au fur et à mesure que l’ADN est copié cycle après cycle. Le problème est que des bactéries étroitement liées peuvent partager des séquences d’ADN très similaires, si bien que des régions génétiques couramment utilisées comme le gène 16S rRNA échouent parfois à distinguer une espèce d’une autre. Cela peut conduire à des tests qui manquent la cible (faux négatifs) ou qui s’activent pour la mauvaise espèce (faux positifs), situations inacceptables pour l’étiquetage des produits et la sécurité.
Concevoir des « codes‑barres » moléculaires plus précis
Pour surmonter cet obstacle, les chercheurs ont analysé des génomes complets afin d’identifier de courts fragments d’ADN à la fois fortement conservés au sein de chaque espèce cible et clairement différents des autres bactéries. Pour chacune des six probiotiques, ils ont conçu un jeu d’amorces et une sonde assortie avec une longueur, une composition en bases, une température de fusion et une propension minimale à former des structures secondaires ou à s’hybrider entre elles soigneusement ajustées. Des contrôles informatiques utilisant la base de données BLAST et des logiciels d’alignement de séquences ont confirmé que les régions d’ADN sélectionnées étaient stables au sein de l’espèce tout en étant distinctes des non‑cibles. L’équipe a ensuite mis au point un mélange réactionnel standard et un programme thermique permettant d’exécuter tous les tests dans des conditions pratiques et homogènes sur le même type d’appareil de PCR en temps réel.
Mettre les nouveaux tests à l’épreuve
Les scientifiques ont ensuite évalué la performance de chaque dosage en conditions pratiques. Pour tester l’inclusivité — la capacité d’un test à détecter de nombreuses souches d’une même espèce —, ils ont appliqué chaque essai à plusieurs échantillons d’ADN provenant de la bactérie cible. Dans tous les cas, toutes les souches testées ont produit une courbe d’amplification nette, suggérant un faible risque de manquer des cibles véritables. Pour vérifier la spécificité — la capacité du test à ignorer les espèces non cibles —, ils ont mis chaque essai au défi avec l’ADN de 13 autres bactéries intestinales, y compris des bactéries lactiques proches et des microbes intestinaux courants comme Escherichia coli. Aucune de ces espèces n’a produit de signal, indiquant un risque très faible de fausses alertes. L’équipe a également examiné l’efficacité d’amplification en réalisant une série de dilutions décimales de l’ADN et a confirmé que les six essais amplifiaient leurs cibles à environ 95–100 % d’efficacité, proche de l’idéal. Enfin, ils ont mesuré la précision en répétant des analyses à deux niveaux d’ADN et ont constaté que les très faibles variations entre répétitions et entre expériences restaient largement en deçà des limites acceptées.
Ce que cela signifie pour les aliments de demain
En termes simples, les auteurs ont mis au point six tests d’« empreinte » d’ADN finement ajustés capables de distinguer rapidement, précisément et de manière fiable des espèces probiotiques clés. Ils soulignent toutefois que des essais plus étendus portant sur davantage de souches, plus d’espèces non cibles et d’autres instruments de PCR sont nécessaires avant une adoption industrielle courante ; les résultats préliminaires restent néanmoins encourageants. Pour les consommateurs, des avancées de ce type contribuent à garantir que les aliments annoncés comme contenant des probiotiques spécifiques contiennent bien les micro‑organismes attendus, favorisant ainsi un étiquetage honnête, un meilleur contrôle qualité et des recherches plus fiables sur la façon dont ces petits partenaires influent sur notre santé.
Citation: Li, SJ., Cui, B., Li, W. et al. Development and preliminary evaluation of real-time PCR assays for six lactic acid bacteria. Sci Rep 16, 6165 (2026). https://doi.org/10.1038/s41598-026-37047-3
Mots-clés: probiotiques, bactéries lactiques, PCR en temps réel, microbiologie alimentaire, identification microbienne