Clear Sky Science · fr
Validation clinique d'architectures CNN légères pour une classification multiclasses fiable du cancer du poumon à partir d'images histopathologiques
Pourquoi cette recherche compte pour les patient·e·s et les médecins
Le cancer du poumon est souvent mortel parce qu’il est détecté tard ou mal classé, ce qui peut retarder le traitement approprié. Cette étude examine si de petits programmes informatiques efficaces — plutôt que des modèles énormes et gourmands en ressources — peuvent reconnaître de façon fiable les différents types de cancer du poumon à partir d’images microscopiques de tissus. Si de tels outils légers fonctionnent bien, ils pourraient être déployés dans des hôpitaux du monde entier, y compris dans des structures aux ressources informatiques limitées, pour aider les pathologistes à établir des diagnostics plus rapides et plus cohérents.
Observer le cancer de près avec des microscopes numériques
Lorsqu’un nodule pulmonaire suspect est retiré ou biopsié, les pathologistes examinent des coupes fines et colorées au microscope pour déterminer s’il s’agit d’un tissu bénin ou de l’un des différents types de cancer. Dans ce travail, les auteurs se concentrent sur trois catégories clés : tissu pulmonaire bénin, adénocarcinome pulmonaire et carcinome épidermoïde du poumon. Ces sous-types sont importants car ils réagissent différemment aux traitements. L’équipe utilise des images numériques de ces lames — des images histopathologiques — et se demande si des réseaux neuronaux compacts peuvent apprendre les motifs visuels subtils qui distinguent chaque classe, des formes cellulaires à l’architecture tissulaire, aussi sûrement que des modèles beaucoup plus volumineux.
Construire des classificateurs numériques plus petits mais plus intelligents
La plupart des systèmes de reconnaissance d’images à la pointe sont extrêmement volumineux et exigent des processeurs graphiques coûteux, ce qui complique leur déploiement dans de nombreuses cliniques. Les chercheurs conçoivent plutôt quatre modèles d’analyse d’images « lite », nommés Lite-V0, Lite-V1, Lite-V2 et Lite-V4, chacun étant une version allégée d’un réseau neuronal convolutionnel (CNN). Les quatre suivent la même recette de base : ils extraient progressivement des caractéristiques visuelles via une pile de blocs simples, puis résument l’image et produisent l’une des trois étiquettes tissulaires. Ce qui change d’une version à l’autre, c’est le nombre de blocs et leur largeur — essentiellement la capacité du modèle à apprendre des motifs complexes. Cette conception contrôlée permet à l’équipe d’étudier quelle complexité est réellement nécessaire pour une classification fiable du cancer.
Entraînement, test et sélection du modèle le plus juste
Pour entraîner et tester ces modèles, les auteurs réunissent un ensemble équilibré de 15 000 images de tissus pulmonaires, soigneusement réparties en groupes d’entraînement, de validation et de test avec un nombre égal d’images par classe. Avant l’entraînement, chaque image est redimensionnée, normalisée et légèrement augmentée par des flips, de petites rotations et des zooms pour simuler les variations d’apparence des lames. De manière cruciale, l’équipe n’évalue pas les modèles uniquement sur l’exactitude brute, car ce métrique peut masquer de mauvaises performances sur une classe donnée. Ils s’appuient plutôt sur le score « macro-F1 », qui oblige le modèle à bien performer sur les trois types de tissus, et pas seulement sur les plus faciles. Une procédure d’entraînement personnalisée surveille en continu ce score équilibré et interrompt automatiquement l’entraînement lorsque les améliorations plafonnent, en conservant la meilleure version de chaque modèle pour comparaison. 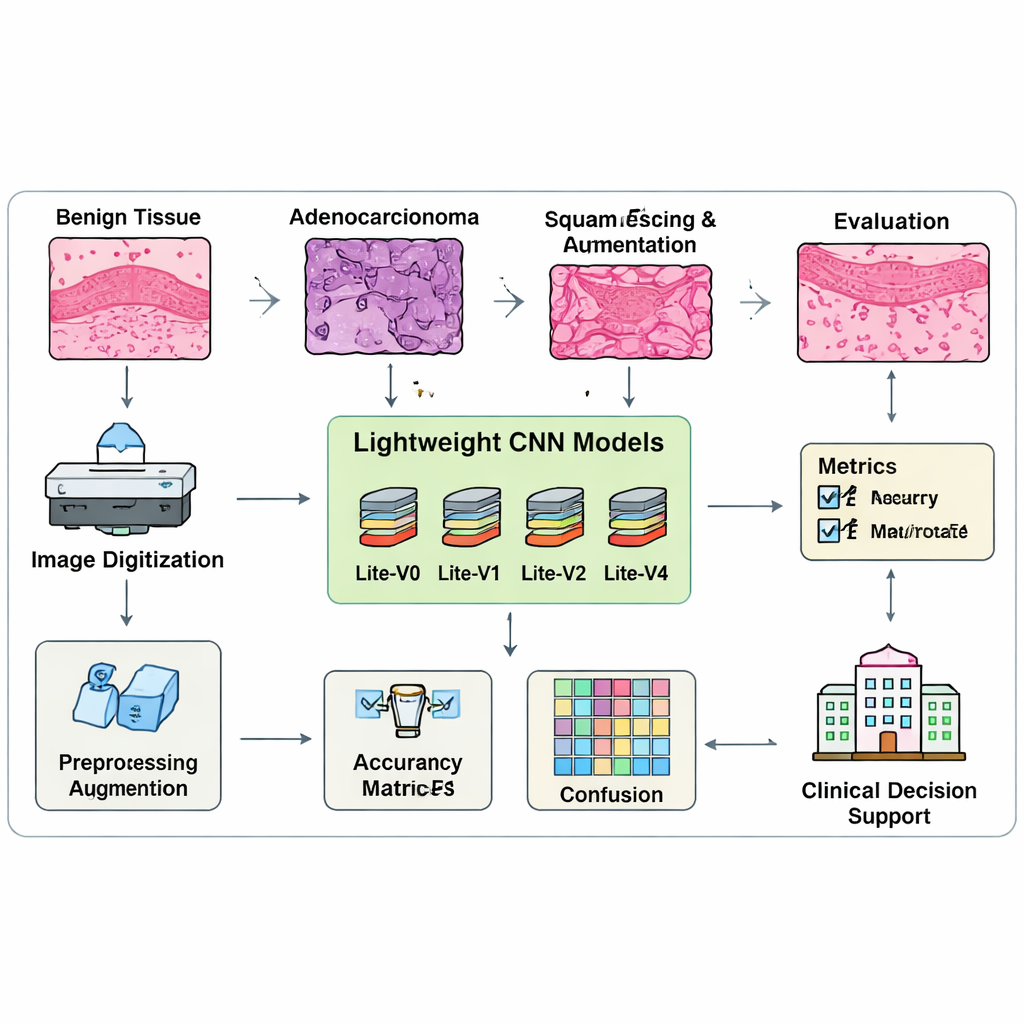
Ce que le meilleur modèle léger peut réellement accomplir
Au final, une variante — Lite-V2 — se démarque. Ce n’est ni le réseau le plus petit ni le plus grand, mais il se situe au milieu et obtient le meilleur compromis entre précision et efficacité. Sur des images de test inédites, Lite-V2 classe correctement les tissus bénins, l’adénocarcinome et le carcinome épidermoïde avec une performance élevée et bien répartie, atteignant un score macro-F1 d’environ 0,96. Les matrices de confusion montrent qu’il confond rarement les trois catégories, tandis que les versions plus profondes commencent à « surapprendre », mémorisant les données d’entraînement au détriment de la fiabilité sur de nouveaux cas. Les auteurs relancent en outre Lite-V2 plusieurs fois avec des initialisations aléatoires différentes et utilisent un test statistique pour confirmer que son avantage sur les autres variantes n’est pas dû au hasard. 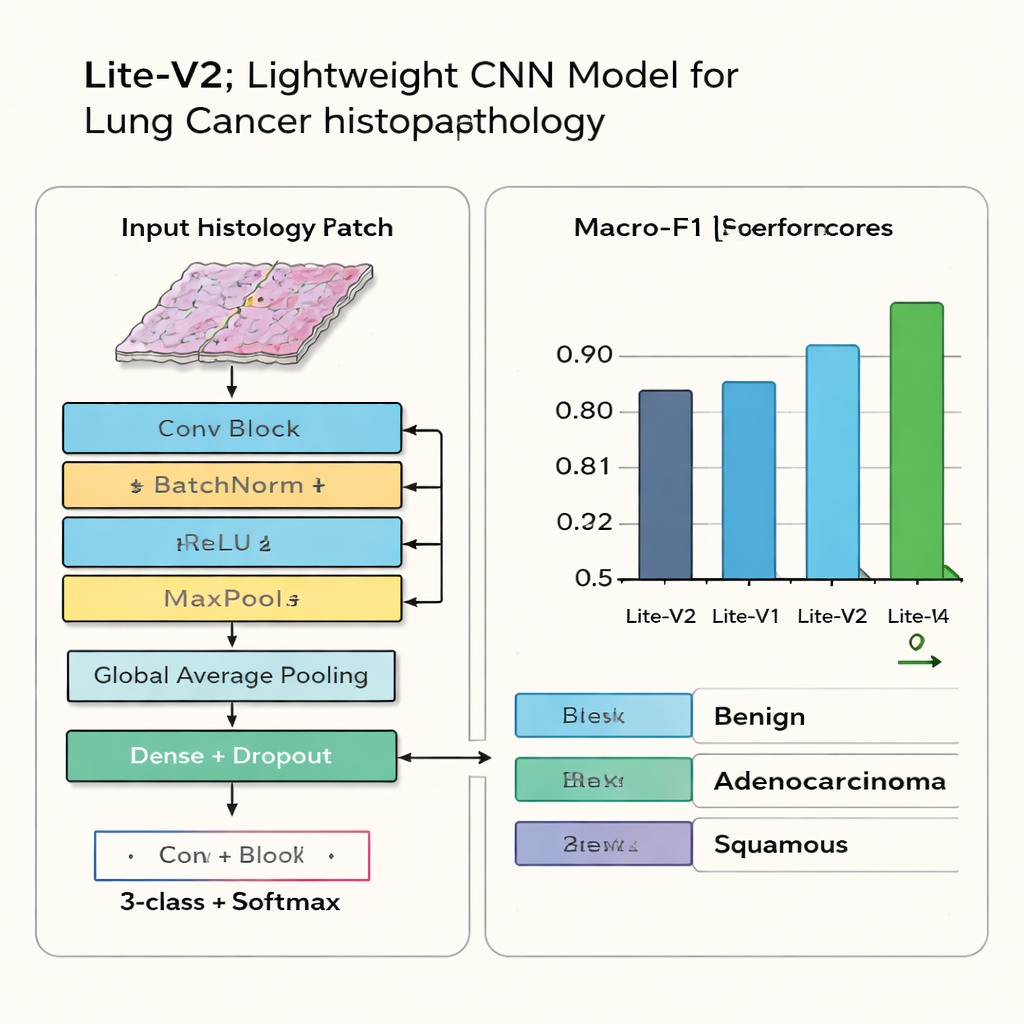
Du code de recherche au soutien en situation réelle
Au-delà des chiffres de performance, l’étude met l’accent sur le déploiement pratique. Parce que Lite-V2 et ses homologues sont compacts, ils peuvent fonctionner sur du matériel hospitalier modeste ou même sur des dispositifs en périphérie sans envoyer d’images sensibles vers le cloud. Les auteurs publient un cadre reproductible qui consigne chaque détail expérimental, du traitement des données aux courbes d’entraînement et aux schémas d’erreur, afin que d’autres équipes puissent vérifier ou étendre le travail. Pour les patient·e·s et les clinicien·ne·s, la conclusion essentielle est qu’une IA légère, conçue avec soin, peut rapprocher une classification fiable du cancer du poumon de la pratique quotidienne en pathologie, en favorisant des décisions plus rapides et plus constantes — même dans des cliniques dépourvues d’infrastructures informatiques de pointe.
Citation: Raza, A., Hanif, F. & Mohammed, H.A. Clinical validation of lightweight CNN architectures for reliable multi-class classification of lung cancer using histopathological imaging techniques. Sci Rep 16, 6512 (2026). https://doi.org/10.1038/s41598-026-36652-6
Mots-clés: cancer du poumon, histopathologie, réseaux neuronaux convolutionnels, IA en imagerie médicale, diagnostic assisté par ordinateur