Clear Sky Science · fr
Identificateur intégré de bactéries en cas d’IS par puce utilisant l’appariement approximatif de k-mers
Pourquoi détecter les germes plus vite importe
Pour les patients recevant des greffes de cellules souches vitales, des infections dans le sang peuvent transformer la convalescence en urgence médicale en l’espace de quelques heures. Les médecins savent que chaque minute compte, mais les outils de laboratoire actuels pour identifier la bactérie responsable peuvent être lents ou exiger des ordinateurs puissants. Cette étude présente une petite puce informatique à faible consommation — appelée PC-CAM — capable d’analyser rapidement l’ADN provenant d’échantillons patients et de signaler en temps réel les bactéries dangereuses, potentiellement au chevet de l’hôpital.
Le risque d’infection après un traitement qui sauve l’intestin
Certaines personnes transplantées développent une complication sévère dans laquelle les cellules immunitaires greffées attaquent l’intestin du patient. Un traitement prometteur est la transplantation de microbiote fécal, où des microbes intestinaux sains d’un donneur sont introduits chez le patient. Bien que cela puisse réparer l’intestin, cela apporte parfois un danger supplémentaire : des bactéries nuisibles de l’intestin peuvent s’échapper dans le sang et provoquer des infections potentiellement mortelles. Pour traiter ces infections efficacement, les médecins doivent identifier rapidement quelles espèces bactériennes sont présentes, mais les tests traditionnels peuvent prendre de plusieurs heures à plusieurs jours et risquent de ne pas détecter des souches peu connues.
Du remaillage lent des génomes aux fragments d’ADN rapides
Les séquenceurs d’ADN modernes peuvent lire le matériel génétique directement à partir d’échantillons de sang ou de selles en quasi temps réel. Le goulot d’étranglement n’est plus la lecture de l’ADN, mais son interprétation. Les méthodes conventionnelles tentent d’abord de reconstruire des génomes entiers à partir de millions de courts fragments d’ADN, puis d’apparier ces génomes assemblés à une bibliothèque de référence — un processus lourd en calcul. Les auteurs remplacent cela par une stratégie plus simple : ils découpent l’ADN en petits segments de longueur fixe, appelés k-mers, et recherchent ces segments directement dans une base de données de séquences bactériennes connues. Plutôt que d’exiger une correspondance parfaite lettre par lettre, leur système tolère un certain nombre de différences, ce qui lui permet de composer avec les erreurs inévitables du séquençage et les mutations naturelles. 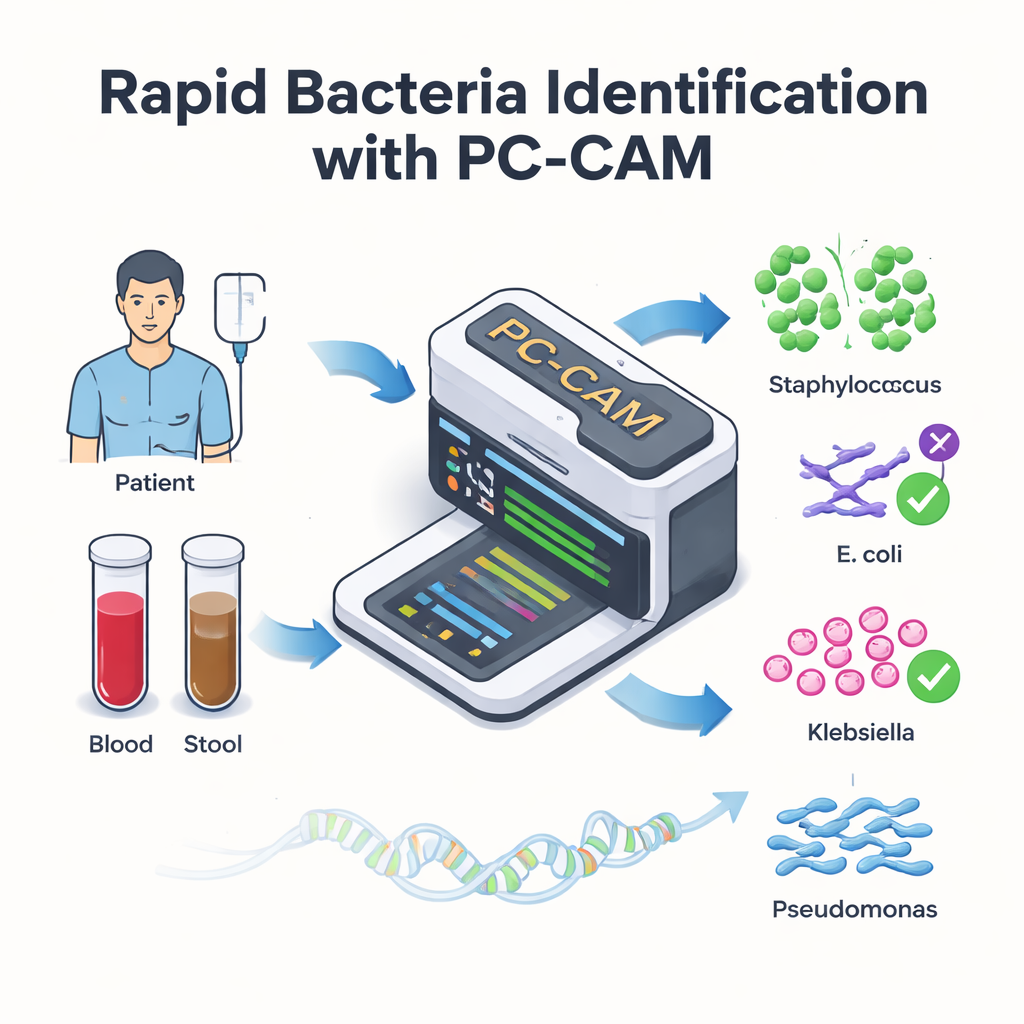
Une puce mémoire intelligente conçue pour la recherche d’ADN
Au cœur du PC-CAM se trouve un type spécialisé de mémoire appelé mémoire adressable par le contenu, qui peut comparer les données entrantes à tout son contenu simultanément. Les chercheurs ont conçu une version « recherche approximative » de cette mémoire (ACAM) réglable pour accepter des quasi-correspondances plutôt que des correspondances exactes. Chaque court fragment d’ADN est codé et stocké comme une ligne dans cette mémoire. Lorsqu’un nouveau fragment provenant d’un échantillon patient arrive, la puce active une ligne de recherche à travers toutes les lignes simultanément et mesure la rapidité avec laquelle de faibles signaux électriques se déchargent. En ajustant deux tensions de commande, le système définit un seuil du nombre de discordances tolérées, modulant ainsi le degré de tolérance de la correspondance. Cette comparaison au niveau matériel permet à la puce de trier les motifs bien plus vite et avec moins d’énergie qu’un ordinateur polyvalent.
Quelle est l’efficacité de la puce pour détecter de vraies bactéries
L’équipe a testé le PC-CAM sur des jeux de données réels de patients ayant subi une transplantation de microbiote fécal, comparant les bactéries détectées dans leur sang et leurs selles aux résultats d’une analyse génomique complète basée sur un logiciel. Même lorsque la puce ne stockait qu’un petit sous-ensemble soigneusement choisi de fragments d’ADN de chaque génome bactérien, elle s’accordait en grande partie avec la méthode plus coûteuse en calcul, identifiant correctement des agents pathogènes clés chez plusieurs patients. Dans des expériences étendues utilisant des lectures d’ADN simulées de diverses bactéries et différents taux d’erreur, la sensibilité de la puce (sa capacité à repérer les vraies correspondances) augmentait avec la tolérance aux différences, tandis que la spécificité (sa capacité à éviter les faux positifs) diminuait à des niveaux de tolérance très élevés. Les auteurs montrent que des étapes simples de post-traitement — comme exiger plusieurs fragments concordants ou éliminer les correspondances faibles — peuvent réduire ces faux positifs. 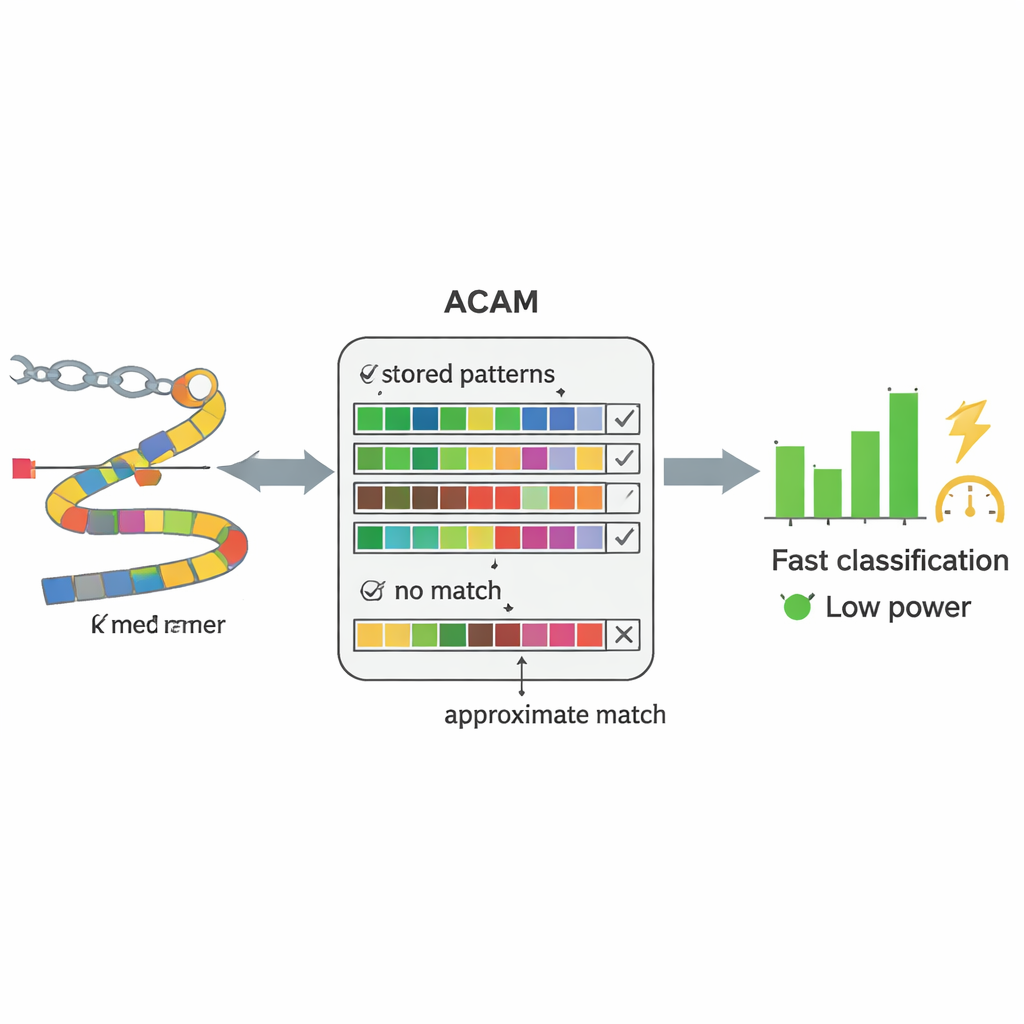
Un matériel minuscule, grande vitesse et faible consommation
PC-CAM intègre la mémoire ACAM avec un petit processeur RISC-V sur une puce de quelques millimètres carrés, fabriquée en technologie standard 65 nanomètres. Des mesures sur matériel réel montrent qu’elle peut classifier environ 960 000 courtes lectures d’ADN chaque seconde tout en consommant environ 1,27 milliwatt de puissance — moins que de nombreuses montres numériques. Comparée à un outil logiciel de pointe tournant sur un processeur de bureau haut de gamme, la puce était environ 1 900 fois plus rapide pour ce type de tâche de classification. Bien que son exactitude soit légèrement réduite du fait du stockage d’une version diluée de chaque génome, les auteurs soutiennent que ce compromis est acceptable lorsque la vitesse et la consommation sont les contraintes primaires, comme en soins d’urgence ou dans des dispositifs portables.
Ce que cela signifie pour les patients et au-delà
En termes simples, l’étude montre qu’une puce minuscule et à basse consommation peut agir comme un moteur de recherche spécialisé pour l’ADN bactérien, repérant presque instantanément des germes dangereux dans des échantillons de sang ou de selles. Bien qu’elle ne remplace pas l’analyse génétique complète réalisée dans un grand laboratoire, elle peut fournir rapidement des indications sur place concernant les bactéries présentes, aidant les médecins à choisir des antibiotiques plus tôt et plus précisément. La même approche pourrait être étendue à la surveillance de la résistance aux antibiotiques, au contrôle de la contamination des aliments et de l’eau, ou à la surveillance des maladies des cultures — le tout avec du matériel compact qui déplace l’analyse avancée de l’ADN hors des centres de données et plus près des lieux où les décisions doivent être prises.
Citation: Garzón, E., Galindo, V., Harary, Y. et al. Integrated BSI bacteria identifier-on-chip using approximate k-mer matching. Sci Rep 16, 5722 (2026). https://doi.org/10.1038/s41598-026-36497-z
Mots-clés: infection du courant sanguin, détection rapide des agents pathogènes, séquençage de l’ADN, laboratoire sur puce, microbiome