Clear Sky Science · fr
Assemblage du transcriptome en pleine longueur et développement de marqueurs SSR pour Spinibarbus hollandi par séquençage PacBio SMRT
Pourquoi un modeste poisson de rivière a de l’importance
Le long des rivières du sud de la Chine nage Spinibarbus hollandi, un poisson ressemblant à la carpe apprécié tant pour la table que comme espèce ornementale. Les éleveurs souhaiteraient l’élever plus efficacement, mais ce poisson croît lentement, mûrit tard et produit relativement peu d’œufs. L’étude décrite ici utilise des outils de séquençage d’ADN et d’ARN de pointe pour établir une « liste de pièces » génétique détaillée pour cette espèce. Ces informations génétiques peuvent finalement aider les sélectionneurs à choisir des poissons plus résistants et à croissance plus rapide et soutenir la conservation des populations sauvages.
Transformer de nombreux tissus en carte génétique
Pour capturer autant d’informations génétiques que possible, les chercheurs ont prélevé six tissus différents — cœur, branchie, cerveau, nageoire, foie et gonade — chez six mâles et femelles adultes. De ces tissus, ils ont extrait l’ARN, la molécule qui transporte les copies des gènes actifs dans les cellules. En utilisant une technologie appelée PacBio SMRT, qui lit de très longs tronçons de copies d’ARN, ils ont assemblé le premier transcriptome en pleine longueur de S. hollandi. En termes simples, ils ont construit un catalogue haute résolution de 15 197 gènes distincts et 23 403 séquences de transcrits, la plupart beaucoup plus longues et plus complètes que ce que les anciennes méthodes à lectures courtes pouvaient produire.
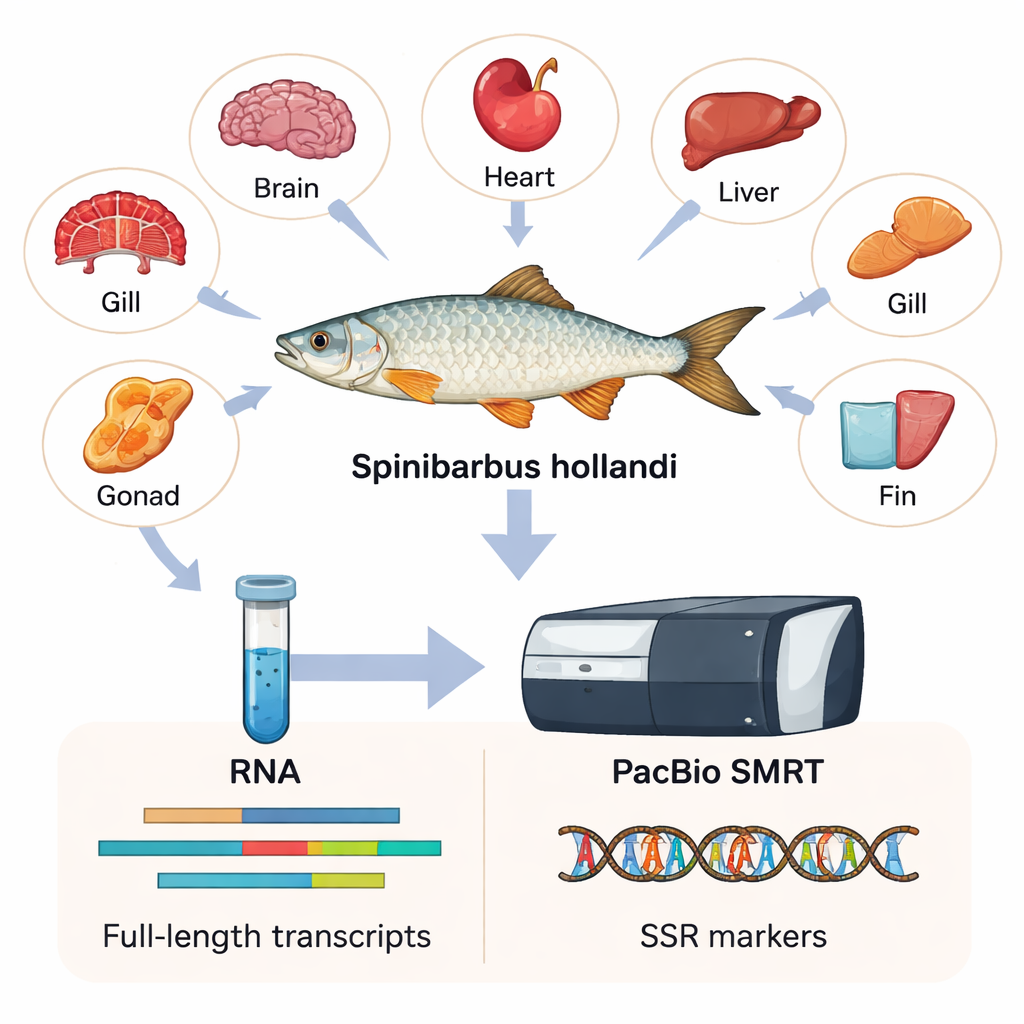
Ce que les gènes révèlent sur le poisson
Ensuite, l’équipe a cherché à savoir ce que font réellement ces gènes. Ils ont comparé chaque séquence à de grandes bases de données publiques qui regroupent les gènes par fonction. Plus de 95 % des gènes ont pu être associés à des entrées connues, un taux de réussite très élevé qui témoigne de la qualité des données. De nombreux gènes se classaient dans des catégories liées aux activités cellulaires de base telles que le métabolisme, la transmission de signaux et le développement, et ressemblaient le plus souvent à des gènes d’autres poissons de la famille des carpes. Cela confirme que le nouveau transcriptome est biologiquement cohérent et fournit une base pour identifier des gènes liés à des traits comme le taux de croissance, la tolérance au stress et la reproduction chez S. hollandi.
Couches cachées de régulation dans l’ARN
Au-delà de l’identification des gènes, les scientifiques ont également examiné comment ces gènes sont contrôlés. Ils ont trouvé 373 cas d’épissage alternatif, où le même gène est découpé et assemblé de manières différentes pour produire des messages ARN distincts. Le schéma le plus courant retenait des segments d’ARN qui sont souvent retirés chez d’autres espèces, suggérant une manière particulière dont ce poisson affine ses protéines. Ils ont aussi découvert 2 397 ARN non codants longs — des molécules d’ARN qui ne fabriquent pas de protéines mais peuvent réguler quand et où d’autres gènes s’expriment. Ensemble, ces découvertes montrent que S. hollandi utilise un riche ensemble de contrôles au niveau de l’ARN qui peuvent influencer la croissance, la maturation sexuelle et l’adaptation aux environnements locaux.
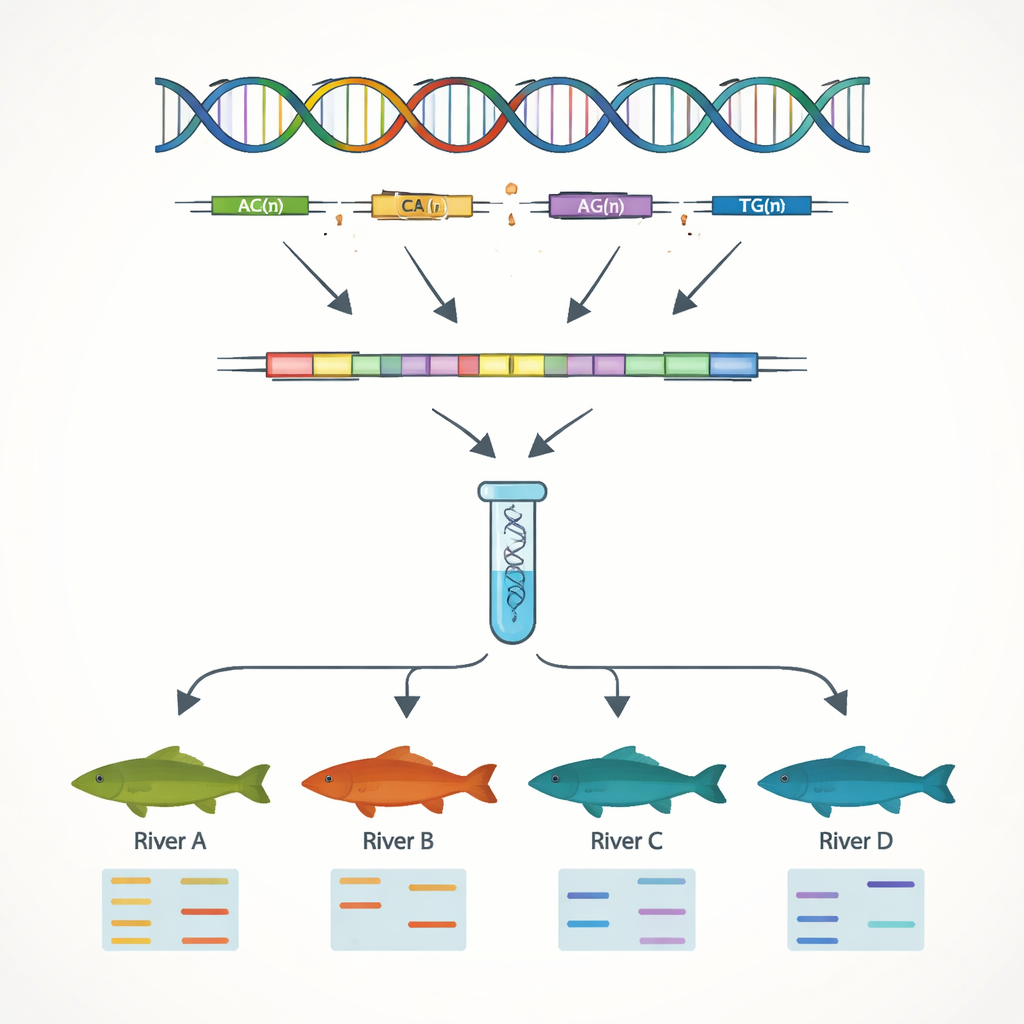
Construire des repères ADN pour l’élevage et la conservation
Un objectif majeur du travail était de développer des marqueurs ADN simples permettant de distinguer individus et populations. En se concentrant sur les séquences de gènes, les auteurs ont recherché des répétitions de séquences simples, ou SSR — de courts motifs d’ADN comme « AC » ou « AAT » répétés de nombreuses fois. Ces régions tendent à varier entre individus, ce qui en fait des codes-barres génétiques utiles. Ils ont mis au jour 7 449 sites SSR et conçu des dizaines d’amorces courtes pour les amplifier en laboratoire. Treize de ces marqueurs se sont révélés très variables et fiables lorsqu’on les a testés sur 51 poissons provenant de quatre bassins fluviaux. Avec seulement ces 13 marqueurs, l’équipe a pu détecter clairement des différences génétiques entre les populations du fleuve Yangtsé et celles du fleuve des Perles, reflétant les chaînes de montagnes qui limitent le mélange naturel entre bassins.
Ce que cela signifie pour les éleveurs et les rivières
Pour les non-spécialistes, l’essentiel est que les auteurs ont créé une référence génétique détaillée et de haute qualité pour S. hollandi ainsi qu’un ensemble de marqueurs ADN pratiques. Cette boîte à outils aidera les chercheurs à identifier les gènes responsables de la croissance lente ou de la faible fertilité, assistera les sélectionneurs dans le choix des reproducteurs avec des caractères souhaitables et permettra aux conservationnistes de suivre la diversité génétique entre les systèmes fluviaux. Bien que des travaux supplémentaires soient nécessaires pour relier des gènes spécifiques aux performances en bassins ou à l’état sauvage, cette étude pose les bases moléculaires pour transformer un poisson de rivière traditionnel en une espèce d’aquaculture moderne et gérée durablement.
Citation: Li, S., Lai, J., Wu, M. et al. Full-Length transcriptome assembly and SSR marker development for Spinibarbus hollandi using PacBio SMRT sequencing. Sci Rep 16, 5629 (2026). https://doi.org/10.1038/s41598-026-36468-4
Mots-clés: Spinibarbus hollandi, transcriptome de poisson, séquençage PacBio, marqueurs microsatellites, génétique de l’aquaculture