Clear Sky Science · fr
Analyse de stabilité et simulation numérique de modèles épidémiques étendus non locaux en utilisant un schéma préservant la positivité
Pourquoi les sauts longue distance comptent dans les épidémies
Quand on imagine la propagation d’une maladie, on pense souvent à des infections qui se déplacent progressivement de ville en ville. En réalité, les déplacements en voiture, train ou avion permettent aux agents pathogènes de sauter d’une région à une autre en une seule journée. Cet article développe une nouvelle méthode de calcul pour capturer ce type de propagation à longue distance, dite « non locale », au sein des modèles épidémiques. En associant des outils mathématiques avancés à des algorithmes efficaces, les auteurs montrent comment simuler des foyers qui reflètent les modèles de mobilité réels tout en préservant des grandeurs essentielles, comme les effectifs de population, de façon physiquement cohérente.
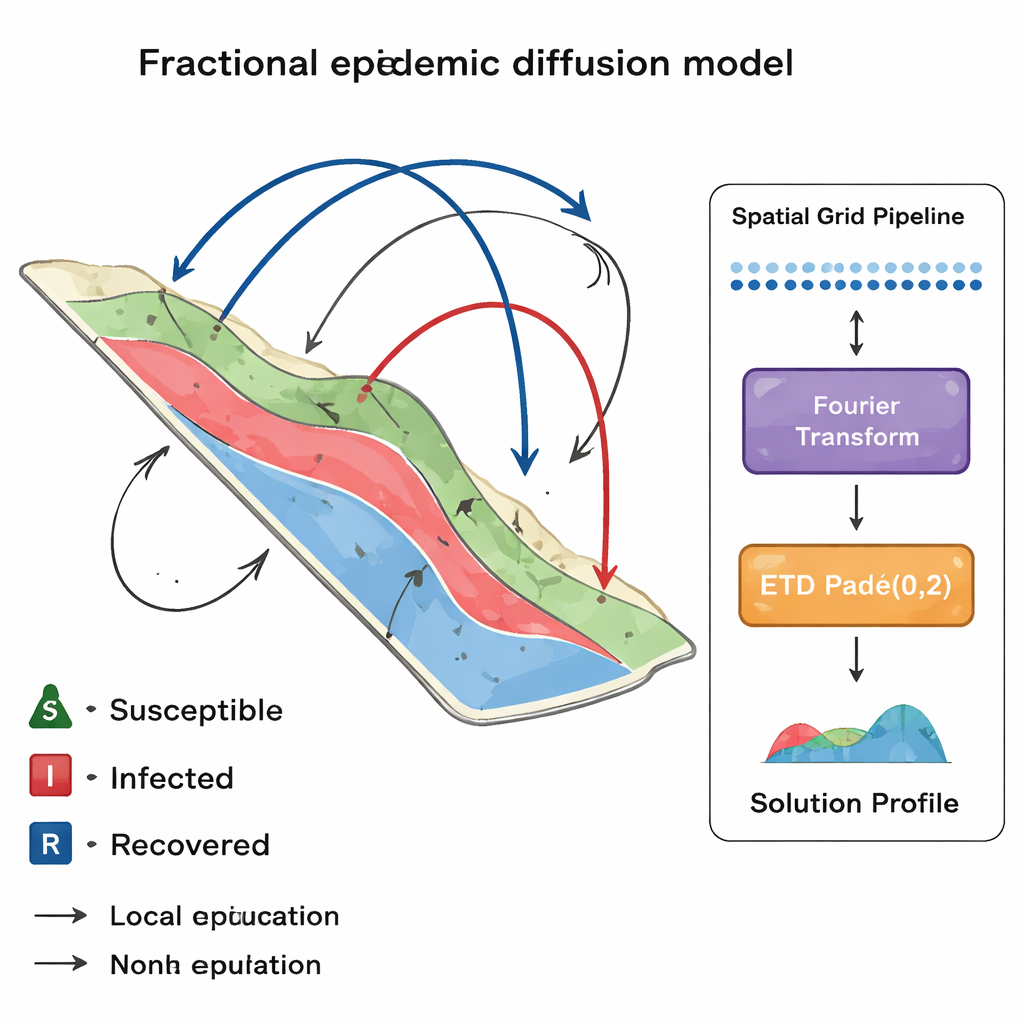
Du brassage local aux sauts lointains
Les modèles épidémiques traditionnels supposent en général que les individus ne se mélangent qu’avec leurs voisins proches, ce qui se décrit mathématiquement par la diffusion classique. Cette vision devient insuffisante en milieu peu dense ou très connecté, par exemple des régions rurales reliées par des autoroutes ou des lignes aériennes. Ici, les auteurs remplacent la diffusion classique par la « diffusion fractionnaire », un outil qui permet aux infections de sauter sur de longues distances selon une probabilité suivant une loi de puissance. Concrètement, le modèle peut représenter des déplacements rares mais significatifs qui ensemencent rapidement de nouveaux points chauds loin du foyer initial, modifiant ainsi le moment et le lieu des pics épidémiques.
Deux modèles familiers, améliorés
L’étude se concentre sur deux cadres épidémiques bien connus : le modèle SIR, qui divise la population en susceptibles, infectés et rétablis, et le modèle SEIR, qui ajoute une classe exposée (infectée mais pas encore contagieuse). Les deux sont étendus pour inclure la diffusion fractionnaire en espace, de sorte que chaque groupe peut se déplacer de façon non locale. Les auteurs analysent la stabilité de ces modèles — montrant quand une maladie s’éteint ou persiste — et calculent le nombre de reproduction de base, c’est‑à‑dire le nombre moyen de nouvelles infections engendrées par un cas unique. Ces résultats théoriques se relient directement aux expériences numériques : lorsque le nombre de reproduction est inférieur à un, l’état sans maladie est stable ; lorsqu’il le dépasse, les modèles aboutissent à un état endémique avec transmission persistante.
Garder les simulations réalistes et bien comportées
Simuler la diffusion fractionnaire est exigeant sur le plan mathématique : les opérateurs non locaux sont coûteux à évaluer et des méthodes naïves peuvent produire des valeurs de population négatives ou des résultats instables. Pour remédier à cela, les auteurs conçoivent un schéma numérique qui combine une méthode spectrale de Fourier en espace avec une stratégie particulière de pas de temps connue sous le nom de « exponential time differencing ». Un ingrédient clé est une approximation rationnelle, appelée Padé(0,2), choisie parce qu’elle est à la fois fortement amortissante (L‑stable) et préservatrice de la positivité. En termes concrets, la méthode lisse les composantes raides et rapidement variables sans introduire d’oscillations parasites et garantit que les tailles des compartiments — nombres de susceptibles, infectés ou rétablis — restent non négatives et conservent la population totale lorsque c’est approprié.
Tester la précision et explorer la propagation
Le cadre est validé sur un problème réaction–diffusion disposant d’une solution exacte connue, montrant un ordre trois en espace et un ordre deux en temps pour différents degrés de diffusion fractionnaire. Les auteurs appliquent ensuite leur méthode aux modèles fractionnaires SIR et SEIR avec des distributions initiales « en chapeau », où la plupart des infections commencent autour du centre d’une région. En faisant varier l’ordre fractionnaire, ils montrent comment des effets non locaux plus marqués entraînent une propagation spatiale plus rapide et des pics plus précoces. Des études de sensibilité sur des paramètres tels que le taux d’infection et les coefficients de mobilité révèlent comment la variation de l’intensité des déplacements ou du comportement de contact fait basculer le système de régimes sans maladie vers des régimes endémiques et modifie la forme des vagues d’infection à travers l’espace et le temps.
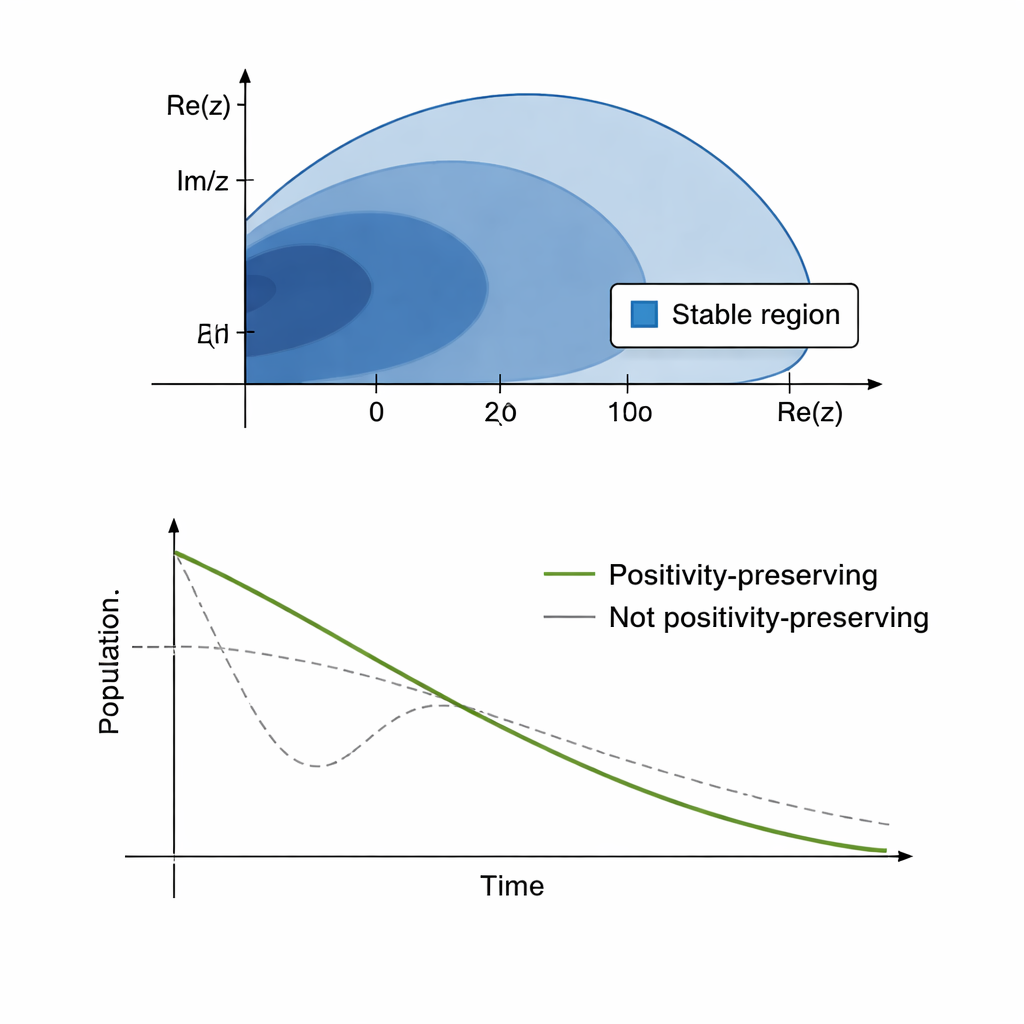
Ce que les résultats signifient pour la modélisation des épidémies
Dans l’ensemble, l’article propose une boîte à outils numérique stable, précise et efficace pour simuler des épidémies dans des contextes où les déplacements longue distance ne peuvent être négligés. Bien que le travail soit méthodologique plutôt que fondé sur des données, il prépare le terrain pour des études futures combinant des données de mobilité réelles avec des modèles de diffusion fractionnaire. Pour les planificateurs de santé publique, cette approche promet des cartes plus réalistes de la manière dont les infections se déplacent à travers des réseaux de communautés, et une base numérique plus sûre évitant des artefacts non physiques tels que des comptes négatifs de population. À ce titre, elle constitue une étape puissante vers une meilleure compréhension — et, en fin de compte, un meilleur contrôle — de la propagation géographique des maladies infectieuses.
Citation: Yousuf, M., Alshakhoury, N. Stability analysis and numerical simulation of nonlocal extended epidemic models using positivity-preserving scheme. Sci Rep 16, 5964 (2026). https://doi.org/10.1038/s41598-026-36463-9
Mots-clés: diffusion fractionnaire, modélisation épidémique, simulation numérique, propagation spatiale, analyse de stabilité