Clear Sky Science · fr
ONCOPLEX : un modèle hypergraphe inspiré de l’oncologie intégrant diverses connaissances biologiques pour la prédiction des gènes conducteurs du cancer
Pourquoi cette recherche est importante
Le cancer est provoqué par un petit nombre de changements génétiques puissants cachés parmi des milliers d’altérations inoffensives. Repérer ces vrais « gènes conducteurs » est essentiel pour améliorer le diagnostic et cibler les traitements, mais c’est comme identifier quelques meneurs dans une foule vaste et bruyante. Cette étude présente ONCOPLEX, un nouveau cadre d’intelligence artificielle qui n’examine pas les gènes un par un, mais les considère dans le contexte des voies biologiques où ils agissent ensemble, offrant une méthode plus précise pour repérer les gènes qui alimentent réellement les tumeurs.
Voir les gènes du cancer dans leurs voisinages biologiques
La plupart des méthodes actuelles scrutent les génomes tumoraux à la recherche de mutations qui apparaissent de façon anormale ou qui se distinguent dans des réseaux géniques simples. Ces approches sont utiles, mais la biologie est rarement si simple. Les gènes agissent généralement en groupes au sein de voies qui régulent la croissance cellulaire, la réparation de l’ADN et bien d’autres processus. ONCOPLEX embrasse cette complexité en représentant les gènes comme des points et les voies comme de larges groupes qui se chevauchent et peuvent contenir de nombreux gènes simultanément. Ce type de structure, appelé hypergraphe, permet au modèle de considérer directement des relations impliquant plusieurs gènes au lieu de les décomposer en de nombreux paires séparées.
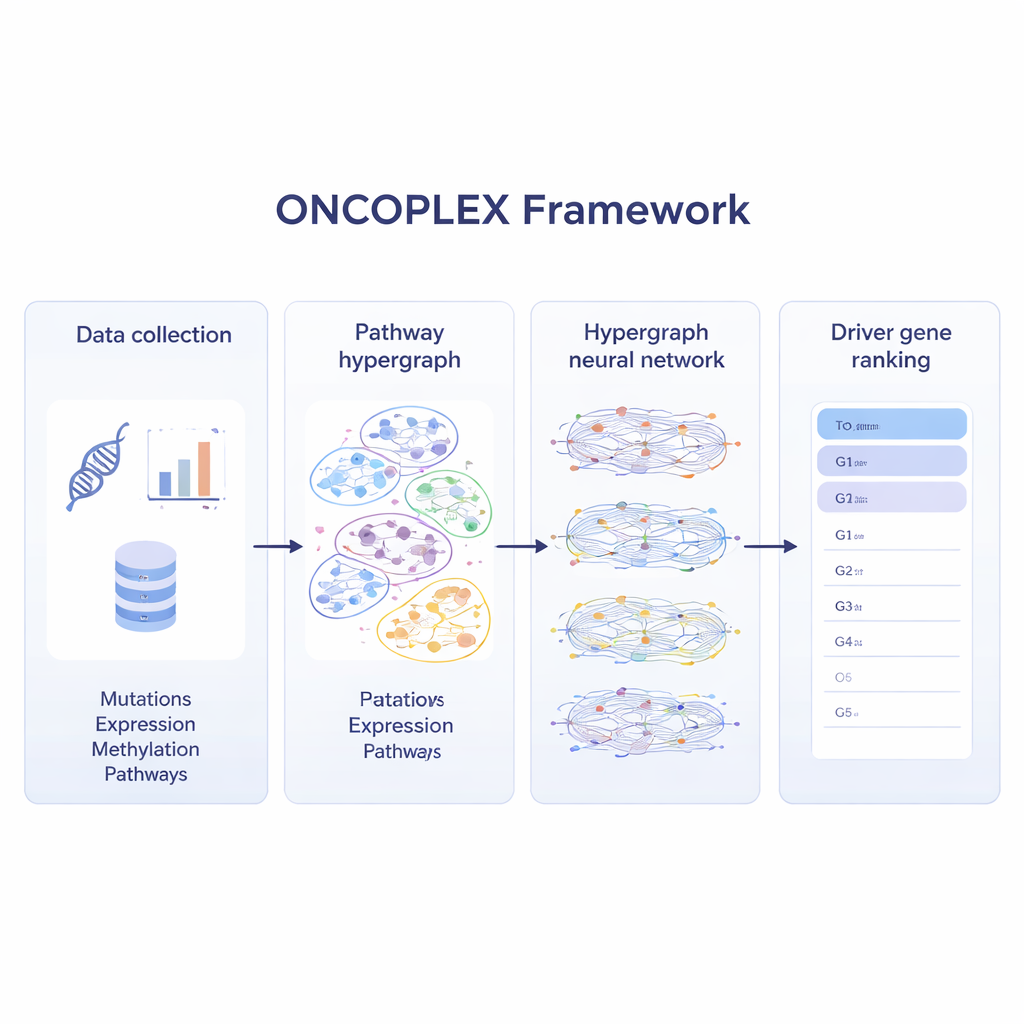
Mêler plusieurs couches de données sur le cancer
Pour tirer parti des jeux de données modernes sur le cancer, ONCOPLEX combine plusieurs types d’informations pour chaque gène. Il utilise les fréquences de mutation, les variations d’expression génique, les marques chimiques sur l’ADN (méthylation) et un ensemble riche de caractéristiques biologiques telles que la conservation évolutive et les annotations fonctionnelles. Ces caractéristiques sont attachées à chaque gène dans l’hypergraphe. Un réseau neuronal spécialisé fait ensuite circuler l’information à travers les voies, permettant à la représentation de chaque gène d’être façonnée à la fois par ses propres données et par le comportement des gènes avec lesquels il interagit. Le modèle est entraîné à l’aide de gènes déjà connus comme conducteurs du cancer, tout en apprenant également à partir de nombreux gènes non étiquetés qui pourraient être importants mais ne sont pas encore reconnus.
Des performances supérieures aux outils existants sur de nombreux cancers
Les chercheurs ont testé ONCOPLEX sur des données de The Cancer Genome Atlas, à la fois en regroupant plusieurs types de tumeurs et en examinant 11 cancers individuels, dont le sein, le poumon, le foie, la vessie et la tête et le cou. Ils l’ont comparé à plusieurs méthodes de pointe basées sur les graphes et les hypergraphes. Dans l’ensemble, ONCOPLEX distinguait mieux les gènes conducteurs connus des non-conducteurs beaucoup plus fréquents et classait les conducteurs probables en haut de ses listes. Son avantage était particulièrement net pour les gènes les mieux classés, où l’identification précise est la plus utile pour des expériences de suivi et la traduction clinique.
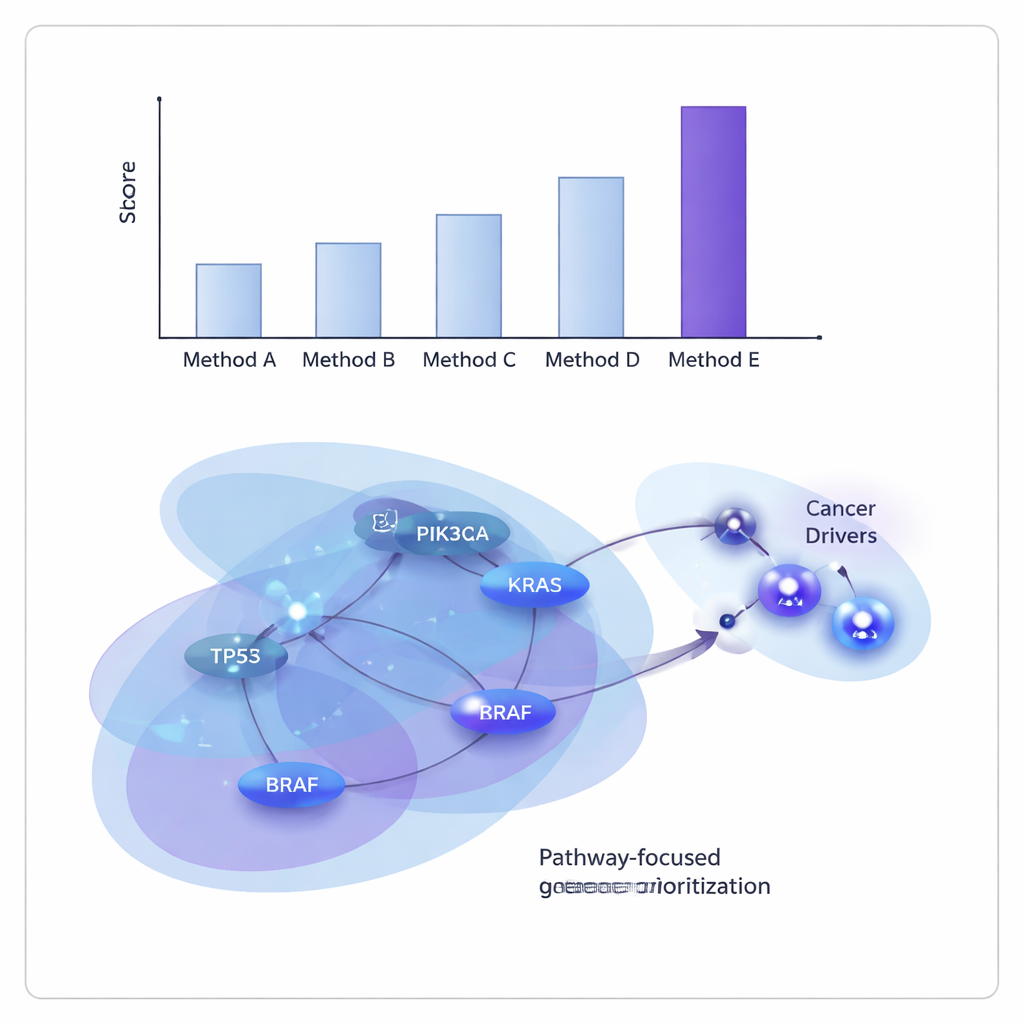
Mettre en lumière des coupables partagés et spécifiques au cancer
Au-delà des simples chiffres de performance, les listes de gènes classés par ONCOPLEX ont retrouvé de nombreux gènes cancéreux familiers, tels que KRAS, BRAF et des membres de la voie de signalisation PI3K–AKT, confirmant que le modèle capture une biologie bien établie. Il a également mis en avant des candidats prometteurs qui ne sont pas encore fermement reconnus comme conducteurs dans certains types de cancer, notamment des gènes comme GRB2 et MAPK3 dans le cancer du sein et SHC1 dans le cancer de l’estomac. Lorsque l’équipe a examiné les gènes les mieux classés via une analyse d’enrichissement de voies, ils ont trouvé des signatures fortes de voies cancéreuses bien connues, y compris la signalisation ErbB et PI3K–AKT–mTOR, ainsi que des voies liées à l’immunité, suggérant qu’ONCOPLEX cible des réseaux d’intérêt clinique.
Forces, limites et perspectives
En montrant que des caractéristiques biologiques plus riches améliorent régulièrement ses prédictions, ONCOPLEX démontre la valeur de la fusion de nombreuses sources de données au sein d’un cadre centré sur les voies. En même temps, l’étude met en évidence une limite : comme de nombreux cancers partagent un grand nombre de voies, le modèle favorise parfois des gènes « pan-cancer » d’action large au détriment de ceux qui sont véritablement spécifiques à un type de tumeur. Les auteurs suggèrent que des travaux futurs devraient affiner l’utilisation de l’information sur les voies afin de distinguer plus clairement les signaux communs et spécifiques au cancer.
Ce que cela signifie pour les patients et les cliniciens
Pour les non-spécialistes, l’essentiel est qu’ONCOPLEX offre une manière plus biologiquement réaliste de rechercher les gènes qui conduisent le cancer. En regardant les gènes dans la compagnie qu’ils tiennent — au sein des voies plutôt qu’isolément — il améliore notre capacité à repérer à la fois les conducteurs bien connus et ceux auparavant négligés, même dans des cancers peu étudiés à ce jour. Ce type d’outil peut aider les chercheurs à prioriser les gènes à étudier en laboratoire, orienter la recherche de nouvelles cibles médicamenteuses et, ultimement, soutenir des stratégies de traitement plus précises et conscientes des voies en oncologie.
Citation: Alotaibi, E.M., Alkhnbashi, O.S. & Tran, V.D. ONCOPLEX: an oncology-inspired hypergraph model integrating diverse biological knowledge for cancer driver gene prediction. Sci Rep 16, 5164 (2026). https://doi.org/10.1038/s41598-026-36127-8
Mots-clés: gènes conducteurs du cancer, réseaux neuronaux hypergraphiques, intégration multi-omique, analyse de voies, oncologie de précision