Clear Sky Science · fr
IL2Pepscan : un cadre d’apprentissage automatique pour prédire les peptides inducteurs d’IL‑2 et leur identification dans les protéomes viraux mondiaux
Apprendre au système immunitaire avec de minuscules fragments de protéines
Les vaccins modernes et les thérapies anticancéreuses reposent de plus en plus sur la modulation précise du système immunitaire plutôt que sur une attaque généralisée de la maladie par des médicaments. Cette étude examine comment de courts fragments de protéines, appelés peptides, peuvent être sélectionnés pour activer un messager immunitaire puissant, l’interleukine‑2 (IL‑2). En utilisant des modèles informatiques avancés, les auteurs explorent à la fois des données immunologiques connues et les catalogues protéiques de milliers de virus pour retrouver des « aiguilles » peptidiques dans une botte de foin moléculaire, en vue de concevoir de meilleurs vaccins et immunothérapies.
Pourquoi l’IL‑2 est importante pour la santé et la maladie
L’IL‑2 est une petite molécule de signalisation qui agit comme un facteur de croissance pour des cellules immunitaires clés appelées lymphocytes T. Lorsqu’elles rencontrent pour la première fois une menace — comme un virus ou une cellule tumorale — ces cellules peuvent libérer de l’IL‑2, qui encourage alors les lymphocytes T à se multiplier, à se spécialiser et à mémoriser l’envahisseur. L’IL‑2 contribue aussi au maintien des cellules T régulatrices qui empêchent le système immunitaire d’attaquer les tissus de l’organisme. En raison de ce double rôle, l’IL‑2 a été utilisée comme médicament pour traiter des cancers tels que le mélanome, et fait l’objet d’études dans les maladies auto‑immunes. Mais l’administration directe d’IL‑2 peut être pénible pour les patients, d’où l’intérêt croissant pour la conception de peptides sûrs qui stimulent la production d’IL‑2 par l’organisme de manière plus contrôlée et ciblée.
Apprivoiser le « goût » des peptides inducteurs d’IL‑2
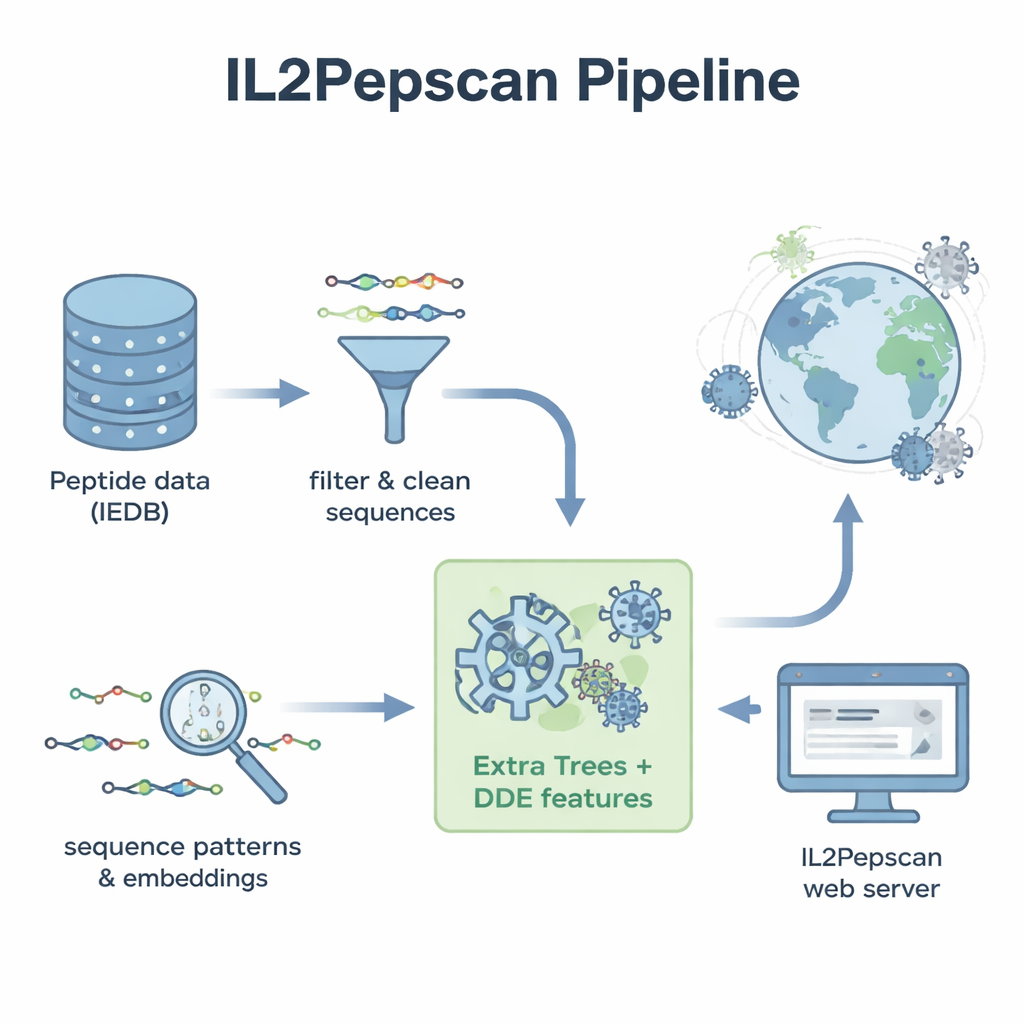
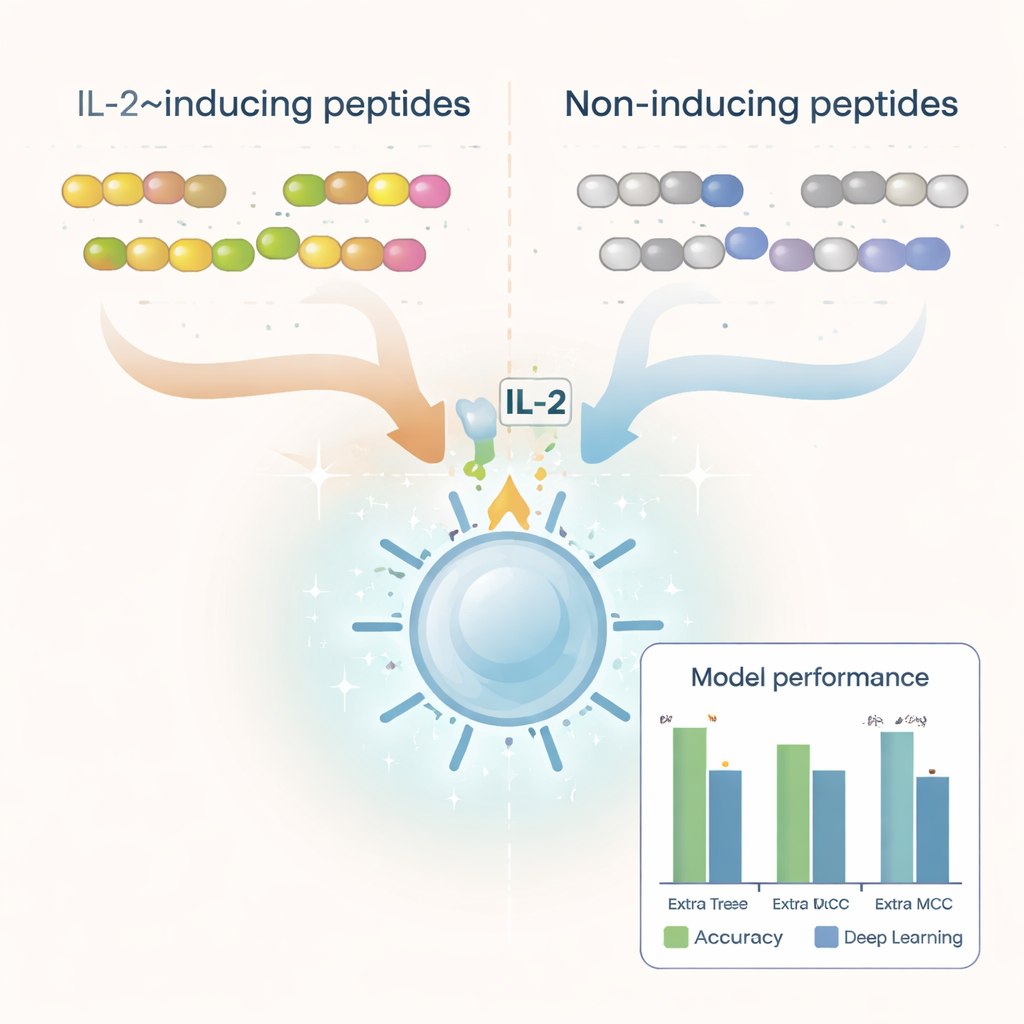
Les chercheurs ont commencé avec des milliers de séquences peptidiques déjà testées en laboratoire et étiquetées comme inductrices d’IL‑2 ou non. Ils ont nettoyé cet ensemble de données pour supprimer les doublons, les blocs de construction inhabituels et les peptides trop courts ou trop longs, aboutissant à plus de 6 000 exemples bien caractérisés. En examinant les acides aminés qui composent ces peptides, ils ont mis en évidence des différences nettes entre les deux groupes. Les peptides inducteurs d’IL‑2 avaient tendance à être plus riches en acides aminés hydrophobes, ou répulsifs à l’eau, comme la leucine et l’alanine, tandis que les peptides non inducteurs penchaient vers des résidus plus polaires et chargés. Certains motifs courts, comme « LEGS » et « ALEG », apparaissaient uniquement dans les peptides inducteurs d’IL‑2, suggérant des signatures structurales susceptibles d’aider à déclencher l’activation immunitaire.
Former des machines à repérer les motifs qui renforcent l’immunité
Pour transformer ces motifs en outil prédictif pratique, l’équipe a converti chaque peptide en descriptions numériques capturant sa composition et l’ordre de ses acides aminés. Ils ont testé une gamme de méthodes d’apprentissage automatique — y compris des algorithmes populaires comme les forêts aléatoires, les machines à vecteurs de support et les arbres boostés — ainsi que des architectures d’apprentissage profond souvent utilisées pour le langage et l’imagerie. Ils ont aussi exploité un grand « modèle de langage » protéique nommé ProtBERT, initialement entraîné sur des centaines de millions de séquences protéiques, et l’ont affiné pour mieux reconnaître les signaux liés à l’IL‑2. Après des tests approfondis par validation croisée et sur un jeu de test indépendant, le meilleur modèle s’est avéré être Extra Trees associé à un ensemble de caractéristiques appelé déviation dipeptidique par rapport à la moyenne attendue (DDE). Ce modèle a atteint près de 80 % de précision et un solide score de corrélation, surpassant plusieurs approches d’apprentissage profond.
Balayer le monde viral à la recherche de déclencheurs immunitaires cachés
Armés de leur meilleur modèle, les auteurs ont élargi leur recherche. Ils ont rassemblé des séquences protéiques de référence provenant de plus de 14 000 virus, découpé ces protéines en environ 156 millions de peptides chevauchants, et demandé au modèle de prédire lesquels pourraient induire l’IL‑2. Parmi les candidats les mieux notés figuraient des peptides de familles virales bien connues, notamment des flavivirus comme le virus du Nil occidental, le Zika, la fièvre jaune et l’hépatite C, ainsi que des virus de la grippe et du SARS‑CoV‑2. De nombreux peptides prometteurs provenaient de protéines d’enveloppe ou de la nucléocapside — les mêmes types de protéines que d’autres études ont montré capables de provoquer des réponses en IL‑2 chez les animaux. Le modèle a également mis en évidence des peptides potentiellement inducteurs d’IL‑2 codés par des bactériophages, des virus qui infectent les bactéries, suggérant un paysage encore plus vaste de séquences pertinentes pour l’immunité.
De l’algorithme à un outil accessible
Pour rendre leur travail utilisable au‑delà du laboratoire informatique, les auteurs ont construit un serveur web public appelé IL2Pepscan. Les chercheurs peuvent coller des séquences peptidiques ou protéiques sur le site pour estimer leur potentiel inducteur d’IL‑2, concevoir de nouvelles variantes en mutant des positions, scanner des protéines entières à la recherche de points chauds, ou rechercher des motifs connus liés à l’IL‑2. Bien que l’étude ne confirme pas encore expérimentalement chaque peptide prédit, la concordance avec des résultats de laboratoire existants suggère qu’IL2Pepscan peut réduire de manière fiable la liste de candidats à tester en priorité. Pour les non‑spécialistes, la conclusion est que des algorithmes bien entraînés peuvent trier d’énormes jeux de données biologiques pour identifier de petits fragments protéiques qui pourraient un jour aider les vaccins et les immunothérapies à susciter une réponse immunitaire plus puissante — et plus précise.
Citation: Arora, P., Abhigyan, R., Periwal, N. et al. IL2Pepscan: A machine learning framework for predicting IL-2 inducing peptides and their identification across global viral proteomes. Sci Rep 16, 6701 (2026). https://doi.org/10.1038/s41598-026-35977-6
Mots-clés: interleukine‑2, vaccins peptidiques, apprentissage automatique, protéome viral, immunothérapie