Clear Sky Science · fr
Analyse structurale de la liaison d’OCT4 aux nucléosomes humains de LIN28B
Comment les cellules accèdent aux instructions génétiques cachées
Toutes les cellules de votre corps portent le même ADN, pourtant seules une fraction de ces instructions génétiques sont utilisées selon le type cellulaire. Une grande partie de ce contrôle tient à la manière dont l’ADN est étroitement enroulé autour de protéines appelées histones, formant des structures nommées nucléosomes. Cet empaquetage serré peut masquer des séquences d’ADN clés à la machinerie cellulaire qui lit les gènes. L’étude décrite ici examine comment une protéine particulière, OCT4, parvient à trouver et à se lier à son ADN cible même lorsque cet ADN est enroulé et partiellement masqué dans des nucléosomes, un processus central pour l’identité des cellules souches et le reprogrammation cellulaire.
Pourquoi les facteurs pionniers sont importants pour les cellules souches
OCT4 appartient à un petit groupe puissant de protéines appelées facteurs de transcription pionniers. Contrairement à la plupart des protéines liant l’ADN, les pionniers peuvent s’insérer dans des régions compactes et « éteintes » du génome et aider à activer des gènes, jouant un rôle crucial dans la détermination de l’identité cellulaire et dans la reprogrammation de cellules adultes vers des états proches des cellules souches. OCT4 agit en coopération avec des partenaires tels que SOX2, KLF4 et c-MYC pour induire la pluripotence, la propriété qui permet aux cellules souches de se différencier en quasiment n’importe quel type cellulaire. Comprendre précisément comment OCT4 s’accroche à l’ADN enroulé dans les nucléosomes est essentiel pour décoder la façon dont les cellules changent de destin et pour concevoir des moyens plus précis de manipuler l’identité cellulaire en recherche et en médecine.
Vérifier si les différences entre espèces comptent
La plupart des études structurales des nucléosomes utilisent des histones provenant soit de grenouilles (Xenopus laevis), soit d’humains, car ces protéines sont très similaires mais pas identiques. De petites différences dans leurs séquences d’acides aminés pourraient, en théorie, modifier la façon dont l’ADN est enroulé ou la manière dont des protéines régulatrices comme OCT4 se lient. Dans des travaux antérieurs, les auteurs ont montré qu’OCT4 se lie à une séquence régulatrice spécifique du gène humain LIN28B lorsque cet ADN est enroulé dans des nucléosomes formés avec des histones de grenouille. Dans la nouvelle étude, ils ont posé une question simple mais importante : OCT4 se comporte-t-il de la même façon lorsque les nucléosomes sont assemblés avec des histones humains plutôt qu’avec des histones de grenouille ?
Assembler et sonder les nucléosomes de LIN28B
Pour répondre à cette question, les chercheurs ont reconstitué des nucléosomes en laboratoire en utilisant un segment de 182 paires de bases de l’ADN de LIN28B et soit des histones humains, soit des histones de grenouille, assemblés par une méthode de « dialyse lente » qui mime les conditions cellulaires. Des essais par électrophorèse ont confirmé que les deux types d’octamères d’histones formaient efficacement des nucléosomes. Ils ont ensuite examiné comment ces nucléosomes se positionnent sur l’ADN de LIN28B. Des expériences sur gel et un découpage de l’ADN suivi de séquençage (MNase-seq) ont montré que l’ADN de LIN28B peut adopter plusieurs positions sur le cœur histone, et ce comportement ne changeait pas lorsque les nucléosomes étaient portés à la température corporelle. Surtout, le fait que les histones proviennent de grenouille ou d’humain n’a eu aucune incidence notable sur le positionnement de l’ADN ni sur l’affinité d’OCT4.
Visualiser OCT4 sur le nucléosome
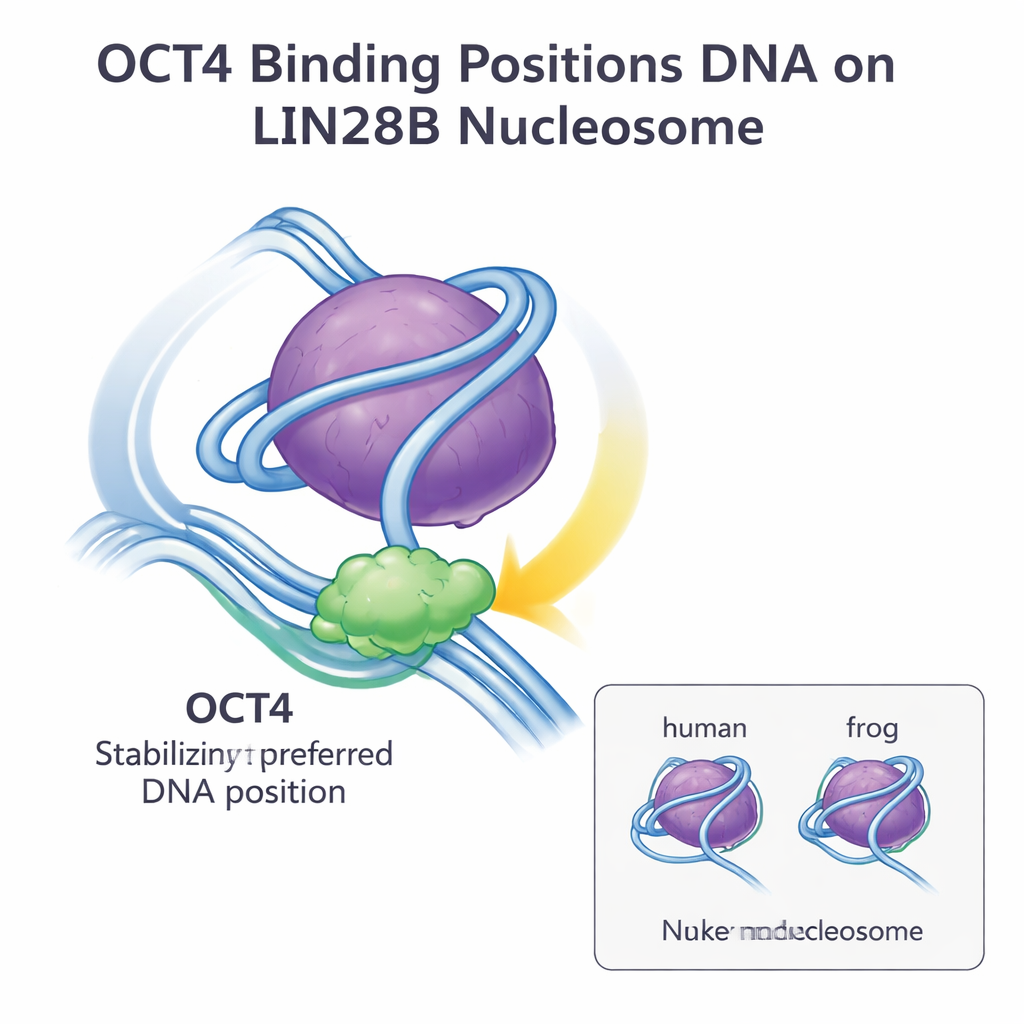
L’équipe a ensuite utilisé la cryo-microscopie électronique (cryo-EM) pour visualiser la structure d’OCT4 lié aux nucléosomes LIN28B contenant des histones humains. À partir d’environ 15 000 particules, ils ont reconstruit une carte tridimensionnelle à une résolution d’environ 6 angströms. Les images ont révélé que les deux domaines de liaison à l’ADN d’OCT4 contactent le même segment exposé d’ADN près du point d’entrée/sortie du nucléosome, la région dite linker. C’est exactement le site et l’orientation observés précédemment lorsque OCT4 était lié à des nucléosomes constitués d’histones de grenouille. Lorsque l’ancien modèle a été ajusté à la nouvelle carte cryo-EM, la concordance était excellente, indiquant que l’architecture globale du complexe OCT4–nucléosome LIN28B est essentiellement identique entre les deux espèces.
Une stratégie générale pour ouvrir la chromatine
Ensemble, ces résultats montrent que de petites différences de séquence entre les histones de grenouille et d’humain n’altèrent pas la reconnaissance et la liaison d’OCT4 au nucléosome LIN28B. L’ADN de LIN28B se place naturellement en plusieurs positions possibles sur le cœur histone, mais la liaison d’OCT4 sélectionne et stabilise une position préférentielle, rendant d’autres sites de liaison plus accessibles à OCT4 et à ses partenaires. Cette stratégie de « positionnement et stabilisation de l’ADN » semble être une manière générale par laquelle les facteurs pionniers accèdent à la chromatine fermée et favorisent la liaison coopérative d’autres régulateurs. Pour un public non spécialisé, la conclusion est que la conception de base du nucléosome et la façon dont des protéines régulatrices clés comme OCT4 travaillent avec lui sont fortement conservées entre espèces, ce qui renforce l’idée que les connaissances issues d’organismes modèles peuvent éclairer de manière fiable notre compréhension du contrôle des gènes humains et de la biologie des cellules souches.
Citation: Sinha, K.K., Halic, M. Structural analysis of OCT4 binding to human LIN28B nucleosomes. Sci Rep 16, 5704 (2026). https://doi.org/10.1038/s41598-026-35959-8
Mots-clés: facteurs de transcription pionniers, OCT4, structure des nucléosomes, accessibilité de la chromatine, régulation des gènes des cellules souches