Clear Sky Science · fr
SwiM-UNet léger avec adapteur multidimensionnel pour une segmentation d’images médicales efficace sur appareil
Des examens plus intelligents au chevet
Les examens cérébraux peuvent révéler des tumeurs menaçant le pronostic vital, mais transformer des images brutes en contours clairs exploitables par les médecins reste souvent lent et gourmand en calcul. Cette étude présente SwiM‑UNet, un nouvel algorithme capable de segmenter les tumeurs cérébrales à partir d’IRM 3D avec une précision de pointe tout en s’exécutant efficacement sur des appareils locaux, rapprochant l’analyse d’images précise du chevet du patient, voire de cliniques mobiles. 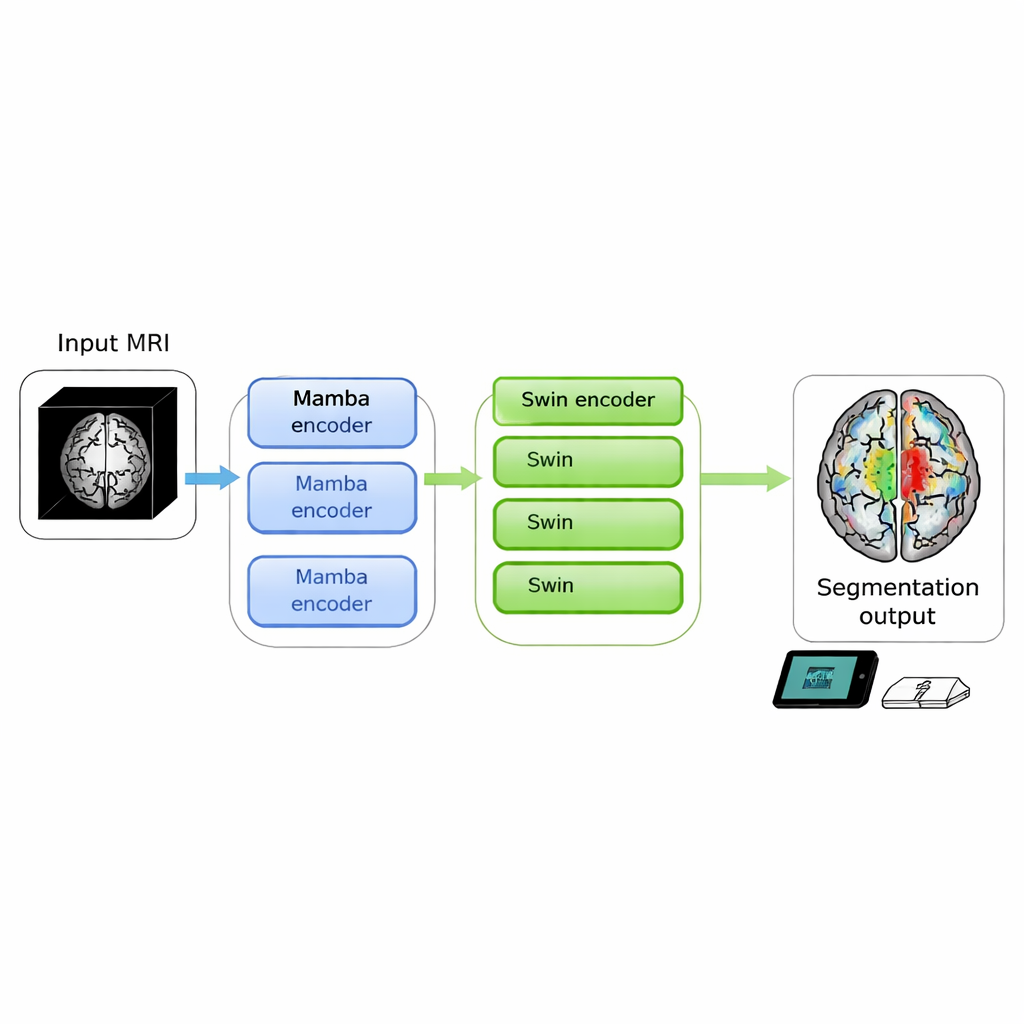
Pourquoi des contours de tumeur précis comptent
La médecine moderne s’appuie fortement sur l’imagerie pour planifier chirurgies, radiothérapies et traitements médicamenteux. Pour les tumeurs cérébrales, les cliniciens ont besoin non seulement de détecter la présence d’une tumeur, mais aussi de connaître précisément où commencent et se terminent ses différentes composantes. Cette tâche, appelée segmentation, est généralement réalisée ou affinée par des spécialistes coupe par coupe — un processus chronophage qui peut retarder les décisions et varier d’un expert à l’autre. Les outils de segmentation automatisée basés sur l’apprentissage profond ont amélioré la situation, mais les modèles les plus précis exigent souvent de puissants processeurs graphiques, ce qui complique leur utilisation directement en clinique, surtout sur des machines portables ou compactes.
Deux idées puissantes qui ne tiennent pas facilement sur de petits appareils
Les percées récentes en vision par ordinateur proviennent principalement de deux familles de modèles. Les systèmes basés sur les transformers, comme le Swin Transformer, excellent à capter des motifs globaux sur un volume 3D entier et ont permis d’obtenir des segmentations de premier plan pour les tumeurs cérébrales. Cependant, leur opération centrale, appelée self‑attention, devient extrêmement coûteuse lorsque la taille de l’image augmente, limitant leur usage en temps réel ou sur du matériel compact. Une famille plus récente, connue sous le nom de Mamba et fondée sur des modèles d’état d’espace, propose une astuce ingénieuse : elle traite les séquences en temps linéaire effectif, réduisant le nombre de calculs nécessaires. Les premiers tests en imagerie médicale ont montré que les modèles de type Mamba sont rapides et efficaces mais accusent généralement un retard par rapport aux transformers en qualité de segmentation, notamment pour des formes tumorales complexes.
Mélanger vitesse et précision dans une même architecture
Les auteurs ont cherché à fusionner les atouts des deux approches au sein d’un seul modèle 3D. Leur SwiM‑UNet conserve la structure en U familière en imagerie médicale, avec un encodeur qui compresse l’information et un décodeur qui reconstruit des segmentations détaillées. Aux premiers niveaux, lorsque le volume est encore grand et de haute résolution, ils utilisent des blocs Mamba efficaces pour maîtriser la charge de calcul. Plus profondément dans le réseau, après sous‑échantillonnage des données, ils basculent vers des blocs Swin Transformer allégés qui peuvent alors se permettre de modéliser des relations à longue portée sans surcharger le matériel. Un pont personnalisé appelé MS‑adapter relie ces deux régimes. Il examine les caractéristiques le long de la largeur, de la hauteur et de la profondeur du volume séparément, ainsi que selon les canaux, puis apprend via de petites unités de gating combien chaque vue doit influencer la représentation finale. 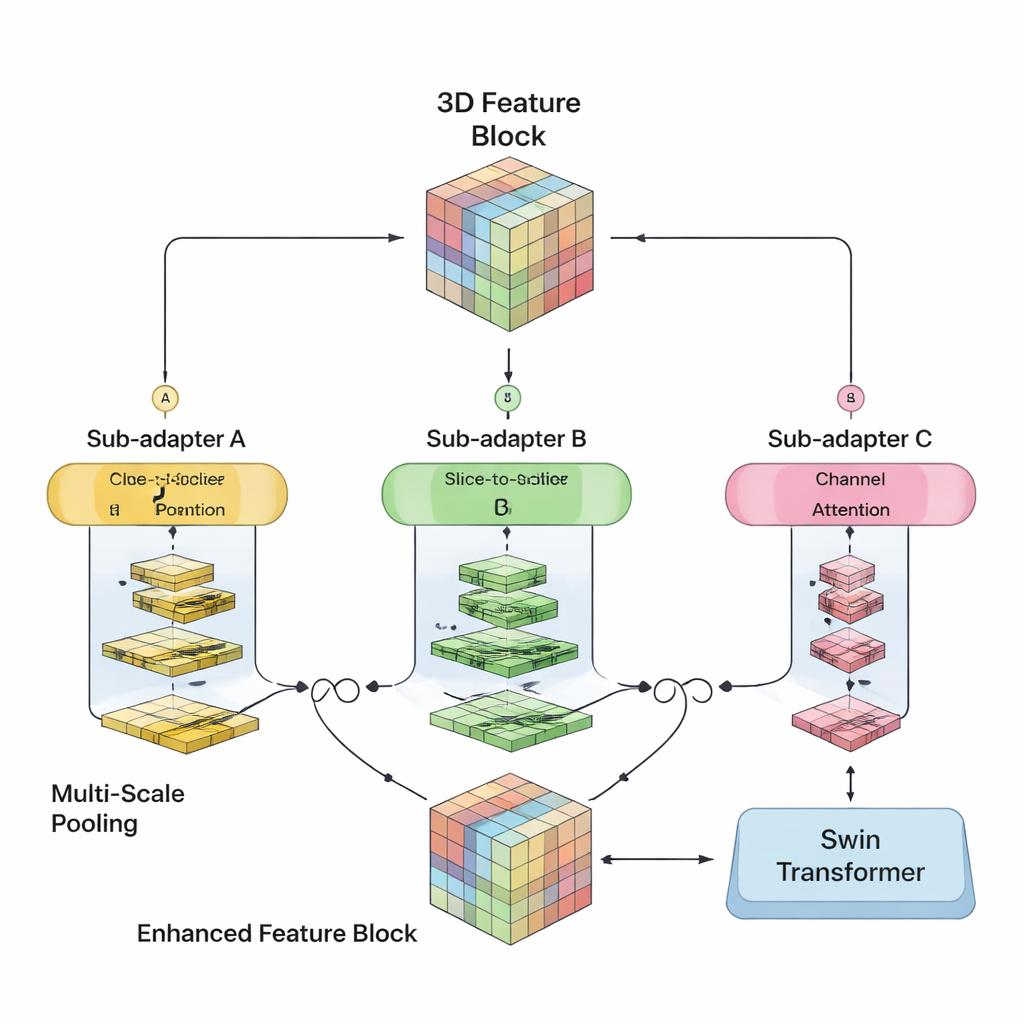
Faire plus avec moins de calcul
Au‑delà de cette architecture hybride, l’équipe réduit les calculs superflus en employant des couches entièrement connectées de faible rang et un décodeur qui diminue délibérément le nombre de canaux à traiter. Ils ont testé plusieurs variantes avec différents mélanges de couches Mamba et Swin et ont constaté que l’utilisation de Mamba dans les trois premiers étages de l’encodeur et de Swin uniquement à l’étage le plus profond offrait le meilleur compromis entre rapidité et précision. Sur deux grands jeux de données publics de tumeurs cérébrales issus des défis BraTS 2023 et 2024, SwiM‑UNet a obtenu une précision supérieure et des contours plus précis que les principaux modèles uniquement basés sur des transformers, uniquement sur Mamba ou précédemment hybrides, tout en utilisant beaucoup moins d’opérations en virgule flottante et en réduisant le temps d’inférence à environ 45 millisecondes par patch de scan sur une carte graphique moderne.
Prêt pour des appareils du monde réel
Pour vérifier si ces gains ont un intérêt hors laboratoire, les auteurs ont comparé les besoins de calcul du modèle aux capacités des systèmes edge cliniques typiques — consoles IRM portables, ordinateurs de point de soin et postes de travail en bloc opératoire. Leur analyse indique que, contrairement aux modèles transformer plus lourds, SwiM‑UNet tient confortablement dans les limites de puissance, de mémoire et de vitesse de tels appareils, répondant souvent aux exigences temps réel. Il a aussi obtenu de bonnes performances sur un jeu de données CT abdominal distinct, ce qui suggère que l’approche peut se généraliser au‑delà des tumeurs cérébrales et même au‑delà de l’IRM.
Ce que cela signifie pour les patients et les cliniciens
En termes pratiques, SwiM‑UNet montre qu’il est possible de se rapprocher de la précision des modèles de segmentation les plus sophistiqués tout en maintenant une charge de calcul suffisamment légère pour un usage sur appareil. Cela pourrait permettre d’obtenir des contours tumoraux plus rapides et plus cohérents dans les services d’urgence, les hôpitaux ruraux ou les unités d’imagerie mobiles sans envoyer des scans sensibles vers des serveurs éloignés. Bien que des travaux supplémentaires soient nécessaires pour adapter la méthode à différents appareils et conditions, ce design hybride ouvre la voie à un futur où l’analyse d’images de haute qualité s’exécute là où se trouve le patient, et non seulement dans des centres de données.
Citation: Noh, Y., Lee, S., Jin, S. et al. Lightweight SwiM-UNet with multi-dimensional adaptor for efficient on-device medical image segmentation. Sci Rep 16, 5807 (2026). https://doi.org/10.1038/s41598-026-35771-4
Mots-clés: segmentation des tumeurs cérébrales, IA en imagerie médicale, réseaux neuronaux hybrides, inférence sur appareil, analyse 3D par IRM