Clear Sky Science · fr
Méthodes PCA dissociatives structurées pour la décomposition de signaux neuroimagerie en haute dimension
Démêler les signaux cachés du cerveau
Les scanners cérébraux modernes peuvent enregistrer l’activité de centaines de milliers d’emplacements chaque seconde, mais transformer ce torrent de chiffres en réseaux clairs et significatifs est extrêmement difficile. Différents processus cérébraux se chevauchent souvent dans l’espace et le temps, comme plusieurs stations de radio émettant sur des fréquences proches. Cet article présente de nouveaux outils mathématiques qui aident à séparer ces signaux embrouillés de manière plus nette, promettant des cartes de fonction cérébrale plus précises pour la recherche fondamentale et les études cliniques.
Pourquoi les méthodes habituelles sont insuffisantes
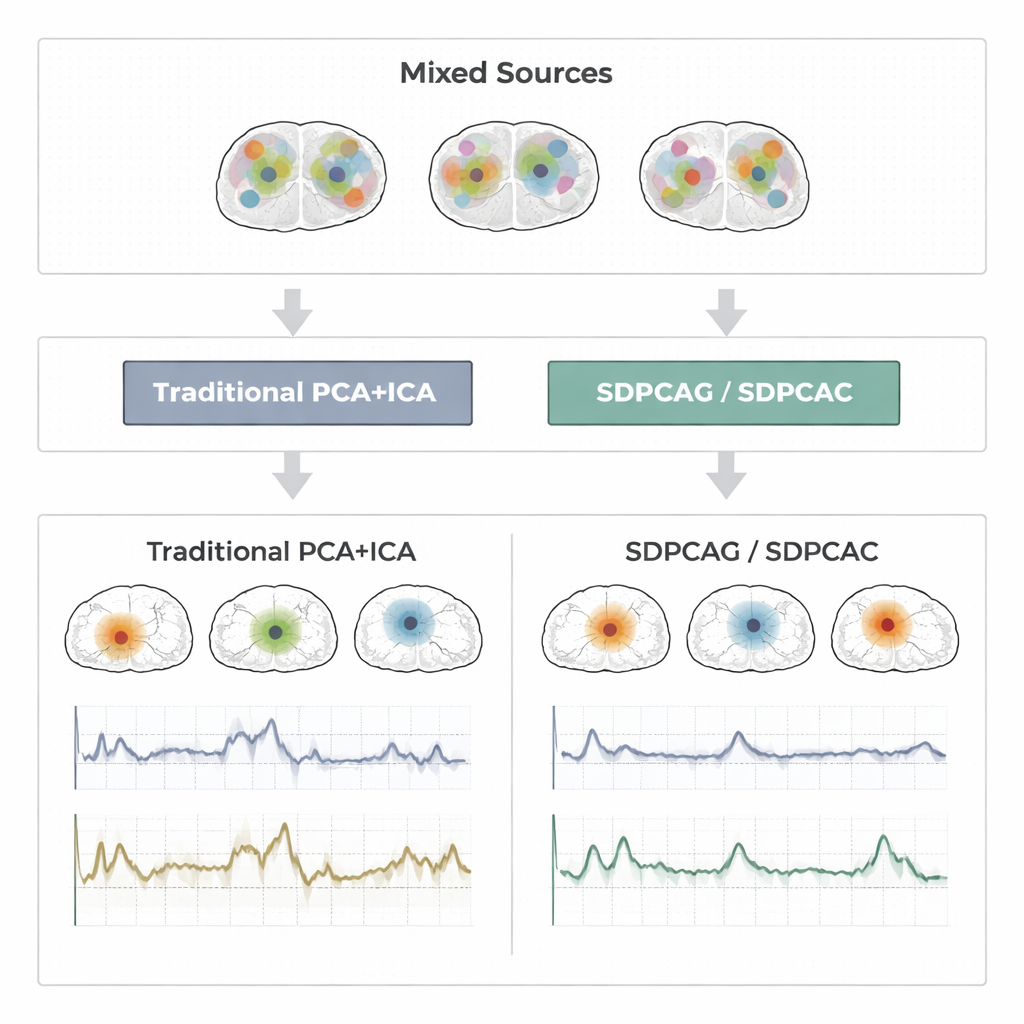
Pendant des décennies, les chercheurs ont utilisé des techniques appelées analyse en composantes principales (PCA), PCA parcimonieuse, et analyse en composantes indépendantes (ICA) pour compresser et séparer les données d’IRM fonctionnelle (fMRI). La PCA identifie des motifs qui expliquent l’essentiel de la variance des données, mais chaque motif mélange l’information provenant d’à peu près tous les emplacements cérébraux, ce qui complique l’interprétation. La PCA parcimonieuse tente de corriger cela en forçant chaque motif à n’utiliser qu’un sous-ensemble d’emplacements, et l’ICA va plus loin en supposant que les signaux cérébraux sous-jacents sont statistiquement indépendants. En pratique, cependant, les réseaux cérébraux réels se chevauchent et s’influencent mutuellement. Lorsque cela se produit, les hypothèses d’indépendance et de parcimonie s’effondrent. Le résultat peut être des cartes fragmentées et des séries temporelles bruyantes qui ne correspondent plus au comportement réel des réseaux cérébraux.
Une nouvelle façon de séparer les signaux
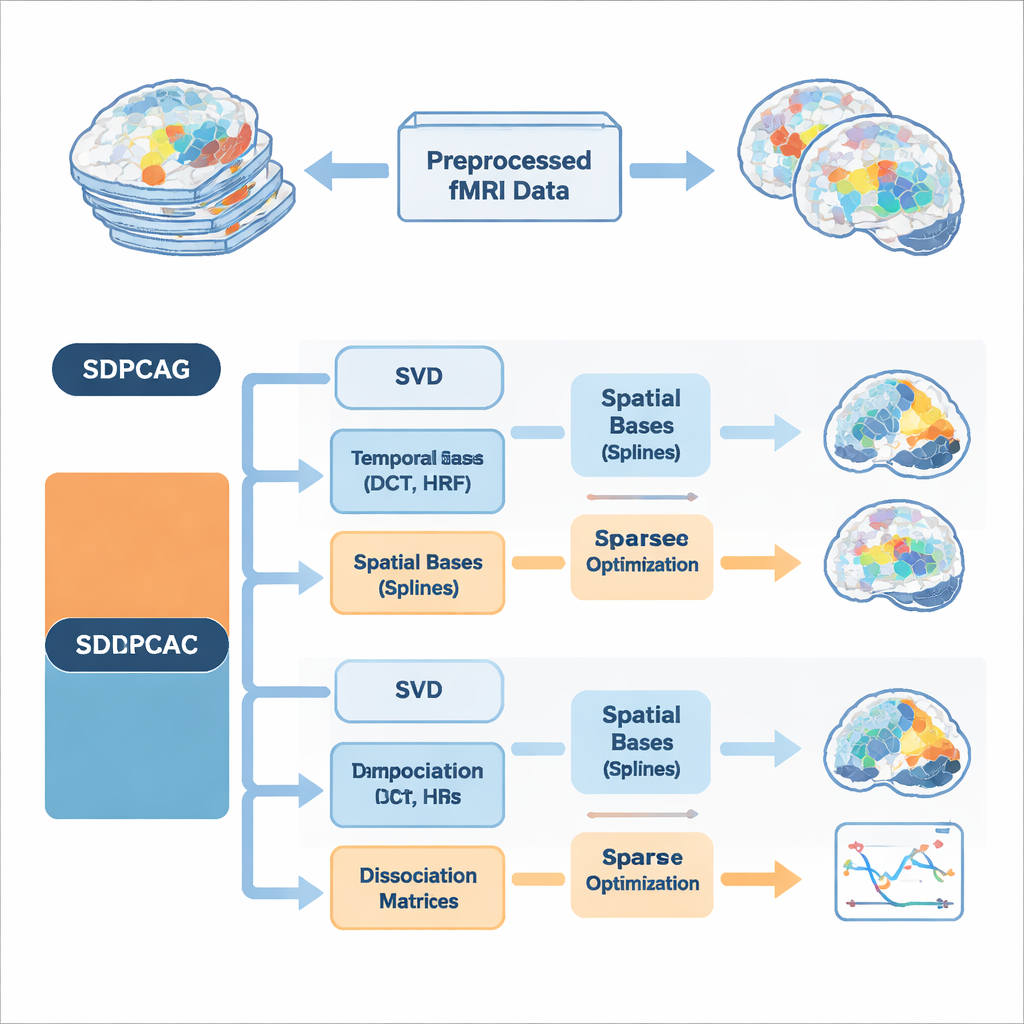
Les auteurs proposent un cadre unifié appelé PCA dissociative structurée, implémenté dans deux algorithmes nommés SDPCAG et SDPCAC. Plutôt que de traiter l’espace et le temps séparément, la méthode reconfigure l’ensemble du jeu de données fMRI via une seule décomposition soigneusement conçue. Elle part d’une décomposition standard de faible rang des données, puis introduit des matrices de « dissociation » spéciales qui repondèrent et tournent ensemble cartes spatiales et courses temporelles. Simultanément, elle représente ces composantes à l’aide d’ensembles d’éléments de base lisses : des ondes temporelles de type cosinus, des modèles de la réponse hémodynamique du cerveau à l’activité neuronale, et des courbes spatiales lisses appelées splines. En apprenant à combiner ces éléments tout en appliquant la parcimonie — ne conservant que les pièces les plus importantes — la méthode peut démêler des réseaux qui se chevauchent sans imposer une indépendance irréaliste.
Intégrer les connaissances cérébrales dès le départ
Une innovation clé est que les algorithmes incorporent les connaissances a priori sur les signaux cérébraux directement dans la décomposition, plutôt que d’assainir les résultats après coup. Côté temporel, ils utilisent des fonctions cosinus discrètes pour encourager des courses temporelles lisses et incluent des modèles standards de la réponse hémodynamique, le signal retardé d’oxygénation sanguine mesuré par la fMRI. Côté spatial, des bases de splines favorisent des motifs d’activation contigus et cohérents au lieu de points dispersés. Des contraintes supplémentaires limitent le nombre de fonctions de base temporelles et spatiales que chaque composante peut utiliser, ce qui réduit le surapprentissage du bruit et reflète l’idée que les réseaux cérébraux réels sont relativement compacts à la fois dans l’espace et dans le temps. Deux stratégies d’optimisation complémentaires sont proposées : SDPCAG met à jour des matrices entières par blocs, tandis que SDPCAC affine une composante à la fois en utilisant les erreurs résiduelles, échangeant un coût légèrement supérieur contre des ajustements plus flexibles.
Évaluer la méthode
Pour juger de l’efficacité de ces idées, les auteurs réalisent des tests approfondis sur trois types de données : des signaux fMRI synthétiques soigneusement conçus avec vérité terrain connue ; une expérience motrice en bloc issue du Human Connectome Project ; et une étude événementielle de tapotement de doigt provenant d’un laboratoire indépendant. Dans ces contextes, ils comparent SDPCAG et SDPCAC à des méthodes concurrentes de premier plan combinant décomposition matricielle pénalisée, PCA parcimonieuse, ICA et apprentissage de dictionnaire. Ils mesurent la concordance entre les courses temporelles retrouvées et les modèles de tâches connus, l’alignement des cartes spatiales avec des réseaux au repos établis, et la précision de la récupération des sources sous différents niveaux de bruit. Les nouvelles méthodes produisent de manière constante des cartes cérébrales plus propres et plus localisées et des séries temporelles moins bruitées, en conservant de bonnes performances même lorsque les données sont fortement corrompues. L’un des algorithmes, SDPCAG, améliore la précision de récupération des sources d’environ 22 % par rapport à une méthode concurrente solide, tout en s’exécutant plus rapidement que sa parente plus détaillée SDPCAC.
Ce que cela signifie pour la recherche cérébrale
En termes simples, ce travail offre une meilleure façon de « démixer » les signaux contenus dans les données fMRI. En modélisant conjointement l’espace et le temps, en utilisant des priors réalistes sur le comportement de l’activité cérébrale et du flux sanguin, et en appliquant une parcimonie intelligente, SDPCAG et SDPCAC produisent des réseaux cérébraux à la fois plus nets sur les images et plus fidèles à leurs courses temporelles sous-jacentes. Cela peut conduire à une détection plus fiable des activations liées aux tâches et à une cartographie plus précise des réseaux au repos, ce qui soutient à son tour les études de pathologies comme la maladie d’Alzheimer, les troubles psychiatriques et d’autres affections cérébrales. Bien qu’il reste possible d’accélérer et d’étendre l’approche — par exemple aux études multi-sujets ou à l’imagerie multimodale — elle représente un progrès significatif vers la transformation des données de scan haute dimension en images interprétables et dignes de confiance du cerveau humain en action.
Citation: Khalid, M.U., Nauman, M.M., Rehman, S.U. et al. Structured dissociative PCA methods for high dimensional neuroimaging signal decomposition. Sci Rep 16, 6911 (2026). https://doi.org/10.1038/s41598-026-35764-3
Mots-clés: décomposition du signal fMRI, PCA parcimonieuse, cartographie des réseaux cérébraux, séparation aveugle des sources, connectivité au repos