Clear Sky Science · fr
Classification des globules blancs à l’aide d’un réseau neuronal profond personnalisé et visualisation des caractéristiques des images par cartes thermiques
Pourquoi des tests sanguins plus intelligents comptent
Une analyse sanguine de routine peut révéler des signes précoces d’infection, d’allergie ou même de cancer — mais aujourd’hui, une grande partie de ces informations dépend encore d’experts inspectant soigneusement les cellules au microscope. Ce processus est lent, coûteux et pas toujours disponible dans les petites cliniques ou les hôpitaux ruraux. L’article décrit ici présente un système d’intelligence artificielle compact capable de reconnaître avec précision différents types de globules blancs à partir d’images au microscope, offrant potentiellement une analyse sanguine plus rapide et plus fiable à un plus grand nombre de patients.
Les petits défenseurs du corps
Les globules blancs sont les défenseurs de première ligne du corps contre les germes et autres menaces. Ils existent en plusieurs variétés principales, chacune avec un rôle distinct : certains attaquent les bactéries, d’autres combattent les parasites, réagissent aux allergies ou aident à coordonner l’immunité à long terme. Les médecins examinent souvent à la fois le nombre et le type de ces cellules pour diagnostiquer des maladies et suivre des traitements. Aujourd’hui, cela se fait généralement soit par comptage manuel au microscope — une tâche qualifiée mais chronophage — soit à l’aide de grandes machines automatisées que de nombreux laboratoires de petite taille ne peuvent pas s’offrir.
Du comptage manuel aux yeux numériques
Au cours de la dernière décennie, les chercheurs se sont tournés vers la vision par ordinateur et l’apprentissage machine pour aider à automatiser l’identification des globules blancs. Les programmes basiques peuvent mesurer formes et couleurs, tandis que des systèmes plus avancés utilisent l’apprentissage profond, qui peut apprendre des motifs complexes directement à partir des images. Toutefois, de nombreux modèles d’apprentissage profond puissants sont énormes, nécessitent une puissance de calcul et une mémoire importantes, et peuvent souffrir de problèmes d’entraînement tels que l’affaiblissement des signaux à l’intérieur du réseau. Cela limite leur utilisation dans les petites cliniques, les dispositifs de santé mobiles ou les hôpitaux aux ressources informatiques modestes.
Un microscope numérique maigre mais puissant
Les auteurs présentent un modèle d’apprentissage profond rationalisé qu’ils appellent réseau neuronal profond personnalisé, ou CDNN. Il est conçu spécifiquement pour reconnaître les globules blancs dans des images au microscope. Le modèle a été entraîné et testé sur deux jeux de données populaires d’images de cellules sanguines : un grand ensemble quelque peu déséquilibré (Raabin WBC) avec cinq types de globules blancs, et un autre plus petit mais équilibré (BCCD) avec quatre types. Avant l’entraînement, toutes les images ont été redimensionnées, leur luminosité normalisée, puis légèrement modifiées — rotation, réflexion et cisaillement — pour reproduire la variation naturelle et réduire le surapprentissage, phénomène où un modèle mémorise les exemples d’entraînement au lieu d’apprendre des motifs généraux.
À l’intérieur du « processus de pensée » du modèle
Le CDNN est construit à partir d’une série de blocs qui l’aident à apprendre efficacement tout en restant compact. Ces blocs incluent des connexions « résiduelles » qui permettent à l’information de contourner certaines couches, empêchant ainsi les signaux d’entraînement de s’atténuer au fur et à mesure qu’ils traversent le réseau. Le modèle augmente progressivement le nombre de filtres internes à mesure que les images le traversent, capturant à la fois les détails fins et les formes plus larges des noyaux cellulaires et du matériau environnant. Malgré un nombre d’hyperparamètres bien inférieur à celui de modèles d’images connus tels que VGG16 ou ResNet-50, le CDNN atteint une très grande précision : environ 98 % sur le jeu Raabin et près de 99,6 % sur le jeu BCCD, surpassant de nombreuses méthodes de pointe plus volumineuses.
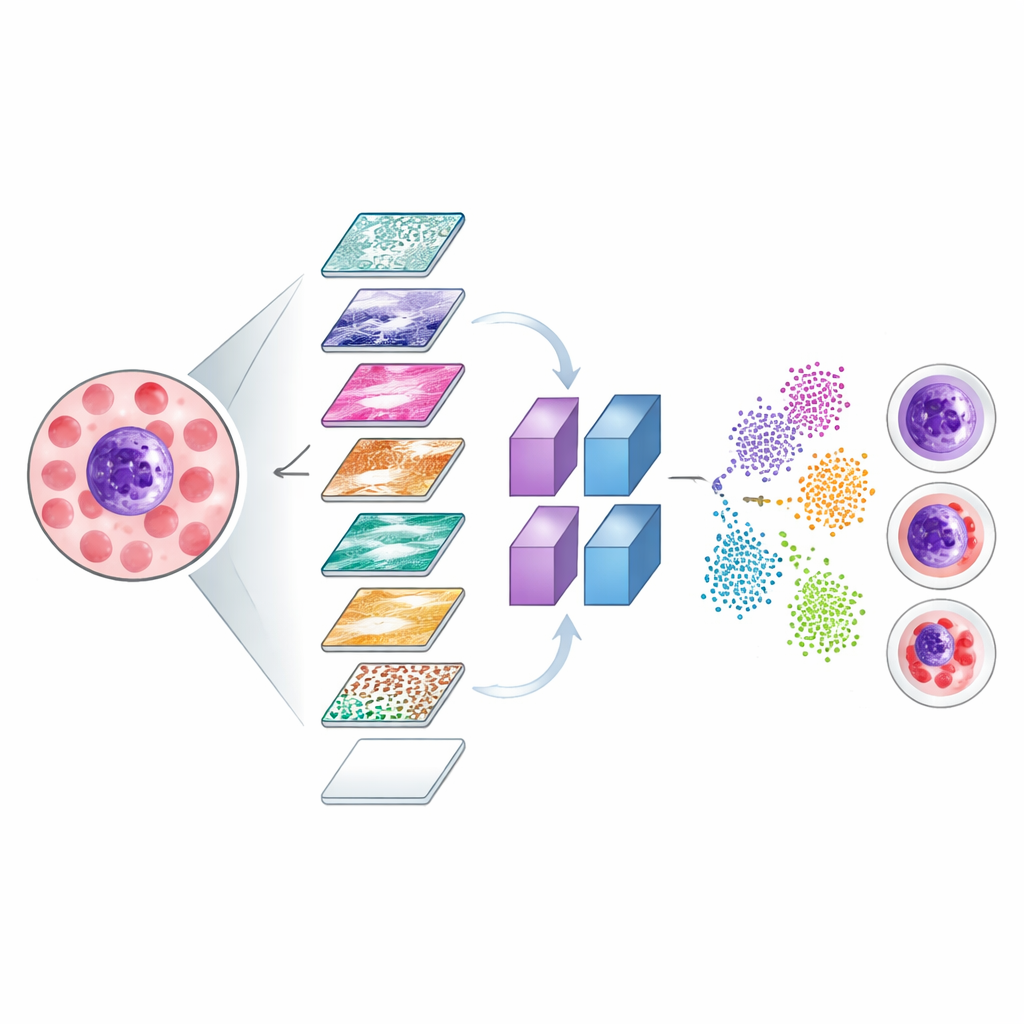
Rendre visibles des décisions invisibles
Pour s’assurer que le système se concentre sur les régions médicalement pertinentes des images, les chercheurs ont utilisé deux outils de visualisation, connus sous les noms de Grad-CAM et LIME. Ces méthodes génèrent des cartes thermiques colorées qui mettent en évidence les régions d’une image cellulaire qui ont le plus influencé les décisions du modèle. Les zones lumineuses de ces cartes tendaient à correspondre à des structures cruciales comme le noyau cellulaire et le cytoplasme environnant, plutôt qu’à l’arrière-plan sans intérêt. L’équipe a également exploré la manière dont le réseau sépare en interne les différents types cellulaires en projetant ses signaux internes sur une carte bidimensionnelle, où les cellules correctement classées forment des grappes distinctes et les cas mal classés peuvent être examinés pour comprendre les difficultés du modèle.
Ce que cela pourrait signifier pour les patients
En termes simples, ce travail montre qu’un modèle d’IA soigneusement conçu et relativement petit peut trier les globules blancs à partir d’images au microscope avec une précision comparable ou supérieure à celle de nombreux systèmes larges et complexes. Parce que le modèle est compact et efficace, il convient mieux à une utilisation dans de plus petits laboratoires, des dispositifs au point de soin ou même des équipements portables, rapprochant potentiellement des analyses sanguines de haute qualité des patients. Bien que des tests supplémentaires en conditions cliniques réelles soient encore nécessaires, cette approche ouvre la voie à des outils plus rapides, plus accessibles et plus transparents qui peuvent aider les pathologistes à diagnostiquer des maladies et à détecter des problèmes plus tôt.
Citation: Karaddi, S.H., Bitra, H., Bairaboina, S.S.R. et al. White blood cell classification using custom deep neural network and visualizing features of the images using heatmaps. Sci Rep 16, 9311 (2026). https://doi.org/10.1038/s41598-026-35138-9
Mots-clés: globules blancs, imagerie médicale, apprentissage profond, diagnostic sanguin, réseaux neuronaux