Clear Sky Science · fr
Diversité génétique de Pseudomonas aeruginosa isolée d’échantillons cliniques avec le marqueur moléculaire ISSR dans un hôpital universitaire de soins tertiaires
Pourquoi les germes hospitaliers nous concernent tous
Toute personne ayant séjourné à l’hôpital — en tant que patient ou pour rendre visite à un proche — compte sur l’efficacité des antibiotiques lorsque cela est crucial. Mais certains microbes deviennent si résistants que même nos médicaments les plus puissants peinent à les arrêter. Cet article examine l’un de ces perturbateurs, une bactérie nommée Pseudomonas aeruginosa, et montre comment des scientifiques d’un hôpital indien ont cartographié sa diversité génétique cachée pour mieux comprendre pourquoi il est si difficile à maîtriser.
Un germe tenace dans les hôpitaux modernes
Pseudomonas aeruginosa est un adversaire difficile. Elle prospère dans les milieux humides, des tubes de ventilation aux pansements, et s’attaque tout particulièrement aux personnes dont les défenses sont affaiblies par la maladie, les brûlures ou un long séjour hospitalier. Elle peut provoquer de graves infections pulmonaires, sanguines, urinaires et de plaies. Ce qui la rend particulièrement dangereuse, c’est sa capacité à résister simultanément à de nombreux antibiotiques, transformant des infections routinières en crises potentiellement mortelles et augmentant les coûts et la durée des soins hospitaliers à l’échelle mondiale.
Regarder sous la surface de l’infection
Pour évaluer à quel point ce germe est diversifié au sein d’un même hôpital, les chercheurs ont collecté 100 échantillons bactériens provenant de sang, d’urine, d’expectorations et de prélèvements de plaies réalisés lors de soins de routine dans un grand hôpital universitaire de l’est de l’Inde. Ils se sont concentrés sur 18 souches multirésistantes et ont testé la réaction de chacune à un large panel d’antibiotiques. Fait préoccupant, plus de quatre prélèvements sur cinq étaient résistants à des médicaments clés tels que la céfopérazone, le méropénem et l’imipénem — des antibiotiques souvent réservés en dernier recours lorsque d’autres échouent. Quelques antibiotiques, y compris certains moins couramment utilisés, restaient plus efficaces, suggérant des options de traitement encore disponibles mais de plus en plus limitées. 
Lire les « codes-barres » des bactéries
Compter les antibiotiques inefficaces n’était qu’une partie de l’enquête. L’équipe voulait aussi savoir si ces infections provenaient d’un « superclone » unique se propageant dans l’hôpital, ou de nombreuses lignées indépendantes arrivant et évoluant séparément. Pour cela, ils ont utilisé une méthode de « fingerprinting » de l’ADN appelée ISSR, qui met en évidence les segments de code génétique situés entre de courtes séquences répétées. Lorsqu’ils sont amplifiés par PCR puis séparés sur gel, ces segments forment un motif de bandes qui agit comme un code‑barres pour chaque souche. En utilisant 17 amorces informatives, les chercheurs ont généré 95 bandes d’ADN distinctes puis comparé les profils des 18 souches avec des outils informatiques regroupant les empreintes similaires.
Beaucoup de cousins éloignés, pas un super‑germe
Les comparaisons génétiques ont révélé que l’hôpital ne faisait pas face à un seul clone incontrôlé. Au contraire, les souches se répartissaient en plusieurs groupes distincts, avec des scores de similarité allant de proches apparentés à des cousins très éloignés. Certains isolats ayant un comportement similaire aux tests d’antibiotiques se sont avérés génétiquement différents, tandis que d’autres, apparentés, partageaient des éléments de résistance. Les tracés de composantes principales et les diagrammes en forme d’arbre ont renforcé l’image d’un coexistence de multiples lignées au sein du même établissement plutôt que d’une souche dominante unique. Cette diversité résulte vraisemblablement des échanges génétiques, des mutations et de l’adaptation sous l’exposition constante aux antibiotiques et au système immunitaire humain. 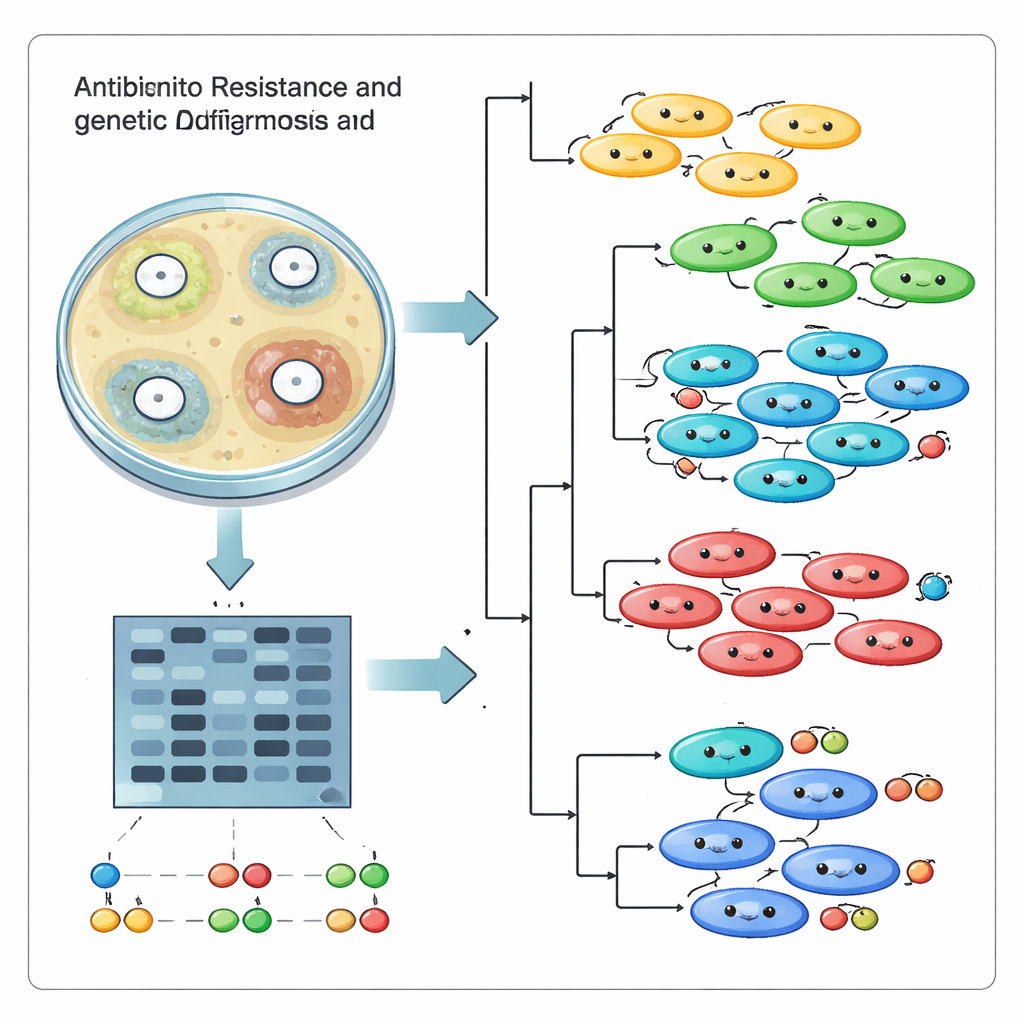
Ce que cela signifie pour les patients et les hôpitaux
Pour les hôpitaux, ces résultats délivrent un message clair : suivre uniquement les antibiotiques inefficaces ne suffit pas. Parce que des souches génétiquement distinctes peuvent présenter des profils de résistance similaires — et que des souches étroitement apparentées peuvent se comporter différemment — les équipes de soins doivent recourir à la fois à des tests de sensibilité aux médicaments de routine et à une surveillance génétique périodique pour suivre l’évolution de la population bactérienne au fil du temps. La méthode ISSR employée ici est relativement simple et peu coûteuse, ce qui la rend intéressante pour les environnements aux ressources limitées, même si les auteurs soulignent que la combiner avec le séquençage du génome entier dans des études futures fournirait un tableau plus complet.
Un paysage caché qui exige de la vigilance
En termes simples, cette étude montre qu’au sein d’un même hôpital, Pseudomonas aeruginosa n’est pas un seul ennemi mais une foule d’éléments liés mais distincts, many déjà armés contre plusieurs antibiotiques. En cartographiant ce paysage caché de diversité, les chercheurs fournissent des outils et des perspectives pouvant aider les médecins à choisir des traitements plus ciblés et les équipes de prévention des infections à concevoir des stratégies de confinement plus intelligentes. La surveillance continue de ces profils génétiques sera essentielle pour garder une longueur d’avance sur ce germe adaptable et maintenir la sécurité des soins hospitaliers pour les patients.
Citation: Mishra, P., Sahoo, D. & Sahu, M.C. Genetic diversity of Pseudomonas aeruginosa isolated from clinical samples with ISSR molecular marker in a tertiary care teaching hospital. Sci Rep 16, 5315 (2026). https://doi.org/10.1038/s41598-026-35090-8
Mots-clés: Pseudomonas aeruginosa, résistance aux antibiotiques, infections nosocomiales, diversité génétique, typage moléculaire