Clear Sky Science · fr
Un jeu de données apparié d’ARNm et de microARN sanguins pendant le choc septique aigu et la récupération
Pourquoi cela compte pour les patients atteints d’infections graves
Quand une infection grave échappe au contrôle, les défenses de l’organisme peuvent devenir néfastes, conduisant au sepsis et au choc septique, des affections qui tuent des centaines de milliers de personnes chaque année dans le monde. Les médecins au chevet voient des patients qui peuvent s’aggraver soudainement ou récupérer lentement, mais ils ne peuvent pas facilement observer ce qui se passe à l’intérieur des cellules sanguines lorsque le système immunitaire passe de la crise à la stabilité. Cette étude présente un jeu de données détaillé qui suit les changements d’activité génique dans le sang des mêmes patients pendant la phase la plus dangereuse du choc septique et à nouveau après leur amélioration, offrant une nouvelle fenêtre sur la façon dont l’organisme retrouve son équilibre.
Un examen plus attentif du sang pendant le sepsis
Le système immunitaire marche habituellement sur une corde raide : il doit attaquer les bactéries, virus ou champignons envahissants sans causer de dommages durables aux tissus de l’organisme. Dans le sepsis, cet équilibre se rompt. Les signaux qui déclenchent l’inflammation et ceux qui l’apaisent ne se coordonnent plus correctement, et les organes peuvent commencer à défaillir. Les cliniciens ont un besoin urgent de marqueurs sanguins rapides et fiables qui révèlent quels patients sont réellement en danger, comment leur maladie évolue et si les traitements fonctionnent. Les mesures traditionnelles, comme les taux du marqueur d’infection procalcitonine, peuvent beaucoup varier d’une personne à l’autre et n’expliquent pas entièrement qui récupère et qui ne récupère pas. C’est pourquoi les chercheurs se tournent de plus en plus vers le profil global d’activité génique de l’organisme — son « transcriptome » — comme lecture plus informative.
Ce que cette étude apporte par rapport aux travaux antérieurs
De grandes études antérieures ont déjà montré que les profils d’ARN messager (ARNm), les molécules qui portent les instructions génétiques pour fabriquer des protéines, et de microARN, de petits régulateurs qui ajustent ces instructions, peuvent distinguer les personnes atteintes de sepsis des volontaires sains, et même séparer le sepsis d’autres formes d’inflammation sévère. Certaines investigations ont aussi utilisé ces profils pour estimer le risque futur de développer un sepsis après une chirurgie majeure. Cependant, nombre de ces comparaisons portaient sur des groupes différents — patients versus témoins sains, ou sepsis versus non-sepsis — ce qui rend difficile de savoir si les différences proviennent de la maladie elle‑même ou de la variation naturelle entre individus.
Suivre les mêmes patients de la crise à la récupération
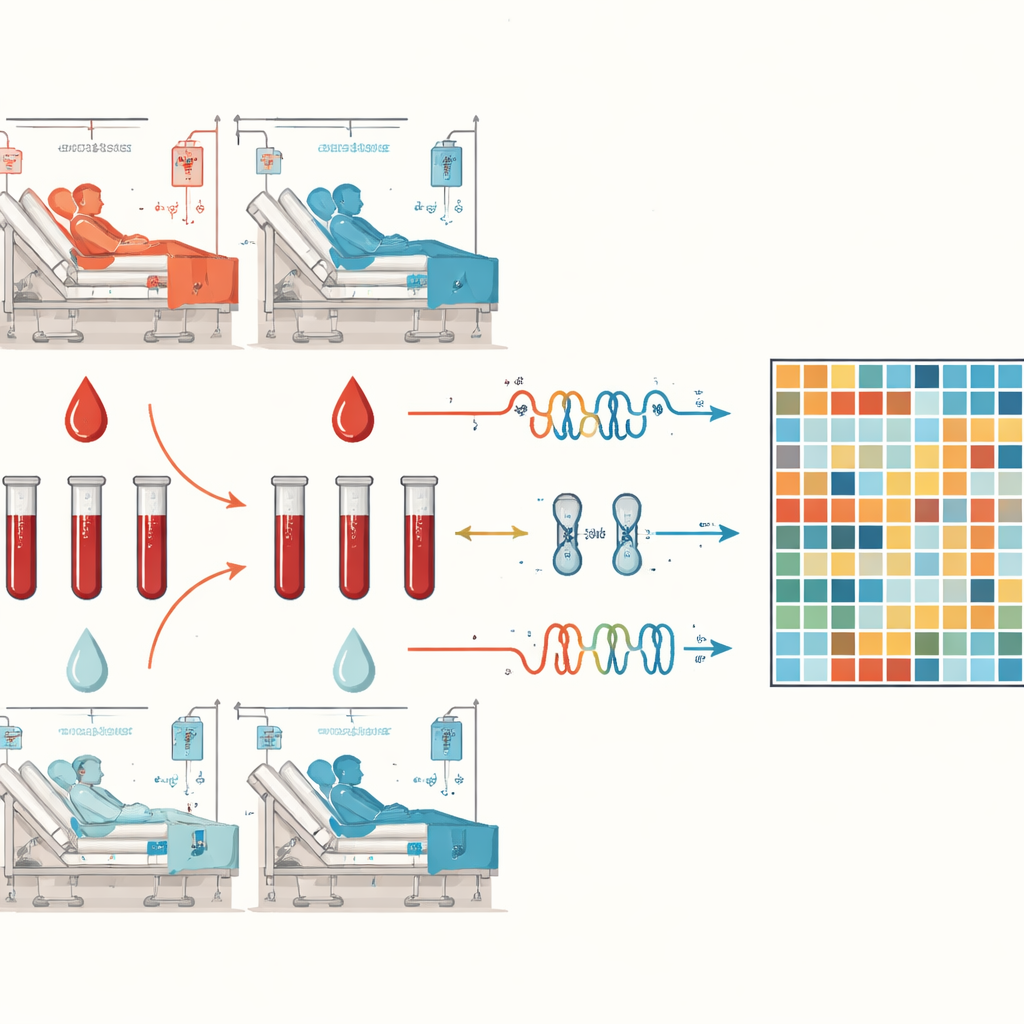
Le nouveau jeu de données se concentre plutôt sur le changement au sein de chaque personne. Six adultes pris en charge en unité de soins intensifs à Budapest pour un choc septique — trois avec des infections pulmonaires et trois avec des infections urinaires — ont chacun fourni deux échantillons de sang. Le premier a été prélevé au pic du choc septique, lorsque la fonction d’organe était gravement altérée et que des médicaments vasopresseurs étaient nécessaires. Le second a été prélevé quelques jours plus tard, au moment de la sortie des soins intensifs, lorsque les patients étaient jugés cliniquement stables et n’avaient plus besoin de médicaments pour remonter la tension artérielle. Les scores cliniques standard, tels que le score SOFA qui résume la fonction des organes, se sont clairement améliorés entre les deux temps, confirmant la transition de la crise vers la récupération.
Comment la carte de l’activité génétique a été créée
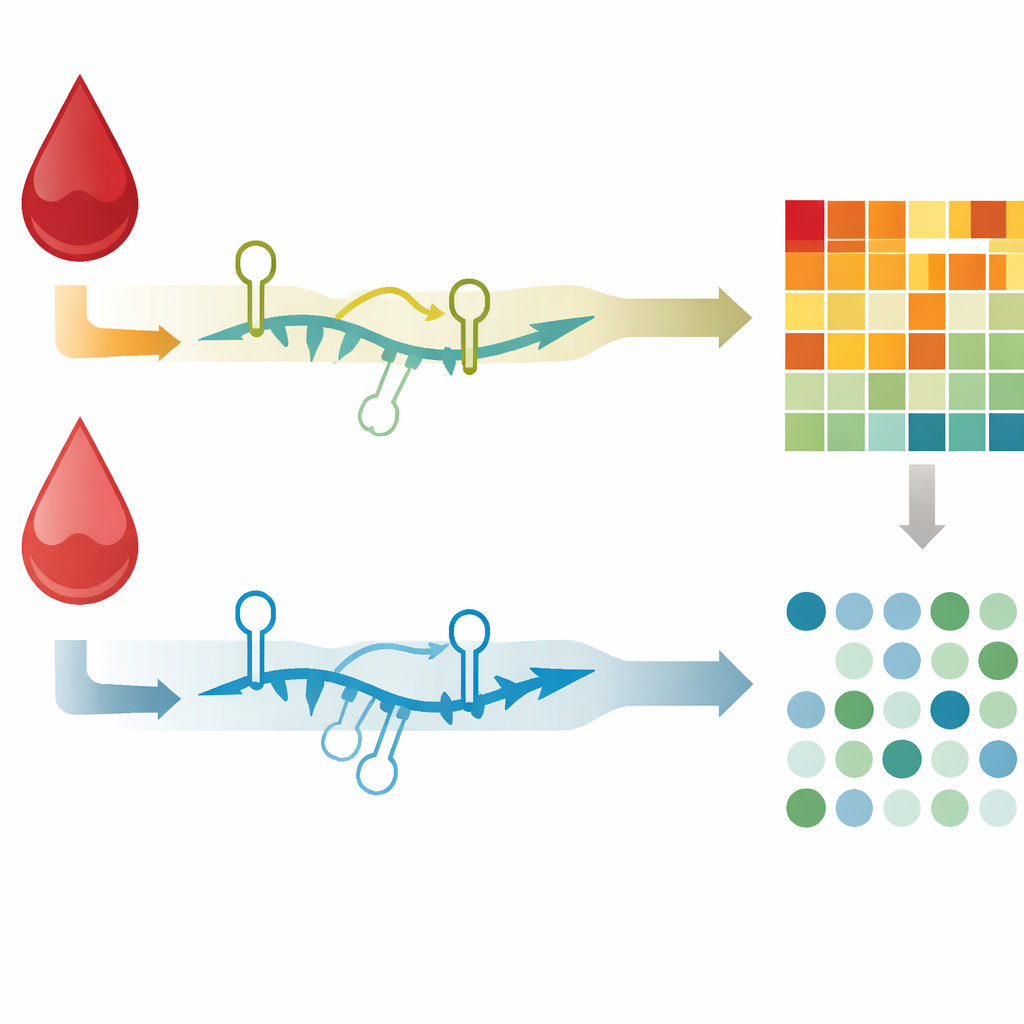
À partir de chaque échantillon sanguin, l’équipe a extrait l’ARN total et préparé deux types de bibliothèques de séquençage : l’une ciblant les ARNm et l’autre les petits ARN, y compris les microARN. À l’aide de machines de séquençage de nouvelle génération, ils ont obtenu en moyenne 15 millions de lectures d’ARNm et 10 millions de lectures de microARN par échantillon, suffisant pour dresser un portrait détaillé des gènes actifs et de leur intensité. Des contrôles de qualité étendus ont garanti que l’ARN était intact et que les bibliothèques de séquençage respectaient des normes strictes. Les lectures ont ensuite été alignées sur le génome humain de référence actuel, et des comptes du nombre de lectures mappées à chaque gène ont été produits, aboutissant à des profils appariés d’activité génique pour chaque patient dans les états de choc et de récupération. Tous les fichiers bruts de séquençage, les tables de comptage et les informations cliniques associées ont été déposés dans une base de données publique pour que d’autres scientifiques puissent les analyser.
Ce que cette ressource signifie pour les soins futurs
Parce que chaque patient sert de témoin à lui‑même, les différences d’activité génique entre les deux temps sont plus susceptibles de refléter la transition du choc menaçant la vie vers la récupération, plutôt que des différences génétiques ou de mode de vie non liées entre les personnes. Le jeu de données est petit, il n’est donc pas, à lui seul, suffisant pour définir des tests diagnostiques définitifs ou expliquer complètement la biologie du sepsis. Il offre cependant une rare vision appariée des ARNm et des microARN pendant la phase la plus critique de la maladie. Les chercheurs peuvent l’utiliser pour explorer des tendances, générer de nouvelles idées sur les dérèglements de la réponse immunitaire et rechercher des signaux précoces d’amélioration ou de dégradation. À terme, l’intégration de telles cartes moléculaires détaillées avec des cohortes de patients plus larges pourrait aider les cliniciens à reconnaître plus tôt des profils immunitaires dangereux et à orienter des traitements plus personnalisés pour les personnes atteintes d’infections graves.
Citation: Molnár, K., Maricza, K., Elek, Z. et al. A dataset of paired blood mRNA and microRNA sequencing across acute septic shock and recovery. Sci Data 13, 453 (2026). https://doi.org/10.1038/s41597-026-06844-w
Mots-clés: sepsis, choc septique, expression génique, séquençage de l’ARN sanguin, biomarqueurs