Clear Sky Science · fr
Assemblage génomique au niveau chromosomique résolu par haplotype d’un camélia oléagineux autohexaploïde, Camellia osmantha
Pourquoi un arbre producteur d’huile de cuisson est important
Beaucoup connaissent les camélias comme de jolis arbustes de jardin, mais certains de leurs cousins sont de véritables piliers de la cuisine. L’huile extraite des graines de camélia est appréciée dans certaines régions d’Asie comme une huile de cuisson favorable au cœur, riche en graisses saines et en composés végétaux protecteurs. Une espèce montante est Camellia osmantha, un arbre robuste à haut rendement capable de produire bien plus d’huile par hectare que les variétés traditionnelles. Pour exploiter pleinement son potentiel, les scientifiques doivent comprendre son plan génétique. Cette étude fournit exactement cela : une carte détaillée et à haute résolution de l’ADN de l’arbre, ouvrant la voie à de meilleurs rendements, à une huile plus saine et à des arbres capables de prospérer dans un monde qui se réchauffe.

Un nouvel arbre oléagineux prometteur
Camellia osmantha est une espèce d camélia oléagineux reconnue récemment. Elle combine plusieurs caractères appréciés des agriculteurs : forte tolérance à la chaleur, au froid et à la sécheresse, et une production d’huile exceptionnellement élevée — environ le double de celle des camélias commerciaux typiques à seulement cinq ans. Comme beaucoup de plantes cultivées sélectionnées pour le rendement, elle possède un génome particulièrement complexe : au lieu des deux copies habituelles de chaque chromosome, elle en porte six. Cette nature « autohexaploïde » signifie que son ADN est énorme, environ cinq fois la taille du génome humain, et riche en séquences répétées. Une telle complexité a rendu difficile la construction d’une carte génomique propre et précise avec les technologies antérieures.
Déchiffrer un puzzle génétique très vaste
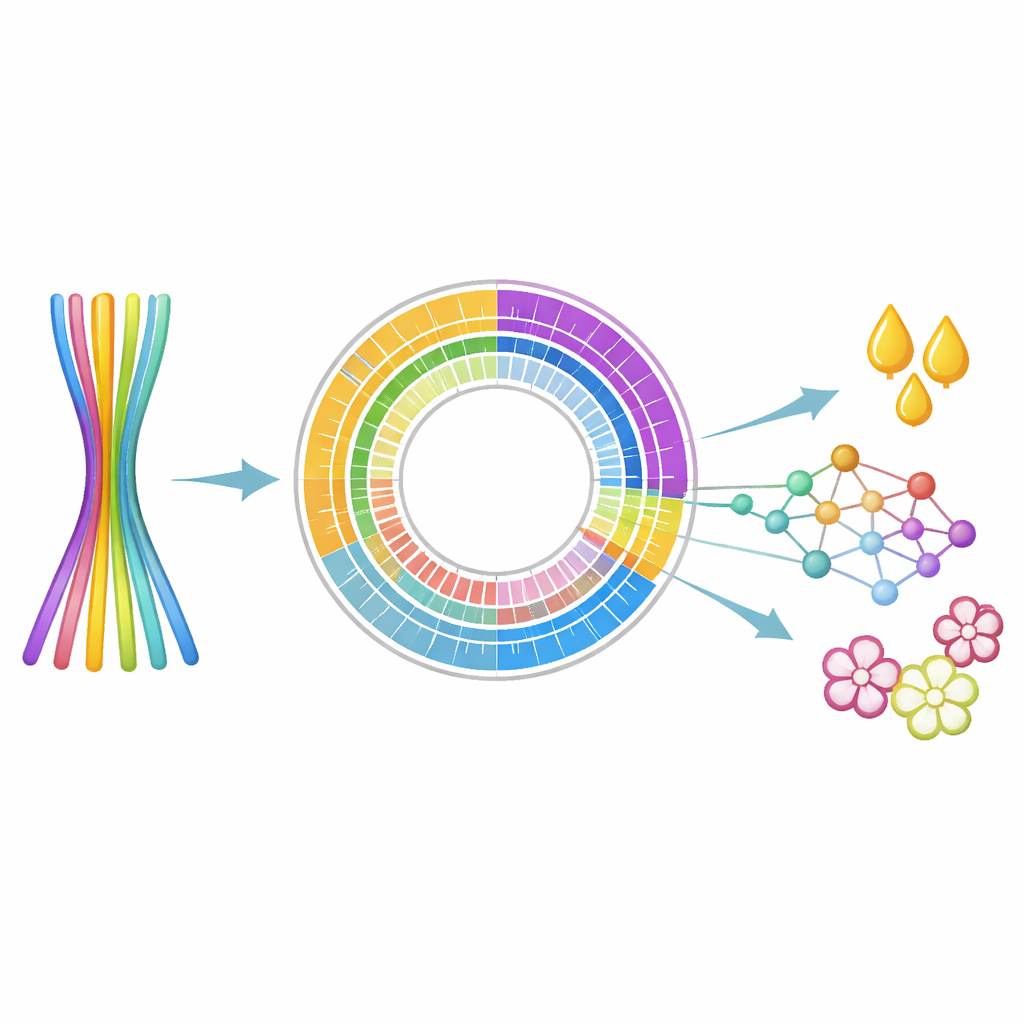
Pour relever ce défi, les chercheurs ont combiné plusieurs méthodes de séquençage d’ADN de pointe. Des lectures longues et très précises issues de la plateforme PacBio HiFi ont fourni des segments de code génétique de plusieurs milliers de bases, tandis que les données Hi‑C ont capturé la façon dont les fragments d’ADN sont repliés et empaquetés dans la cellule — des indices aidant à assembler les fragments en chromosomes complets. Ils ont également recueilli des données d’ARN à partir de feuilles pour voir quels gènes sont effectivement exprimés. En utilisant de nouveaux algorithmes d’assemblage conçus pour les plantes polyploïdes, l’équipe a reconstitué un génome de 14,38 milliards de paires de bases et, fait crucial, l’a séparé en six « haplotypes » distincts mais appariés, chacun représentant un jeu complet de chromosomes.
Six copies complètes, vues clairement pour la première fois
L’assemblage final a ancré 11,08 milliards de paires de bases sur 90 échafaudages longs et de type chromosomique, groupés proprement en six versions de 15 chromosomes. Une version, appelée Haplotype 1, était particulièrement complète et propre, avec seulement un petit nombre d’espaces non résolus et des tests de référence montrant plus de 95 % de complétude. À l’échelle du génome, les scientifiques ont catalogué un vaste paysage de séquences répétées, en particulier des éléments à répétition terminale longue qui représentent presque la moitié de la séquence. Sur cette carte structurelle, ils ont identifié 60 212 gènes codant des protéines, et confirmé que presque tous possèdent des domaines fonctionnels reconnaissables, suggérant que l’ensemble génique est à la fois large et fiable.
Gènes liés à l’huile et à la floraison
Avec le génome en main, l’équipe a recherché spécifiquement les gènes associés aux caractères d’intérêt. Ils ont trouvé 3 269 facteurs de transcription — des « interrupteurs » clés contrôlant d’autres gènes — et 2 655 gènes ressemblant à des gènes de résistance aux maladies connus, qui peuvent aider les sélectionneurs à choisir des arbres résistants aux ravageurs et pathogènes. Plus intéressant pour l’agriculture, ils ont identifié 80 gènes impliqués dans la synthèse des huiles et des lipides, y compris des enzymes qui initient la synthèse des graisses et d’autres qui ajustent les types d’acides gras stockés dans les graines. Ils ont également répertorié 497 gènes liés au moment de la floraison et au développement floral, des leviers importants pour adapter les arbres à différents climats et saisons de culture.
Une base pour de meilleurs arbres et une meilleure huile
En résolvant chacune des six copies chromosomiques et en annotant soigneusement des dizaines de milliers de gènes, ce travail transforme une masse d’ADN énorme et emmêlée en un manuel de référence exploitable pour Camellia osmantha. Les sélectionneurs et les biologistes moléculaires peuvent désormais retracer quelles versions de gènes sont liées à un rendement huileux plus élevé, une meilleure qualité d’huile, une résistance accrue aux maladies ou une résilience à la chaleur et à la sécheresse. Concrètement, l’étude fournit une feuille de route pour développer de nouvelles variétés de camélia oléagineux plus productives, plus robustes et mieux adaptées à nourrir les populations dans un climat changeant — le tout à partir d’une image plus claire de ce qui se trouve à l’intérieur des cellules de cet arbre remarquable.
Citation: Zhang, Z., Hao, B., Li, M. et al. Haplotype-resolved chromosome-level genome assembly of an autohexaploid oil camellia tree Camellia osmantha. Sci Data 13, 395 (2026). https://doi.org/10.1038/s41597-026-06786-3
Mots-clés: Camellia osmantha, génome de plante, cultures polyploïdes, huiles comestibles, amélioration des cultures